DESCRIPCIÓN DE LA OFERTA DE ANÁLISIS
|
|
|
- Teresa Soriano
- hace 4 años
- Vistas:
Transcripción
1 DESCRIPCIÓN DE LA OFERTA DE ANÁLISIS Análisis de peso molecular por MALDI-TOF de péptidos y proteínas El objetivo de este análisis es obtener el espectro de masas con la masa exacta de proteínas y péptidos. Este análisis se utiliza con péptidos naturales o péptidos sintéticos y proteínas recombinantes o purificadas. La Espectrometría de Masas mediante Ionización con Láser Asistida por Matriz y acoplada a un analizador de Tiempo de Vuelo (MALDI-TOF MS) permite el análisis de péptidos y proteínas con gran sensibilidad y una ionización suave con poca o ninguna fragmentación. Los iones se forman a través de reacciones de trasferencia de protones en fase gaseosa con moléculas de matriz fotoionizadas. La matriz es típicamente una molécula pequeña que absorbe energía como el ácido 2, 5-dihidroxibenzoico (para péptidos) o el ácido sinapínico (para proteínas intactas). El análisis mediante MALDI- TOF MS proporciona datos para la determinación del peso molecular de péptidos y proteínas. MALDI-MS es sensible a la presencia de contaminantes como sales o surfactantes, y las soluciones de proteínas que tienen niveles altos de estos contaminantes a menudo no proporcionan señal o la señal es muy pobre. Esta contaminación intrínsecamente resulta de algunos procedimientos de purificación, y en ciertos casos, las sales o los surfactantes se necesitan para evitar que las proteínas precipiten en solución. Los contaminantes comúnmente disminuyen la señal MALDI-MS porque alteran la cocristalización de las moléculas de matriz y analito. Para evitar este problema recomendamos: 1. Dializar la muestra. 2. Entregar la muestra tan concentrada como sea posible para que permita su dilución con los solventes adecuados. 3. Desalar la muestra mediante zip-tip, oasis, OMIX (puntas /columnas con resinas de fase reversa C4 o C18). La cantidad necesaria para el análisis de péptidos está en el rango de femtomoles (50-100) y para proteínas en el rango de picomoles. El rango de masas para proteínas es de hasta unos 60 kda y el error de masas es de aproximadamente la masa media de un aminoácido. El error de masa para péptidos es de unas 80 ppm. Procedimiento: Una alícuota (0,5 µl) de muestra (proteína/péptido) se analiza en un espectrómetro de masas tipo MALDI-TOF empleando un modelo Autoflex de Bruker Daltonic (Bremen, Germany), en modo reflector positivo (lineal para proteínas), y empleando como matriz (0,5 µl) ácido sinapínico para proteínas y ácido 2, 5-dihidroxibenzoico (0,5 µl) para péptidos y una placa de tipo Anchor-Chip (Bruker Daltonic). La identificación de picos y la asignación de masas monoisotópicas para péptidos se realiza automáticamente mediante el programa Flexanalysis, version 2.2 (Bruker Daltonics).
2 Electroforesis 1D SDS-PAGE (Electroforesis en geles de poliacrilamida en presencia de sodio dodecil sulfato) es utilizada frecuentemente en el laboratorio para la separación de proteínas en función de su peso molecular. SDS-PAGE separa proteínas de acuerdo a su peso molecular, basado en sus distintas velocidades de migración a través de una matriz (un gel) donde se está aplicando un campo eléctrico. Tamaños de gel: Minigel (sistema Bio-Rad). Tinción con coomassie coloidal La tinción de geles con Coomassie es una tinción lista para usar basada en el colorante coomassie coloidal G-250 que permite la detección a nivel de nanogramos así como una claridad excelente en geles de poliacrilamida. Este colorante solo tiñe proteínas y, a diferencia de las tinciones tradicionales con coomassie basadas en la forma del colorante R-250, permite que las bandas se vean directamente en el gel durante el proceso de tinción. Después de la tinción, una etapa opcional de lavado con agua aumenta la sensibilidad y clarifica el fondo. Protocolo: 1. Lavar el gel tres veces con metanol-acético en agua (50:10:40) 15 minutos. 2. Lavar el gel tres veces con agua MQ 15 minutos. 3. Añadir el coomassie coloidal 1 hora/over-night. 4. Para aumentar la claridad usar la etapa de lavado con agua (1 hora). Instrucciones para el usuario: 1. Los solventes empleados deben de ser de alto grado analítico (no reusar). 2. El recipiente utilizado será preferiblemente nuevo (o de vidrio). 3. Los usuarios extremarán la precaución en la manipulación para evitar la contaminación con queratinas. 4. Los usuarios traerán el gel al Servicio en metanol:acético:agua (50:10:40) Digestión enzimática La digestión se puede realizar a partir de la muestra: 1. En solución. 2. En gel, bien sea procedente de un gel 1D o 2D.
3 En solución se digieren muestras cuya composición en el buffer sea compatible con la enzima y/o cuando queramos digerir todas las proteínas de una muestra (ya sea una proteína purificada a homogeneidad o una mezcla de proteínas). En gel se digieren muestras cuya composición en el buffer no sea compatible con las condiciones de digestión enzimática y/o cuando el objetivo sea una banda o spot en particular. La proteasa comúnmente empleada es la tripsina (corta específicamente detrás de K y R), aunque en trabajos en los que es necesario obtener una cobertura distinta de secuencia empleamos también quimotripsina (corta preferentemente detrás de aromáticos, F, Y, W, en menor medida de L y M, e inespecíficamente en otros sitios). Las condiciones de digestión, total o parcial, también son una alternativa en trabajos dirigidos hacia la búsqueda o caracterización de un péptido en particular, así como el empleo conjunto de ambas proteasas. Otras proteasas empleadas son la V8 proteasa (E/E+D) y la LisargiNasa (delante de K y R). Identificación de proteínas mediante Peptide Mass Fingerprinting El mapeo mediante huella peptídica (PMF) es una técnica empleada para identificar proteínas mediante la coincidencia de las masas de sus fragmentos constituyentes (masas de péptidos) con las masas de los péptidos teóricos generados a partir de bases de datos de proteínas o de DNA. La primera etapa en el PMF es el corte de la proteína desconocida e intacta con una enzima proteolítica para generar péptidos. La enzima más comúnmente utilizada es tripsina. Usualmente se realiza un análisis MALDI-TOF tras el que se realiza un PMF en la base de datos. La premisa del mapeo peptídico es que toda proteína única tiene un conjunto único de péptidos y, por lo tanto, con masas de péptidos únicas. La identificación se realiza mediante la coincidencia de las masas de los péptidos observados con las masas teóricas derivadas de la base de datos. La identificación mediante PMF se basa en la observación de un alto número de péptidos, 5+, de la misma proteína con una gran exactitud de masa. Esta técnica funciona bien con spots de geles 2D donde la pureza de la proteína es mayor. La identificación de proteínas mediante PMF tiene dificultades con mezclas complejas de proteínas. Los bajos niveles de identificación a veces son debidos a la contaminación por queratinas. Instrucciones para el usuario: 1. Los solventes empleados deben de ser de alto grado analítico. 2. El recipiente utilizado será preferiblemente nuevo (o de vidrio). 3. Los usuarios extremarán la precaución en la manipulación para evitar la contaminación con queratinas. 4. Correr en un carril estándares de peso molecular no modificados. 5. Los usuarios traerán el gel al Servicio en metanol:acético:agua (50:10:40). 6. No cortar las bandas/spots.
4 7. Lo ideal es que la/s bandas se vean por coomassie, ya que asegura que la cantidad de proteína es más que suficiente. Para aumentar la sensibilidad se puede teñir el gel con Sypro-Ruby (nunca con plata). Procedimiento: Las bandas/spots de proteínas (de geles 1D o 2D) se digieren con tripsina. Después de desalar la muestra, una alícuota (0,5 µl) del sobrenadante de la digestión tríptica se analiza directamente en un espectrómetro de masas de tipo MALDI-TOF, empleando un modelo Autoflex de Bruker Daltonic (Bremen, Alemania) equipado con un reflector y utilizando como matriz ácido 2,5-dihidroxibenzoico y una placa con superficie Anchor- Chip (Bruker Daltonic). Los espectros de masas obtenidos son utilizados como huella peptídica para la identificación de proteínas en bases de datos (NCBI no redundante, empleando el programa MASCOT Se considera la puntuación p<0,05 la que tiene una probabilidad significativa en MASCOT para una apropiada identificación. Identificación de proteínas mediante LC-MS/MS Los métodos basados en espectrometría de masas para la identificación de proteínas se han convertido en una plataforma estándar en proteómica. Las estrategias más populares basadas en MS comienzan con la digestión proteolítica de las proteínas en péptidos antes de su análisis en el espectrómetro de masas. La digestión de las proteínas en péptidos de un tamaño similar, ayuda a solventar los problemas de solubilidad y manipulación asociados con las proteínas intactas y genera fragmentos de péptidos que son fácilmente ionizables en el espectrómetro de masas. Los iones-péptidos se miden primero como iones de fragmentos intactos, a continuación, seleccionados en base a su valor m/z, se someten a disociación inducida por colisión (CID), en un proceso conocido como espectrometría de masas en tándem (MS / MS). Bajo las condiciones de baja energía empleadas para CID, los péptidos ionizados se fragmentan en patrones predecibles. Debido a que los patrones de fragmentación son predecibles, los espectros teóricos pueden ser construidos a partir de las secuencias en bases de datos de proteínas o de nucleótidos. Los algoritmos informáticos utilizan los patrones de fragmentación CID de los péptidos de la muestra para determinar la secuencia del péptido, y esta información de la secuencia se utiliza para buscar contra espectros teóricos generados a partir de bases de datos de nucleótidos y proteínas. La identificación de proteínas se hace mediante la búsqueda de la mejor correlación entre la información de la secuencia obtenida experimentalmente y las secuencias en la base de datos. Instrucciones para el usuario: 1. Recomendamos encarecidamente almacenar los extractos de proteínas a -70ºC y nunca volver a congelar tras su descongelación. 2. Correr un gel SDS-PAGE para poder estimar la cantidad de proteína presente en la muestra, la complejidad proteica, el rango dinámico y el nivel de contaminantes. 3. La muestra puede estar en gel o en solución. 4. La cantidad mínima de muestra depende de los objetivos del trabajo.
5 Procedimiento: Los digeridos de proteínas se analizan mediante LC-MS/MS en un espectrómetro de masas LTQ-Velos (Thermo Scientific) o en un espectrómetro de masas LTQ-Orbitrap- Velos-Pro (Thermo Scientific). El equipo LTQ-Velos está acoplado a un cromatógrafo líquido de alta resolución (HPLC) Agilent 1100 y el equipo LTQ-Orbitrap-Velos-Pro está acoplado a un cromatógrafo líquido de alta resolución (HPLC) Easy-nLC II de Proxeon, para la separación de péptidos. La elección del instrumento (determinada por el personal del Servicio de Proteómica) depende del proyecto y de la cantidad de muestra disponible. Normalmente, el gradiente empleado para muestras de baja complejidad (<5 proteínas) es de min, de min para complejidad media (<50 proteínas) y de min para alta complejidad (>50 proteínas). La identificación de péptidos a partir de los ficheros raw se realiza con el programa PEAKS X+ (Bioinformatics Solutions, Waterloo, Ontario, Canada). Caracterización de modificaciones post-traduccionales Las modificaciones post-traduccionales de las proteínas son importantes para la regulación de procesos celulares, incluyendo la localización celular de la proteína, la regulación de la función de la proteína, y la formación de complejos de proteínas. El análisis de las modificaciones post-traduccionales (PTMs) por espectrometría de masas puede ser difícil y el nivel de dificultad depende de (i) el desplazamiento de masa en el peso molecular del péptido, (ii) la abundancia global del péptido modificado, (iii) la estabilidad de la modificación durante la espectrometría de masas (MS) y análisis MS/MS, y (iv) el efecto de la modificación en la eficiencia de ionización del péptido (y por lo tanto la sensibilidad). El péptido modificado debe ser detectado. Si bien es posible identificar una proteína (o una familia de proteínas homólogas) a partir de espectros MS/MS de sólo unos pocos de sus péptidos, localizar el sitio exacto de una modificación requiere la detección y en la mayoría de los casos la secuenciación MS/MS del péptido específico modificado. Esto puede ser difícil ya que no todos los péptidos se detectan igualmente. El análisis de modificaciones post-traduccionales puede necesitar de diferentes aproximaciones técnicas: 1. Enriquecimiento de los péptidos modificados. 2. Mapeo empleando diferentes proteasas para obtener la máxima cobertura de secuencia. 3. Digestión en gel y/o en solución. 4. Análisis mediante diferentes espectrómetros de masas. Cada proyecto, cada tipo de modificación y cada objetivo requieren un diseño experimental apropiado. El experimento será diseñado para cada trabajo con cada usuario.
6 Cuantificación relativa de proteínas en proteomas Se puede decir que la Espectrometría de masas no es cuantitativa de forma inherente, ya que los péptidos proteolíticos tienen diferentes respuestas cuando se someten a este análisis, debido a sus diversas propiedades fisicoquímicas como el tamaño, la carga y la hidrofobicidad. La proteómica cuantitativa, también llamada proteómica de expresión diferencial, tiene como objetivo identificar cambios específicos entre las muestras control y unas condiciones experimentales específicas, a menudo centrándose en un subconjunto particular de proteínas. La caracterización de los cambios proteómicos dinámicos, asociados con diferentes condiciones biológicas tales como enfermedades, revela mecanismos patogénicos y ayuda a identificar proteínas como biomarcadores y dianas terapéuticas. Por lo tanto, es crucial encontrar métodos analíticos sensibles, específicos y precisos para medir los cambios. En el siguiente esquema están plasmados los distintos métodos para realizar una cuantificación relativa de proteínas en proteomas:
7 Instrucciones para el usuario: Es imprescindible planificar el tipo de experimento con los técnicos del servicio. En función del número de muestras a comparar, de la cantidad de proteína disponible y de los objetivos del trabajo, se realizará un método u otro de cuantificación. Procedimiento: 1. Cuantificación relativa empleando marcaje con isótopos estables isobáricos TMT-6 plex / itraq 4plex: Las muestras de proteínas a comparar, tras ser digeridas enzimáticamente y desaladas, se marcan con las correspondientes sondas. Posteriormente se mezclan y se analizan mediante LC-MS/MS. 2. Cuantificación relativa sin marcaje Label-Free : En este abordaje, dado que las muestras a comparar no se someten juntas al análisis por no estar marcadas, es necesario realizar réplicas técnicas para poder obtener una significatividad estadística del/los cambios. 3. Cuantificación relativa mediante marcaje metabólico con isótopos estables SILAC: Para llevar a cabo esta cuantificación, el usuario realiza el marcaje metabólico en sus células.
8 Los extractos de proteínas se pueden preparar en conjunto, mezclando las células de las distintas situaciones, de este modo minimizamos la variabilidad técnica del experimento desde etapas tempranas. El Análisis de Datos se realiza empleando el programa PEAKS X+
OFERTA DE ANÁLISIS. Tinción con coomassie coloidal
 Tinción con coomassie coloidal OFERTA DE ANÁLISIS La tinción de geles con Coomassie es una tinción lista para usar basada en el colorante coomassie coloidal G-250 que permite la detección a nivel de nanogramos
Tinción con coomassie coloidal OFERTA DE ANÁLISIS La tinción de geles con Coomassie es una tinción lista para usar basada en el colorante coomassie coloidal G-250 que permite la detección a nivel de nanogramos
IDENTIFICACIÓN DE PROTEÍNAS MEDIANTE ESPECTROMETRÍA DE MASAS. ANÁLISIS BIONFORMÁTICO
 IDENTIFICACIÓN DE PROTEÍNAS MEDIANTE ESPECTROMETRÍA DE MASAS. ANÁLISIS BIONFORMÁTICO Mª Luisa Hernáez ESTRATEGIAS PROTEÓMICAS Muestras complejas. Extractos proteicos: proteomas, subproteomas... Proteómica
IDENTIFICACIÓN DE PROTEÍNAS MEDIANTE ESPECTROMETRÍA DE MASAS. ANÁLISIS BIONFORMÁTICO Mª Luisa Hernáez ESTRATEGIAS PROTEÓMICAS Muestras complejas. Extractos proteicos: proteomas, subproteomas... Proteómica
PURIFICACION Y CARACTERIZACION DE LAS PROTEINAS.
 PURIFICACION Y CARACTERIZACION DE LAS PROTEINAS. 1 METODOS GENERALES DE PURIFICACION DE PROTEINAS. 1)Ruptura del material y obtención de un extracto libre de células. 2)Precipitación (sales, ph, alta temperatura,
PURIFICACION Y CARACTERIZACION DE LAS PROTEINAS. 1 METODOS GENERALES DE PURIFICACION DE PROTEINAS. 1)Ruptura del material y obtención de un extracto libre de células. 2)Precipitación (sales, ph, alta temperatura,
IDENTIFICACIÓN DE PROTEÍNAS POR ESPECTROMETRÍA DE MASAS. EQUIPAMIENTO
 IDENTIFICACIÓN DE PROTEÍNAS POR ESPECTROMETRÍA DE MASAS. EQUIPAMIENTO La Espectrometría de Masas es una tecnología analítica esencial en el contexto de la proteómica actual debido a su alta capacidad de
IDENTIFICACIÓN DE PROTEÍNAS POR ESPECTROMETRÍA DE MASAS. EQUIPAMIENTO La Espectrometría de Masas es una tecnología analítica esencial en el contexto de la proteómica actual debido a su alta capacidad de
PROTEÓMICA DIFERENCIAL:
 PROTEÓMICA DIFERENCIAL: Técnicas, aplicaciones y dificultades Proteómica: Qué es? Para qué sirve? Conocer el proteoma de un organismo es tener una imagen dinámica de todas las proteínas expresadas por
PROTEÓMICA DIFERENCIAL: Técnicas, aplicaciones y dificultades Proteómica: Qué es? Para qué sirve? Conocer el proteoma de un organismo es tener una imagen dinámica de todas las proteínas expresadas por
CENTRO NACIONAL DE INVESTIGACIONES ONCOLÓGICAS RED NACIONAL DE CENTROS DE CÁNCER PROGRAMA DE GENÓMICA
 CENTRO NACIONAL DE INVESTIGACIONES ONCOLÓGICAS RED NACIONAL DE CENTROS DE CÁNCER PROGRAMA DE GENÓMICA CATÁLOGO DE OFERTA DE SERVICIOS GENÓMICOS I. INFORMACIÓN GENERAL: NOMBRE DE UNIDAD: Unidad de Genómica
CENTRO NACIONAL DE INVESTIGACIONES ONCOLÓGICAS RED NACIONAL DE CENTROS DE CÁNCER PROGRAMA DE GENÓMICA CATÁLOGO DE OFERTA DE SERVICIOS GENÓMICOS I. INFORMACIÓN GENERAL: NOMBRE DE UNIDAD: Unidad de Genómica
La Unidad de Proteómica ofrece apoyo y servicio de las siguientes tecnologías: 1. Separación de proteínas y análisis de expresión diferencial.
 Unidad de Proteómica DESCRIPCIÓN GENERAL El Instituto i+12 cuenta con el apoyo de la Unidad de Proteómica desde el año 2007. Esta Unidad tiene como objetivos principales prestar servicio y apoyo a los
Unidad de Proteómica DESCRIPCIÓN GENERAL El Instituto i+12 cuenta con el apoyo de la Unidad de Proteómica desde el año 2007. Esta Unidad tiene como objetivos principales prestar servicio y apoyo a los
Técnicas de Caracterización y purificación
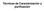 Técnicas de Caracterización y purificación hidrofobicidad carga Propiedades de las proteínas utilizadas para caracterizar y purificar Carga Tamaño Forma Actividad biologica Hidrofobicidad PM Estabilidad
Técnicas de Caracterización y purificación hidrofobicidad carga Propiedades de las proteínas utilizadas para caracterizar y purificar Carga Tamaño Forma Actividad biologica Hidrofobicidad PM Estabilidad
MÉTODOS DE ESTUDIO DE PROTEÍNAS
 MÉTODOS DE ESTUDIO DE PROTEÍNAS ANÁLISIS DE EXPRESIÓN DE PROTEÍNAS Al estudiar la expresión de un gen puede analizarse el ARN (Northern blot, PCR a tiempo real, etc), y también la expresión de la proteína,
MÉTODOS DE ESTUDIO DE PROTEÍNAS ANÁLISIS DE EXPRESIÓN DE PROTEÍNAS Al estudiar la expresión de un gen puede analizarse el ARN (Northern blot, PCR a tiempo real, etc), y también la expresión de la proteína,
PROPIEDADES FISICOQUÍMICAS DE LOS ÁCIDOS NUCLEICOS. Es un ácido capaz de formar sales con iones cargados
 Extracción de ADN Genética molecular PROPIEDADES FISICOQUÍMICAS DE LOS ÁCIDOS NUCLEICOS Es un ácido capaz de formar sales con iones cargados positivamente (cationes). Es soluble en soluciones concentradas
Extracción de ADN Genética molecular PROPIEDADES FISICOQUÍMICAS DE LOS ÁCIDOS NUCLEICOS Es un ácido capaz de formar sales con iones cargados positivamente (cationes). Es soluble en soluciones concentradas
Técnicas de Estudio de las células
 Técnicas de Estudio de las células Microscopia Preparaciones permanentes: Fijación Deshidratación Inclusión Corte Fijación: Acidos, solventes orgánicos como alcohol, aldehídos (Formaldehído, glutaraldehídos)
Técnicas de Estudio de las células Microscopia Preparaciones permanentes: Fijación Deshidratación Inclusión Corte Fijación: Acidos, solventes orgánicos como alcohol, aldehídos (Formaldehído, glutaraldehídos)
Dirección de Vinculación y Desarrollo Institucional. Anexo I Política para alto y bajo volumen en los servicios de la Unidad de Proteómica
 Dirección de Vinculación y Desarrollo Institucional Anexo I Política para alto y bajo volumen en los servicios de la Unidad de Proteómica Servicio Bajo volumen Alto volumen (a partir de ) Gel 1D 7cm Coomassie
Dirección de Vinculación y Desarrollo Institucional Anexo I Política para alto y bajo volumen en los servicios de la Unidad de Proteómica Servicio Bajo volumen Alto volumen (a partir de ) Gel 1D 7cm Coomassie
Ensayos southwestern y northwestern
 Búsqueda de proteínas que se unen a DNA (secuencia conocida, promotor) Ensayo southwestern encontrar proteínas ligantes de DNA que reconozcan en éste una determinada secuencia de nucleótidos Ensayo northwestern
Búsqueda de proteínas que se unen a DNA (secuencia conocida, promotor) Ensayo southwestern encontrar proteínas ligantes de DNA que reconozcan en éste una determinada secuencia de nucleótidos Ensayo northwestern
METODOLOGÍA DE EXTRACCIÓN Y PURIFICACIÓN DE INHIBIDORES DE PROTEASAS EN Opuntia streptacantha
 METODOLOGÍA DE EXTRACCIÓN Y PURIFICACIÓN DE INHIBIDORES DE PROTEASAS EN Opuntia streptacantha RESUMEN Estudiante: Jannet Alejandra Vargas Sánchez Instituto Tecnológico de Roque jannettitajm@hotmail.com
METODOLOGÍA DE EXTRACCIÓN Y PURIFICACIÓN DE INHIBIDORES DE PROTEASAS EN Opuntia streptacantha RESUMEN Estudiante: Jannet Alejandra Vargas Sánchez Instituto Tecnológico de Roque jannettitajm@hotmail.com
ANÁLISIS INSTRUMENTAL_UII_PARTE DOS. Propiedades magnéticas de cuatro importantes núcleos que tienen un número cuántico de espín de ½
 RESONANCIA MAGNÉTICA NUCLEAR ANÁLISIS INSTRUMENTAL_UII_PARTE DOS Propiedades magnéticas de cuatro importantes núcleos que tienen un número cuántico de espín de ½ Desplazamiento químico Desdoblamiento spin-
RESONANCIA MAGNÉTICA NUCLEAR ANÁLISIS INSTRUMENTAL_UII_PARTE DOS Propiedades magnéticas de cuatro importantes núcleos que tienen un número cuántico de espín de ½ Desplazamiento químico Desdoblamiento spin-
Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular
 Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular Aislamiento, análisis y manipulación de ácidos nucleicos Generación de moléculas de DNA recombinante Ingeniería Genética AISLAMIENTO
Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular Aislamiento, análisis y manipulación de ácidos nucleicos Generación de moléculas de DNA recombinante Ingeniería Genética AISLAMIENTO
Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular
 Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular Aislamiento, análisis y manipulación de ácidos nucleicos Generación de moléculas de DNA recombinante Ingeniería Genética AISLAMIENTO
Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular Aislamiento, análisis y manipulación de ácidos nucleicos Generación de moléculas de DNA recombinante Ingeniería Genética AISLAMIENTO
Purificación de proteínas
 Purificación de proteínas Purificación Proceso que cuenta con varias etapas cuyo objetivo es lograr la concentración diferencial de la proteína o molécula de interés Condiciones generales a evaluar Calidad
Purificación de proteínas Purificación Proceso que cuenta con varias etapas cuyo objetivo es lograr la concentración diferencial de la proteína o molécula de interés Condiciones generales a evaluar Calidad
ACTIVIDAD ENZIMÁTICA. Dra. Lilian González Segura Departamento de Bioquímica Facultad de Química
 ACTIVIDAD ENZIMÁTICA Dra. Lilian González Segura Departamento de Bioquímica Facultad de Química Porqué la gran mayoría de las reacciones en los seres vivos necesitan ser catalizadas para que ocurran a
ACTIVIDAD ENZIMÁTICA Dra. Lilian González Segura Departamento de Bioquímica Facultad de Química Porqué la gran mayoría de las reacciones en los seres vivos necesitan ser catalizadas para que ocurran a
Tema 6 Cuantificación de proteínas
 Tema 6 Cuantificación de proteínas Procedimiento de estudio de proteínas Selección de fuente Fraccionamiento de células Centrifugación Cromatografía Cromatografía en capa fina Cromatografía en columna
Tema 6 Cuantificación de proteínas Procedimiento de estudio de proteínas Selección de fuente Fraccionamiento de células Centrifugación Cromatografía Cromatografía en capa fina Cromatografía en columna
CROMATOGRAFÍA. A.- INTERCAMBIO IONICO: A.1. ANIONICA A.2. CATIONCA B.- FILTRACIÓN EN GEL
 CROMATOGRAFÍA. A.- INTERCAMBIO IONICO: A.1. ANIONICA A.2. CATIONCA B.- FILTRACIÓN EN GEL C.- AFINIDAD A. CROMATOGRAFÍA DE INTERCAMBIO IÓNICO. Usos 1.- Purificar Proteínas 2.- Concentrar Proteínas Ventajas
CROMATOGRAFÍA. A.- INTERCAMBIO IONICO: A.1. ANIONICA A.2. CATIONCA B.- FILTRACIÓN EN GEL C.- AFINIDAD A. CROMATOGRAFÍA DE INTERCAMBIO IÓNICO. Usos 1.- Purificar Proteínas 2.- Concentrar Proteínas Ventajas
Eduardo Martínez Morillo, Paula Lafuente Ganuza, Belén Prieto García, Francisco V. Álvarez Menéndez
 DESARROLLO DE UN MÉTODO DE CROMATOGRAFÍA DE GASES ACOPLADA A ESPECTROMETRÍA DE MASAS EN TÁNDEM PARA LA DETECCIÓN DE ESCOPOLAMINA Y CONFIRMACIÓN DE BENZODIACEPINAS EN MUESTRAS DE ORINA Eduardo Martínez
DESARROLLO DE UN MÉTODO DE CROMATOGRAFÍA DE GASES ACOPLADA A ESPECTROMETRÍA DE MASAS EN TÁNDEM PARA LA DETECCIÓN DE ESCOPOLAMINA Y CONFIRMACIÓN DE BENZODIACEPINAS EN MUESTRAS DE ORINA Eduardo Martínez
RESULTADOS Y DISCUSIONES. El análisis por medio de electroforesis a demostrado ser uno de los
 39 RESULTADOS Y DISCUSIONES El análisis por medio de electroforesis a demostrado ser uno de los mejores métodos de separación para complejos proteicos, además de necesitar cantidades muy pequeñas de muestra.
39 RESULTADOS Y DISCUSIONES El análisis por medio de electroforesis a demostrado ser uno de los mejores métodos de separación para complejos proteicos, además de necesitar cantidades muy pequeñas de muestra.
Dr. Roque Bru Martinez. Departamento de Agroquímica y Bioquímica. Grupo Proteómica y Genómica Funcional de Plantas. Jornada LC-MS
 Cromatografía Líquida acoplada a Espectrometría de Masas: una herramienta esencial para el análisis estructural y cuantitativo de proteínas y proteomas Dr. Roque Bru Martinez Grupo Proteómica y Genómica
Cromatografía Líquida acoplada a Espectrometría de Masas: una herramienta esencial para el análisis estructural y cuantitativo de proteínas y proteomas Dr. Roque Bru Martinez Grupo Proteómica y Genómica
Titulo del estudio: Determinación estructural de un analito en baja resolución en Ionización Química (IQ)
 RIAIDT Rede de Infraestruturas de Apoio á Investigación e ao Desenvolvemento Tecnolóxico Vicerrectorado de investigación http://www.usc.es/gl/investigacion/riaidt/ Titulo del estudio: Determinación estructural
RIAIDT Rede de Infraestruturas de Apoio á Investigación e ao Desenvolvemento Tecnolóxico Vicerrectorado de investigación http://www.usc.es/gl/investigacion/riaidt/ Titulo del estudio: Determinación estructural
Por que se considera una técnica confirmatoria?
 Espectrometría de masas Por que se considera una técnica confirmatoria? Espectrometría de masas Técnicas de ionización Ionización electrónica Ionización química Bombardeo de átomos y espectrometría de
Espectrometría de masas Por que se considera una técnica confirmatoria? Espectrometría de masas Técnicas de ionización Ionización electrónica Ionización química Bombardeo de átomos y espectrometría de
Antes de comenzar a hablar de proteómica y
 35:12 La metodología proteómica, una herramienta para la búsqueda de función Concha Gil García Departamento de Microbiología II, Facultad de Farmacia, Universidad Complutense de Madrd E-mail: conchagil@farm.ucm.es.
35:12 La metodología proteómica, una herramienta para la búsqueda de función Concha Gil García Departamento de Microbiología II, Facultad de Farmacia, Universidad Complutense de Madrd E-mail: conchagil@farm.ucm.es.
Titulo del estudio: Determinación estructural de un analito en baja resolución en Impacto electrónico (IE)
 RIAIDT Rede de Infraestruturas de Apoio á Investigación e ao Desenvolvemento Tecnolóxico Vicerrectorado de investigación http://www.usc.es/gl/investigacion/riaidt/ Titulo del estudio: Determinación estructural
RIAIDT Rede de Infraestruturas de Apoio á Investigación e ao Desenvolvemento Tecnolóxico Vicerrectorado de investigación http://www.usc.es/gl/investigacion/riaidt/ Titulo del estudio: Determinación estructural
Sistemas LC/MS Agilent Serie 6000 Todo el Rendimiento. En Todo Momento.
 Sistemas LC/MS Agilent Serie 6000 Todo el Rendimiento. En Todo Momento. Un mayor compromiso con LC/MS La nueva familia de sistemas LC/MS Agilent Serie 6000, representa uno de los principales compromisos
Sistemas LC/MS Agilent Serie 6000 Todo el Rendimiento. En Todo Momento. Un mayor compromiso con LC/MS La nueva familia de sistemas LC/MS Agilent Serie 6000, representa uno de los principales compromisos
Unidad de Espectrometría de masas. Servicios Científico-Técnicos. Universidad de Oviedo
 Unidad de Espectrometría de masas Servicios Científico-Técnicos. Universidad de Oviedo Ubicación Edificio Severo Ochoa. Campus del Cristo (plantas baja y 1ª) Servicios Científico-Técnicos: Unidad de Espectrometría
Unidad de Espectrometría de masas Servicios Científico-Técnicos. Universidad de Oviedo Ubicación Edificio Severo Ochoa. Campus del Cristo (plantas baja y 1ª) Servicios Científico-Técnicos: Unidad de Espectrometría
Hasta ahora sabemos de las proteínas: Función. Con quien interacciona. Su mapa 3D.
 Hasta ahora sabemos de las proteínas: Función. Con quien interacciona. Su mapa 3D. Pero es importante distinguir entre todas las posibles interaciones de los proteomas y las interacciones que ocurren realmente
Hasta ahora sabemos de las proteínas: Función. Con quien interacciona. Su mapa 3D. Pero es importante distinguir entre todas las posibles interaciones de los proteomas y las interacciones que ocurren realmente
Proteínas: Métodos para su Estudio
 Proteínas: Métodos para su Estudio Propiedades Espectroscópicas Todos los aminoácidos absorben luz en la región infraroja Sólo Phe, Tyr, & Trp absorben UV Absorbancia a 280 nm es un buen diagnóstico para
Proteínas: Métodos para su Estudio Propiedades Espectroscópicas Todos los aminoácidos absorben luz en la región infraroja Sólo Phe, Tyr, & Trp absorben UV Absorbancia a 280 nm es un buen diagnóstico para
GENOMICA Y PROTEOMICA
 GENOMICA Y PROTEOMICA Dr. José A Gutiérrez Bustamante Area de Genética y Biología Molecular y Celular Depto. de Morfología Humana Fac. de Medicina - UNT Célula ADN gen A gen B gen C ARN Tecnología Bioinformática
GENOMICA Y PROTEOMICA Dr. José A Gutiérrez Bustamante Area de Genética y Biología Molecular y Celular Depto. de Morfología Humana Fac. de Medicina - UNT Célula ADN gen A gen B gen C ARN Tecnología Bioinformática
ELISA y Western Blot
 Universidad Central de Venezuela Facultad de Medicina Escuela de Medicina José María Vargas Cátedra de Inmunología ELISA y Western Blot Práctica 1 2018 Prof. Edwin Escobar edscobar@gmail.com Aplicaciones
Universidad Central de Venezuela Facultad de Medicina Escuela de Medicina José María Vargas Cátedra de Inmunología ELISA y Western Blot Práctica 1 2018 Prof. Edwin Escobar edscobar@gmail.com Aplicaciones
[...] INFORMA, Vicerrectorado de Política Científica Servicio Central de Apoyo a la Investigación
![[...] INFORMA, Vicerrectorado de Política Científica Servicio Central de Apoyo a la Investigación [...] INFORMA, Vicerrectorado de Política Científica Servicio Central de Apoyo a la Investigación](/thumbs/75/71471128.jpg) Vicerrectorado de Política Científica Servicio Central de Apoyo a la Investigación [...] INFORMA, Que en relación al expediente de contratación Expte. 2013/000013 para el Suministro e instalación de Equipamiento
Vicerrectorado de Política Científica Servicio Central de Apoyo a la Investigación [...] INFORMA, Que en relación al expediente de contratación Expte. 2013/000013 para el Suministro e instalación de Equipamiento
PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN DE LAS COMPETENCIAS PROFESIONALES CUESTIONARIO DE AUTOEVALUACIÓN PARA LAS TRABAJADORAS Y TRABAJADORES
 MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
A. Anexo: Extracción de dsrna por columnas de exclusión de Sephadex G-50
 A. Anexo: Extracción de dsrna por columnas de exclusión de Sephadex G-50 (Tomado de Guzmán, 1994; Rodríguez, 2006) 1. En un tubo eppendorf tapa rosca estéril colocar 100 mg de material vegetal pulverizado
A. Anexo: Extracción de dsrna por columnas de exclusión de Sephadex G-50 (Tomado de Guzmán, 1994; Rodríguez, 2006) 1. En un tubo eppendorf tapa rosca estéril colocar 100 mg de material vegetal pulverizado
Desarrollo y Validación de Técnicas Analíticas
 Desarrollo y Validación de Técnicas Analíticas Nerea Leal Eguiluz DynaKin, S.L. Farmacoterapia Personalizada en Oncología 3 de julio de 2009 Definiciones Método Bioanálitico: conjunto de todos los procedimientos
Desarrollo y Validación de Técnicas Analíticas Nerea Leal Eguiluz DynaKin, S.L. Farmacoterapia Personalizada en Oncología 3 de julio de 2009 Definiciones Método Bioanálitico: conjunto de todos los procedimientos
HOSPITAL UNIVERSITARI VALL D'HEBRON INSTITUT DE RECERCA RED NACIONAL DE CENTROS DE CÁNCER PROGRAMA DE GENÓMICA Y PROTEÓMICA
 HOSPITAL UNIVERSITARI VALL D'HEBRON INSTITUT DE RECERCA RED NACIONAL DE CENTROS DE CÁNCER PROGRAMA DE GENÓMICA Y PROTEÓMICA CATÁLOGO DE OFERTA DE SERVICIOS GENÓMICOS I. INFORMACIÓN GENERAL: NOMBRE DE UNIDAD:
HOSPITAL UNIVERSITARI VALL D'HEBRON INSTITUT DE RECERCA RED NACIONAL DE CENTROS DE CÁNCER PROGRAMA DE GENÓMICA Y PROTEÓMICA CATÁLOGO DE OFERTA DE SERVICIOS GENÓMICOS I. INFORMACIÓN GENERAL: NOMBRE DE UNIDAD:
Instrucciones de uso MBT Galaxy HCCA Matrix GPR
 Instrucciones de uso MBT Galaxy HCCA Matrix GPR Sustancia matriz purificada para uso en espectrometría de masas de desorción y ionización láser asistida por matriz y tiempo de vuelo (MALDI-TOF-MS). Para
Instrucciones de uso MBT Galaxy HCCA Matrix GPR Sustancia matriz purificada para uso en espectrometría de masas de desorción y ionización láser asistida por matriz y tiempo de vuelo (MALDI-TOF-MS). Para
CURSO DE TÉCNICAS PARA EL ANÁLISIS DE SUPERFICIES Técnicas EGA
 CURSO DE TÉCNICAS PARA EL ANÁLISIS DE SUPERFICIES Técnicas EGA EGA Análisis de Gases Evolucionados. El estudio mediante una técnica adecuada de los gases que evolucionan (se producen-se consumen) cuando
CURSO DE TÉCNICAS PARA EL ANÁLISIS DE SUPERFICIES Técnicas EGA EGA Análisis de Gases Evolucionados. El estudio mediante una técnica adecuada de los gases que evolucionan (se producen-se consumen) cuando
ESTRUCTURA Y PROPIEDADES DE PROTEÍNAS
 ESTRUCTURA Y PROPIEDADES DE PROTEÍNAS Purificación de la enzima lactato deshidrogenasa de músculo esquelético de pollo PARTE I. EXTRACCIÓN Y PRECIPITACIÓN POR SALADO. Las proteínas se purifican mediante
ESTRUCTURA Y PROPIEDADES DE PROTEÍNAS Purificación de la enzima lactato deshidrogenasa de músculo esquelético de pollo PARTE I. EXTRACCIÓN Y PRECIPITACIÓN POR SALADO. Las proteínas se purifican mediante
Purificación de la enzima lactato deshidrogenasa de músculo esquelético de pollo
 Purificación de la enzima lactato deshidrogenasa de músculo esquelético de pollo ESQUEMA GENERAL Sesión 1. Extracción y precipitación con sulfato de amonio. Sesión 2. Purificación por cromatografía Sesión
Purificación de la enzima lactato deshidrogenasa de músculo esquelético de pollo ESQUEMA GENERAL Sesión 1. Extracción y precipitación con sulfato de amonio. Sesión 2. Purificación por cromatografía Sesión
Las proteínas. Dra. Nardy Diez García Investigadora
 Las proteínas Dra. Nardy Diez García Investigadora Son la clave de la vida Glicina o glicocola R=H Grupo Carboxilo Grupo Amino Es importante comprender estas propiedades porque son la clave de la estructura
Las proteínas Dra. Nardy Diez García Investigadora Son la clave de la vida Glicina o glicocola R=H Grupo Carboxilo Grupo Amino Es importante comprender estas propiedades porque son la clave de la estructura
qprotein (BCA) Kit para cuantificar proteinas totales PB-L Productos Bio-Lógicos
 qprotein () Kit para cuantificar proteinas totales PB-L http://www.pb-l.com.ar qprotein () Cat. no. RA03 CONTENIDO Componentes RA0301 RA0302 Buffer A 250 ml 500 ml Buffer B 5 ml 10 ml Proteína Patrón 5
qprotein () Kit para cuantificar proteinas totales PB-L http://www.pb-l.com.ar qprotein () Cat. no. RA03 CONTENIDO Componentes RA0301 RA0302 Buffer A 250 ml 500 ml Buffer B 5 ml 10 ml Proteína Patrón 5
Ensayos de restricción
 Ensayos de restricción Vector con inserto= Vector recombinante 6500pb Objetivos de ensayos de restricción de plásmidos Conocer el principio de separación y detección de ácidos nucleicos en geles de agarosa.
Ensayos de restricción Vector con inserto= Vector recombinante 6500pb Objetivos de ensayos de restricción de plásmidos Conocer el principio de separación y detección de ácidos nucleicos en geles de agarosa.
Trabajo Fin de Máster
 MÁSTER EN CIENCIAS ANALÍTICAS Y BIOANALÍTICAS Trabajo Fin de Máster Determinación de proteínas biomarcadoras del glaucoma mediante análisis por Dilución Isotópica y Cromatografía de Líquidos acoplada a
MÁSTER EN CIENCIAS ANALÍTICAS Y BIOANALÍTICAS Trabajo Fin de Máster Determinación de proteínas biomarcadoras del glaucoma mediante análisis por Dilución Isotópica y Cromatografía de Líquidos acoplada a
Análisis de antibióticos polipeptídicos en matrices de origen animal
 Análisis de antibióticos polipeptídicos en matrices de origen animal Antoni Rubies Laboratorio de la Agencia de Salud Pública de Barcelona. CNA, 30 Mayo 2017 Indice I. Introducción II. Objetivos III. Espectrometría
Análisis de antibióticos polipeptídicos en matrices de origen animal Antoni Rubies Laboratorio de la Agencia de Salud Pública de Barcelona. CNA, 30 Mayo 2017 Indice I. Introducción II. Objetivos III. Espectrometría
Validación de métodos, ensayos de aptitud y biometrología en OGM
 Validación de métodos, ensayos de aptitud y biometrología en OGM AMOUNT OF DNA 8 256 PCR Punto 9 Final 512 10 1,024 11 2,048 12 4,096 CYCLE No. de NUMBER ciclo 13 AMOUNT Copias OF de DNA ADN 8,192 140
Validación de métodos, ensayos de aptitud y biometrología en OGM AMOUNT OF DNA 8 256 PCR Punto 9 Final 512 10 1,024 11 2,048 12 4,096 CYCLE No. de NUMBER ciclo 13 AMOUNT Copias OF de DNA ADN 8,192 140
FUNDAMENTOS EN CROMATOGRAFÍA DE LÍQUIDOS DE ALTA RESOLUCIÓN. ACOPLAMIENTO A DETECTORES DE ESPECTROMETRÍA DE MASAS
 Universidad de Vigo, 22 Junio 2010 FUNDAMENTOS EN CROMATOGRAFÍA DE LÍQUIDOS DE ALTA RESOLUCIÓN. ACOPLAMIENTO A DETECTORES DE ESPECTROMETRÍA DE MASAS Manuel Gayo González Responsable de Ventas Zona Centro
Universidad de Vigo, 22 Junio 2010 FUNDAMENTOS EN CROMATOGRAFÍA DE LÍQUIDOS DE ALTA RESOLUCIÓN. ACOPLAMIENTO A DETECTORES DE ESPECTROMETRÍA DE MASAS Manuel Gayo González Responsable de Ventas Zona Centro
La proteómica para la identificación de moléculas y su interés en salud. Dra. Nardy Diez García Fundación IDEA Proyecto Prometeo
 La proteómica para la identificación de moléculas y su interés en salud Dra. Nardy Diez García Fundación IDEA Proyecto Prometeo Estudios omics Proteómica Agronomía Parasitología Biomedicina "Conocer el
La proteómica para la identificación de moléculas y su interés en salud Dra. Nardy Diez García Fundación IDEA Proyecto Prometeo Estudios omics Proteómica Agronomía Parasitología Biomedicina "Conocer el
PURIFICACIÓN DE ENZIMAS
 PURIFICACIÓN DE ENZIMAS MÉTODOS GENERALES DE EXTRACCIÓN Y PURIFICACIÓN CAMILO BECERRA (TUQ) MARÍA FERNANDA FERRERO (TUQ) INTRODUCCIÓN EN LA NATURALEZA EXISTEN CANTIDADES INIMAGINABLES DE COMPUESTOS, PERO
PURIFICACIÓN DE ENZIMAS MÉTODOS GENERALES DE EXTRACCIÓN Y PURIFICACIÓN CAMILO BECERRA (TUQ) MARÍA FERNANDA FERRERO (TUQ) INTRODUCCIÓN EN LA NATURALEZA EXISTEN CANTIDADES INIMAGINABLES DE COMPUESTOS, PERO
Titulo del estudio: Determinación estructural de un analito en baja resolución en L-SIMS (FAB)
 RIAIDT Rede de Infraestruturas de Apoio á Investigación e ao Desenvolvemento Tecnolóxico Vicerrectorado de investigación http://www.usc.es/gl/investigacion/riaidt/ Titulo del estudio: Determinación estructural
RIAIDT Rede de Infraestruturas de Apoio á Investigación e ao Desenvolvemento Tecnolóxico Vicerrectorado de investigación http://www.usc.es/gl/investigacion/riaidt/ Titulo del estudio: Determinación estructural
CROMATOGRAFÍA. A.- INTERCAMBIO IONICO: A.1. ANIONICA A.2. CATIONCA B.- FILTRACIÓN EN GEL
 CROMATOGRAFÍA. A.- INTERCAMBIO IONICO: A.1. ANIONICA A.2. CATIONCA B.- FILTRACIÓN EN GEL C.- AFINIDAD B. CROMATOGRAFÍA DE FILTRACIÓN EN GEL. 1. Principios. No requiere la unión de la proteína, lo cual
CROMATOGRAFÍA. A.- INTERCAMBIO IONICO: A.1. ANIONICA A.2. CATIONCA B.- FILTRACIÓN EN GEL C.- AFINIDAD B. CROMATOGRAFÍA DE FILTRACIÓN EN GEL. 1. Principios. No requiere la unión de la proteína, lo cual
BIOLOGIA MOLECULAR. Dra. Ma. Laura Tondo
 TÉCNICAS BASADAS EN HIBRIDACIÓN MOLECULAR BIOLOGIA MOLECULAR 2016 Dra. Ma. Laura Tondo DESNATURALIZACION Y RENATURALIZACION DEL DNA Cómo se mantienen unidas las dos hebras del DNA? - Puentes de hidrógeno
TÉCNICAS BASADAS EN HIBRIDACIÓN MOLECULAR BIOLOGIA MOLECULAR 2016 Dra. Ma. Laura Tondo DESNATURALIZACION Y RENATURALIZACION DEL DNA Cómo se mantienen unidas las dos hebras del DNA? - Puentes de hidrógeno
METODOLOGÍA ANALÍTICA ICP-MS
 METODOLOGÍA ANALÍTICA ICP-MS 1. CONDICIONES EXPERIMENTALES 2. MÉTODOS SEMICUANTITATIVOS 3. MÉTODOS DE BARRIDO 4. MÉTODOS CUANTITATIVOS 5. CALIBRACIÓN CONDICIONES EXPERIMENTALES SINTONIZACIÓN DIARIA 1.
METODOLOGÍA ANALÍTICA ICP-MS 1. CONDICIONES EXPERIMENTALES 2. MÉTODOS SEMICUANTITATIVOS 3. MÉTODOS DE BARRIDO 4. MÉTODOS CUANTITATIVOS 5. CALIBRACIÓN CONDICIONES EXPERIMENTALES SINTONIZACIÓN DIARIA 1.
Pantones: PANTONE 369 C PANTONE 293 C. PANTONE 293 C al 50%
 Pantones: PANTONE 369 C PANTONE 293 C PANTONE 293 C al 50% Justificación Antecedentes Los rápidos avances tecnológicos están permitiendo la secuenciación sistemática de los genomas de diversos organismos.
Pantones: PANTONE 369 C PANTONE 293 C PANTONE 293 C al 50% Justificación Antecedentes Los rápidos avances tecnológicos están permitiendo la secuenciación sistemática de los genomas de diversos organismos.
AMPLIFICACIÓN Y DETECCIÓN POR PCR DEL LOCUS HUMANO D1S80
 AMPLIFICACIÓN Y DETECCIÓN POR PCR DEL LOCUS HUMANO D1S80 Ref. PCR1 1. OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción
AMPLIFICACIÓN Y DETECCIÓN POR PCR DEL LOCUS HUMANO D1S80 Ref. PCR1 1. OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción
GENERALIDADES Y APLICACIONES DE LA ELECTROFORESIS. Influencia de campo cargado eléctricamente Movimiento al cátodo (-) o al anodo (+)
 GENERALIDADES Y APLICACIONES DE LA ELECTROFORESIS Electroforésis Separación de especies cargadas (anión (-) y catión (+) ) Influencia de campo cargado eléctricamente Movimiento al cátodo (-) o al anodo
GENERALIDADES Y APLICACIONES DE LA ELECTROFORESIS Electroforésis Separación de especies cargadas (anión (-) y catión (+) ) Influencia de campo cargado eléctricamente Movimiento al cátodo (-) o al anodo
Instrucciones de uso MBT Galaxy HCCA Matrix GPR
 Instrucciones de uso MBT Galaxy HCCA Matrix GPR Sustancia matriz purificada para uso en espectrometría de masas de desorción/ionización láser asistida por matriz y tiempo de vuelo (MALDI-TOF-MS). Los productos
Instrucciones de uso MBT Galaxy HCCA Matrix GPR Sustancia matriz purificada para uso en espectrometría de masas de desorción/ionización láser asistida por matriz y tiempo de vuelo (MALDI-TOF-MS). Los productos
Universidad Tecnológica de la Mixteca
 Universidad Tecnológica de la Mixteca Maestría en Ciencias Productos Naturales y Alimentos Separación y determinación de tocoferoles en aceites vegetales por extracción en fase sólida con cartuchos de
Universidad Tecnológica de la Mixteca Maestría en Ciencias Productos Naturales y Alimentos Separación y determinación de tocoferoles en aceites vegetales por extracción en fase sólida con cartuchos de
ESPECTROMETRÍA DE MASAS EN TANDEM (MS/MS): SECUENCIACIÓN DE PÉPTIDOS. Ionización por electrospray (ESI) Espectrometría de masas en tandem (MS/MS)
 ESPECTROMETRÍA DE MASAS EN TANDEM (MS/MS): SECUENCIACIÓN DE PÉPTIDOS Ionización por electrospray (ESI) Espectrometría de masas en tandem (MS/MS) Identificación de proteínas Separación detección Adquisición
ESPECTROMETRÍA DE MASAS EN TANDEM (MS/MS): SECUENCIACIÓN DE PÉPTIDOS Ionización por electrospray (ESI) Espectrometría de masas en tandem (MS/MS) Identificación de proteínas Separación detección Adquisición
Espectrometría de masas molecular EMM
 Espectrometría de masas molecular EMM Etapas de un análisis por EMM - Ionización - Conversión de las moléculas en un flujo de iones (generalmente +1) - Separación de los iones según relación masa/carga
Espectrometría de masas molecular EMM Etapas de un análisis por EMM - Ionización - Conversión de las moléculas en un flujo de iones (generalmente +1) - Separación de los iones según relación masa/carga
PCR gen 16S ARNr bacteriano
 PCR gen 16S ARNr bacteriano Ref. PCR16S 1. OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y la práctica de la Reacción en Cadena de la Polimerasa
PCR gen 16S ARNr bacteriano Ref. PCR16S 1. OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y la práctica de la Reacción en Cadena de la Polimerasa
Electroforesis de proteínas en geles de poliacrilamida
 Electroforesis de proteínas en geles de poliacrilamida Electroforesis de proteínas en geles de poliacrilamida: Introducción y técnica básica La electroforesis de proteínas en geles con una matriz de poliacrilamida,
Electroforesis de proteínas en geles de poliacrilamida Electroforesis de proteínas en geles de poliacrilamida: Introducción y técnica básica La electroforesis de proteínas en geles con una matriz de poliacrilamida,
LAS PROTEINASAS COMO UN PROBLEMA EN PURIFICACION DE PROTEÍNAS. SINTOMAS QUE SUGIEREN UN PROBLEMA PROTEOLITICO:
 LAS PROTEINASAS COMO UN PROBLEMA EN PURIFICACION DE PROTEÍNAS. SINTOMAS QUE SUGIEREN UN PROBLEMA PROTEOLITICO: 1) Ausencia de una proteína específica (por actividad o inmunorreactividad). 2) Bajos rendimientos
LAS PROTEINASAS COMO UN PROBLEMA EN PURIFICACION DE PROTEÍNAS. SINTOMAS QUE SUGIEREN UN PROBLEMA PROTEOLITICO: 1) Ausencia de una proteína específica (por actividad o inmunorreactividad). 2) Bajos rendimientos
Métodos analíticos para el control de alergenos en alimentos. Dr. Luis Mata Responsable de I+D ZEULAB
 Métodos analíticos para el control de alergenos en alimentos Dr. Luis Mata Responsable de I+D ZEULAB Por qué analizar alergenos? Seguridad del consumidor Producto final Control de materias primas Asegurar
Métodos analíticos para el control de alergenos en alimentos Dr. Luis Mata Responsable de I+D ZEULAB Por qué analizar alergenos? Seguridad del consumidor Producto final Control de materias primas Asegurar
2. ESTRUCTURA Y PROPIEDADES DE PROTEÍNAS. 25 Agosto, 2009
 2. ESTRUCTURA Y PROPIEDADES DE PROTEÍNAS. 25 Agosto, 2009 El genoma haploide de un humano contiene 20,000-25,000 genes que codifican a proteínas. Transportadores Enzimas Receptores Estructurales Hormonas
2. ESTRUCTURA Y PROPIEDADES DE PROTEÍNAS. 25 Agosto, 2009 El genoma haploide de un humano contiene 20,000-25,000 genes que codifican a proteínas. Transportadores Enzimas Receptores Estructurales Hormonas
PRACTICA CROMATOGRAFIA EN GEL Y CUANTIFICACIÓN DE PROTEÍNAS J.A. REIG. 1 de 20 2 de 10 1 moneda de 1 10 monedas monedas monedas de 0.
 PRACTICA CROMATOGRAFIA EN GEL Y CUANTIFICACIÓN DE PROTEÍNAS J.A. REIG Para saber lo que tengo debo separar las partes y cuantificar 1 de 20 2 de 10 1 moneda de 1 10 monedas 0.20 4 monedas 0.10 3 monedas
PRACTICA CROMATOGRAFIA EN GEL Y CUANTIFICACIÓN DE PROTEÍNAS J.A. REIG Para saber lo que tengo debo separar las partes y cuantificar 1 de 20 2 de 10 1 moneda de 1 10 monedas 0.20 4 monedas 0.10 3 monedas
ELECTROFORESIS. Objetivo de la clase. *fundamentos *procedimientos *algunas aplicaciones. Conocer los métodos electroforéticos
 ELECTROFORESIS Objetivo de la clase Conocer los métodos electroforéticos *fundamentos *procedimientos *algunas aplicaciones Definición de electroforesis Proceso de separación que se basa en la diferente
ELECTROFORESIS Objetivo de la clase Conocer los métodos electroforéticos *fundamentos *procedimientos *algunas aplicaciones Definición de electroforesis Proceso de separación que se basa en la diferente
Ficha descriptiva SERVICIOS CENTRALES DEL CENTRO DE APOYO TECNOLÓGICO DE LA URJC. Nombre de la UNIDAD/Técnica: Genómica y Citometría de Flujo.
 Página 1 de 5 Nombre de la UNIDAD/Técnica: Genómica y Citometría de Flujo. Responsable: José Antonio Mas Gutiérrez Teléfono: 914 888 645 / 914 887 184 Email joseantonio.mas@urjc.es Principios de la Técnica
Página 1 de 5 Nombre de la UNIDAD/Técnica: Genómica y Citometría de Flujo. Responsable: José Antonio Mas Gutiérrez Teléfono: 914 888 645 / 914 887 184 Email joseantonio.mas@urjc.es Principios de la Técnica
Cuantificación y análisis químico de proteínas
 Cuantificación y análisis químico de proteínas Enlace peptídico R 1 R 2 Secuencia: AlaGluGlyLys o AEGK Puentes disulfuro COO- COO- COO- NH 2 NH 2 NH 2 Modificaciones Post-traduccionales I Análisis químico
Cuantificación y análisis químico de proteínas Enlace peptídico R 1 R 2 Secuencia: AlaGluGlyLys o AEGK Puentes disulfuro COO- COO- COO- NH 2 NH 2 NH 2 Modificaciones Post-traduccionales I Análisis químico
PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN DE LAS COMPETENCIAS PROFESIONALES CUESTIONARIO DE AUTOEVALUACIÓN PARA LAS TRABAJADORAS Y TRABAJADORES
 MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
Espectrometría de masas Instrumentación y aplicaciones
 Clase 02 Espectroscopía de Compuestos Orgánicos MALDI-MS ESI-MS Espectrometría de masas Instrumentación y aplicaciones Espectrometría de Masa Fluid (no salt) + _ cyano-hydroxy cinnamic acid Gold tip needle
Clase 02 Espectroscopía de Compuestos Orgánicos MALDI-MS ESI-MS Espectrometría de masas Instrumentación y aplicaciones Espectrometría de Masa Fluid (no salt) + _ cyano-hydroxy cinnamic acid Gold tip needle
Entregable E3.1 INFORME SOBRE MÉTODOS ANALÍTICOS PARA FTALATOS Y MBT
 EXPEDIENTE IMDEEA/2017/6 ACRÓNIMO AINOCBABY PROGRAMA Proyectos de I+D de carácter no económico realizados en cooperación con empresas TÍTULO DEL PROYECTO ALTERNATIVAS TÉCNICAMENTE VIABLES PARA LA ELIMINACIÓN
EXPEDIENTE IMDEEA/2017/6 ACRÓNIMO AINOCBABY PROGRAMA Proyectos de I+D de carácter no económico realizados en cooperación con empresas TÍTULO DEL PROYECTO ALTERNATIVAS TÉCNICAMENTE VIABLES PARA LA ELIMINACIÓN
UNIVERSIDAD SANTO TOMAS SECCIONAL BUCARAMANGA. División de Ingenierías - Facultad de Química Ambiental
 UNIVERSIDAD SANTO TOMAS SECCIONAL BUCARAMANGA División de Ingeniería Facultad de Química Ambiental Nombre de Asignatura: QUÍMICA INSTRUMENTAL II Àrea: Básicas de Química / Química Analítica Créditos: 4
UNIVERSIDAD SANTO TOMAS SECCIONAL BUCARAMANGA División de Ingeniería Facultad de Química Ambiental Nombre de Asignatura: QUÍMICA INSTRUMENTAL II Àrea: Básicas de Química / Química Analítica Créditos: 4
PURIFICACIÓN DE PROTEÍNAS
 PURIFICACIÓN DE PROTEÍNAS ESQUEMA DE PURIFICACIÓN DE UNA PROTEÍNA tejido vegetal animal homogeneizar cultivo celular bacterias levaduras células mamíferos PREPARACIÓN EXTRACTO crudo fraccionamiento subcelular
PURIFICACIÓN DE PROTEÍNAS ESQUEMA DE PURIFICACIÓN DE UNA PROTEÍNA tejido vegetal animal homogeneizar cultivo celular bacterias levaduras células mamíferos PREPARACIÓN EXTRACTO crudo fraccionamiento subcelular
Trabajo Fin de Máster
 MÁSTER EN CIENCIAS ANALíTICAS Y BIOANALíTICAS Trabajo Fin de Máster Análisis cuantitativo de péptidos/proteínas intactos o modificados post-traduccionalmente mediante HPLC y Espectrometría de masas LAURA
MÁSTER EN CIENCIAS ANALíTICAS Y BIOANALíTICAS Trabajo Fin de Máster Análisis cuantitativo de péptidos/proteínas intactos o modificados post-traduccionalmente mediante HPLC y Espectrometría de masas LAURA
DIPLOMADO DE CROMATOGRAFIA
 DIPLOMADO DE CROMATOGRAFIA Objetivos 1.-Brindar elementos teórico-prácticos de la cromatografía partiendo desde los principios fundamentales hasta la aplicación de las técnicas cualitativas y cuantitativas.
DIPLOMADO DE CROMATOGRAFIA Objetivos 1.-Brindar elementos teórico-prácticos de la cromatografía partiendo desde los principios fundamentales hasta la aplicación de las técnicas cualitativas y cuantitativas.
CROMATOGRAFIA DE GASES
 CROMATOGRAFIA DE GASES Prof. Jorge Mendoza C. Dpto. Química Inorgánica y Analítica Definición: La cromatografía es un método de separación física en la cual los componentes aser separados son distribuidos
CROMATOGRAFIA DE GASES Prof. Jorge Mendoza C. Dpto. Química Inorgánica y Analítica Definición: La cromatografía es un método de separación física en la cual los componentes aser separados son distribuidos
INSULINA GLARGINA BIOFÁRMACO
 MONOGRAFÍA NUEVA Con fundamento en el numeral 4.11.1 de la Norma Oficial Mexicana NOM-001-SSA1-2010, se publica el presente proyecto a efecto de que los interesados, a partir del 1º de agosto y hasta el
MONOGRAFÍA NUEVA Con fundamento en el numeral 4.11.1 de la Norma Oficial Mexicana NOM-001-SSA1-2010, se publica el presente proyecto a efecto de que los interesados, a partir del 1º de agosto y hasta el
Biocromatografía: intercambio iónico
 Biocromatografía: intercambio iónico Intercambio Iónico Columnas TSK-GEL El método más utilizado en la purificación de proteínas y otras moléculas que presenten carga eléctrica es la Cromatografía de Intercambio
Biocromatografía: intercambio iónico Intercambio Iónico Columnas TSK-GEL El método más utilizado en la purificación de proteínas y otras moléculas que presenten carga eléctrica es la Cromatografía de Intercambio
BIOANÁLISIS DE PROTEÍNAS TERAPÉUTICAS
 BIOANÁLISIS DE PROTEÍNAS Introducción TERAPÉUTICAS Caracterización farmacocinética: Determinación de niveles de proteínas en fluidos biológicos Estudios de inmunogenicidad: Determinación y caracterización
BIOANÁLISIS DE PROTEÍNAS Introducción TERAPÉUTICAS Caracterización farmacocinética: Determinación de niveles de proteínas en fluidos biológicos Estudios de inmunogenicidad: Determinación y caracterización
Código TP Trabajo Presencial 7 Habilitable NO
 1 de 1. IDENTIFICACIÓN Nombre de la Asignatura Análisis Instrumental Código 780501 Área Profesionalización Naturaleza Teórico-práctica Semestre V No de Créditos 4 Duración 19 TP Trabajo Presencial 7 Habilitable
1 de 1. IDENTIFICACIÓN Nombre de la Asignatura Análisis Instrumental Código 780501 Área Profesionalización Naturaleza Teórico-práctica Semestre V No de Créditos 4 Duración 19 TP Trabajo Presencial 7 Habilitable
ANALIZADORES. Facultad de Ciencias Exactas y Naturales UBA
 ANALIZADORES 1 Analizadores Cuadrupolo (Q) Trampa de iones (IT) Sector magnético-eléctrico (BE) Tiempo de vuelo (TOF) Resonancia iónica ciclotrónica (ICR) 2 Analizadores Analizador de Tiempo de Vuelo (TOF)
ANALIZADORES 1 Analizadores Cuadrupolo (Q) Trampa de iones (IT) Sector magnético-eléctrico (BE) Tiempo de vuelo (TOF) Resonancia iónica ciclotrónica (ICR) 2 Analizadores Analizador de Tiempo de Vuelo (TOF)
Proceso que cuenta con varias etapas cuyo objetivo es separar una proteína de interés de una mezcla de proteínas.
 Proceso que cuenta con varias etapas cuyo objetivo es separar una proteína de interés de una mezcla de proteínas. La selección de técnicas de purificación depende de las propiedades de las proteínas. Características
Proceso que cuenta con varias etapas cuyo objetivo es separar una proteína de interés de una mezcla de proteínas. La selección de técnicas de purificación depende de las propiedades de las proteínas. Características
Titulo del estudio: Determinación de una medida de masa exacta en alta resolución en L-SIMS (FAB)
 RIAIDT Rede de Infraestruturas de Apoio á Investigación e ao Desenvolvemento Tecnolóxico Vicerrectorado de investigación http://www.usc.es/gl/investigacion/riaidt/ Titulo del estudio: Determinación de
RIAIDT Rede de Infraestruturas de Apoio á Investigación e ao Desenvolvemento Tecnolóxico Vicerrectorado de investigación http://www.usc.es/gl/investigacion/riaidt/ Titulo del estudio: Determinación de
Perfiles metabólicos por cromatografía gaseosa acoplada a espectrometría de masas (GC-MS) en plantas. Dra. Mariana G. López
 Perfiles metabólicos por cromatografía gaseosa acoplada a espectrometría de masas (GC-MS) en plantas Dra. Mariana G. López mglopez@cnia.inta.gov.ar PROTOCOLO PARA LA OBTENCIÓN DE PERFILES METABOLICOS EN
Perfiles metabólicos por cromatografía gaseosa acoplada a espectrometría de masas (GC-MS) en plantas Dra. Mariana G. López mglopez@cnia.inta.gov.ar PROTOCOLO PARA LA OBTENCIÓN DE PERFILES METABOLICOS EN
Tópicos en Biofísica Molecular 2do Cuatrimestre de 2015 Docentes: Lía Pietrasanta y Alan Bush
 Tópicos en Biofísica Molecular 2do Cuatrimestre de 2015 Docentes: Lía Pietrasanta y Alan Bush Guía 4: Electroforesis Northern, Southern y Western blots. Problema 1 Una proteína en su estado nativo tiene
Tópicos en Biofísica Molecular 2do Cuatrimestre de 2015 Docentes: Lía Pietrasanta y Alan Bush Guía 4: Electroforesis Northern, Southern y Western blots. Problema 1 Una proteína en su estado nativo tiene
PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN DE LAS COMPETENCIAS PROFESIONALES CUESTIONARIO DE AUTOEVALUACIÓN PARA LAS TRABAJADORAS Y TRABAJADORES
 MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
Aspectos técnicos para establecer el límite de la detección mediante amplificación por PCR
 Aspectos técnicos para establecer el límite de la detección mediante amplificación por PCR Martha Graciela Rocha Munive Centro Nacional de Investigación y capacitación ambiental Instituto Nacional de Ecología
Aspectos técnicos para establecer el límite de la detección mediante amplificación por PCR Martha Graciela Rocha Munive Centro Nacional de Investigación y capacitación ambiental Instituto Nacional de Ecología
Introducción. Electroforesis zonal Campo aplicado a un soporte estabilizante Muestra dispuesta sobre una zona reducida del soporte
 Introducción Técnica analítica separativa: Transporte de moléculas cargadas bajo la acción de un campo eléctrico Movilidad electroforética depende de: La carga de la molécula Depende del medio ph Fuerza
Introducción Técnica analítica separativa: Transporte de moléculas cargadas bajo la acción de un campo eléctrico Movilidad electroforética depende de: La carga de la molécula Depende del medio ph Fuerza
Institut de Recerca Hospital Universitari Vall d Hebron
 Institut de Recerca Hospital Universitari Vall d Hebron Institut d Investigació Sanitària de l Instituto de Salud Carlos III (ISCIII) Introducció a la metabolòmica. Proteòmica i Metabolòmica: Tècniques
Institut de Recerca Hospital Universitari Vall d Hebron Institut d Investigació Sanitària de l Instituto de Salud Carlos III (ISCIII) Introducció a la metabolòmica. Proteòmica i Metabolòmica: Tècniques
3. MATERIALES Y MÉTODOS
 3. MATERIALES Y MÉTODOS El proceso general llevado a cabo en la presente tesis se ilustra en el siguiente esquema: Exudado uretral/ cervical y/o biopsias Extracción del ADN PCR Digestión Algoritmo computacional:
3. MATERIALES Y MÉTODOS El proceso general llevado a cabo en la presente tesis se ilustra en el siguiente esquema: Exudado uretral/ cervical y/o biopsias Extracción del ADN PCR Digestión Algoritmo computacional:
EXTRACCIÓN DE ADN. BIOLOGÍA GENERAL (Evolución y Genética)
 EXTRACCIÓN DE ADN BIOLOGÍA GENERAL (Evolución y Genética) Curso Académico 2015-2016 Abril 2016 INTRODUCCIÓN Y CONCEPTOS Extracción de ADN La extracción de ADN requiere una serie de etapas básicas. En primer
EXTRACCIÓN DE ADN BIOLOGÍA GENERAL (Evolución y Genética) Curso Académico 2015-2016 Abril 2016 INTRODUCCIÓN Y CONCEPTOS Extracción de ADN La extracción de ADN requiere una serie de etapas básicas. En primer
Espectrometría de Masa
 Espectrometría de Masa La espectrometría de masa crea partículas cargadas (iones). Luego estos iones se analizan y pueden entregar información sobre el peso molecular de la molécula y acerca de su estructura
Espectrometría de Masa La espectrometría de masa crea partículas cargadas (iones). Luego estos iones se analizan y pueden entregar información sobre el peso molecular de la molécula y acerca de su estructura
INTRODUCCIÓN Las plantas y su respuesta frente a cambios ambientales..3
 INTRODUCCIÓN..1 1. Las plantas y su respuesta frente a cambios ambientales..3 2. Las Poliaminas como metabolitos reguladores de crecimiento, división y muerte celular...4 2.1. Metabolismo de PAs...5 2.2.
INTRODUCCIÓN..1 1. Las plantas y su respuesta frente a cambios ambientales..3 2. Las Poliaminas como metabolitos reguladores de crecimiento, división y muerte celular...4 2.1. Metabolismo de PAs...5 2.2.
Política para la aplicación del Tabulador de Cuotas de Recuperación de los Servicios de Investigación, de Consultoría y de Enseñanza
 Política para la aplicación del Tabulador de Cuotas de Recuperación de los Servicios de Investigación, de Consultoría y de Enseñanza Debido a las condiciones cambiantes del mercado y a las necesidades
Política para la aplicación del Tabulador de Cuotas de Recuperación de los Servicios de Investigación, de Consultoría y de Enseñanza Debido a las condiciones cambiantes del mercado y a las necesidades
Módulo: ANÁLISIS INSTRUMENTAL
 DEPARTAMENTO DE QUÍMICA ANÁLISIS DE BIODIESEL MEDIANTE CROMATOGRAFÍA DE GASES Y ESPECTROMETRÍA DE MASAS Módulo: ANÁLISIS INSTRUMENTAL Tema: CG-MS Laboratorio: Análisis Instrumental Duración (horas): 3
DEPARTAMENTO DE QUÍMICA ANÁLISIS DE BIODIESEL MEDIANTE CROMATOGRAFÍA DE GASES Y ESPECTROMETRÍA DE MASAS Módulo: ANÁLISIS INSTRUMENTAL Tema: CG-MS Laboratorio: Análisis Instrumental Duración (horas): 3
INSTITUTO DE QUÍMICA PROGRAMA BIOQUIMICA QUI 132. HORAS SEMANALES : Teóricas: 4 Experimentales: 4
 PONTIFICIA UNIVERSIDAD CATÓLICA DE VALPARAÍSO FACULTAD DE CIENCIAS INSTITUTO DE QUÍMICA INSTITUTO DE QUÍMICA PROGRAMA BIOQUIMICA QUI 132 Patricio Baeza Ch. Secretario Académico CLAVE ASIGNATURA : QUI 132
PONTIFICIA UNIVERSIDAD CATÓLICA DE VALPARAÍSO FACULTAD DE CIENCIAS INSTITUTO DE QUÍMICA INSTITUTO DE QUÍMICA PROGRAMA BIOQUIMICA QUI 132 Patricio Baeza Ch. Secretario Académico CLAVE ASIGNATURA : QUI 132
