Northern blot control
|
|
|
- María Rosario Muñoz Pinto
- hace 8 años
- Vistas:
Transcripción
1 TRANSCRIPTOMA
2 - Northern blot - Aporta información sobre la presencia de un transcrito, su abundancia y su tamaño - Electroforesis: Se realiza en condiciones desnaturalizantes, Gel: agarosa 0,8-1,4% y formaldehído 6%, en buffer MOPS (3-(N-morfolino)propano-sulfónico) - Las muestras deben desnaturalizarse, buffer de carga: MOPS, formamida, formaldehído, colorante - Transferencia: por capilaridad o vacío, similar a Southern - Hibridación: similar a Southern, buffer con más formamida (50%) - Para comparar diferencias en los niveles de expresión de un gen es muy importante la utilización de un control: generalmente un gen que se exprese constitutivamente: citoesqueleto ( -actina), un gen de ARNr. Las intensidades de la señal del gen en estudio deben normalizarse con las del control
3 - RT-PCR - PCR tiempo real
4 - ANÁLISIS DE LA EXPRESIÓN DIFERENCIAL - Obtener información sobre genes que se transcriben únicamente o con mayor intensidad en una determinada condición respecto a otra. Se busca analizar el transcriptoma completo. - Estos métodos se basan en la utilización de dos poblaciones de ADNc obtenidas a partir del ARN de las dos condiciones a ensayar: Métodos clásicos: - Hibridación substractiva - Differential display -cdna-aflp - ESTs Métodos basados en genómica: - Microarreglos - RNA sequencing
5 - ANÁLISIS DE LA EXPRESIÓN DIFERENCIAL - Hibridación substractiva -Se basa en la eliminación de las moléculas de ADNc que están repetidas en las dos condiciones a través de un proceso de hibridación; las moléculas híbridas formadas entre ADNc de las dos condiciones son entonces eliminadas, el resto (expresadas diferencialmente) se aíslan y estudian. - p.ej. Sistema SSH (Supression Substractive hybridization), de Clontech
6 - Hibridación substractiva
7 - ANÁLISIS DE LA EXPRESIÓN DIFERENCIAL - cdna-aflp - Similar al método de AFLPs pero partiendo del ADNc obtenido a partir de dos condiciones en lugar de DNA genómico. Los patrones de bandas obtenidos con ambas condiciones se comparan para detectar bandas presentes sólo en una condición, indicativo la expresión diferencial de un transcrito.
8
9
10 - ANÁLISIS DE LA EXPRESIÓN DIFERENCIAL - Differential display - Consiste en visualizar en un gel el nivel de expresión de los transcritos provenientes de dos condiciones diferentes y detectar diferencias en la misma. - Actualmente se utilizan métodos basados en PCR (DD-PCR). - Esquema: - Para cada población de RNA se ponen 3 reacciones de síntesis de ADNc, cada una con un primer oligo-dt anclado: T 12 A, T 12 C, T 12 G - Finalizada la síntesis de la hebra de ADNc, se añade el primer arbitrario (10-12 bases) y todos los componentes para una reacción de PCR, con 32 P-dCTP - Se cargan las muestras, previa desnaturalización, en un gel de acrilamida del 6% desnaturalizante (7 M urea). Autorradiografía - Cortar las bandas de interés (expresadas diferencialmente), eluir el ADN y precipitar con acetato de potasio, glicógeno y etanol. - Reamplificar por PCR usando la combinación adecuada de primer T 12 M (M= A, C o G) con arbitrario - Correr un gel de agarosa con el producto de la PCR. Extraer el fragmento del gel para subclonarlo, secuenciarlo, etc.
11 - Differential display Para cada condición se tiene un pool de RNA que se utiliza para síntesis de ADNc y amplificación con: primer oligo-dt anclado + primer arbitrario. Se obtiene así un patrón de bandas amplificadas para cada condición, las cuales se comparan en un gel de poliacrilamida para detectar transcritos expresados diferencialmente.
12
13 - ANÁLISIS DE LA EXPRESIÓN DIFERENCIAL - SAGE: Serial analysis of gene expression - Se basa en tres principios - Una secuencia corta, tag (etiqueta), de nucleótidos, contiene suficiente información para identificar de forma única un transcrito. - Una vez aislados, estos tags pueden unirse para formar largas series de moléculas de ADN que pueden clonarse y secuenciarse. - La cuantificación del número de veces que un determinado tag está presente en una condición indica el nivel de expresión del gen correspondiente en esa condición
14 - SAGE - Se cortan con las enzimas NlaIII y BsmFI las secuencias tag de cada transcrito de una condición determinada - Se ligan las secuencias aisladas formando largas cadenas de ADN que se secuencian - La secuencia nos indica el número de veces que un tag particular está presente, lo que refleja la abundancia de ese transcrito en una determinada condición, permitiendo hacer comparaciones cuantitativas entre dos o más condiciones - Finalmente se identifican los genes a que corresponden los tags mediante comparación de la secuencia del tag con una base de datos que contenga todos los genes caracterizados de la especie en cuestión
15 - SAGE Obtención de los tags: Se corta con NlaIII, se añaden adaptadores (linkers) para BsmFI y se corta con esta enzima. BsmFI es del tipo IIs, corta a una distancia de unos 15 pares de bases del sitio de reconocimiento (en el linker), generando fragmentos con una secuencia de 15 pb (SAGE tag), que se ligan para formar concatémeros.
16 - ANÁLISIS DE LA EXPRESIÓN DIFERENCIAL - ESTs: Expressed Sequence Tags - Más que un método de differential display es una técnica que permite identificar cientos de transcritos que se están expresando en una célula en un momento y condiciones determinados: transcriptoma - Consiste en la obtención de ADNc de la muestra o muestras en estudio, y en la realización de una única reacción de secuencia que permita identificar mediante búsquedas en bases de datos los genes a que corresponden cada uno de los clones secuenciados. Se obtiene así una representación del transcriptoma que puede compararse entre dos condiciones distintas.
17 - MICROARREGLOS -Un arreglo de ADN es una colección de moléculas de ADN (ADNC u oligonucleótidos) dispuestas sobre un soporte sólido como una matriz de filas y columnas - Macroarreglos: puntos sobre una membrana de nylon o nitrocelulosa, pequeño número. Las sondas (ADNc que proviene de dos condiciones) se marcan por radiactividad. Se detecta la intensidad de la señal en cada punto y se compara la misma entre las dos condiciones. - Microarreglos: Habitualmente oligonucleótidos (20-80 nucleótidos), cada uno de ellos es una secuencia identificativa de un gen. Contienen hasta puntos. El marcaje de las sondas de ADNc se realiza con fluorescencia: rojo (Cy5) para la condición problema y verde (Cy3) para la condición de referencia. El detector compara la intensidad de la fluorescencia e integra el resultado en cada punto, observándose el resultado final como un punto rojo (genes sobreexpresados en la condición problema), verde (genes con menor expresión en la condición problema) o amarillo-naranja (genes con expresión similar en las condiciones problema y de referencia)
18 Confección del microarreglo 1. Colecciones de Expressed Sequences Tags (EST) 2. Bibliotecas de ADNc 3. Secuencias genómicas Procedencia de la información de secuencia para la elaboración de los oligonucleótidos o fragmentos de ADN que se fijarán al arreglo.
19 Confección de arreglos MICROARREGLOS Siembra 0,25-1 nl/punto generando puntos de m de diámetro.
20 Confección de microarreglos
21 Hibridación en microarreglos El experimento tipo consiste en la comparación de los niveles de expresión de todos los genes de un organismo en dos estados celulares (condiciones). Proceso 1. Aislar ARNm a partir de una muestra biológica. 2. Convertir el ARNm en ADNc, utilizando una transcriptasa reversa. 3. Marcar el ADNc con nucleótidos fluorescentes (Cy5 y Cy3) 4. Hibridar el ADNc marcado en el microarreglo. 5. Detectar y cuantificar la fluorescencia utilizando un laser scanner confocal. 6. Analizar los resultados.
22 Síntesis de ADNc
23 Hibridación en microarreglos 1 2 Cy5 = 633 nm Cy3 = 532 nm Cy5 Cy3 Expresión de 1 > 2 Expresión de 1 = 2 Expresión de 1 < 2
24 Microarreglo de levadura
25 - RNA Sequencing - Secuenciación del transcriptoma mediante los nuevos métodos de secuenciación (Next Generation Sequencing) - Permite la obtención de millones de secuencias: gran precisión estadística - Permite la detección de ARNm con maduración alternativa o transcritos no descritos, mientras que los microarreglos sólo permiten estudiar transcritos ya conocidos (lo que se ha depositado en el microarreglo) -Puede realizarse con especies en las cuales no existe información previa de su secuencia genómica (si bien los resultados óptimos se consiguen cuando sí está secuenciado el genoma)
26 PROTEOMA
27 ESTUDIOS CON PROTEÍNAS: SDS-PAGE SDS-PAGE: Polyacrilamide Gel Electrophoresis. Permite separar proteínas desnaturalizadas en un gel de poliacrilmida en función de su tamaño. Se utiliza acrilamida/bis 37:1. La mezcla que se indica es para un gel con un porcentaje de acrilamida del 12%, si este porcentaje varía debe recalcularse la cantidad de acrilamida/bis y de agua destilada a añadir. Mezcla para gel separador: Acrilamida/bis 40% 9 ml Tris-HCl 1,5 M ph 8,5 7.5 ml Agua destilada 13 ml 10% SDS 300 l 10% APS 100 l TEMED 15 l Mezcla para gel concentrante: Acrilamida/bis 40% 1 ml Tris-HCl 1M ph 6, ml Agua destilada 7.6 ml 10% SDS 100 l 10% APS 35 l TEMED 5 l
28 SDS-PAGE Buffers y soluciones Tampón de electroforesis: 25 mm Tris, 192 mm Glicina, 0.1% SDS, ph 8.3 Tampón de muestra: 0.3 M Tris HCl, ph 6.8, 5% SDS, 50% glycerol, Azul de bromofenol 0.01%, 2- mercaptoetanol 0,5% Solución de teñido: 0.125% Coomassie Brilliant Blue R-250, 50% Metanol, 10% Ácido Acético Solución de desteñido: 50% Metanol, 10% Ácido Acético
29 SDS-PAGE Tinción con Coomasie Solución de teñido: 0.125% Coomassie Brilliant Blue R-250, 50% Metanol, 10% Ácido Acético Tinción con sales de plata 1- Etanol, ácido acético, H 2 O (30:10:60) 2- Etanol 30% 3- Nitrato de plata 0,1% 4- NaCl, CuSO 4, NH 4 OH, tiosulfato sódico 5- Ácido acético 1%
30 PAGE PAGE: Gel de poliacrilamida nativo, sin SDS - Cuando se pretende extraer una proteína del gel de forma que conserve su actividad, o bien cuando se quiere ensayar una actividad enzimática en el propio gel, las proteínas no deben desnaturalizarse. Para ello se llevan a cabo las siguientes modificaciones: - No se añade SDS al gel, buffer de muestra ni buffer de electroforesis - No se añade -mercaptoetanol al buffer de muestra para evitar la reducción de los puentes disulfuro - Las muestras no se calientan y la electroforesis se desarrolla a 4ºC - Para ver actividad en el gel: éste se incuba con el sustrato adecuado hasta que aparezcan bandas de actividad Debe tenerse muy en cuenta el ph del gel, ya que las proteína entrarán y se moverán en el gel sólo si tienen carga neta negativa, y esto depende de su punto isoeléctrico. - Si se quiere recuperar la actividad de una proteína despues de un SDS-PAGE existen protocolos para renaturalizar la proteína
31 Western Blot Detección de una proteína mediante anticuerpos tras un SDS-PAGE
32 Western Blot Actividad de la enzima fosfatasa alcalina conjugada con el anticuepo secundario
33 Western Blot Reacción cruzada con anticuerpos policlonales
34 Western Blot Cuantificación de la proteína tras un Western blot como método de determinación de la expresión del gen
35 Técnicas de Proteómica Electroforesis bidimensional: 2D SDS-PAGE Isoelectroenfoque: separación de las proteínas en función de su punto isoeléctrico: ph al cual la carga neta total de la proteína es 0 SDS-PAGE: separación de las proteínas en función de su tamaño
36 Técnicas de Proteómica Electroforesis bidimensional: 2D SDS-PAGE Pueden llegar a detectarse todas las proteínas que se están expresando en una célula Permite establecer comparaciones entre dos condiciones: sistema de análisis de expresión diferencial
37 Técnicas de Proteómica Métodos de identificación de las proteínas Las proteínas separadas en un 2D (o purificadas por cualquier otro método) pueden analizarse para conocer su masa molecular, huella peptídica y secuencias de péptidos internos en sistemas de espectrometría de masas; esto permite su identificación. - Huella peptídica: tras digestión con tripsina se obtiene la masa molecular precisa de todos los péptidos resultantes, la cual se compara con la masa virtual obtenida de la información de los genes en la base de datos. Se lleva a cabo con un MALDI-TOF (Matrix-assisted laser desorption ionization-time of flight) - Para completar la identificación puede hacerse una microsecuenciación de péptidos internos con un LC-MS/MS (Liquid chromatography-tandem MS). Se obtienen secuencias de longitud corta (6-14 aminoácidos) que a menudo presentan ambigüedades. - Microsecuenciación por Degradación de Edman : Método clásico de secuenciación de péptidos. Requiere al menos 0,5 g de proteína. Es un método más directo, pueden obtenerse secuencias de hasta aa, mayor fiabilidad.
38 Técnicas de Proteómica Huella peptídica
39 Técnicas de Proteómica Huella peptídica
40 Técnicas de Proteómica Huella peptídica
41 SECUENCIACIÓN DEL ADN
42 Método de Sanger o de los didesoxinucleótidos - Se basa en la utilización de terminadores: moléculas de didesoxinucleótidos que al incorporarse a la cadena de ADN detienen la reacción de polimerización.
43 - Una mezcla de los 4 desoxinucleótidos con 1 didesoxinucleótido concreto ocasionará que la reacción de polimerización se detenga al azar generando moléculas de diferente tamaño que se separan en un gel de acrilamida
44 ANÁLISIS DE LA SECUENCIA DE NUCLEÓTIDOS ddatp ddgtp 5 -A-3 5 -AGA-3 5 -AGACCTGCA-3 5 -AGACCTGCATTTA-3 5 -AGACCTGCATTTATA-3 5 -AGACCTGCATTTATAA-3 5 -AGACCTGCATTTATAAGCCGCCGCA-3 3 -TCTGGACGTAAATATTCGGCGGCGTCA-5 5 -AG-3 5 -AGACCTG-3 5 -AGACCTGCATTTATAAG-3 5 -AGACCTGCATTTATAAGCCG-3 5 -AGACCTGCATTTATAAGCCGCCG-3 5 -AGACCTGCATTTATAAGCCGCCGCAG-3 4 reacciones: ddatp, ddgtp, ddctp, ddttp ddatp ddctp ddttp 3 -TCTGGACGTAAATATTCGGCGGCGTCA-5 5 -A-3 5 -AGA-3 5 -AGACCTGCA-3 5 -AGACCTGCAT-3 5 -AGACCTGCATTTA-3 3 -TCTGGACGTAAATATTCGGCGGCGTCA-5 5 -AGAC-3 5 -AGACC-3 5 -AGACCTGC-3 5 -AGACCTGCATTTATAAGC-3 5 -AGACCTGCATTTATAAGCC-3 5 -AGACCTGCATTTATAAGCCGC-3 5 -AGACCTGCATTTATAAGCCGCC-3 5 -AGACCTGCATTTATAAGCCGCCGC-3 3 -TCTGGACGTAAATATTCGGCGGCGTCA-5 5 -AGACCT-3 5 -AGACCTGCATT-3 5 -AGACCTGCATTTATAA-3 5 -AGACCTGCATTT-3 5 -AGACCTGCATTTATAAGCCGCCGCA-3 5 -AGACCTGCATTTAT-3 5 -AGACCTGCATTTATAAGCCGCCGCAGT-3
45 - Gel de acrilamida con reacciones de secuencia, se visualiza una autorradiografía generada por la señal del isótopo 35 S-dATP
46
47 - En la actualidad el proceso se hace de forma automática. Los terminadores llevan incorporados colorantes fluorescentes de diferente longitud de onda, que permiten hacer la reacción en un único tubo. Tras un proceso de electroforesis capilar un detector láser recoge la señal de cada terminador (ddatp, ddctp, ddgtp, ddttp)
48 Secuenciación automática
49
50 Secuenciación primer walking - Tenemos un fragmento para secuenciar clonado en un vector plasmídico. Se lleva a cabo la primera reacción de secuencia con un primer universal. A partir de la secuencia obtenida se diseña un segundo primer hacia el extremo 3 de la misma para que haga de iniciador en la siguiente reacción, y así sucesivamente hasta completar el fragmento a secuenciar Secuenciación shot-gun 5 3
51 Estrategias de secuenciación en proyectos genoma Shot-gun Clon a clon de una genoteca
52 Algunos sitios web relacionados con proyectos genoma
MÉTODOS DE ESTUDIO DE PROTEÍNAS
 MÉTODOS DE ESTUDIO DE PROTEÍNAS ANÁLISIS DE EXPRESIÓN DE PROTEÍNAS Al estudiar la expresión de un gen puede analizarse el ARN (Northern blot, PCR a tiempo real, etc), y también la expresión de la proteína,
MÉTODOS DE ESTUDIO DE PROTEÍNAS ANÁLISIS DE EXPRESIÓN DE PROTEÍNAS Al estudiar la expresión de un gen puede analizarse el ARN (Northern blot, PCR a tiempo real, etc), y también la expresión de la proteína,
DNA RECONBINANTE Depende de enzimas capaces de: Cortar Unir Replicar Transcribir inversamente el RNA Otra herramienta es el uso de Sondas específicas
 DNA RECONBINANTE Depende de enzimas capaces de: Cortar Unir Replicar Transcribir inversamente el RNA Otra herramienta es el uso de Sondas específicas ELEMENTOS BÁSICOS DE LA INVESTIGACIÓN EN GENES Análisis
DNA RECONBINANTE Depende de enzimas capaces de: Cortar Unir Replicar Transcribir inversamente el RNA Otra herramienta es el uso de Sondas específicas ELEMENTOS BÁSICOS DE LA INVESTIGACIÓN EN GENES Análisis
Técnicas de Biología Molecular
 Técnicas de Biología Molecular DNA I. Enzimas de restricción Análisis Las enzimas de restricción fueron aisladas de bacterias; su función natural es proteger contra DNA extraño II. Separación electroforética
Técnicas de Biología Molecular DNA I. Enzimas de restricción Análisis Las enzimas de restricción fueron aisladas de bacterias; su función natural es proteger contra DNA extraño II. Separación electroforética
Módulo 1 Biología Molecular Genética Molecular II 2009. Módulo 1. Amplificación de un fragmento de ADN genómico por PCR
 Módulo 1 Amplificación de un fragmento de ADN genómico por PCR En este primer módulo se amplificará por PCR, mediante el uso de oligonucleótidos específicos, un fragmento de ADN genómico de Aspergillus
Módulo 1 Amplificación de un fragmento de ADN genómico por PCR En este primer módulo se amplificará por PCR, mediante el uso de oligonucleótidos específicos, un fragmento de ADN genómico de Aspergillus
CUESTIONES. 1. Por qué la PCR convencional no es cuantitativa?
 2º BIOQUÍMICA CUESTIONES 1. Por qué la PCR convencional no es cuantitativa? En la PCR convencional, la cuantificación del ADN de la muestra es complicada debido a que la eficacia de amplificación va disminuyendo
2º BIOQUÍMICA CUESTIONES 1. Por qué la PCR convencional no es cuantitativa? En la PCR convencional, la cuantificación del ADN de la muestra es complicada debido a que la eficacia de amplificación va disminuyendo
Materiales para la secuenciación de ADN
 Introduccion La Secuenciación Sanger es un método de secuenciación de ADN en el que el ADN diana se desnaturaliza y se hibrida con un cebador de oligonucleótidos, que se extiende entonces gracias a la
Introduccion La Secuenciación Sanger es un método de secuenciación de ADN en el que el ADN diana se desnaturaliza y se hibrida con un cebador de oligonucleótidos, que se extiende entonces gracias a la
PCR gen 18S ARNr humano
 PCR gen 18S ARNr humano Ref.PCR18S 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa (PCR)
PCR gen 18S ARNr humano Ref.PCR18S 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa (PCR)
El Banco Nacional de ADN oferta un control de calidad de muestras de ADN y ARN.
 PROGRAMA CONTROL DE CALIDAD DE MUESTRAS El Banco Nacional de ADN oferta un control de calidad de muestras de ADN y ARN. El programa completo de control de calidad de muestras de ADN y ARN engloba diferentes
PROGRAMA CONTROL DE CALIDAD DE MUESTRAS El Banco Nacional de ADN oferta un control de calidad de muestras de ADN y ARN. El programa completo de control de calidad de muestras de ADN y ARN engloba diferentes
Practica la genética Ficha didáctica del profesorado Bachillerato
 Ficha didáctica del profesorado Bachillerato www.eurekamuseoa.es Extracción de ADN Cuál es la función de cada uno de los ingredientes utilizados para realizar la disolución tampón para la visualización
Ficha didáctica del profesorado Bachillerato www.eurekamuseoa.es Extracción de ADN Cuál es la función de cada uno de los ingredientes utilizados para realizar la disolución tampón para la visualización
ELABORACIÓN N DE MEZCLA PARA PCR. Raquel Asunción Lima Cordón
 ELABORACIÓN N DE MEZCLA PARA PCR Raquel Asunción Lima Cordón PCR Polymerase Chain reaction (reacción en cadena de la polimerasa) Sintetizar muchas veces un fragmento de ADN PCR: simulación de lo que sucede
ELABORACIÓN N DE MEZCLA PARA PCR Raquel Asunción Lima Cordón PCR Polymerase Chain reaction (reacción en cadena de la polimerasa) Sintetizar muchas veces un fragmento de ADN PCR: simulación de lo que sucede
Genómica y transcriptómica para la generación de datos en Evolución
 recuadro Genómica y transcriptómica para la generación de datos en Evolución Gabriela Bedó Genómica. Sus objetivos Compilar todas las secuencias de un organismo Establecer la localización de los genes
recuadro Genómica y transcriptómica para la generación de datos en Evolución Gabriela Bedó Genómica. Sus objetivos Compilar todas las secuencias de un organismo Establecer la localización de los genes
Detección de patógenos en alimentos, utilizando la técnica de PCR, reacción en cadena de la polimerasa.
 Detección de patógenos en alimentos, utilizando la técnica de PCR, reacción en cadena de la polimerasa. Lic. Esp. Mariano Diego Massari 1er Congreso Bioquímico Córdoba 2011 8ª Jornada de Actualización
Detección de patógenos en alimentos, utilizando la técnica de PCR, reacción en cadena de la polimerasa. Lic. Esp. Mariano Diego Massari 1er Congreso Bioquímico Córdoba 2011 8ª Jornada de Actualización
Identificación varietal en vid por técnicas de Biología Molecular. Lic. Luciana Garcia Lic. Carolina Chiconofri
 Identificación varietal en vid por técnicas de Biología Molecular. Lic. Luciana Garcia Lic. Carolina Chiconofri OBJETIVO Desarrollar un banco de datos a partir de plantas de origen indudable y del uso
Identificación varietal en vid por técnicas de Biología Molecular. Lic. Luciana Garcia Lic. Carolina Chiconofri OBJETIVO Desarrollar un banco de datos a partir de plantas de origen indudable y del uso
Reacción en cadena de la polimerasa (PCR)
 Dr. Alejandro Leal Reacción en cadena de la polimerasa (PCR) La reacción en cadena de la polimerasa (PCR, por sus siglas en inglés de "polymerase chain reaction") es un método de amplificación in vitro
Dr. Alejandro Leal Reacción en cadena de la polimerasa (PCR) La reacción en cadena de la polimerasa (PCR, por sus siglas en inglés de "polymerase chain reaction") es un método de amplificación in vitro
PCR. Componentes del PCR. PCR Polymerase Chain Reaction (Reacción en Cadena de la Polimerasa)
 PCR PCR Polymerase Chain Reaction (Reacción en Cadena de la Polimerasa) Es una técnica de biología molecular descrita en 1986 por Kary Mullis. (Nobel de química en 1993) Necesidad de pruebas de diagnóstico
PCR PCR Polymerase Chain Reaction (Reacción en Cadena de la Polimerasa) Es una técnica de biología molecular descrita en 1986 por Kary Mullis. (Nobel de química en 1993) Necesidad de pruebas de diagnóstico
Transcriptomics and Proteomics
 Transcriptomics and Proteomics Tipificación de la expresión: permite el estudio de la funcion de los genes Tipificación del RNA depende de la hibridizacion de los ácidos nucleicos Northern blot Producir
Transcriptomics and Proteomics Tipificación de la expresión: permite el estudio de la funcion de los genes Tipificación del RNA depende de la hibridizacion de los ácidos nucleicos Northern blot Producir
Nuevos paneles de PCR Real Time: El diagnóstico molecular más rápido, fiable y eficaz
 IDEXX VetLab Suite IDEXX SNAP Tests Laboratorio de Referencia IDEXX Nuevos paneles de PCR Real Time: El diagnóstico molecular más rápido, fiable y eficaz Obtenga respuestas definitivas con la IDEXX RealPCR
IDEXX VetLab Suite IDEXX SNAP Tests Laboratorio de Referencia IDEXX Nuevos paneles de PCR Real Time: El diagnóstico molecular más rápido, fiable y eficaz Obtenga respuestas definitivas con la IDEXX RealPCR
PROBLEMAS MAS FRECUENTES DURANTE LA SECUENCIACIÓN NO SE PRODUCE REACCION O ESTA DECAE POCO DESPUÉS DE COMENZAR
 PROBLEMAS MAS FRECUENTES DURANTE LA SECUENCIACIÓN NO SE PRODUCE REACCION O ESTA DECAE POCO DESPUÉS DE COMENZAR Las causas pueden ser las siguientes: No hay ADN o se encuentra en muy baja concentración.
PROBLEMAS MAS FRECUENTES DURANTE LA SECUENCIACIÓN NO SE PRODUCE REACCION O ESTA DECAE POCO DESPUÉS DE COMENZAR Las causas pueden ser las siguientes: No hay ADN o se encuentra en muy baja concentración.
BIOTECNOLOGÍA. 1.- Ingeniería Genética, ADN recombinante
 BIOTECNOLOGÍA 1.- Ingeniería Genética, ADN recombinante Técnica del ADN recombinante: es la más usada en ingeniería genética, esta basada en el uso de las enzimas de restricción o endonucleasas de restricción
BIOTECNOLOGÍA 1.- Ingeniería Genética, ADN recombinante Técnica del ADN recombinante: es la más usada en ingeniería genética, esta basada en el uso de las enzimas de restricción o endonucleasas de restricción
TÉCNICAS GENÓMICAS. 2) Cuantificación del número de virus presentes en muestras de sangre o suero: carga vírica
 TÉCNICAS GENÓMICAS Utilidad/Objetivos: 1) Detección de microorganismos directamente en muestras clínicas identificando un fragmento específico del genoma del microorganismo concreto 2) Cuantificación del
TÉCNICAS GENÓMICAS Utilidad/Objetivos: 1) Detección de microorganismos directamente en muestras clínicas identificando un fragmento específico del genoma del microorganismo concreto 2) Cuantificación del
Instituto de Biomedicina y Biotecnología de Cantabria (IBBTEC) SERVICIO DE SECUENCIACIÓN MASIVA
 1. DESCRIPCIÓN DEL SERVICIO El servicio de Secuenciación Masiva tiene como finalidad el proporcionar asesoramiento y soporte técnico a los grupos de investigación interesados en realizar proyectos de ultrasecuenciación.
1. DESCRIPCIÓN DEL SERVICIO El servicio de Secuenciación Masiva tiene como finalidad el proporcionar asesoramiento y soporte técnico a los grupos de investigación interesados en realizar proyectos de ultrasecuenciación.
7.012 Serie de ejercicios 5
 Nombre Grupo 7.012 Serie de ejercicios 5 Pregunta 1 Al estudiar los problemas de esterilidad, usted intenta aislar un hipotético gen de conejo que explique la prolífica reproducción de estos animales.
Nombre Grupo 7.012 Serie de ejercicios 5 Pregunta 1 Al estudiar los problemas de esterilidad, usted intenta aislar un hipotético gen de conejo que explique la prolífica reproducción de estos animales.
AMINOÁCIDOS SE PUEDEN UNIR POR ENLACES PEPTÍDICOS
 Tema 4. Proteínas: funciones biológicas y estructura primaria. Enlace peptídico. Péptidos y proteínas. Diversidad de funciones biológicas. Niveles de organización estructural de las proteínas. Separación
Tema 4. Proteínas: funciones biológicas y estructura primaria. Enlace peptídico. Péptidos y proteínas. Diversidad de funciones biológicas. Niveles de organización estructural de las proteínas. Separación
- Clonar un gen (molde ADN o ARN)
 APLICACIONES PCR Aplicaciones de la PCR - Clonar un gen (molde ADN o ARN) - Secuencia conocida - Genes homólogos en especies próximas (primers degenerados) - Información de secuencia proteica (primers
APLICACIONES PCR Aplicaciones de la PCR - Clonar un gen (molde ADN o ARN) - Secuencia conocida - Genes homólogos en especies próximas (primers degenerados) - Información de secuencia proteica (primers
PROBLEMAS MÁS FRECUENTES Y POSIBLES SOLUCIONES
 PROBLEMAS MÁS FRECUENTES Y POSIBLES SOLUCIONES NO SE PRODUCE REACCIÓN O ÉSTA DECAE POCO DESPUÉS DE COMENZAR No hay ADN o hay menos del necesario No hay cebador o la concentración es inferior a la necesaria.
PROBLEMAS MÁS FRECUENTES Y POSIBLES SOLUCIONES NO SE PRODUCE REACCIÓN O ÉSTA DECAE POCO DESPUÉS DE COMENZAR No hay ADN o hay menos del necesario No hay cebador o la concentración es inferior a la necesaria.
ELECTROFORESIS. Agarosa. Poliacrilamida
 ELECTROFORESIS DE ADN ELECTROFORESIS Agarosa Poliacrilamida Finalidad de la electroforesis Separar Identificar Purificar 1 2 3 4 5 Tinción del ADN Bromuro de etidio Absorbancia a 302 y 366 y emisión a
ELECTROFORESIS DE ADN ELECTROFORESIS Agarosa Poliacrilamida Finalidad de la electroforesis Separar Identificar Purificar 1 2 3 4 5 Tinción del ADN Bromuro de etidio Absorbancia a 302 y 366 y emisión a
TEMA 6. PURIFICACIÓN DE PROTEÍNAS
 TEMA 6. PURIFICACIÓN DE PROTEÍNAS 1. Introducción 2. Métodos de rotura celular y extracción de proteínas 3. Métodos cromatográficos 4. Métodos electroforéticos 1. Introducción La mayor parte de las investigaciones
TEMA 6. PURIFICACIÓN DE PROTEÍNAS 1. Introducción 2. Métodos de rotura celular y extracción de proteínas 3. Métodos cromatográficos 4. Métodos electroforéticos 1. Introducción La mayor parte de las investigaciones
Código: IDX-016 Ver: 1 TOXO. Sistema para la detección de la presencia de ADN de Toxoplasma gondii. Reg. MSP 21205
 Sistema para la detección de la presencia de ADN de Toxoplasma gondii Reg. MSP 21205 Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336 71 60. info@atgen.com.uy www.atgen.com.uy
Sistema para la detección de la presencia de ADN de Toxoplasma gondii Reg. MSP 21205 Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336 71 60. info@atgen.com.uy www.atgen.com.uy
Técnicas descritas en el curso 7.28
 Técnicas descritas en el curso 7.28 Técnica: Clase 1 Experimento de incorporación de dntps Ensayo de extensión del cebador Ensayo de unión en filtro Electroforesis en gel Análisis de ADN Helicasa Polaridad
Técnicas descritas en el curso 7.28 Técnica: Clase 1 Experimento de incorporación de dntps Ensayo de extensión del cebador Ensayo de unión en filtro Electroforesis en gel Análisis de ADN Helicasa Polaridad
PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN DE LAS COMPETENCIAS PROFESIONALES CUESTIONARIO DE AUTOEVALUACIÓN PARA LAS TRABAJADORAS Y TRABAJADORES
 MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
CLASE DE RESOLUCIÓN DE PROBLEMAS DE PCR LIC. BIOTECNOLOGÍA 2015
 CLASE DE RESOLUCIÓN DE PROBLEMAS DE PCR LIC. BIOTECNOLOGÍA 2015 DEFINICIÓN PCR: Constituye la técnica más importante para amplificar ácidos nucleicos in vitro. Ambas hebras del DNA de interés son replicadas
CLASE DE RESOLUCIÓN DE PROBLEMAS DE PCR LIC. BIOTECNOLOGÍA 2015 DEFINICIÓN PCR: Constituye la técnica más importante para amplificar ácidos nucleicos in vitro. Ambas hebras del DNA de interés son replicadas
velocidades de movimiento mediante la aplicación de un campo eléctrico a través de una matriz porosa
 INTRODUCCIÓN En general, la electroforesis es una técnica que separa las moléculas en base a sus diferentes velocidades de movimiento mediante la aplicación de un campo eléctrico a través de una matriz
INTRODUCCIÓN En general, la electroforesis es una técnica que separa las moléculas en base a sus diferentes velocidades de movimiento mediante la aplicación de un campo eléctrico a través de una matriz
PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN DE LAS COMPETENCIAS PROFESIONALES CUESTIONARIO DE AUTOEVALUACIÓN PARA LAS TRABAJADORAS Y TRABAJADORES
 MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
APLICACIÓN DE LA PCR: DIAGNÓSTICO DE PARÁSITOS
 Prácticas docentes en la COD: 10-71 APLICACIÓN DE LA PCR: DIAGNÓSTICO DE PARÁSITOS FUNDAMENTO TEÓRICO La PCR es una técnica que permite llevar a cabo la síntesis in vitro de fragmentos de ADN. Está basada
Prácticas docentes en la COD: 10-71 APLICACIÓN DE LA PCR: DIAGNÓSTICO DE PARÁSITOS FUNDAMENTO TEÓRICO La PCR es una técnica que permite llevar a cabo la síntesis in vitro de fragmentos de ADN. Está basada
Instituto de Biomedicina y Biotecnología de Cantabria (IBBTEC) SERVICIO DE SECUENCIACIÓN MASIVA
 1. DESCRIPCIÓN DEL SERVICIO El servicio de Secuenciación Masiva tiene como finalidad el proporcionar asesoramiento y soporte técnico a los grupos de investigación interesados en realizar proyectos de ultrasecuenciación.
1. DESCRIPCIÓN DEL SERVICIO El servicio de Secuenciación Masiva tiene como finalidad el proporcionar asesoramiento y soporte técnico a los grupos de investigación interesados en realizar proyectos de ultrasecuenciación.
3. COMPONENTES. Tampón de electroforesis concentrado 2 x 50 ml 10 X (2 envases 500ml)
 PCR SIMULADA Ref.PCR Simulada (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa
PCR SIMULADA Ref.PCR Simulada (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa
Caracterización morfo-agronómica y molecular de frijoles criollos de color rojo claro en Nicaragua y de frijoles negros en Ipala, Guatemala
 Caracterización morfo-agronómica y molecular de frijoles criollos de color rojo claro en Nicaragua y de frijoles negros en Ipala, Guatemala IICA/Red SICTA-CIAT INFORME DE AVANCE Gerardo Gallego - Harold
Caracterización morfo-agronómica y molecular de frijoles criollos de color rojo claro en Nicaragua y de frijoles negros en Ipala, Guatemala IICA/Red SICTA-CIAT INFORME DE AVANCE Gerardo Gallego - Harold
ELECTROFORESIS EN GELES DE POLIACRILAMIDA SDS-PAGE. Presencia de Sodio Dodecil Sulfato bajo condiciones reductoras (SDSPAGE)
 ELECTROFORESIS EN GELES DE POLIACRILAMIDA SDSPAGE Presencia de Sodio Dodecil Sulfato bajo condiciones reductoras (SDSPAGE) Método rápido, reproducible y de bajo costo Utilizado para cuantificar, comparar
ELECTROFORESIS EN GELES DE POLIACRILAMIDA SDSPAGE Presencia de Sodio Dodecil Sulfato bajo condiciones reductoras (SDSPAGE) Método rápido, reproducible y de bajo costo Utilizado para cuantificar, comparar
ELECTROFORESIS BASICA
 Ref.ELECBASICA (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO ELECTROFORESIS BASICA El objetivo de este experimento es introducir a los alumnos en el conocimiento de la teoría electroforética y familiarizarse
Ref.ELECBASICA (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO ELECTROFORESIS BASICA El objetivo de este experimento es introducir a los alumnos en el conocimiento de la teoría electroforética y familiarizarse
Tecnología de DNA recombinante I
 Tecnología de DNA recombinante I Base: capacidad de manipular moléculas de DNA en un tubo de ensayo Enzimas: Purificadas, con actividades conocidas y controladas DNA polimerasas Síntesis de DNA Nucleasas
Tecnología de DNA recombinante I Base: capacidad de manipular moléculas de DNA en un tubo de ensayo Enzimas: Purificadas, con actividades conocidas y controladas DNA polimerasas Síntesis de DNA Nucleasas
METODOLOGÍAS UTILIZADAS EN INVESTIGACIÓN BÁSICA Y APLICADA REACCION EN CADENA DE LA POLIMERASA (PCR)
 METODOLOGÍAS UTILIZADAS EN INVESTIGACIÓN BÁSICA Y APLICADA REACCION EN CADENA DE LA POLIMERASA (PCR) Centro de de Microscopía Electrónica Facultad de de Ciencias Médicas Universidad Nacional de de Córdoba
METODOLOGÍAS UTILIZADAS EN INVESTIGACIÓN BÁSICA Y APLICADA REACCION EN CADENA DE LA POLIMERASA (PCR) Centro de de Microscopía Electrónica Facultad de de Ciencias Médicas Universidad Nacional de de Córdoba
Western Blotting (o inmunotransferencia) es un procedimiento estándar de laboratorio que permite a
 Introducción Western Blotting (o inmunotransferencia) es un procedimiento estándar de laboratorio que permite a los investigadores verificar la expresión de una proteína, determinar la cantidad relativa
Introducción Western Blotting (o inmunotransferencia) es un procedimiento estándar de laboratorio que permite a los investigadores verificar la expresión de una proteína, determinar la cantidad relativa
SECUENCIACIÓN SANGER DE ADN: GUÍA DE SOLUCIONES TÉCNICAS
 SECUENCIACIÓN SANGER DE ADN: GUÍA DE SOLUCIONES TÉCNICAS Secugen recomienda que para la visualización de las secuencias se usen programas que permitan ver el dato crudo, ya que a partir de ese dato se
SECUENCIACIÓN SANGER DE ADN: GUÍA DE SOLUCIONES TÉCNICAS Secugen recomienda que para la visualización de las secuencias se usen programas que permitan ver el dato crudo, ya que a partir de ese dato se
Técnicas de ADN recombinante: la manipulación genética
 Técnicas de ADN recombinante: la manipulación genética A partir de los años 70 se desarrollaron las herramientas de la biología molecular o la ingeniería genética o lo que se ha llamado técnicas del ADN
Técnicas de ADN recombinante: la manipulación genética A partir de los años 70 se desarrollaron las herramientas de la biología molecular o la ingeniería genética o lo que se ha llamado técnicas del ADN
TEST de PATERNIDAD. Ref.PCR paternidad (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO
 Ref.PCR paternidad (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO TEST de PATERNIDAD Este experimento introduce a los alumnos en el uso del ADN y la PCR para simular una determinación de paternidad. Los estudiantes
Ref.PCR paternidad (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO TEST de PATERNIDAD Este experimento introduce a los alumnos en el uso del ADN y la PCR para simular una determinación de paternidad. Los estudiantes
III. Material genético. b. Composición y estructura del RNA.
 III. Material genético b. Composición y estructura del RNA. RNA (ácido ribonucléico) Polímero de nucleótidos La pentosa de los nucleótidos es la Ribosa: en la posición 2' del anillo del azúcar hay un grupo
III. Material genético b. Composición y estructura del RNA. RNA (ácido ribonucléico) Polímero de nucleótidos La pentosa de los nucleótidos es la Ribosa: en la posición 2' del anillo del azúcar hay un grupo
DETERMINACIÓN DEL FACTOR Rh por PCR
 Ref.PCRRh DETERMINACIÓN DEL FACTOR Rh por PCR 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa
Ref.PCRRh DETERMINACIÓN DEL FACTOR Rh por PCR 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa
Tema 11. Herramientas de la genética molecular
 Tema 11. Herramientas de la genética molecular Genética CC. Mar 2004-05 Objetivos Técnicas de clonación Construcción de genotecas e identificación de secuencias Mapas de restricción Amplificación (PCR)
Tema 11. Herramientas de la genética molecular Genética CC. Mar 2004-05 Objetivos Técnicas de clonación Construcción de genotecas e identificación de secuencias Mapas de restricción Amplificación (PCR)
ADN y RNA caracterización y métodos de estudio
 ADN y RNA caracterización y métodos de estudio Separación por centrifugación de equilibrio en gradiente de densidad de en CsCl Separación por centrifugación de equilibrio en gradiente de densidad de en
ADN y RNA caracterización y métodos de estudio Separación por centrifugación de equilibrio en gradiente de densidad de en CsCl Separación por centrifugación de equilibrio en gradiente de densidad de en
5. DETECCION DE GENES DE VIRULENCIA MEDIANTE HIBRIDACIÓN CON SONDAS DE ADN
 5. DETECCION DE GENES DE VIRULENCIA MEDIANTE HIBRIDACIÓN CON SONDAS DE ADN Materiales - Eppendorf de 1,5 ml estériles - Eppendorf de pared fina para PCR - Puntas de pipeta estériles desechables - Guantes
5. DETECCION DE GENES DE VIRULENCIA MEDIANTE HIBRIDACIÓN CON SONDAS DE ADN Materiales - Eppendorf de 1,5 ml estériles - Eppendorf de pared fina para PCR - Puntas de pipeta estériles desechables - Guantes
DANAGENE RNA PURIFICATION KIT
 DANAGENE RNA PURIFICATION KIT REF.0801.1 100 EXTRACCIONES REF.0801.2 500 EXTRACCIONES 1.INTRODUCCION Este kit permite la permite la obtención de ARN total a partir de cultivos celulares, tejidos animales,
DANAGENE RNA PURIFICATION KIT REF.0801.1 100 EXTRACCIONES REF.0801.2 500 EXTRACCIONES 1.INTRODUCCION Este kit permite la permite la obtención de ARN total a partir de cultivos celulares, tejidos animales,
HOSPITAL CLÍNIC-IDIBAPS RED NACIONAL DE CENTROS DE CÁNCER PROGRAMA DE GENÓMICA Y PROTEÓMICA
 HOSPITAL CLÍNIC-IDIBAPS RED NACIONAL DE CENTROS DE CÁNCER PROGRAMA DE GENÓMICA Y PROTEÓMICA CATÁLOGO DE OFERTA DE SERVICIOS GENÓMICOS I. INFORMACIÓN GENERAL: NOMBRE DE UNIDAD: Unidad de Genómica CENTRO
HOSPITAL CLÍNIC-IDIBAPS RED NACIONAL DE CENTROS DE CÁNCER PROGRAMA DE GENÓMICA Y PROTEÓMICA CATÁLOGO DE OFERTA DE SERVICIOS GENÓMICOS I. INFORMACIÓN GENERAL: NOMBRE DE UNIDAD: Unidad de Genómica CENTRO
MÉTODOS CROMATOGRÁFICOS: 1. Exclusión molecular 2. Intercambio iónico 3. Afinidad SSN
 MÉTODOS CROMATOGRÁFICOS: 1. Exclusión molecular 2. Intercambio iónico 3. Afinidad SSN Propiedades de una proteína que son útiles para su purificación por cromatografía Peso molecular Carga iónica Hidrofobicidad
MÉTODOS CROMATOGRÁFICOS: 1. Exclusión molecular 2. Intercambio iónico 3. Afinidad SSN Propiedades de una proteína que son útiles para su purificación por cromatografía Peso molecular Carga iónica Hidrofobicidad
FRAGMENTO OLIGO 5-3 Hebra SECUENCIA 5' - - > 3' TAMAÑO (pb) F1. hmtl 569 L AACCAAACCCCAAAGACACC hmth2982 H CTGATCCAACATCGAGGTCG
 ANEXO 1 Protocolo para la PCR para la amplificación del mtdna en 10 fragmentos solapantes: Se prepara la siguiente mezcla: Tampón ( TRIS 100 mm, MgCl 2 12 mm, KCl 500 mm, ph 8,3): 10X dntps : 10 mm (cada
ANEXO 1 Protocolo para la PCR para la amplificación del mtdna en 10 fragmentos solapantes: Se prepara la siguiente mezcla: Tampón ( TRIS 100 mm, MgCl 2 12 mm, KCl 500 mm, ph 8,3): 10X dntps : 10 mm (cada
ELECTROFORESIS WESTERN BLOT ELISA
 ELECTROFORESIS WESTERN BLOT ELISA INTEGRANTES: Arguelles, Rocío Assandri, Matías Almirón, Marianela Buonanduci, Facundo Gómez, Alan Miller, Florencia López, Rocío Vidal, Sol Sillingardi, Leonardo Soria,
ELECTROFORESIS WESTERN BLOT ELISA INTEGRANTES: Arguelles, Rocío Assandri, Matías Almirón, Marianela Buonanduci, Facundo Gómez, Alan Miller, Florencia López, Rocío Vidal, Sol Sillingardi, Leonardo Soria,
Easy PDF Creator is professional software to create PDF. If you wish to remove this line, buy it now.
 Unidad Curricular: Virología y Micología Veterinaria 1 TRABAJO PRÁCTICO No. 3 AMPLIFICACIÓN DE GENES VIRALES Reacción en Cadena de la Polimerasa, conocida como PCR (por sus siglas en inglés: Polimerase
Unidad Curricular: Virología y Micología Veterinaria 1 TRABAJO PRÁCTICO No. 3 AMPLIFICACIÓN DE GENES VIRALES Reacción en Cadena de la Polimerasa, conocida como PCR (por sus siglas en inglés: Polimerase
GUÍA PARA LA SECUENCIACIÓN AUTOMÁTICA DE DNA
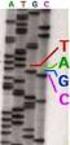 Página 1 de 16 GUÍA PARA LA SECUENCIACIÓN AUTOMÁTICA DE DNA SERVICIO DE SECUENCIACIÓN-S.C.S.I.E. UNIVERSITAT DE VALÈNCIA Página 2 de 16 CONTENIDOS: 1.- Secuenciación automática de DNA 2.- Tipos de molde
Página 1 de 16 GUÍA PARA LA SECUENCIACIÓN AUTOMÁTICA DE DNA SERVICIO DE SECUENCIACIÓN-S.C.S.I.E. UNIVERSITAT DE VALÈNCIA Página 2 de 16 CONTENIDOS: 1.- Secuenciación automática de DNA 2.- Tipos de molde
AQUAGESTION. ISAv: Un acercamiento actualizado en la detección de sus variantes en la región. Departamento de Desarrollo y Laboratorio Diagnóstico.
 AQUAGESTION ISAv: Un acercamiento actualizado en la detección de sus variantes en la región. Departamento de Desarrollo y Laboratorio Diagnóstico. Noviembre 2011 ACTUALIDAD Este año Sernapesca confirma
AQUAGESTION ISAv: Un acercamiento actualizado en la detección de sus variantes en la región. Departamento de Desarrollo y Laboratorio Diagnóstico. Noviembre 2011 ACTUALIDAD Este año Sernapesca confirma
OLIMPÍADA ARGENTINA DE BIOLOGÍA APEB ÁREA DE ACTUALIZACIÓN Y PERFECCIONAMIENTO EN LA ENSEÑANZA DE LA BIOLOGÍA CONTINUIDAD Y CAMBIO DE LAS ESPECIES I:
 MINISTERIO DE EDUCACIÓN, CIENCIA Y TECNOLOGIA UNIVERSIDAD NACIONAL DE RIO CUARTO FACULTAD DE CIENCIAS EXACTAS, FÍSICO - QUÍMICAS Y NATURALES DEPARTAMENTO DE CIENCIAS NATURALES OLIMPÍADA ARGENTINA DE BIOLOGÍA
MINISTERIO DE EDUCACIÓN, CIENCIA Y TECNOLOGIA UNIVERSIDAD NACIONAL DE RIO CUARTO FACULTAD DE CIENCIAS EXACTAS, FÍSICO - QUÍMICAS Y NATURALES DEPARTAMENTO DE CIENCIAS NATURALES OLIMPÍADA ARGENTINA DE BIOLOGÍA
Análisis en Genética 1
 Análisis en Genética 1 Análisis Genético FUNCION BIOLOGICA Gen o genes implicados Localización Cartografiado Función Interacciones TIPOS DE MUTACIÓN MUTACIÓN GÉNICA -El alelo de un gen sufre un cambio,
Análisis en Genética 1 Análisis Genético FUNCION BIOLOGICA Gen o genes implicados Localización Cartografiado Función Interacciones TIPOS DE MUTACIÓN MUTACIÓN GÉNICA -El alelo de un gen sufre un cambio,
La PCR. La Reacción en Cadena de la Polimerasa es la herramienta más utilizada
 La PCR La Reacción en Cadena de la Polimerasa es la herramienta más utilizada PCR- Ventajas y Usos Amplificación ilimitada de secuencias de interés. Rápida, Sencilla y Eficaz. Técnica altamente sensible
La PCR La Reacción en Cadena de la Polimerasa es la herramienta más utilizada PCR- Ventajas y Usos Amplificación ilimitada de secuencias de interés. Rápida, Sencilla y Eficaz. Técnica altamente sensible
Instituto de Innovación en Biotecnología e Industria
 Instituto de Innovación en Biotecnología e Industria Centro de Biotecnología Vegetal (CEBIVE) Marcadores moleculares para caracterizar cultivares de aguacates criollos (Persea americana) del tipo antillano,
Instituto de Innovación en Biotecnología e Industria Centro de Biotecnología Vegetal (CEBIVE) Marcadores moleculares para caracterizar cultivares de aguacates criollos (Persea americana) del tipo antillano,
Clonación molecular. Clonar significa hacer copias idénticas
 INGENIERÍA GENÉTICA Clonación molecular Clonar significa hacer copias idénticas Este término originalmente fue aplicado al procedimiento de aislar una célula y permitirle reproducirse creando una población
INGENIERÍA GENÉTICA Clonación molecular Clonar significa hacer copias idénticas Este término originalmente fue aplicado al procedimiento de aislar una célula y permitirle reproducirse creando una población
ELECTROFORESIS AVANZADA
 Ref.ELECAVANZADA (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO ELECTROFORESIS AVANZADA El objetivo de este experimento es introducir a los alumnos en el conocimiento de la teoría electroforética y familiarizarse
Ref.ELECAVANZADA (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO ELECTROFORESIS AVANZADA El objetivo de este experimento es introducir a los alumnos en el conocimiento de la teoría electroforética y familiarizarse
Técnicas moleculares.
 Técnicas moleculares. DMTV Carolina Acevedo Curso de Microbiología 2015 SÍNTESIS IN VITRO DE UNA GRAN CANTIDAD DE COPIAS DE UN SEGMENTO DE ADN EXISTENTE EN UNA MUESTRA. O sea. Amplificamos en forma exponencial
Técnicas moleculares. DMTV Carolina Acevedo Curso de Microbiología 2015 SÍNTESIS IN VITRO DE UNA GRAN CANTIDAD DE COPIAS DE UN SEGMENTO DE ADN EXISTENTE EN UNA MUESTRA. O sea. Amplificamos en forma exponencial
METODOLOGIA DEL PCR. Lic. Jorge Mato Luis. Laboratorio de Genética Molecular Hospital Clínico Quirúrgico Hermanos Ameijeiras
 METODOLOGIA DEL PCR Lic. Jorge Mato Luis Laboratorio de Genética Molecular Hospital Clínico Quirúrgico Hermanos Ameijeiras Desnaturalización del DNA 5 A G G T T A G T G G A C C C T T G A T 3 3 T C C A
METODOLOGIA DEL PCR Lic. Jorge Mato Luis Laboratorio de Genética Molecular Hospital Clínico Quirúrgico Hermanos Ameijeiras Desnaturalización del DNA 5 A G G T T A G T G G A C C C T T G A T 3 3 T C C A
1. Cuáles son las diferencias en los componentes químicos del ADN y ARN?
 ACTIVIDADES TEMA 4 - BIOTECNOLOGÍA 1. Cuáles son las diferencias en los componentes químicos del ADN y ARN? Las cadenas de ADN están formadas por fosfato y desoxirribosa y la del ARN por fosfato y ribosa.
ACTIVIDADES TEMA 4 - BIOTECNOLOGÍA 1. Cuáles son las diferencias en los componentes químicos del ADN y ARN? Las cadenas de ADN están formadas por fosfato y desoxirribosa y la del ARN por fosfato y ribosa.
INTRODUCCIÓN A LA METODOLOGÍA MOLECULAR. 2002 `Derechos Reservados Pontificia Universidad Javeriana Instituto de Genética Humana Bogotá COLOMBIA
 INTRODUCCIÓN A LA METODOLOGÍA MOLECULAR 2002 `Derechos Reservados Pontificia Universidad Javeriana Instituto de Genética Humana Bogotá COLOMBIA Equipos de Laboratorio Un equipo de laboratorio es un conjunto
INTRODUCCIÓN A LA METODOLOGÍA MOLECULAR 2002 `Derechos Reservados Pontificia Universidad Javeriana Instituto de Genética Humana Bogotá COLOMBIA Equipos de Laboratorio Un equipo de laboratorio es un conjunto
Metodología y aplicaciones de la amplificación de material genético: Introducción a la bioinformática.
 Departamento de Bioquímica Médica y Biología Molecular Práctica 3 Metodología y aplicaciones de la amplificación de material genético: Introducción a la bioinformática. Curso 1 Medicina (Abril) 2012 BIOQUÍMICA
Departamento de Bioquímica Médica y Biología Molecular Práctica 3 Metodología y aplicaciones de la amplificación de material genético: Introducción a la bioinformática. Curso 1 Medicina (Abril) 2012 BIOQUÍMICA
VII.-Capítulo 2. Métodos para el estudio de la expresión de genes
 VII.-Capítulo 2 Métodos para el estudio de la expresión de genes Pessino, Silvina C.; Martelotto, Luciano G. 1 Introducción La capacidad de secuenciar genomas completos desarrollada en la última década
VII.-Capítulo 2 Métodos para el estudio de la expresión de genes Pessino, Silvina C.; Martelotto, Luciano G. 1 Introducción La capacidad de secuenciar genomas completos desarrollada en la última década
CUANTIFICACIÓN DE ADENOSIN DESAMINASA (ADA)
 CUANTIFICACIÓN DE ADENOSIN DESAMINASA (ADA) PROTOCOLO ADA FUNDAMENTO DEL METODO: La adenosindesaminasa (ADA) es una enzima del catabolismo de las purinas que cataliza la conversión de la adenosina en inosina
CUANTIFICACIÓN DE ADENOSIN DESAMINASA (ADA) PROTOCOLO ADA FUNDAMENTO DEL METODO: La adenosindesaminasa (ADA) es una enzima del catabolismo de las purinas que cataliza la conversión de la adenosina en inosina
Métodos de análisis biomédicos
 Métodos de análisis biomédicos 1 Aplicación de la biología molecular en medicina *Estudio y diagnóstico de enfermedades producidas por alteraciones genéticas (hereditarias ó somáticas) y aquellas producidas
Métodos de análisis biomédicos 1 Aplicación de la biología molecular en medicina *Estudio y diagnóstico de enfermedades producidas por alteraciones genéticas (hereditarias ó somáticas) y aquellas producidas
MATERIALES Y MÉTODOS
 MATERIALES Y MÉTODOS Para la obtención, aislamiento y caracterización de la proteína de superficie HSPB66 de H. pylori ATCC 43504 se realizó un cultivo de esta cepa, seguido de la extracción de proteínas
MATERIALES Y MÉTODOS Para la obtención, aislamiento y caracterización de la proteína de superficie HSPB66 de H. pylori ATCC 43504 se realizó un cultivo de esta cepa, seguido de la extracción de proteínas
Electroforesis de proteínas en geles de poliacrilamida. Electroforesis de proteínas en geles de poliacrilamida: Introducción y técnica básica
 Electroforesis de proteínas en geles de poliacrilamida Electroforesis de proteínas en geles de poliacrilamida: Introducción y técnica básica La electroforesis de proteínas en geles con una matriz de poliacrilamida,
Electroforesis de proteínas en geles de poliacrilamida Electroforesis de proteínas en geles de poliacrilamida: Introducción y técnica básica La electroforesis de proteínas en geles con una matriz de poliacrilamida,
TaqMan GMO Maize Quantification Kit. Part No: 4481972
 TaqMan GMO Maize Quantification Kit Part No: 4481972 1. Introducción Los organismos modificados genéticamente (OMG) se encuentran ampliamente distribuidos, siendo la soja y el maíz los vegetales que ocupan
TaqMan GMO Maize Quantification Kit Part No: 4481972 1. Introducción Los organismos modificados genéticamente (OMG) se encuentran ampliamente distribuidos, siendo la soja y el maíz los vegetales que ocupan
UNIVERSIDAD NACIONAL ABIERTA Y A DISTANCIA
 UNIVERSIDAD NACIONAL ABIERTA Y A DISTANCIA PROGRAMA DE INGENIERIA DE ALIMENTOS 211612 TRANSFERENCIA DE MASA ACTIVIDAD 11 RECONOCIMIENTO UNIDAD 3 BOGOTA D.C. Extracción líquido - líquido La extracción líquido-líquido,
UNIVERSIDAD NACIONAL ABIERTA Y A DISTANCIA PROGRAMA DE INGENIERIA DE ALIMENTOS 211612 TRANSFERENCIA DE MASA ACTIVIDAD 11 RECONOCIMIENTO UNIDAD 3 BOGOTA D.C. Extracción líquido - líquido La extracción líquido-líquido,
CÓDIGO GENÉTICO Y SÍNTESIS DE PROTEÍNAS
 CÓDIGO GENÉTICO Y SÍNTESIS DE PROTEÍNAS Sumario Mitosis y meiosis Código genético y síntesis de proteínas: 1. Concepto de gen 2. Estructura del ADN 3. La replicación del ADN 4. La transcripción 5. La traducción
CÓDIGO GENÉTICO Y SÍNTESIS DE PROTEÍNAS Sumario Mitosis y meiosis Código genético y síntesis de proteínas: 1. Concepto de gen 2. Estructura del ADN 3. La replicación del ADN 4. La transcripción 5. La traducción
Comprobando la calidad del DNA genómico mediante electroforesis en gel
 Comprobando la calidad del DNA genómico mediante electroforesis en gel GELES 1 Y 2 Agarosa 0.8 %, electroforesis a 1 V/cm Muestras: Se ha cargado muestras de DNA genómico no digerido, antes (líneas impares)
Comprobando la calidad del DNA genómico mediante electroforesis en gel GELES 1 Y 2 Agarosa 0.8 %, electroforesis a 1 V/cm Muestras: Se ha cargado muestras de DNA genómico no digerido, antes (líneas impares)
ADN ARN Proteínas. La información genética es portada por el ADN y se hereda con él.
 Todos los organismos contienen información que les permite coordinar sus procesos. Esta información, a fin de poder ser transferida a la descendencia, esta asentada en una molécula capaz de replicarse,
Todos los organismos contienen información que les permite coordinar sus procesos. Esta información, a fin de poder ser transferida a la descendencia, esta asentada en una molécula capaz de replicarse,
ESI-MALDI-TOF. El análisis por espectrometría de masas se realiza en cuatro etapas básicas:
 ESI-MALDI-TOF Introducción Espectrometría de masas La espectrometría de masas es una técnica analítica en la que los átomos o moléculas de una muestra son ionizados, con mayor frecuencia positivamente,
ESI-MALDI-TOF Introducción Espectrometría de masas La espectrometría de masas es una técnica analítica en la que los átomos o moléculas de una muestra son ionizados, con mayor frecuencia positivamente,
Práctica 1A Ensayo de Granulometría Prácticas de Laboratorio
 1A ENSAYO DE GRANULOMETRÍA 1. TIPOS DE SUELO. RECONOCIMIENTO VISUAL Desde un punto de vista geotécnico, existen cuatro grandes tipos de suelos: gravas, arenas, limos y arcillas, caracterizados principalmente
1A ENSAYO DE GRANULOMETRÍA 1. TIPOS DE SUELO. RECONOCIMIENTO VISUAL Desde un punto de vista geotécnico, existen cuatro grandes tipos de suelos: gravas, arenas, limos y arcillas, caracterizados principalmente
PCR en Tiempo Real. Introducción
 Introducción Página 1 de 6 Introducción general La reacción en cadena de la polimerasa, cuyas iniciales en inglés son PCR ("polymerase chain reaction"), es una técnica que fue desarrollada por Kary Mullis
Introducción Página 1 de 6 Introducción general La reacción en cadena de la polimerasa, cuyas iniciales en inglés son PCR ("polymerase chain reaction"), es una técnica que fue desarrollada por Kary Mullis
Investigación en genes. Tecnología del ADN recombinante
 Investigación en genes Tecnología del ADN recombinante Tecnología del ADN recombinante 1º parte: Conocimientos básicos que posibilitaron su desarrollo 2º parte: Instrumentos básicos 3º parte Ejemplos Conocimientos
Investigación en genes Tecnología del ADN recombinante Tecnología del ADN recombinante 1º parte: Conocimientos básicos que posibilitaron su desarrollo 2º parte: Instrumentos básicos 3º parte Ejemplos Conocimientos
2.3 SISTEMAS HOMOGÉNEOS.
 2.3 SISTEMAS HOMOGÉNEOS. 2.3.1 DISOLUCIONES. Vemos que muchos cuerpos y sistemas materiales son heterogéneos y podemos observar que están formados por varias sustancias. En otros no podemos ver que haya
2.3 SISTEMAS HOMOGÉNEOS. 2.3.1 DISOLUCIONES. Vemos que muchos cuerpos y sistemas materiales son heterogéneos y podemos observar que están formados por varias sustancias. En otros no podemos ver que haya
CROMOSOMA 21. Pintado Cromosómico Total 21
 CROMOSOMA 21 Pintado Cromosómico Total 21 21q21.3 Early onset Alzheimer region probe EN 21 Break Apart 21q22 [AML1(RUNX1)] Doble Fusión t(12;21)(p13;q22)[etv6/aml1(runx1)] Doble Fusión t(8;21)(q21;q22)
CROMOSOMA 21 Pintado Cromosómico Total 21 21q21.3 Early onset Alzheimer region probe EN 21 Break Apart 21q22 [AML1(RUNX1)] Doble Fusión t(12;21)(p13;q22)[etv6/aml1(runx1)] Doble Fusión t(8;21)(q21;q22)
AUTOR: JORGE CONTRERAS PINEDA 1. Titulo:
 Página 1 de 1 1. Titulo: Electroforesis de DNA 2. Objetivo Conocer los principios básicos de la electroforesis horizontal en geles de agarosa y aplicarlo para la separación de DNA humano, plasmídico, recombinante
Página 1 de 1 1. Titulo: Electroforesis de DNA 2. Objetivo Conocer los principios básicos de la electroforesis horizontal en geles de agarosa y aplicarlo para la separación de DNA humano, plasmídico, recombinante
Tema 7: Solubilidad. (Fundamentos de Química, Grado en Física) Equilibrio químico Enero Mayo, 2011 1 / 24
 Tema 7: Solubilidad. Producto de solubilidad. Efecto del ion común en la solubilidad. Limitaciones al producto de solubilidad: K ps. Criterios para la precipitación de la sal. Precipitación fraccionada.
Tema 7: Solubilidad. Producto de solubilidad. Efecto del ion común en la solubilidad. Limitaciones al producto de solubilidad: K ps. Criterios para la precipitación de la sal. Precipitación fraccionada.
Capítulo 9. Archivos de sintaxis
 Capítulo 9 Archivos de sintaxis El SPSS permite generar y editar archivos de texto con sintaxis SPSS, es decir, archivos de texto con instrucciones de programación en un lenguaje propio del SPSS. Esta
Capítulo 9 Archivos de sintaxis El SPSS permite generar y editar archivos de texto con sintaxis SPSS, es decir, archivos de texto con instrucciones de programación en un lenguaje propio del SPSS. Esta
RESULTADOS Y DISCUSIÓN. Estimación de la Concentración Proteica del Filtrado de Cultivo de Mycobacterium tuberculosis H37Rv
 RESULTADOS Y DISCUSIÓN Estimación de la Concentración Proteica del Filtrado de Cultivo de Mycobacterium tuberculosis H37Rv La curva estándar con la que se estimó la concentración proteica del filtrado
RESULTADOS Y DISCUSIÓN Estimación de la Concentración Proteica del Filtrado de Cultivo de Mycobacterium tuberculosis H37Rv La curva estándar con la que se estimó la concentración proteica del filtrado
Preguntas de selectividad en Andalucía. Ácidos nucleicos. Análisis e interpretación de imágenes, esquemas, figuras...
 Año 2001 Describa las funciones más relevantes de los nucleótidos. Cite un ejemplo de nucleótido que participe en cada una de ellas [1,5]. Explique las funciones de los distintos tipos de RNA que participan
Año 2001 Describa las funciones más relevantes de los nucleótidos. Cite un ejemplo de nucleótido que participe en cada una de ellas [1,5]. Explique las funciones de los distintos tipos de RNA que participan
IDENTIFICACIÓN DE PROTEÍNAS POR ESPECTROMETRÍA DE MASAS. EQUIPAMIENTO
 IDENTIFICACIÓN DE PROTEÍNAS POR ESPECTROMETRÍA DE MASAS. EQUIPAMIENTO La Espectrometría de Masas es una tecnología analítica esencial en el contexto de la proteómica actual debido a su alta capacidad de
IDENTIFICACIÓN DE PROTEÍNAS POR ESPECTROMETRÍA DE MASAS. EQUIPAMIENTO La Espectrometría de Masas es una tecnología analítica esencial en el contexto de la proteómica actual debido a su alta capacidad de
Soluciones de la serie de ejercicios 4 (Curso 7.012)
 Pregunta 1 Soluciones de la serie de ejercicios 4 (Curso 7.012) Usted está estudiando la síntesis del aminoácido triptófano en las bacterias. Las enzimas TrpA, TrpB, TrpC, TrpD, TrpE and AroH son necesarias
Pregunta 1 Soluciones de la serie de ejercicios 4 (Curso 7.012) Usted está estudiando la síntesis del aminoácido triptófano en las bacterias. Las enzimas TrpA, TrpB, TrpC, TrpD, TrpE and AroH son necesarias
11.2-DISCUSIÓN Prueba rápida
 11.2-DISCUSIÓN Prueba rápida Como se observa en la tabla 9 del total de las embarazadas (62,214) a las que se les realizo la prueba rápida un 99.3%(61,808) de ellas dio como resultado no reactivo, tan
11.2-DISCUSIÓN Prueba rápida Como se observa en la tabla 9 del total de las embarazadas (62,214) a las que se les realizo la prueba rápida un 99.3%(61,808) de ellas dio como resultado no reactivo, tan
DETERMINACIÓN ESPECTROFOTOMÉTRICA DE KMnO 4, CuSO 4 y K 2 Cr 2 O 7
 DETERMINACIÓN ESPECTROFOTOMÉTRICA DE KMnO 4, CuSO 4 y K 2 Cr 2 O 7 El objetivo de esta investigación es la determinación cuantitativa de la concentración de KMnO 4 en una muestra problema mediante espectroscopía
DETERMINACIÓN ESPECTROFOTOMÉTRICA DE KMnO 4, CuSO 4 y K 2 Cr 2 O 7 El objetivo de esta investigación es la determinación cuantitativa de la concentración de KMnO 4 en una muestra problema mediante espectroscopía
Genoma y Ensamblado Seminario de Modelos y Métodos cuantitativos (Bioinformática)
 Genoma y Ensamblado Seminario de Modelos y Métodos cuantitativos (Bioinformática) Rodrigo Fernández Cristián Maureira Gabriel Zamora Universidad Técnica Federico Santa María 18 de noviembre de 2010 Genoma
Genoma y Ensamblado Seminario de Modelos y Métodos cuantitativos (Bioinformática) Rodrigo Fernández Cristián Maureira Gabriel Zamora Universidad Técnica Federico Santa María 18 de noviembre de 2010 Genoma
GUIA DE LABORATORIO PRACTICA 8 EXTRACCIÓN ADN PROGRAMA DE ENFERMERIA CURSO INTEGRADO DE PROCESOS BIOLOGICOS
 GUIA DE LABORATORIO PRACTICA 8 EXTRACCIÓN ADN PROGRAMA DE ENFERMERIA CURSO INTEGRADO DE PROCESOS BIOLOGICOS Leidy Diana Ardila Leal Docente. INTRODUCCIÓN En esta práctica se va a realizar la extracción
GUIA DE LABORATORIO PRACTICA 8 EXTRACCIÓN ADN PROGRAMA DE ENFERMERIA CURSO INTEGRADO DE PROCESOS BIOLOGICOS Leidy Diana Ardila Leal Docente. INTRODUCCIÓN En esta práctica se va a realizar la extracción
1) a) En la figura señale, englobando con un trazo continuo, lo siguiente:
 CÁTEDRA: BIOQUÍMICA Carreras: Farmacia Profesorado en Química Licenciatura en Química Licenciatura en Alimentos ÁCIDOS NUCLEICOS 1) a) En la figura señale, englobando con un trazo continuo, lo siguiente:
CÁTEDRA: BIOQUÍMICA Carreras: Farmacia Profesorado en Química Licenciatura en Química Licenciatura en Alimentos ÁCIDOS NUCLEICOS 1) a) En la figura señale, englobando con un trazo continuo, lo siguiente:
imegen Alfa-1-AT Manual de Usuario Referencia: IMG-211
 Manual de Usuario imegen Alfa-1-AT Genotipado de las mutaciones Glu342Lys (PI-Z) y Glu264Val (PI-S) del gen SERPINA1 mediante PCR a tiempo real Referencia: Fabricado en España Garantías y responsabilidades
Manual de Usuario imegen Alfa-1-AT Genotipado de las mutaciones Glu342Lys (PI-Z) y Glu264Val (PI-S) del gen SERPINA1 mediante PCR a tiempo real Referencia: Fabricado en España Garantías y responsabilidades
Métodos de análisis biomédicos
 Métodos de análisis biomédicos 1 Métodos de análisis biomédicos Comprenden métodos de análisis a nivel de DNA, RNA y proteínas que permitan tener un mayor conocimiento de una enfermedad dada, que puedan
Métodos de análisis biomédicos 1 Métodos de análisis biomédicos Comprenden métodos de análisis a nivel de DNA, RNA y proteínas que permitan tener un mayor conocimiento de una enfermedad dada, que puedan
Electroforesis en gel de poliacrilamida y electrotransferencia
 Electroforesis en gel de poliacrilamida y electrotransferencia INDICE ELECTROFORESIS Fundamento y características Tipos de electroforesis: libre y de zona Electroforesis en papel, acetato de celulosa Electroforesis
Electroforesis en gel de poliacrilamida y electrotransferencia INDICE ELECTROFORESIS Fundamento y características Tipos de electroforesis: libre y de zona Electroforesis en papel, acetato de celulosa Electroforesis
