Cómo identificamos bacterias?
|
|
|
- José Carlos Caballero Navarro
- hace 5 años
- Vistas:
Transcripción
1 Cómo identificamos bacterias? Las bacterias son microorganismos unicelulares que miden tan solo unos micrómetros de largo. Son los organismos más abundantes que hay en el planeta encontrándose en todo hábitat de la tierra y además son muy diversas. La salinidad, temperatura, ph, concentración de oxígeno, etc. del ambiente pueden determinar la distribución y abundancia de las diferentes especies de bacterias. El valle de Cuatrociénegas, Coahuila es un buen modelo para determinar la relación entre diversidad con respecto a las condiciones y recursos, por lo que se ha realizado un muestreo de bacterias que nos interesa identificar. Para identificar bacterias de algún ambiente primero tenemos que colectarlas; una vez en el laboratorio rompemos su pared celular y la membrana plasmática para extraer únicamente el DNA, que es el material genético de las células y es el que determina las características de los seres vivos. La molécula de DNA está formada por compuestos químicos llamados nucleótidos. Existen cuatro tipos de nucleótidos: adenina, timina, citosina y guanina. El DNA de una bacteria puede contener hasta 300 millones de nucleótidos. Para identificar bacterias solo usamos una pequeña porción del DNA, un gen llamado 16S que tan solo tiene 1500 nucleótidos. Para obtener el gen 16S utilizamos una técnica de biología molecular llamada reacción en cadena de la polimerasa (PCR) que nos permite hacer muchas copias de cualquier gen. La reacción de PCR consiste en agregar a un tubo: 1. Una pequeña fracción de DNA 2. DNA polimerasa la molécula encargada de sacar las copias. 3. Dos iniciadores que le indican a la DNA polimerasa cual es el fragmento que se va a copiar. Para la identificación de bacterias se usan iniciadores específicos para el gen 16S. 4. Nucleótidos que son los ladrillos para construir nuevos fragmentos de
2 DNA. Así pues, la reacción de PCR amplificará un millón de veces el gen 16S. Cómo se detecta el gen amplificado? Se utiliza una técnica que consiste en separar el fragmento de DNA en una matriz de gel y posteriormente teñir el DNA para poder verlo directamente. Este el el método de electroforesis cuyo procedimiento se describe más adelante. Para que me sirve tener amplificado el gen 16S? Este gen es una molécula muy antigua, presente en todas las bacterias actuales de modo que si leemos la secuencia de los 1500 nucleótidos, es decir el orden de las adeninas, AISLAMIENTO DE DNA GENOMICO DE BACTERIAS POR EL METODO QUICK GENE Materiales: -cultivo de 24 hrs -TRIS ph 8 -Lizosima -Triton 10% -Etanol 100% -Agua desionizada -Rnasa -Kit QuickGene DNA tissue DT-S -Palillos -Tuboes eppendorff -Guantes -Puntas para micropipetas Equipo: -Micropipetas -Microcentrifuga -Vortex -Termoblock -Quick Gene mini 80 2
3 Crecer la bacteria en 5 ml de medio a 37 C toda la noche. Centrifugar 1 ml del cultivo por 10 min. Desechar el sobrenadante y resuspender la pastilla en 100 μl de agua, agregar 2 μl de Tris ph 8 y lizosima en un palillo. Vórtex máxima velocidad por 15 s. Incubar a 37 C por 30 minutos. Dar un pulso de microcentrifuga. Agregar 180 μl de LDT, 20 μl de EDT y 20 μl de triton 100X al 10%. Vórtex máxima velocidad por 15 s. Incubar a 65 C por 10 min. Dar un pulso de microcentrifuga. Agregar 240 μl de etanol 100%. Vortex máxima velocidad por 15 s. Dar un pulso de microcentrifuga. Cargar el lisado en las columnas. Lavar la columna 3 veces con el buffer WDT. Para resuspender el DNA agregar a la columna 30 μl de agua con RNAsa. PCR con oligonucleótidos 16S a partir de DNA obtenido de cultivos En 1983, el bioquímico Kary Mullis desarrolló la técnica de Biología Molecular que desde entonces ha revolucionado la investigación biológica y médica, lo que le llevó a recibir el premio Nobel de Química de Esta técnica, denominada reacción en cadena de la polimerasa (PCR por sus siglas en ingles) transformó a la Biología Molecular en una herramienta multidisciplinaria. Muchas de las técnicas de Biología Molecular usadas antes de la invención de la PCR para amplificar fragmentos de DNA consumían mucho tiempo y requerían un alto nivel de especialización técnica. La PCR es una técnica que replica enzimáticamente al DNA in vitro, permitiendo que una pequeña cantidad de moléculas de DNA (molde o
4 templado) sean amplificadas selectivamente de manera exponencial. Una de las principales razones por las cuales la PCR es una herramienta tan poderosa es su simplicidad y especificidad. El primer paso crítico es la selección del ácido nucleico a partir del cual se amplificará la secuencia de interés; a este acido nucleico se le llama molde o templado. Por lo general, la PCR está diseñada para permitir la amplificación selectiva de una secuencia específica de DNA blanco. El siguiente punto a considerar es la selección de primers, pues para amplificar selectivamente una secuencia de DNA, es necesaria cierta información previa de esa secuencia blanco para diseñar dos primers de unos 18 a 25 nucleótidos de largo, que son específicos complementarios a las secuencias que flanquean a la secuencia blanco. Para reducir la posibilidad de que los primers se enlacen en otros sitios del DNA que no sean los deseados, es necesario tomar en cuenta varias consideraciones en su diseño: - Composición de bases. El contenido de GC debe ser de 40 a 60% con una distribución uniforme de los 4 nucleótidos A, T, C y G. -Temperatura de fusión (Tm). Los valores de Tm calculados para los dos primers usados juntos no debe variar en más de 5 C. -Secuencias terminales 3. No deben ser secuencias complementarias a alguna región del otro primer utilizado en la misma reacción. -Secuencias autocomplementarias. Deben evitarse repeticiones invertidas o cualquier secuencia autocomplementaria de más de 3 pb de largo. La PCR estándar consiste en una serie de ciclos de 3 reacciones sucesivas: A) Desnaturalización. Se ajusta a una temperatura de 93 a 95 C para el DNA genómico. B) Alineamiento (annealing). A temperatura variable (entre 45 a 65 C) de acuerdo con la Tm de los primers (por lo regular la temperatura de alineamiento se ajusta a 5 C menos respecto a la Tm calculada). En esta fase los dos primers se hibridan con sus respectivas secuencias complementarias en el molde. C) Síntesis o polimerización. De manera característica alrededor de 70 a 75 C (temperatura óptima a la cual trabaja la enzima). La DNA polimerasa empleada es termoestable, por lo que no se afecta por los pasos de desnaturalización.
5 Las cadenas recién sintetizadas pueden servir a su vez como moldes para la síntesis del nuevo DNA, lo que da lugar a una reacción en cadena con un incremento exponencial del producto. La PCR tuvo gran impacto en 4 áreas principales de la Biología Molecular: el mapeo de genes, la clonación, la secuenciación de DNA y la detección de genes. La PCR es ahora utilizada como una herramienta de diagnóstico médico de enfermedades infecciosas o para detectar mutaciones específicas que pueden causar enfermedades genéticas, en las investigaciones criminales para identificar a los sospechosos a nivel molecular, en pruebas de paternidad y en la secuenciación del genoma humano, por mencionar algunos usos. Materiales -Primer directo: 16S forward: AGAGTTTGATCMTGGCTCAG -Primer reverso: 16S reverse: TACGGYTACCTTGTTACGACTT -Taq DNA polimerasa Equipo -Termociclador 1) Colocar en el tubo de PCR : Muestra DNA de Buffer de PCR 10x dntp s Primer directo Primer reverso Agua Reacción total 1 μl 2.5 μl 2 μl 1 μl 1 μl μl 25 μl
6 2) Programar el termociclador con las condiciones de amplificación necesarias, siguiendo como guía la Tabla mostrada a continuación 3) Analizar el resultado del PCR en electroforesis horizontal en geles de agarosa
7 -Tubos de PCR de 0.2 ml -Tubos de 1.5 ml estériles -Muestra de DNA molde -Agua Milli-QTM estéril - Buffer de PCR 10x con MgCl2 15mM -Mezcla de dntp s (a una concentración de 10 mm de cada uno: datp, dctp, dgtp, dttp) Separación de DNA por electroforesis horizontal en geles de agarosa La electroforesis es el proceso de movimiento de moléculas cargadas en una solución al aplicar un campo eléctrico. Debido a que las moléculas en un campo eléctrico se mueven a una velocidad dependiente de su carga, forma y tamaño, la electroforesis se ha desarrollado ampliamente para la separación de diversas biomoléculas. Debido a que es una herramienta analítica simple y relativamente rápida, se utiliza para el análisis y la purificación de moléculas grandes como proteínas y ácidos nucleicos o de moléculas pequeñas como azúcares, aminoácidos, péptidos y nucleótidos. La electroforesis de macromoléculas se realiza normalmente aplicando un volumen pequeño de la muestra en una matriz porosa. Bajo la influencia del voltaje aplicado, las diferentes moléculas presentes en la muestra se moverán a través de la matriz a diferentes velocidades. Al final se podrá observar la separación de las moléculas detectadas como bandas en distintas posiciones dentro de la matriz. La matriz puede estar compuesta por diferentes materiales como papel, acetato de celulosa, agarosa o poliacrilamida. En la unidad de electroforesis, el gel se encuentra colocado entre dos cámaras que contienen buffer. La conexión eléctrica ente las dos cámaras es a través del gel. Debido a que los ácidos nucleicos tienen carga negativa, los pozos para muestras deben colocarse del lado del electrodo negativo para que estos migren hacia el lado positivo.
8 Los ácidos nucleicos son comúnmente separados en geles de agarosa. La agarosa es un polisacárido altamente purificado, derivado del agar. La velocidad de migración del DNA en matrices de agarosa está determinada por los siguientes factores: -Tamaño molecular del DNA. Las moléculas más grandes migran más lentamente por que su fricción de arrastre es mayor y porque se mueven a través de los poros del gel con mayor dificultad que las moléculas pequeñas. - Forma o conformación del DNA. El DNA súper-enrollado migra más rápido que el DNA lineal. -Concentración de agarosa. Al disminuir la concentración de agarosa, los poros del gel son más grandes y las moléculas migrarán con mayor velocidad. -Voltaje aplicado. Con voltajes bajos, la velocidad de migración de los fragmentos de DNA es proporcional al voltaje aplicado. -Buffer de electroforesis. La movilidad electroforética del DNA es influenciada por la composición y la fuerza iónica del buffer de electroforesis. En ausencia de iones (agua desionizada) la conductividad eléctrica es mínima y el DNA migra lentamente. En un buffer con una fuerza iónica demasiado alta, la conductividad eléctrica es muy buena, aún con voltajes moderados y se generan grandes cantidades de calor, lo que podría fundir el gel y desnaturalizar el DNA. La fuerza fundamental del movimiento por electroforesis es el voltaje aplicado al sistema. La velocidad de las moléculas es directamente proporcional al gradiente de voltaje. Durante la electroforesis, el voltaje y la corriente son proporcionados por una fuente de poder y electrodos. El buffer y el gel actúan como resistencia. Algunos de los problemas más comunes cuando se separan ácidos nucleicos por electroforesis en geles de agarosa son: -Bandas poco definidas. Puede ocurrir cuando la agarosa no polimeriza adecuadamente, causando que los pozos estén mal formados (presencia de burbujas o tiempo de polimerización insuficiente); también puede deberse a
9 que el gel se haya preparado con agua y no con buffer, o bien, a que se hayan cargado grandes cantidades de DNA en el pozo. La degradación del DNA también se observa como un barrido a lo largo de todo el carril, debido a la presencia de fragmentos más cortos de diferentes longitudes. - Ausencia de bandas. Puede deberse a que la muestra se haya salido del gel por corrimiento excesivo o porque los cables fueron colocados incorrectamente en sus electrodos respectivos. También puede ocurrir cuando se cargan cantidades inferiores al límite de detección. -Bandas tenues. Este problema se puede presentar si la muestra no ingresa completamente al pozo, o bien si el pozo fue perforado accidentalmente con la punta de la micropipeta al cargar la muestra. También puede deberse a una tinción incorrecta. -Separación insuficiente de las bandas. Ocurre por corrimiento insuficiente o porcentaje de agarosa incorrecto. Materiales -Agarosa grado Biología Molecular -Buffer TAE 1X -Buffer de carga 5X -Muestras de DNA -Marcadores de peso molecular - Gel Green Equipo - Cámara de electroforesis horizontal - Fuente de poder 1) Limpiar y secar las charolas de preparación de geles y los peines con agua destilada y ensamblarlos. Colocar las charolas en una superficie horizontal y nivelada. 2) Acomodar los peines en cada charola a mm del fondo de ellas. 3) Preparar, en una botella
10 una solución de agarosa al 1% (p/v) y, en otra al buffer TAE 1X, disolver la agarosa calentando las mezclas en horno de microondas. No apretar las tapas de las botellas. Verificar que la agarosa esté completamente disuelta por medio de agitación. 4) Dejar enfriar las soluciones de agarosa por debajo de 60 C. 5) Verter la agarosa tibia en cada charola nivelada y esperar a que solidifique. 6) Remover cuidadosamente los peines y montar los geles con cada charola en las cámaras de electroforesis. 7) Verter el buffer TAE 1X en las cámaras hasta cubrir el gel (1 mm por encima del gel). 8) En un trozo de Parafilm mezclar las muestras de DNA y los marcadores de peso molecular con el buffer de carga 5X 10) Utilizando la micropipeta, cargar lentamente las muestras. No tocar el fondo del pozo con la punta para evitar perforar el gel. Evitar burbujear con la micropipeta mientras se coloca la muestra para que ésta no se salga del pozo. 11) Cerrar las cámaras de electroforesis y aplicar una corriente de 85 V. Si la cámara se coloca adecuadamente, se observará la formación de burbujas en los electrodos. 12) Cuando el color naranja haya migrado lo suficiente (¾ partes del gel), apagar la fuente de poder y sacar el gel de la cámara. 13) Observar el resultado en el transiluminador de luz ultravioleta. La luz UV es mutagénica, por lo que su exposición debe ser mínima y empleando siempre protección para cara, ojos y manos.
11 Análisis de resultados Especifica el amaño de los Productos amplificados: Qué esperas observar en el control sin DNA? Qué esperas observar en el control con DNA e iniciadores 16S?
12 Cómo se secuencia el DNA? La reacción de secuenciación es comparable a una reacción de PCR donde se replica DNA. La mezcla de reacción incluye el DNA molde (templado), nucleótidos, DNA polimerasa modificada (variante de la Taq polimerasa) y un oligonucleótido o premer (20-30 nt de longitud) que puede hibridar en una de las cadenas del templado de DNA. La reacción inicia con la separación de las cadenas de DNA. Posteriormente el oligonucleótido se alinea al templado y la DNA polimerasa inicia la síntesis de la cadena complementaria. Este ciclo se repite hasta la obtención de varias copias. Dideoxinucleótidos: En la reacción de secuenciación se introducen además dideoxiribonucleótidos (nucléotidos similares a los que presenta el DNA excepto que carece de grupos hidroxilo en el Carbono 3 ), que al introducirse en la cadena en vía de síntesis provocan que se detenga la polimerización. Esto produce cadenas de distintos tamaños, dependiendo de dónde se introducen, e indican el punto preciso donde se ubica cada uno de los 4 diferentes nucleótidos. Los dideoxinucleótidos están marcados con un fluoróforo que es diferente para cada base, emitiendo una señal específica cuando se excita con un láser (A= verde, T= rojo, C= azul y G= amarillo). Duplicación de una cadena de DNA en presencia de dideoxi-t: La mayor parte del tiempo cuando se requiere una timina (T) para hacer la nueva hebra, la enzima podrá adicionar una T normal y no hay problema, la síntesis continuará. Sin embargo, 5% de las veces la enzima adicionará un dideoxi-t y la hebra no puede ser elongada o extendida. Ésta eventualmente se separara de la enzima y la síntesis de la hebra terminara.de esta manera, todas las copias terminaran con una T, pero cada vez que la enzima sintetice una nueva
13 hebra el lugar donde la síntesis se detenga será al azar. Produciéndose así millones de cadenas de tamaño variable. Esto mismo ocurre para cada uno de los dideoxinucleótidos.
14 Reconstrucción filogenética e identificación bacterias 1ª Parte Relación entre las especies Charles Darwin. Libro de notas. biológica. Posiblemente la imagen de la relación entre especies de Charles Darwin de su libro de notas B sea una de las imágenes clásicas de una reconstrucción filogenética. En esta se representa el sistema de ramificación de descendencia donde se comparte un antepasado, los organismos más antiguos se encuentran en la parte inferior y sus descendientes se ramifican en forma irregular. Las líneas con un final transversal son especies o linajes existentes y los que no representan especies extintas. Dando pie en el libro del origen de las especies a le que conocemos como evolución La evolución es un proceso continuo de cambio heredable a través del tiempo que genera diversidad a partir de un ancestro común y actúa por selección natural. De esta se clasifica en dos: Evolución a pequeña escala, que representa cambios en la frecuencia génica de una población entre una generación y la siguiente, es decir abuelos hijos y nietos fig. R2; Evolución a gran escala, descendencia de especies diferentes a partir de un antepasado común después de muchas generaciones, como mariposas, abejas y escarabajos Fig. R3.
15 Fig. R2. Evolución a pequeña escala, que representa cambios en la frecuencia génica de una población entre una generación y la siguiente, es decir abuelos hijos y nietos fig. R2 Fig. R3. Evolución a gran escala, descendencia de especies diferentes a partir de un antepasado común después de muchas generaciones, como mariposas, abejas y escarabajos Fig. R3. La evolución nos ayuda a entender la historia de la vida, considerando que toda la vida de la Tierra comparte un antepasado común.
16 Cómo hacemos una reconstrucción filogenética y para que me sirve? Lo primero es observar las características de los organismos y ordenarlas en forma de las características que más se comparte a las que suelen ser más raras Fig R4. Fig. R4 Características del grupo de los vertebrados. Las características más comunes siempre constituyen la base de los arboles filogenéticos, conforme se van perdiendo estas características se sigue la estructura hacia la parte superior del árbol, con concluyendo con las características para cada organismo Fig R5.
17 Fig. 5. Reconstrucción filogenética de los vertebrados Cómo sabemos cuando paso? 1. Datación radiométrica se basa en la descomposición de vida media de los elementos radiactivos para permitir a los científicos a las rocas y materiales actualizados directamente. 2. Estratigrafía proporciona una secuencia de acontecimientos de los que las fechas relativas pueden ser extrapolados.
18 3. Los relojes moleculares permiten a los científicos a utilizar la cantidad diferencias genéticas entre organismos para extrapolar hacia atrás para calcular las fechas. Un relojes molecular puede ser el DNA mitocondrial (mtdna) Esta molécula está presente en eucariotas, incluyendo organismos extintos. Permite dilucidar las relaciones evolutivas entre las especies. El DNA mitocondrial es Importante estudios de antropología que permite saber en que periodos fueron domesticadas ciertas plantas y animales por distintas culturas, además de poder diferenciar entre distintas poblaciones étnicas. En biología el DNA mitocondrial es empleado para poder diferenciar entre poblaciones de animales, plantas o incluso de humanos estableciendo los periodos de especiación o la simbiosis entre cada uno de los organismos. Uno de los ejemplos clásicos es el de los homínidos Fig R6. La reconstrucción filogenética nos permite establecer relaciones entre ellos, esto se puede ver en el transcurso de esta práctica, mediante el uso de bases de datos de algunas pruebas de de datación radiométrica y estratigrafía, además de algunos programas computacionales especializados podemos determinar el tiempo de divergencia de cada uno de los organismos y su relación entre ellos.
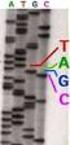
19 Cómo identificar un microorganismo? Empleamos una molécula similar a un Código de barras, Estas son por lo general genes ribosomales como 16S para el caso de bacterias y las regiones ITS1 y ITS2 para del caso de eucariotas. Estos son amplificados por Reaccion en Cadena de la Polimerasa (PCR), como se describió en secciones anteriores. Y se manda secuenciar por la técnica de secuenciación automática Sanger descrita de igual forma en secciones anteriores. El producto de secuenciaciones es un cromatograma como es que se ejemplifica en la figura R7, de este se verifica que la secuencia cumpla con un parámetro de calidad llamado phred en el programa computacional FinchTV, y posteriormente se analiza en la página obteniendo ciertos parámetros con los cuales podremos decidir a qué grupo corresponde nuestro microorganismo y así tener su identificación.
20 Fig R7 Cromatograma de secuenciación Sanger empleando el programa computacional FinchTV
21 Preguntas de la práctica En la práctica se te proporcionaran dos electroferogramas tipo, obtenidos de secuencias de 16S ribosomal de aislados bacterianos de Cuatrociénegas, Coahuila. El objetivo de esta sección, calificar las secuencias que se te proporcionaron. Al final de esta sección responde las preguntas: 1. Dentro del programa FinchTV, deberás visualizar los electroferogramas que se te proporcionaron. Es posible determinar las regiones de baja calidad en la secuencia? 2. Sabes que indican los colores de cada uno de los picos? 3. Aparecen nucleótidos diferentes a T, A, G y C? Si es así Qué quiere decir esto? 4. Por qué el inicio y final de la secuencia son de baja calidad? 5. De qué tamaños son las secuencias proporcionadas? Secuencia 1: Secuencia 2:
22 2ª Parte El objetivo de esta sección es identificar la filiación taxonómica del aislado. Los archivos en formato FASTA de tus secuencias se compararan con la base de datos de nucleótidos depositados en la página 1. De los resultados de tus secuencias, determina cuál es la secuencia a la cual se parece más?
23 *Busca tus fotos, videos y próximos eventos en:
Taller Ciencia para Jóvenes CIMAT 2012 Bachillerato julio 8 14 Cinvestav Campus Guanajuato
 Introducción Taller Ciencia para Jóvenes CIMAT 2012 Bachillerato julio 8 14 Cinvestav Campus Guanajuato Visita al CINVESTAV - Irapuato. 19 julio, 2012. Las bacterias son los organismos más abundantes que
Introducción Taller Ciencia para Jóvenes CIMAT 2012 Bachillerato julio 8 14 Cinvestav Campus Guanajuato Visita al CINVESTAV - Irapuato. 19 julio, 2012. Las bacterias son los organismos más abundantes que
Material complementario UD 5
 Material complementario UD 5 Componentes de la PCR ADN molde que es el que se quiere replicar. Oligonucleótidos iniciadores, primers o cebadores: - Son oligonucleótidos monocatenarios cuya secuencia es
Material complementario UD 5 Componentes de la PCR ADN molde que es el que se quiere replicar. Oligonucleótidos iniciadores, primers o cebadores: - Son oligonucleótidos monocatenarios cuya secuencia es
EXTRACCIÓN DE ADN (Doyle & Doyle, 1987)
 EXTRACCIÓN DE ADN (Doyle & Doyle, 1987) MATERIALES Y REACTIVOS (Grado biología molecular a analítico) Cloroformo Alcohol Isoamilico Isopropanol. Etanol al 70%. Bloques de Hielo Microcentrifuga Bloque de
EXTRACCIÓN DE ADN (Doyle & Doyle, 1987) MATERIALES Y REACTIVOS (Grado biología molecular a analítico) Cloroformo Alcohol Isoamilico Isopropanol. Etanol al 70%. Bloques de Hielo Microcentrifuga Bloque de
PCR SIMULADA. Ref.PCR Simulada (4 prácticas) 1. OBJETIVO DEL EXPERIMENTO
 Ref.PCR Simulada (4 prácticas) 1. OBJETIVO DEL EXPERIMENTO PCR SIMULADA El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa
Ref.PCR Simulada (4 prácticas) 1. OBJETIVO DEL EXPERIMENTO PCR SIMULADA El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa
TEMA 14 NUEVAS TECNOLOGÍAS PARA EL ESTUDIO DE LAS ENFERMEDADES INFECCIOSAS: MÉTODOS GENÉTICOS
 TEMA 14 NUEVAS TECNOLOGÍAS PARA EL ESTUDIO DE LAS ENFERMEDADES INFECCIOSAS: MÉTODOS GENÉTICOS Tema 14. Nuevas tecnologías para el estudio de enfermedades infecciosas: métodos genéticos Métodos genéticos
TEMA 14 NUEVAS TECNOLOGÍAS PARA EL ESTUDIO DE LAS ENFERMEDADES INFECCIOSAS: MÉTODOS GENÉTICOS Tema 14. Nuevas tecnologías para el estudio de enfermedades infecciosas: métodos genéticos Métodos genéticos
PCR gen 16S ARNr bacteriano
 PCR gen 16S ARNr bacteriano Ref. PCR16S 1. OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y la práctica de la Reacción en Cadena de la Polimerasa
PCR gen 16S ARNr bacteriano Ref. PCR16S 1. OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y la práctica de la Reacción en Cadena de la Polimerasa
Práctica: Electroforesis de DNA y transferencia a membranas de celulosa o nylon.
 Biología Celular y Molecular para Medicina Jorge Contreras Pineda Práctica: Electroforesis de DNA y transferencia a membranas de celulosa o nylon. GENERALIDADES La electroforesis es una técnica de laboratorio
Biología Celular y Molecular para Medicina Jorge Contreras Pineda Práctica: Electroforesis de DNA y transferencia a membranas de celulosa o nylon. GENERALIDADES La electroforesis es una técnica de laboratorio
REACCIÓN EN CADENA DE LA POLIMERASA (PCR) Microbiología de los Alimentos Ingeniería en alimentos
 REACCIÓN EN CADENA DE LA POLIMERASA (PCR) Microbiología de los Alimentos Ingeniería en alimentos 2015 Desarrollada por Kary Mullis en 1986 Técnica in vitro que permite amplificar enzimáticamente una región
REACCIÓN EN CADENA DE LA POLIMERASA (PCR) Microbiología de los Alimentos Ingeniería en alimentos 2015 Desarrollada por Kary Mullis en 1986 Técnica in vitro que permite amplificar enzimáticamente una región
REACCIÓN EN CADENA DE LA POLIMERASA (PCR)
 REACCIÓN EN CADENA DE LA POLIMERASA (PCR) Lic. en Bioquímica Lic. en Biotecnología Microbiología de los Alimentos 2016 Desarrollada por Kary Mullis en 1986 Técnica in vitro que permite amplificar enzimáticamente
REACCIÓN EN CADENA DE LA POLIMERASA (PCR) Lic. en Bioquímica Lic. en Biotecnología Microbiología de los Alimentos 2016 Desarrollada por Kary Mullis en 1986 Técnica in vitro que permite amplificar enzimáticamente
REACCIÓN EN CADENA DE LA POLIMERASA (PCR)
 REACCIÓN EN CADENA DE LA POLIMERASA (PCR) Microbiología General Microbiología M de los Alimentos Licenciatura en Bioquímica i Ingeniería en alimentos c Microbiología r 2015 Licenciatura en Biotecnología
REACCIÓN EN CADENA DE LA POLIMERASA (PCR) Microbiología General Microbiología M de los Alimentos Licenciatura en Bioquímica i Ingeniería en alimentos c Microbiología r 2015 Licenciatura en Biotecnología
Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular
 Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular Aislamiento, análisis y manipulación de ácidos nucleicos Generación de moléculas de DNA recombinante Ingeniería Genética AISLAMIENTO
Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular Aislamiento, análisis y manipulación de ácidos nucleicos Generación de moléculas de DNA recombinante Ingeniería Genética AISLAMIENTO
Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular
 Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular Aislamiento, análisis y manipulación de ácidos nucleicos Generación de moléculas de DNA recombinante Ingeniería Genética AISLAMIENTO
Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular Aislamiento, análisis y manipulación de ácidos nucleicos Generación de moléculas de DNA recombinante Ingeniería Genética AISLAMIENTO
PRÁCTICA 9 ELECTROFORESIS EN GEL DE AGAROSA
 INTRODUCCIÓN PRÁCTICA 9 ELECTROFORESIS EN GEL DE AGAROSA La electroforesis es una técnica que permite separar moléculas cargadas eléctricamente, entre las cuales se encuentran los ácidos nucleicos (DNA
INTRODUCCIÓN PRÁCTICA 9 ELECTROFORESIS EN GEL DE AGAROSA La electroforesis es una técnica que permite separar moléculas cargadas eléctricamente, entre las cuales se encuentran los ácidos nucleicos (DNA
Reacción en cadena de la polimerasa (PCR)
 Curso: Biología Molecular y Genómica Enero 2014. Conceptos elementales sobre la técnica de reacción en cadena de la polimerasa (PCR) Dr. Juan Venegas Hermosilla Programa de Biología Celular y Molecular
Curso: Biología Molecular y Genómica Enero 2014. Conceptos elementales sobre la técnica de reacción en cadena de la polimerasa (PCR) Dr. Juan Venegas Hermosilla Programa de Biología Celular y Molecular
AMPLIFICACIÓN Y DETECCIÓN POR PCR DEL LOCUS HUMANO D1S80
 AMPLIFICACIÓN Y DETECCIÓN POR PCR DEL LOCUS HUMANO D1S80 Ref. PCR1 1. OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción
AMPLIFICACIÓN Y DETECCIÓN POR PCR DEL LOCUS HUMANO D1S80 Ref. PCR1 1. OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción
Seminario Genética. Técnicas de Biología Molecular
 Seminario Genética Técnicas de Biología Molecular Contenidos Extracción de ADN Enzimas de restricción PCR Southern Blot Secuenciación método de Sanger y automática 1º Extracción de ADN Se pueden tomar
Seminario Genética Técnicas de Biología Molecular Contenidos Extracción de ADN Enzimas de restricción PCR Southern Blot Secuenciación método de Sanger y automática 1º Extracción de ADN Se pueden tomar
41. Comprobación de colonias transformantes mediante PCR y electroforesis
 41. Comprobación de colonias transformantes mediante PCR y electroforesis Aurora Galván Cejudo, Manuel Tejada, Antonio Camargo, José Javier Higuera, Vicente Mariscal, Emilio Fernández Reyes Departamento
41. Comprobación de colonias transformantes mediante PCR y electroforesis Aurora Galván Cejudo, Manuel Tejada, Antonio Camargo, José Javier Higuera, Vicente Mariscal, Emilio Fernández Reyes Departamento
Relator: José Ramón Vidal Juviño 1
 Práctica 4. Amplificación de ADN por PCR y electroforesis P4A: Ampliación de ADN por Reacción en Cadena de la Polimerasa Estudio de polimorfismos humanos ALU por PCR (BioTed, cod. PCR3) P4B: Separación
Práctica 4. Amplificación de ADN por PCR y electroforesis P4A: Ampliación de ADN por Reacción en Cadena de la Polimerasa Estudio de polimorfismos humanos ALU por PCR (BioTed, cod. PCR3) P4B: Separación
Protocolos de preparación de muestras
 Protocolos de preparación de muestras Contenido 1. TIPOS DE MUESTRA 2. PROTOCOLO DE PREPARACIÓN DE MUESTRA 2.1 Producto de PCR crudo (sin purificar). 2.2 Producto de PCR crudo en gel (sin purificar). 2.3
Protocolos de preparación de muestras Contenido 1. TIPOS DE MUESTRA 2. PROTOCOLO DE PREPARACIÓN DE MUESTRA 2.1 Producto de PCR crudo (sin purificar). 2.2 Producto de PCR crudo en gel (sin purificar). 2.3
UNIVERSIDAD NACIONAL DE MISIONES Facultad de Ciencias Exactas Químicas y Naturales COLOQUIO N 6/15 FUNDAMENTOS DE SECUENCIACIÓN
 COLOQUIO N 6/15 FUNDAMENTOS DE SECUENCIACIÓN OBJETIVO: el presente trabajo práctico tiene como objetivo principal que el alumno adquiera destreza en el análisis de electroferogramas generados por equipos
COLOQUIO N 6/15 FUNDAMENTOS DE SECUENCIACIÓN OBJETIVO: el presente trabajo práctico tiene como objetivo principal que el alumno adquiera destreza en el análisis de electroferogramas generados por equipos
RT- PCR diagnóstica del Cotton leafroll dwarf virus (CLRDV) en plantas de algodón
 RT- PCR diagnóstica del Cotton leafroll dwarf virus (CLRDV) en plantas de algodón La identificación rápida y precisa de los patógenos que afectan a los cultivos de interés agronómico es crítica para predecir
RT- PCR diagnóstica del Cotton leafroll dwarf virus (CLRDV) en plantas de algodón La identificación rápida y precisa de los patógenos que afectan a los cultivos de interés agronómico es crítica para predecir
KITS EDUCATIVOS DE BIOLOGÍA MOLECULAR
 KITS EDUCATIVOS DE BIOLOGÍA MOLECULAR Índice General Aula GENYCA. Flujo de trabajo. 3 Kits Educativos de Técnicas Básicas 5 P1-A. Extracción de ADN de Sangre 6 P1-B. Extracción de ADN en Columna 7 P2.
KITS EDUCATIVOS DE BIOLOGÍA MOLECULAR Índice General Aula GENYCA. Flujo de trabajo. 3 Kits Educativos de Técnicas Básicas 5 P1-A. Extracción de ADN de Sangre 6 P1-B. Extracción de ADN en Columna 7 P2.
4. TIPADO GENÉTICO DE BACTERIAS PATÓGENAS MEDIANTE ELECTROFORESIS EN CAMPOS PULSADOS (PFGE) Materiales - Bacterias crecidas en placas de agar
 4. TIPADO GENÉTICO DE BACTERIAS PATÓGENAS MEDIANTE ELECTROFORESIS EN CAMPOS PULSADOS (PFGE) Materiales - Bacterias crecidas en placas de agar - Agarosa de grado molecular - Agarosa de bajo punto de fusión
4. TIPADO GENÉTICO DE BACTERIAS PATÓGENAS MEDIANTE ELECTROFORESIS EN CAMPOS PULSADOS (PFGE) Materiales - Bacterias crecidas en placas de agar - Agarosa de grado molecular - Agarosa de bajo punto de fusión
BIOLOGÍA MOLECULAR TOTAL DE PUNTOS: 90. País: ESPAÑA
 XII OLIMPIADA IBEROAMERICANA DE BIOLOGÍA SETIEMBRE 2018 LOJA-ECUADOR EXAMEN PRÁCTICO BIOLOGÍA MOLECULAR TOTAL DE PUNTOS: 90 TIEMPO PERMITIDO: 120 minutos País: ESPAÑA ESCRIBA EL CÓDIGO EN EL SIGUIENTE
XII OLIMPIADA IBEROAMERICANA DE BIOLOGÍA SETIEMBRE 2018 LOJA-ECUADOR EXAMEN PRÁCTICO BIOLOGÍA MOLECULAR TOTAL DE PUNTOS: 90 TIEMPO PERMITIDO: 120 minutos País: ESPAÑA ESCRIBA EL CÓDIGO EN EL SIGUIENTE
Ensayos de restricción
 Ensayos de restricción Vector con inserto= Vector recombinante 6500pb Objetivos de ensayos de restricción de plásmidos Conocer el principio de separación y detección de ácidos nucleicos en geles de agarosa.
Ensayos de restricción Vector con inserto= Vector recombinante 6500pb Objetivos de ensayos de restricción de plásmidos Conocer el principio de separación y detección de ácidos nucleicos en geles de agarosa.
Métodos de Biología Molecular y de Ingeniería Genética
 Métodos de Biología Molecular y de Ingeniería Genética I. Enzimas de restricción Análisis Las enzimas de restricción fueron aisladas de bacterias; su función natural es proteger contra DNA extraño II.
Métodos de Biología Molecular y de Ingeniería Genética I. Enzimas de restricción Análisis Las enzimas de restricción fueron aisladas de bacterias; su función natural es proteger contra DNA extraño II.
TECNICAS DE BIOLOGIA MOLECULAR
 Química Biológica Patológica TECNICAS DE BIOLOGIA MOLECULAR IV- Parte Aplicadas al diagnóstico de Enfermedades Genéticas Tema:1 (1) Dra. Silvia Varas qbpatologica.unsl@gmail.com TIPO DE MUTACION DEFINE
Química Biológica Patológica TECNICAS DE BIOLOGIA MOLECULAR IV- Parte Aplicadas al diagnóstico de Enfermedades Genéticas Tema:1 (1) Dra. Silvia Varas qbpatologica.unsl@gmail.com TIPO DE MUTACION DEFINE
Test Genéticos Moleculares
 CERPO Centro de Referencia Perinatal Oriente Facultad de Medicina, Universidad de Chile Test Genéticos Moleculares Dr. Guillermo Parrao Barrera Residente Medicina Materno Fetal Pontificia Universidad Católica
CERPO Centro de Referencia Perinatal Oriente Facultad de Medicina, Universidad de Chile Test Genéticos Moleculares Dr. Guillermo Parrao Barrera Residente Medicina Materno Fetal Pontificia Universidad Católica
B) Añadir al medio LB, además de la ampicilina, el IPTG (conc final, 0.5 mm) y X-Gal (conc. final 80 µg/ml). Es decir, para 100 ml de LB adicionar:
 Medios utilizados en este apartado: 1.-IPTG stock solution (0.1 M) - 0.6 g IPTG. - Añadir agua estéril a un volumen final de 25 ml. Filtrar con papel secante pasando la solución a tubos eurotubos. Guardar
Medios utilizados en este apartado: 1.-IPTG stock solution (0.1 M) - 0.6 g IPTG. - Añadir agua estéril a un volumen final de 25 ml. Filtrar con papel secante pasando la solución a tubos eurotubos. Guardar
GENÉTICA MOLECULAR E INGENIERÍA GENÉTICA: Conceptos, Técnicas y Aplicaciones. Blga: Wendy Morales Oviedo 2017
 GENÉTICA MOLECULAR E INGENIERÍA GENÉTICA: Conceptos, Técnicas y Aplicaciones Blga: Wendy Morales Oviedo 2017 TEMA 1. ÁCIDOS NUCLEICOS: Preparación, Purificación y análisis de ácidos nucleicos 1.1. INTRODUCCIÓN
GENÉTICA MOLECULAR E INGENIERÍA GENÉTICA: Conceptos, Técnicas y Aplicaciones Blga: Wendy Morales Oviedo 2017 TEMA 1. ÁCIDOS NUCLEICOS: Preparación, Purificación y análisis de ácidos nucleicos 1.1. INTRODUCCIÓN
ELECTROFORESIS AVANZADA
 Ref. ELECAVANZADA (4 prácticas) 1. OBJETIVO DEL EXPERIMENTO ELECTROFORESIS AVANZADA El objetivo de este experimento es introducir a los alumnos en el conocimiento de la teoría electroforética y familiarizarse
Ref. ELECAVANZADA (4 prácticas) 1. OBJETIVO DEL EXPERIMENTO ELECTROFORESIS AVANZADA El objetivo de este experimento es introducir a los alumnos en el conocimiento de la teoría electroforética y familiarizarse
DEPARTAMENTO DE GENÉTICA UNIVERSIDAD DE GRANADA FUNDAMENTOS DE BIOLOGÍA APLICADA I 4º CURSO DE BIOLOGÍA
 DEPARTAMENTO DE GENÉTICA UNIVERSIDAD DE GRANADA FUNDAMENTOS DE BIOLOGÍA APLICADA I 4º CURSO DE BIOLOGÍA MÓDULO DE GENÉTICA TÉCNICAS MOLECULARES DE ANÁLISIS GENÉTICO AISLAMIENTO Y CLONACIÓN DE ADN SATÉLITE
DEPARTAMENTO DE GENÉTICA UNIVERSIDAD DE GRANADA FUNDAMENTOS DE BIOLOGÍA APLICADA I 4º CURSO DE BIOLOGÍA MÓDULO DE GENÉTICA TÉCNICAS MOLECULARES DE ANÁLISIS GENÉTICO AISLAMIENTO Y CLONACIÓN DE ADN SATÉLITE
Técnicas del ADN recombinante Introducción
 Técnicas del ADN recombinante Introducción Estructura primaria del ADN Enzimas de restricción (ER) Son enzimas (endonucleasas) de origen bacteriano que reconocen y cortan secuencias específicas (4-8 pb)
Técnicas del ADN recombinante Introducción Estructura primaria del ADN Enzimas de restricción (ER) Son enzimas (endonucleasas) de origen bacteriano que reconocen y cortan secuencias específicas (4-8 pb)
ESTUDIO DE POLIMORFISMOS ALU HUMANOS POR PCR
 ESTUDIO DE POLIMORFISMOS ALU HUMANOS POR PCR Ref. PCRALU 1. OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena
ESTUDIO DE POLIMORFISMOS ALU HUMANOS POR PCR Ref. PCRALU 1. OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena
TEST de PATERNIDAD. Ref. PCR paternidad (4 prácticas) 1. OBJETIVO DEL EXPERIMENTO
 Ref. PCR paternidad (4 prácticas) 1. OBJETIVO DEL EXPERIMENTO TEST de PATERNIDAD Este experimento introduce a los alumnos en el uso del ADN y la PCR para simular una determinación de paternidad. Los estudiantes
Ref. PCR paternidad (4 prácticas) 1. OBJETIVO DEL EXPERIMENTO TEST de PATERNIDAD Este experimento introduce a los alumnos en el uso del ADN y la PCR para simular una determinación de paternidad. Los estudiantes
BIOLOGIA CELULAR Y MOLECULAR. LABORATORIO No 7: REACCION EN CADENA DE LA POLIMERASA (PCR)
 BIOLOGIA CELULAR Y MOLECULAR LABORATORIO No 7: REACCION EN CADENA DE LA POLIMERASA (PCR) 1. INTRODUCCIÓN La Reacción en Cadena de la Polimerasa (PCR) es una técnica in Vitro que imita la habilidad natural
BIOLOGIA CELULAR Y MOLECULAR LABORATORIO No 7: REACCION EN CADENA DE LA POLIMERASA (PCR) 1. INTRODUCCIÓN La Reacción en Cadena de la Polimerasa (PCR) es una técnica in Vitro que imita la habilidad natural
Materia de Articulación CEBI_A5. Teórica 2 - Replicación del ADN
 CARRERA DE ESPECIALIZACION EN BIOTECNOLOGIA INDUSTRIAL FCEyN-INTI Materia de Articulación CEBI_A5 Biología Molecular l Teórica 2 - Replicación del ADN La división celular requiere la duplicación del material
CARRERA DE ESPECIALIZACION EN BIOTECNOLOGIA INDUSTRIAL FCEyN-INTI Materia de Articulación CEBI_A5 Biología Molecular l Teórica 2 - Replicación del ADN La división celular requiere la duplicación del material
Secuenciar una molécula de ADN consiste en determinar en qué orden se disponen los cuatro nucleótidos (A, T, C y G) que componen la molécula.
 SECUENCIACIÓN DEL ADN Secuenciar una molécula de ADN consiste en determinar en qué orden se disponen los cuatro nucleótidos (A, T, C y G) que componen la molécula. El primer método diseñado para secuenciar
SECUENCIACIÓN DEL ADN Secuenciar una molécula de ADN consiste en determinar en qué orden se disponen los cuatro nucleótidos (A, T, C y G) que componen la molécula. El primer método diseñado para secuenciar
Técnicas de Biología Molecular. Biol 3051L
 Técnicas de Biología Molecular Biol 3051L Objetivos El cortar el DNA con enzimas de restricción y hacer corridas de geles usando electroforesis es muchas veces el primer paso para estudiar un gen. En este
Técnicas de Biología Molecular Biol 3051L Objetivos El cortar el DNA con enzimas de restricción y hacer corridas de geles usando electroforesis es muchas veces el primer paso para estudiar un gen. En este
Transferencia de material genético II. 1) Aislamiento de plásmidos Lisis alcalina
 Transferencia de material genético II 1) Aislamiento de plásmidos Lisis alcalina ESQUEMA GENERAL SESIÓN I: TRANSFORMAR cepas de E. coli con un plásmido. Verificar que hay células transformantes de acuerdo
Transferencia de material genético II 1) Aislamiento de plásmidos Lisis alcalina ESQUEMA GENERAL SESIÓN I: TRANSFORMAR cepas de E. coli con un plásmido. Verificar que hay células transformantes de acuerdo
Reacción en cadena de la Polimerasa (PCR)
 Explicación de TP Nº 3 Reacción en cadena de la Polimerasa (PCR) Química Biológica Patológica Bioq. Mariana L. Ferramola 2013 Definición de PCR Es la amplificación enzimática de un fragmento de interés
Explicación de TP Nº 3 Reacción en cadena de la Polimerasa (PCR) Química Biológica Patológica Bioq. Mariana L. Ferramola 2013 Definición de PCR Es la amplificación enzimática de un fragmento de interés
PROPIEDADES FISICOQUÍMICAS DE LOS ÁCIDOS NUCLEICOS. Es un ácido capaz de formar sales con iones cargados
 Extracción de ADN Genética molecular PROPIEDADES FISICOQUÍMICAS DE LOS ÁCIDOS NUCLEICOS Es un ácido capaz de formar sales con iones cargados positivamente (cationes). Es soluble en soluciones concentradas
Extracción de ADN Genética molecular PROPIEDADES FISICOQUÍMICAS DE LOS ÁCIDOS NUCLEICOS Es un ácido capaz de formar sales con iones cargados positivamente (cationes). Es soluble en soluciones concentradas
3. Materiales y Métodos
 3. Materiales y Métodos El análisis de haplotipos se realizó mediante la caracterización de variaciones alélicas reportadas con anterioridad. En total de analizaron cinco marcadores polimórficos: tres
3. Materiales y Métodos El análisis de haplotipos se realizó mediante la caracterización de variaciones alélicas reportadas con anterioridad. En total de analizaron cinco marcadores polimórficos: tres
Reacción en cadena de la Polimerasa (PCR)
 Explicación de TP Nº 2 Reacción en cadena de la Polimerasa (PCR) Química Biológica Patológica Bioq. Mariana L. Ferramola 2014 Definición de PCR Es la amplificación enzimática de un fragmento de interés
Explicación de TP Nº 2 Reacción en cadena de la Polimerasa (PCR) Química Biológica Patológica Bioq. Mariana L. Ferramola 2014 Definición de PCR Es la amplificación enzimática de un fragmento de interés
 Química Biológica Patológica Técnicas de Biología Molecular aplicadas a Bioquímica Clínica Tema 2 Dra. Silvia Varas qbpatologica.unsl@gmail.com Tema 2 PCR Historia Bases Optimización de una reacción de
Química Biológica Patológica Técnicas de Biología Molecular aplicadas a Bioquímica Clínica Tema 2 Dra. Silvia Varas qbpatologica.unsl@gmail.com Tema 2 PCR Historia Bases Optimización de una reacción de
A. Anexo: Extracción de dsrna por columnas de exclusión de Sephadex G-50
 A. Anexo: Extracción de dsrna por columnas de exclusión de Sephadex G-50 (Tomado de Guzmán, 1994; Rodríguez, 2006) 1. En un tubo eppendorf tapa rosca estéril colocar 100 mg de material vegetal pulverizado
A. Anexo: Extracción de dsrna por columnas de exclusión de Sephadex G-50 (Tomado de Guzmán, 1994; Rodríguez, 2006) 1. En un tubo eppendorf tapa rosca estéril colocar 100 mg de material vegetal pulverizado
Código: IDK-003 Ver: 1. Factor V Leiden
 Sistema para detección de la alteración G1691A en el gene que codifica para el Factor V de la coagulación humana Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336 71
Sistema para detección de la alteración G1691A en el gene que codifica para el Factor V de la coagulación humana Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336 71
Materia de Articulación CEBI_A5
 CARRERA DE ESPECIALIZACION EN BIOTECNOLOGIA INDUSTRIAL FCEyN-INTI Materia de Articulación CEBI_A5 Biología Molecular l Replicación ió del ADN La división celular requiere la duplicación del material genético
CARRERA DE ESPECIALIZACION EN BIOTECNOLOGIA INDUSTRIAL FCEyN-INTI Materia de Articulación CEBI_A5 Biología Molecular l Replicación ió del ADN La división celular requiere la duplicación del material genético
Código: KIT-005 Ver: 1 MTHFR C677T
 Sistema para detección de la alteración C677T en el gene que codifica para la Metilen-tetrahidrofolato reductasa humana 1 Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598)
Sistema para detección de la alteración C677T en el gene que codifica para la Metilen-tetrahidrofolato reductasa humana 1 Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598)
Construcción de la biblioteca en cósmidos de Azospirillum brasilense CBG 497.
 Construcción de la biblioteca en cósmidos de Azospirillum brasilense CBG 497. Extracción de DNA genómico El DNA de A. brasilense CBG 497 se extrajo siguiendo el método descrito por la casa comercial distribuidora
Construcción de la biblioteca en cósmidos de Azospirillum brasilense CBG 497. Extracción de DNA genómico El DNA de A. brasilense CBG 497 se extrajo siguiendo el método descrito por la casa comercial distribuidora
TAXONOMÍA MOLECULAR TAXONOMÍA MOLECULAR
 TAXONOMÍA MOLECULAR TAXONOMÍA MOLECULAR Microbiología a General Área Micología Dra. Alicia Luque CEREMIC Taxonomía clásica Carecen de reproducibilidad: los caracteres fenotípicos pueden variar con las
TAXONOMÍA MOLECULAR TAXONOMÍA MOLECULAR Microbiología a General Área Micología Dra. Alicia Luque CEREMIC Taxonomía clásica Carecen de reproducibilidad: los caracteres fenotípicos pueden variar con las
Electroforesis. Dr. Héctor L. Ayala del Río AMGEN Bruce Wallace Program Departamento de Biología UPR-Humacao VER VIDEO CARGADO GEL
 Electroforesis Dr. Héctor L. Ayala del Río AMGEN Bruce Wallace Program Departamento de Biología UPR-Humacao VER VIDEO CARGADO GEL 1 Electroforesis l Método utilizado para separar y purificar macromoléculas:
Electroforesis Dr. Héctor L. Ayala del Río AMGEN Bruce Wallace Program Departamento de Biología UPR-Humacao VER VIDEO CARGADO GEL 1 Electroforesis l Método utilizado para separar y purificar macromoléculas:
1. OBTENCIÓN DE ADN DE BACTERIAS PATÓGENAS
 1. OBTENCIÓN DE ADN DE BACTERIAS PATÓGENAS Existen diferentes métodos para la obtención de ADN bacteriano que varían en duración y complejidad del procedimiento en función de la calidad del ADN que queramos
1. OBTENCIÓN DE ADN DE BACTERIAS PATÓGENAS Existen diferentes métodos para la obtención de ADN bacteriano que varían en duración y complejidad del procedimiento en función de la calidad del ADN que queramos
Introducción a la Secuenciación Masiva y a la Bioinformática
 Introducción a la Secuenciación Masiva y a la Bioinformática Dietmar Fernández Orth, PhD 24 de Abril de 2014 1 El DNA (Ácido desoxirribonucleico) contiene la información genética usada en el desarrollo
Introducción a la Secuenciación Masiva y a la Bioinformática Dietmar Fernández Orth, PhD 24 de Abril de 2014 1 El DNA (Ácido desoxirribonucleico) contiene la información genética usada en el desarrollo
La geosfera. Genética molecular. 4º ESO Biología y Geología
 4º ESO Biología y Geología 1. LOS ÁCIDOS NUCLEICOS Los ácidos nucleicos son macromoléculas formadas por la unión de moléculas más sencillas, llamadas nucleótidos. Los nucleótidos, a su vez, están constituidos
4º ESO Biología y Geología 1. LOS ÁCIDOS NUCLEICOS Los ácidos nucleicos son macromoléculas formadas por la unión de moléculas más sencillas, llamadas nucleótidos. Los nucleótidos, a su vez, están constituidos
TÉCNICAS DE ANÁLISIS GENÉTICO: Extracción de ADN.
 Trabajo Práctico 2.2 TÉCNICAS DE ANÁLISIS GENÉTICO: Extracción de ADN. Desde el reconocimiento del ADN como "la molécula de la vida", se conoce que en ella se encuentran cifradas las instrucciones que
Trabajo Práctico 2.2 TÉCNICAS DE ANÁLISIS GENÉTICO: Extracción de ADN. Desde el reconocimiento del ADN como "la molécula de la vida", se conoce que en ella se encuentran cifradas las instrucciones que
UNIVERSIDAD NACIONAL DE MISIONES Facultad de Ciencias Exactas Químicas y Naturales TRABAJO PRÁCTICO Nº 4 REACCIÓN EN CADENA DE LA POLIMERASA (PCR)
 TRABAJO PRÁCTICO Nº 4 REACCIÓN EN CADENA DE LA POLIMERASA (PCR) INTRODUCCIÓN La reacción en cadena de la polimerasa o PCR (del inglés Polymerase Chain Reaction) es una técnica relativamente simple y poderosa
TRABAJO PRÁCTICO Nº 4 REACCIÓN EN CADENA DE LA POLIMERASA (PCR) INTRODUCCIÓN La reacción en cadena de la polimerasa o PCR (del inglés Polymerase Chain Reaction) es una técnica relativamente simple y poderosa
Técnicas moleculares para el diagnóstico de microorganismos fitopatógenos
 Técnicas moleculares para el diagnóstico de microorganismos fitopatógenos Dra. Ing. Agr. Sandra Alaniz Unidad de Fitopatología setiembre de 2015 Unidades taxonómicas Dominio Orden Familia Género Especie
Técnicas moleculares para el diagnóstico de microorganismos fitopatógenos Dra. Ing. Agr. Sandra Alaniz Unidad de Fitopatología setiembre de 2015 Unidades taxonómicas Dominio Orden Familia Género Especie
Easy PDF Creator is professional software to create PDF. If you wish to remove this line, buy it now.
 1 Virología y Micología Veterinaria Trabajo Práctico No. 4 ELECTROFORESIS La electroforesis es una técnica utilizada para separar grandes moléculas por tamaño a través de la aplicación de un campo eléctrico
1 Virología y Micología Veterinaria Trabajo Práctico No. 4 ELECTROFORESIS La electroforesis es una técnica utilizada para separar grandes moléculas por tamaño a través de la aplicación de un campo eléctrico
PCR Múltiplex. Listeria monocytogenes
 PCR Múltiplex Listeria monocytogenes PCR-múltiplex En una sola reacción de PCR se amplifican al mismo tiempo 2 o más genes Condiciones similares de PCR para los genes amplificar: Desnaturalización Alineamiento
PCR Múltiplex Listeria monocytogenes PCR-múltiplex En una sola reacción de PCR se amplifican al mismo tiempo 2 o más genes Condiciones similares de PCR para los genes amplificar: Desnaturalización Alineamiento
Capítulo 6. Procedimientos para el sexaje de embriones bovinos por PCR
 Capítulo 6 Procedimientos para el sexaje de embriones bovinos por PCR Autores: Luisa Fernanda Ortiz Román y Diana Maritza Echeverry Berrío En los casos en los que no se puede realizar fertilización con
Capítulo 6 Procedimientos para el sexaje de embriones bovinos por PCR Autores: Luisa Fernanda Ortiz Román y Diana Maritza Echeverry Berrío En los casos en los que no se puede realizar fertilización con
INGENIERÍA GENÉTICA. Sinónimos: Manipulación genética Clonaje génico Tecnología del DNA recombinante
 INGENIERÍA GENÉTICA Es una revolución metodológica que ha puesto a nuestra disposición gran número de técnicas procedentes de diversos campos de la ciencia con un objetivo común muy importante: el acceso
INGENIERÍA GENÉTICA Es una revolución metodológica que ha puesto a nuestra disposición gran número de técnicas procedentes de diversos campos de la ciencia con un objetivo común muy importante: el acceso
PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN DE LAS COMPETENCIAS PROFESIONALES CUESTIONARIO DE AUTOEVALUACIÓN PARA LAS TRABAJADORAS Y TRABAJADORES
 MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
Ficha descriptiva SERVICIOS CENTRALES DEL CENTRO DE APOYO TECNOLÓGICO DE LA URJC. Nombre de la UNIDAD/Técnica: Genómica y Citometría de Flujo.
 Página 1 de 5 Nombre de la UNIDAD/Técnica: Genómica y Citometría de Flujo. Responsable: José Antonio Mas Gutiérrez Teléfono: 914 888 645 / 914 887 184 Email joseantonio.mas@urjc.es Principios de la Técnica
Página 1 de 5 Nombre de la UNIDAD/Técnica: Genómica y Citometría de Flujo. Responsable: José Antonio Mas Gutiérrez Teléfono: 914 888 645 / 914 887 184 Email joseantonio.mas@urjc.es Principios de la Técnica
Genética de bacterias Transferencia horizontal de genes Electrotransformación de plásmidos con gen codificante de proteína verde fluorescente en E.
 Genética de bacterias Transferencia horizontal de genes Electrotransformación de plásmidos con gen codificante de proteína verde fluorescente en E. coli Transformación Células naturalmente competentes
Genética de bacterias Transferencia horizontal de genes Electrotransformación de plásmidos con gen codificante de proteína verde fluorescente en E. coli Transformación Células naturalmente competentes
UNIVERSIDAD NACIONAL DE GRAL. SAN MARTÍN ECyT BIOLOGÍA CPU. Biología. Información genética, ADN, Cromosomas
 UNIVERSIDAD NACIONAL DE GRAL. SAN MARTÍN ECyT BIOLOGÍA CPU Biología Información genética, ADN, Cromosomas Qué es la información genética? Es la información biológica heredable: Toda la información que
UNIVERSIDAD NACIONAL DE GRAL. SAN MARTÍN ECyT BIOLOGÍA CPU Biología Información genética, ADN, Cromosomas Qué es la información genética? Es la información biológica heredable: Toda la información que
Técnicas de biología molecular utilizadas en el diagnóstico de enfermedades hereditarias
 Explicación de TP Nº 1 Técnicas de biología molecular utilizadas en el diagnóstico de enfermedades hereditarias Química Biológica Patológica Dra. Mariana L. Ferramola Dra. Gabriela Lacoste 2015 Conceptos
Explicación de TP Nº 1 Técnicas de biología molecular utilizadas en el diagnóstico de enfermedades hereditarias Química Biológica Patológica Dra. Mariana L. Ferramola Dra. Gabriela Lacoste 2015 Conceptos
GENERALIDADES Y APLICACIONES DE LA ELECTROFORESIS. Influencia de campo cargado eléctricamente Movimiento al cátodo (-) o al anodo (+)
 GENERALIDADES Y APLICACIONES DE LA ELECTROFORESIS Electroforésis Separación de especies cargadas (anión (-) y catión (+) ) Influencia de campo cargado eléctricamente Movimiento al cátodo (-) o al anodo
GENERALIDADES Y APLICACIONES DE LA ELECTROFORESIS Electroforésis Separación de especies cargadas (anión (-) y catión (+) ) Influencia de campo cargado eléctricamente Movimiento al cátodo (-) o al anodo
Ensayos southwestern y northwestern
 Búsqueda de proteínas que se unen a DNA (secuencia conocida, promotor) Ensayo southwestern encontrar proteínas ligantes de DNA que reconozcan en éste una determinada secuencia de nucleótidos Ensayo northwestern
Búsqueda de proteínas que se unen a DNA (secuencia conocida, promotor) Ensayo southwestern encontrar proteínas ligantes de DNA que reconozcan en éste una determinada secuencia de nucleótidos Ensayo northwestern
LABORATORIO DE MICROBIOLOGÍA DE ALIMENTOS. DETERMINACIÓN DE MICROORGANISMOS AISLADOS DE ALIMENTOS POR TÉCNICAS MOLECULARES QFB. Martha Giles Gómez
 LABORATORIO DE MICROBIOLOGÍA DE ALIMENTOS DETERMINACIÓN DE MICROORGANISMOS AISLADOS DE ALIMENTOS POR TÉCNICAS MOLECULARES QFB. Martha Giles Gómez PREPARACIÓN Y ANÁLISIS DE ADN La aplicación de las técnicas
LABORATORIO DE MICROBIOLOGÍA DE ALIMENTOS DETERMINACIÓN DE MICROORGANISMOS AISLADOS DE ALIMENTOS POR TÉCNICAS MOLECULARES QFB. Martha Giles Gómez PREPARACIÓN Y ANÁLISIS DE ADN La aplicación de las técnicas
CUADERNO DE PRÁCTICAS GENETICA MOLECULAR HUMANA. Grado en Medicina
 DEPARTAMENTO DE BIOQUÍMICA Y BIOLOGÍA MOLECULAR III FACULTAD DE MEDICINA UNIVERSIDAD COMPLUTENSE DE MADRID CUADERNO DE PRÁCTICAS GENETICA MOLECULAR HUMANA Grado en Medicina CURSO ACADÉMICO 2017/2018 INDICE
DEPARTAMENTO DE BIOQUÍMICA Y BIOLOGÍA MOLECULAR III FACULTAD DE MEDICINA UNIVERSIDAD COMPLUTENSE DE MADRID CUADERNO DE PRÁCTICAS GENETICA MOLECULAR HUMANA Grado en Medicina CURSO ACADÉMICO 2017/2018 INDICE
SEGUNDA SESIÓN: AMPLIFICACIÓN DE LOS GENES inla E inlc DE Listeria monocytogenes POR PCR-MÚLTIPLE.
 SEGUNDA SESIÓN: AMPLIFICACIÓN DE LOS GENES inla E inlc DE Listeria monocytogenes POR PCR-MÚLTIPLE. La reacción en cadena de la polimerasa (PCR por sus siglas en inglés), es un procedimiento rápido para
SEGUNDA SESIÓN: AMPLIFICACIÓN DE LOS GENES inla E inlc DE Listeria monocytogenes POR PCR-MÚLTIPLE. La reacción en cadena de la polimerasa (PCR por sus siglas en inglés), es un procedimiento rápido para
Código: KIT-001 Ver: 1. Pre-FRAXA. Sistema para la detección del número de repetidos CGG en el gene FMR1 PM F M M F M M M C. Reg.
 Pre-FRAXA Sistema para la detección del número de repetidos CGG en el gene FMR1 PM F M M F M M M C Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336 71 60. www.atgen.com.uy
Pre-FRAXA Sistema para la detección del número de repetidos CGG en el gene FMR1 PM F M M F M M M C Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336 71 60. www.atgen.com.uy
1. Escribir la secuencia de bases de las cadenas complementarias de las siguientes: 5' AGCCTAGCAA 3' 5 GATCAATCGA 3 5 TACCATACGC 3
 DEPARTAMENTO DE BIOLOGIA MOLECULAR FACULTAD DE MEDICINA Isabel Andrés PROBLEMAS TEMA 10. INFORMACION GENETICA. 1. Escribir la secuencia de bases de las cadenas complementarias de las siguientes: 5' AGCCTAGCAA
DEPARTAMENTO DE BIOLOGIA MOLECULAR FACULTAD DE MEDICINA Isabel Andrés PROBLEMAS TEMA 10. INFORMACION GENETICA. 1. Escribir la secuencia de bases de las cadenas complementarias de las siguientes: 5' AGCCTAGCAA
Métodos de secuenciación de ADN
 Métodos de secuenciación de ADN Valeria Tekiel Breve historia. 1871 Descubrimiento de los ácidos nucleicos 1903 Los cromosomas son unidades hereditarias 1910 Los genes están en los cromosomas 1944 El ADN
Métodos de secuenciación de ADN Valeria Tekiel Breve historia. 1871 Descubrimiento de los ácidos nucleicos 1903 Los cromosomas son unidades hereditarias 1910 Los genes están en los cromosomas 1944 El ADN
CYP 2C9 A1075C CYP2C9*3
 CYP 2C9 A1075C Sistema para la detección de la mutación A1075C en el gene del citocromo P450 2C9. Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336 71 60. Info@atgen.com.uy
CYP 2C9 A1075C Sistema para la detección de la mutación A1075C en el gene del citocromo P450 2C9. Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336 71 60. Info@atgen.com.uy
TECNOLOGÍA. Biología. Molecular. Al Alcance de Casi Cualquier Laboratorio para la Industria Alimentaria. INDUALIMENTOS abril
 TECNOLOGÍA Biología Molecular Al Alcance de Casi Cualquier Laboratorio para la Industria Alimentaria Qué se imagina usted cuando escucha hablar de Biología Molecular? Parece un tema tan complicado que
TECNOLOGÍA Biología Molecular Al Alcance de Casi Cualquier Laboratorio para la Industria Alimentaria Qué se imagina usted cuando escucha hablar de Biología Molecular? Parece un tema tan complicado que
BIOLOGIA MOLECULAR. Dra. Ma. Laura Tondo
 TÉCNICAS BASADAS EN HIBRIDACIÓN MOLECULAR BIOLOGIA MOLECULAR 2016 Dra. Ma. Laura Tondo DESNATURALIZACION Y RENATURALIZACION DEL DNA Cómo se mantienen unidas las dos hebras del DNA? - Puentes de hidrógeno
TÉCNICAS BASADAS EN HIBRIDACIÓN MOLECULAR BIOLOGIA MOLECULAR 2016 Dra. Ma. Laura Tondo DESNATURALIZACION Y RENATURALIZACION DEL DNA Cómo se mantienen unidas las dos hebras del DNA? - Puentes de hidrógeno
ELECTROFORESIS EN GEL DE POLIACRILAMIDA CON SDS SDS-PAGE
 Departamento de Biología de Sistemas Unidad Docente de Bioquímica y Biología Molecular ELECTROFORESIS EN GEL DE POLIACRILAMIDA CON SDS SDS-PAGE 1. FUNDAMENTO TEÓRICO La electroforesis es una técnica de
Departamento de Biología de Sistemas Unidad Docente de Bioquímica y Biología Molecular ELECTROFORESIS EN GEL DE POLIACRILAMIDA CON SDS SDS-PAGE 1. FUNDAMENTO TEÓRICO La electroforesis es una técnica de
TRABAJO PRÁCTICO N 3: Identificación microbiana
 TRABAJO PRÁCTICO N 3: Identificación microbiana PARTE A: Identificación Fenotípica 1.-Pruebas Bioquímicas 2- Coloraciones 3. Uso del Manual Bergey Pruebas Bioquímicas Son una serie de pruebas que permiten
TRABAJO PRÁCTICO N 3: Identificación microbiana PARTE A: Identificación Fenotípica 1.-Pruebas Bioquímicas 2- Coloraciones 3. Uso del Manual Bergey Pruebas Bioquímicas Son una serie de pruebas que permiten
Estructura y Función de los ácidos nucleicos
 1 Estructura y Función de los ácidos nucleicos Estructura de los Ácidos Nucleicos Componentes Básicos Núcleotidos Azúcar Fosfato Base Nitrogenada 2 Bases Nitrogenadas Purinas Adenina Guanina Pirimidinas
1 Estructura y Función de los ácidos nucleicos Estructura de los Ácidos Nucleicos Componentes Básicos Núcleotidos Azúcar Fosfato Base Nitrogenada 2 Bases Nitrogenadas Purinas Adenina Guanina Pirimidinas
EXTRACCIÓN DE ADN DE HONGOS FILAMENTOSOS
 EXTRACCIÓN DE ADN DE HONGOS FILAMENTOSOS Los hongos poseen un genoma complejo consistente en: ADN nuclear (n ADN) ADN mitocondrial (mt ADN) en algunos casos ADN plasmídico EXTRACCIÓN DE ADN DE HONGOS FILAMENTOSOS
EXTRACCIÓN DE ADN DE HONGOS FILAMENTOSOS Los hongos poseen un genoma complejo consistente en: ADN nuclear (n ADN) ADN mitocondrial (mt ADN) en algunos casos ADN plasmídico EXTRACCIÓN DE ADN DE HONGOS FILAMENTOSOS
K ADN PuriPrep-P kit. Extracción y purificación rápida de ADN plasmídico (miniprep)
 K 1207 ADN PuriPrep-P kit Extracción y purificación rápida de ADN plasmídico (miniprep) Indice Presentación... 6 Importante... 6 Componentes del kit... 6 Condiciones de conservación... 7 Garantía... 7
K 1207 ADN PuriPrep-P kit Extracción y purificación rápida de ADN plasmídico (miniprep) Indice Presentación... 6 Importante... 6 Componentes del kit... 6 Condiciones de conservación... 7 Garantía... 7
ELECTROFORESIS. Objetivo de la clase. *fundamentos *procedimientos *algunas aplicaciones. Conocer los métodos electroforéticos
 ELECTROFORESIS Objetivo de la clase Conocer los métodos electroforéticos *fundamentos *procedimientos *algunas aplicaciones Definición de electroforesis Proceso de separación que se basa en la diferente
ELECTROFORESIS Objetivo de la clase Conocer los métodos electroforéticos *fundamentos *procedimientos *algunas aplicaciones Definición de electroforesis Proceso de separación que se basa en la diferente
Acción de la enzima de restricción EcoRI
 Acción de la enzima de restricción EcoRI S Lobos C - U de Chile 1 S Lobos C - U de Chile 2 S Lobos C - U de Chile 3 Nucleic Acids Res. 2001 September 15; 29(18): 3705 3727. Structure and function of type
Acción de la enzima de restricción EcoRI S Lobos C - U de Chile 1 S Lobos C - U de Chile 2 S Lobos C - U de Chile 3 Nucleic Acids Res. 2001 September 15; 29(18): 3705 3727. Structure and function of type
APLICACIÓN DE LA PCR: DIAGNÓSTICO DE PARÁSITOS
 Prácticas docentes en la COD: 10-71 APLICACIÓN DE LA PCR: DIAGNÓSTICO DE PARÁSITOS FUNDAMENTO TEÓRICO La PCR es una técnica que permite llevar a cabo la síntesis in vitro de fragmentos de ADN. Está basada
Prácticas docentes en la COD: 10-71 APLICACIÓN DE LA PCR: DIAGNÓSTICO DE PARÁSITOS FUNDAMENTO TEÓRICO La PCR es una técnica que permite llevar a cabo la síntesis in vitro de fragmentos de ADN. Está basada
K ADN PuriPrep-GP kit. Extracción y purificación rápida de ADN a partir de: Gel de agarosa y Productos de PCR en solución
 K 1206 ADN PuriPrep-GP kit Extracción y purificación rápida de ADN a partir de: Gel de agarosa y Productos de PCR en solución Indice Presentación... 6 Importante... 6 Componentes del kit... 6 Condiciones
K 1206 ADN PuriPrep-GP kit Extracción y purificación rápida de ADN a partir de: Gel de agarosa y Productos de PCR en solución Indice Presentación... 6 Importante... 6 Componentes del kit... 6 Condiciones
Transcripción. - Generalidades - DNA RNA. - Mecanismo. - Modelos Protein. - Moléculas. - Métodos de detección de RNA. Chromosome RNA DNA
 TRANSCRIPCIÓN Transcripción - Generalidades Chromosome - DNA RNA - Mecanismo - Modelos Protein RNA - Moléculas - Métodos de detección de RNA DNA Transcripción - Primer proceso de la expresión genética
TRANSCRIPCIÓN Transcripción - Generalidades Chromosome - DNA RNA - Mecanismo - Modelos Protein RNA - Moléculas - Métodos de detección de RNA DNA Transcripción - Primer proceso de la expresión genética
PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN DE LAS COMPETENCIAS PROFESIONALES CUESTIONARIO DE AUTOEVALUACIÓN PARA LAS TRABAJADORAS Y TRABAJADORES
 MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
COMPOSICIÓN DEL ADN ÁCIDO FOSFÓRICO BASE NITROGENADA AZÚCAR
 ÁCIDOS NUCLEICOS COMPOSICIÓN DEL ADN ÁCIDO FOSFÓRICO O O O P O O C O N O N BASE NITROGENADA AZÚCAR BASES NITROGENADAS Citosina Timina (exclusiva del ADN) Uracilo (exclusiva del ARN) Adenina Guanina FORMACIÓN
ÁCIDOS NUCLEICOS COMPOSICIÓN DEL ADN ÁCIDO FOSFÓRICO O O O P O O C O N O N BASE NITROGENADA AZÚCAR BASES NITROGENADAS Citosina Timina (exclusiva del ADN) Uracilo (exclusiva del ARN) Adenina Guanina FORMACIÓN
Código: IDK-004 Ver: 1. Factor II 20210
 20210 Sistema para detección de la alteración G20210A en el gene que codifica para el de la coagulación humana PM 1 2 Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2
20210 Sistema para detección de la alteración G20210A en el gene que codifica para el de la coagulación humana PM 1 2 Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2
DANAGENE SPIN GENOMIC DNA KIT
 DANAGENE SPIN GENOMIC DNA KIT Ref.0605.1 50 extracciones Ref.0605.2 250 extracciones Ref.0605.3 1000 extracciones 1. INTRODUCCION Este kit está designado para una rápida extracción y purificación de ADN
DANAGENE SPIN GENOMIC DNA KIT Ref.0605.1 50 extracciones Ref.0605.2 250 extracciones Ref.0605.3 1000 extracciones 1. INTRODUCCION Este kit está designado para una rápida extracción y purificación de ADN
AMPLIFICACIÓN DE ADN POR REACCIÓN EN CADENA DE POLIMERASA (PCR)
 Universidad Interamericana de Puerto Rico Recinto de Fajardo Departamento de Ciencias y Tecnología AMPLIFICACIÓN DE ADN POR REACCIÓN EN CADENA DE POLIMERASA (PCR) Trasfondo La reacción en cadena de la
Universidad Interamericana de Puerto Rico Recinto de Fajardo Departamento de Ciencias y Tecnología AMPLIFICACIÓN DE ADN POR REACCIÓN EN CADENA DE POLIMERASA (PCR) Trasfondo La reacción en cadena de la
UNIDAD 6: GENÉTICA MODERNA Y MANIPULACIÓN GENÉTICA
 UNIDAD 6: GENÉTICA MODERNA Y MANIPULACIÓN GENÉTICA Para comenzar vamos a remarcar que existen dos ácidos nucleicos DNA y RNA El DNA Estructura Estructura Estructura La información sobre los caracteres
UNIDAD 6: GENÉTICA MODERNA Y MANIPULACIÓN GENÉTICA Para comenzar vamos a remarcar que existen dos ácidos nucleicos DNA y RNA El DNA Estructura Estructura Estructura La información sobre los caracteres
Código: IDK-006 Ver: 1 MTHFR A1298C. Sistema para detección de la alteración A1298C en el gene de la Mutilen Tetrahidrofolato Reductasa
 Sistema para detección de la alteración A1298C en el gene de la Mutilen Tetrahidrofolato Reductasa Reg. MSP 21199 Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336
Sistema para detección de la alteración A1298C en el gene de la Mutilen Tetrahidrofolato Reductasa Reg. MSP 21199 Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336
MÁSTER MÁSTER EN BIOLOGÍA MOLECULAR Y CITOGENÉTICA. MAS241
 MÁSTER MÁSTER EN BIOLOGÍA MOLECULAR Y CITOGENÉTICA. MAS241 Escuela asociada a: CONFEDERACIÓN ESPAÑOLA DE EMPRESAS DE FORMACIÓN ASOCIACIÓN ESPAÑOLA PARA LA CALIDAD ASOCIACIÓN ESPAÑOLA DE ESCUELAS DE NEGOCIOS
MÁSTER MÁSTER EN BIOLOGÍA MOLECULAR Y CITOGENÉTICA. MAS241 Escuela asociada a: CONFEDERACIÓN ESPAÑOLA DE EMPRESAS DE FORMACIÓN ASOCIACIÓN ESPAÑOLA PARA LA CALIDAD ASOCIACIÓN ESPAÑOLA DE ESCUELAS DE NEGOCIOS
Investigación en evolución
 Investigación en evolución Análisis de secuencias de: nucleótidos en DNA (genómica) aminoácidos en Proteínas (proteómica) Comparación de secuencias de: nucleótidos aminoácidos Bioinformática Análisis de
Investigación en evolución Análisis de secuencias de: nucleótidos en DNA (genómica) aminoácidos en Proteínas (proteómica) Comparación de secuencias de: nucleótidos aminoácidos Bioinformática Análisis de
