ES A1 C12Q 1/68 ( ) OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA. 11 Número de publicación:
|
|
|
- Luz Medina Camacho
- hace 8 años
- Vistas:
Transcripción
1 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: Número de solicitud: Int. Cl.: C12Q 1/68 (06.01) 12 SOLICITUD DE PATENTE A1 22 Fecha de presentación: Fecha de publicación de la solicitud: Solicitante/s: Consejo Superior de Investigaciones Científicas c/ Serrano, Madrid, ES 72 Inventor/es: Zimmermann, Johannes; González Grau, Juan Miguel y Sáiz Jiménez, Cesáreo 43 Fecha de publicación del folleto de la solicitud: Agente: No consta 4 Título: Oligonucleótidos dirigidos al gen ARN ribosómico 23S de Acidobacterias y su utilización. 7 Resumen: Oligonucleótidos dirigidos al gen ARN ribosómico 23S de Acidobacterias y su utilización. La detección rápida de bacterias es esencial para determinar su papel en los distintos procesos, tanto de organismos beneficiosos como perjudiciales. El objeto de esta invención es el diseño de secuencias características que permiten identificar las Acidobacterias y los subgrupos a los que pertenecen de forma rápida y eficaz. La identificación de esta división bacteriana se ha llevado a cabo en base a secuencias previamente desconocidas del gen 23S del RNA ribosómico de Acidobacterias. Esos oligonucleótidos pueden ser utilizados para preparar cebadores (primers) para su uso en reacciones de amplificación de ADN, como sondas de ácidos nucleicos, o para su uso en arrays de ADN/ARN. La detección de las Acidobacterias y la diferenciación de sus subgrupos es de aplicación en muestras de diversos tipos, preferentemente, en muestras ambientales, biológicas y/o médicas. ES A1 Venta de fascículos: Oficina Española de Patentes y Marcas. Pº de la Castellana, Madrid
2 DESCRIPCIÓN Oligonucleótidos dirigidos al gen ARN ribosómico 23S de Acidobacterias y su utilización Sector de la técnica El sector principal de aplicación es la biotecnología en aquellos campos que requieran la detección de Acidobacterias tanto cultivadas como no cultivadas. Entre los campos de aplicación figuran la conservación de obras y objetos de arte, estudios biogeoquímicos y trabajos in situ sobre cualquier tipo de muestras. Estado de la técnica Hoy en día, los microorganismos pueden ser identificados sin necesidad de ser cultivados utilizando técnicas moleculares como la amplificación por PCR ( Polymerase Chain Reaction ) y secuenciación, Fluorescent In Situ Hybridization (FISH) o hibridación in situ con sondas de ADN marcadas fluorescentemente, o con el empleo de microarrays de ADN. Estas técnicas requieren el uso de oligonucleótidos o sondas específicas diseñadas para detectar genes determinados. Uno de los genes o fragmentos de ADN más utilizados con este fin es el del ARN ribosómico 16S ya que el número de copias por célula de este gen es más elevado que el de otras secuencias. Los procedimientos de PCR y FISH son habituales en laboratorios de biología molecular. Ambos requieren el uso de oligonucleótidos que constan de una secuencia de unos 1- nucleótidos de longitud. En el caso de sondas de ADN, estos oligonucleótidos son marcados, generalmente, en su lado terminal con un colorante fluorescente o radioisótopos. Estos oligonucleótidos, también llamados primers o cebadores, en la reacción PCR sirven para amplificar el gen o fragmento de ADN de interés. Una reacción positiva indicaría la presencia de microorganismos del tipo buscado. El procedimiento FISH permite una rápida detección con la utilización de sondas de ADN marcadas fluorescentemente, permitiendo la rápida detección de células determinadas in situ (De Long et al. 1989). El uso de microarrays se está extendiendo en los últimos años ya que permite la utilización de numerosos oligonucleótidos simultáneamente dirigidos a la detección de diversos grupos microbianos o genes sobre un mismo portaobjetos o membrana (Peplies et al. 03). Estas técnicas constituyen los métodos más importantes que tenemos disponibles hoy en día para la detección de microorganismos no cultivables en ambientes naturales (Amann et al. 01) y en muestras médicas (Moter y Gbbel 00). Se han publicado muchos primers generales para microorganismos y para algunos grupos específicos así como sondas oligonucleotídicas para el rrna (Loy et al. 03). Las Acidobacterias constituyen una División bacteriana hasta hoy constituida por tan solo tres especies cultivadas Acidobacterium, Holophaga y Geothrix. Sin embargo, recientemente, se ha descubierto la existencia de mayor número de Acidobacterias utilizando métodos moleculares basados en secuencias del gen 16S rrna obtenidas por PCR. Se sabe que las Acidobacterias constituyen una fracción altamente significativa de la comunidad microbiana presente en suelos y monumentos, pueden alcanzar el 2% de presencia en muestras de cuevas, por ejemplo. Su papel en la biogeoquímica de estos ecosistemas, dada su elevada presencia, es sin duda de gran importancia. Esta abundancia justifica la necesidad de conocer con mayor detalle dichas acidobacterias para lo cual es preciso su previa identificación. Dado el interés por descubrir y comprender el papel de las Acidobacterias y sus implicaciones en los ecosistemas donde se desarrollan, se hace necesaria la existencia de una metodología capaz de detectar estos microorganismos de la manera más fiable y precisa posible. Las Acidobacterias descubiertas hasta ahora, mediante técnicas moleculares basadas en los genes de ARN ribosómico 16S, han sido clasificadas en ocho (8) subgrupos (Hugenholtz et al. 1998), siendo los correspondientes a las especies cultivadas los subgrupos número 1 y 8. Estos 8 subgrupos pueden caracterizarse en el gen ARN ribosómico 16S por las siguientes secuencias, con los números de acceso dados (GenBank, subgrupo 1, D26171; subgrupo 3, AF0131; subgrupo 4-I, U68644; subgrupo 4-II, AF013; subgrupo 4-III, AF013; subgrupo, Z9707; subgrupo 6, Z9733; subgrupo 7-I, Z9729; subgrupo 7-II, Z9713; subgrupo 8, U4163. Trabajos posteriores llevados a cabo por nuestro grupo (con 16S y 23S) han dado lugar al descubrimiento de nuevas secuencias que al ser clasificadas en base a su distancia filogenética no pertenecen a ninguno de los 8 subgrupos diferenciados con el 16S, indicando la existencia de nuevos subgrupos distintos. El gen de ARN ribosómico 23S es de mayor longitud (unas 00 bases) que el ARN ribosómico 16S (unas 0 bases). Tanto el gen 16S como el 23S de ARN ribosómico se encuentran en todas las bacterias y ambos reflejan fielmente la filogenia microbiana. El gen de ARN ribosómico 23S presenta zonas con gran variabilidad entre microorganismos distintos mientras que las diferencias encontradas entre genes ARN ribosómicos 16S son menores debido a su menor tamaño. El gen 23S ARN ribosómico ofrece por tanto más posibilidades para la diferenciación de microorganismos distintos y mayores opciones para el diseño de oligonucleotidos específicos para la detección de microorganismos determinados y, concretamente, para el análisis de la diversidad microbiana. En contrapartida, el trabajo de secuencia- 2
3 ción del 16S es más fácil que el del 23S por ser aquel más corto y esta es la razón por la que hasta el momento el gen ARN ribosómico 16S sea el gen más utilizado. En la presente invención se han diseñado primers y sondas que permiten la detección del gen ARN ribosómico 23S de las Acidobacterias. Referencias Amann R, Fuchs BM, Behrens S. 01. The identification of microorganisms by fluorescence in situ hybridisation. Curr Opin Biotechnol 12: DeLong EF, Wickham GS, Pace NR Phylogenetic stains: ribosomal RNA based probes for the identification of single cells. Science 243: Hugenholtz, P., Goebel, B.M., and Pace, N.R Impact of Culture-Independent Studies on the Emerging Phylogenetic View of Bacterial Diversity. J Bacteriol 180: Loy A, Horn M, Wagner M. 03. ProbeBase: an online resource for rrna-targeted oligonucleotide probes. Nucleic Acids Res 31: Moter A, Gdbel UB. 00. Fluorescence in situ hybridization (FISH) for direct visualization of microorganisms. J Microbiol Methods 41: Peplies J, Glockner F0, Amann R. 03. Optimization strategies for DNA microarray-based detection of bacteria with 16S rrna-targeting oligonucleotide probes. Appl Environ Microbiol. 69: Zimmermann, J., W. Ludwig, K.-H. Schleifer. 01. DNA polynucleotide probes generated from representatives of the genus Acinetobacter and their application in fluorescence in situ hybridization of environmental samples. System. Appl. Microbiol. 24: Breve descripción Tal como se ha mencionado previamente se hace necesaria una tecnología capaz de detectar a los microorganismos pertenecientes al grupo de las Acidobacterias, de la manera más rápida, fiable y precisa posible, y a su vez distinguirlas de otros microorganismos. La presente invención se refiere a la detección de Acidobacterias, utilizando secuencias de nucleótidos como sondas o primers (cebadores), y su aplicación en búsquedas de presencia, cuantificación y/o identificación de Acidobacterias. 4 0 La presente invención describe una sonda y oligonucleótido de ADN específico diseñado para la detección de las Acidobacterias basándose en el gen ARN ribosómico 23S; más concretamente, utilizando el oligonucleótido propuesto ACIPHY631 en la presente invención que es específico para Acidobacterias, o su complementario. Constituye, por tanto, un objeto de la presente invención una secuencia aislada de nucleótidos útil para la detección, cuantificación y/o identificación de Acidobacterias que comprende la secuencia complementaria inversa a una secuencia parcial del gen ARN ribosómico 23S de Acidobacterias de ACIPHY631 o su complementaria, en adelante la secuencia. Asimismo, constituye otro objeto de la presente invención un kit de detección, cuantificación y/o identificación de Acidobacterias caracterizado porque comprende la secuencia o sonda mencionada anteriormente. El método de detección, cuantificación, e identificación de Acidobacterias que utiliza al menos la secuencia, o sonda, o un kit de los mencionados anteriormente, constituye igualmente un objeto de la invención. La presente invención presenta el diseño de una secuencia de oligonucleótidos para la detección bien como primer o sonda de Acidobacterias en aplicaciones como por ejemplo, pero no restringido a, la amplificación por PCR, FISH, microarrays de ADN o reacciones de transcripción inversa a partir de ARN, así como el empleo de esos oligonucleótidos como reactivo o método para la detección de Acidobacterias. Estos oligonucleótidos van dirigidos a detectar específicamente las Acidobacterias utilizando secuencias únicas del gen de ARN ribosómico 23S de estos microorganismos. La utilización de estos oligonucleótidos permite la detección rápida de Acidobacterias sin necesidad de cultivar estos microorganismos con la utilización de técnicas moleculares (PCR, FISH, microarrays). 6 Otro aspecto de la presente invención se relaciona con la utilización de la secuencia, o sonda, o kits, objetos de la presente invención, en la detección, identificación y/o cuantificación de Acidobacterias en cualquier tipo de muestras, preferentemente en muestras ambientales, biológicas y/o médicas. 3
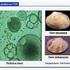
4 Descripción de las figuras Figura Análisis electroforético en gel de agarosa que muestra los productos de PCR obtenidos con la utilización del primer propuesto ACIPHY631 (reverse) y el primer universal 616 (forward). La detección positiva de acidobacterias se comprueba rápidamente por la presencia de producto ( muestra positiva ) y su ausencia denota la ausencia de acidobacterias ( muestra negativa ) en otra muestra analizada. Se presenta el resultado de un gradiente de temperatura de hibridación de los primers al ADN molde durante la PCR (desde 3 hasta 62.3ºC) para cada muestra. Figura 2 Microfotografías mostrando la detección de Acidobacterias. La técnica utilizada es FISH con la sonda de ADN propuesta ACIPHY631. A, fotografía utilizando luz de excitación verde con el colorante Cy3 unido a la sonda mencionada que muestra la presencia de los filamentos correspondientes a Acidobacterias. B, fotografía utilizando luz de excitación azul y el colorante SYBR Green I que tiñe inespecíficamente ADN mostrando todas las bacterias presentes en la muestra. C, fotografía en contraste de fases de la misma muestra de A y B. Las flechas indican las células de Acidobacteria a las que se dirigía la sonda. Descripción detallada de la invención Un objeto de la presente invención una secuencia aislada de nucleótidos útil para la detección, cuantificación y/o identificación de Acidobacterias que comprende la secuencia complementaria inversa a una secuencia parcial del gen ARN ribosómico 23S de Acidobacterias de ACIPHY631 o su complementaria, en adelante la secuencia. La invención se relaciona con el diseño de una secuencia de oligonucleótidos dirigida a detectar específicamente las Acidobacterias en cualquier tipo de muestra. Este oligonucleótido utiliza una secuencia única del gen ARN ribosómico 23S de estos microorganismos y puede ser empleada como primers para la amplificación de fragmentos del gen ARN ribosómico 23S de las Acidobacterias (por PCR o cualquier otro método de amplificación de ácidos nucleicos), como sonda de ADN para análisis por FISH, o microarrays de ADN. Tras realizar análisis exhaustivos de las secuencias conocidas y otras obtenidas durante los experimentos, se ha observado que la utilización del gen de ARN ribosómico 23S proporciona una secuencia de mayor longitud que la del gen ARN ribosómico 16S y existe un gran número de posiciones en esta secuencia que ofrecen gran interés para el diseño de sondas de hibridación y oligómeros o primers para su amplificación. Estas secuencias han sido utilizadas para el diseño de primers que permiten la amplificación de fragmentos del gen de ARN ribosómico 23S de Acidobacterias y de sondas de ADN que marcadas con colorantes fluorescentes sirven para la rápida detección de Acidobacterias en cualquier tipo de muestras. Constituye por tanto otro objeto de la presente invención, una sonda de ácido nucleico que comprende la secuencia mencionada anteriormente. Utilizando la secuencia y sonda propuesta en la presente invención se puede detectar y distinguir cualquier Acidobacteria entre un grupo de microorganismos. TABLA 1 Secuencia de oligonucleótidos propuesta y localización en el gen ARN ribosómico 23S de Acidobacterium capsulatum 6 Constituye, asimismo, otro objeto de la presente invención un kit de detección, cuantificación y/o identificación de Acidobacterias caracterizado porque comprende la secuencia o sonda de mencionada anteriormente. Otro objeto de la invención lo constituye un método de detección, cuantificación, e identificación de Acidobacterias en el que se utiliza la secuencia, o una sonda, o un kit mencionado anteriormente. 4
5 Otro aspecto de la presente invención se relaciona con la utilización de la secuencia, o sonda, o kit, objeto de la presente invención, en la detección, identificación y/o cuantificación de Acidobacterias en cualquier tipo de muestras, preferentemente en muestras ambientales, biológicas y/o médicas. Ejemplo de realización de la invención Ejemplo Detección de la presencia de Acidobacterias tras amplificación por PCR de fragmentos del gen ARN ribosómico 23S a partir de muestras ambientales Una muestra de la pared de la cueva de Altamira se recogió en un tubo de 1. ml estéril. La muestra se congeló hasta su posterior análisis. Se extrajo el ADN con el kit dé extracción Nucleospin food (Macherey-Nagel, Alemania). Un microlitro de la solución de ADN se utilizó en una reacción de PCR siguiendo el procedimiento estandard. Se utilizó la taq ADN polimerasa Extaq (Takara) y las condiciones recomendadas para esta enzima en su manual de utilización. Los primers utilizados fueron el oligonucleótido propuesto ACIPHY631 en la presente invención (Tabla 1) específico para Acidobacterias y el primer universal 616F ( - AGA GTT TGA TYM TGG CTC AG). Se ensayaron una muestra positiva (con Acidobacterias) y otra negativa (sin Acidobacterias). Los productos de amplificación se observaron en geles de agarosa (1.% agarosa en TAE 0.x) siguiendo procedimientos establecidos en laboratorios de Biología Molecular. Los resultados se muestran en la Figura 1. Se observa que la presencia de Acidobacterias se revela por la obtención de un producto de PCR del tamaño esperado (muestra positiva) mientras que la ausencia de Acidobacterias (o presencia por debajo del nivel de detección) resulta en la ausencia de producto de amplificación y por tanto en la ausencia de la banda esperada (muestra negativa) en el gel de agarosa. Así, queda demostrada la utilidad del oligonucleótido propuesto en la detección de Acidobacterias. Ejemplo 2 Detección de Acidobacterias por FISH utilizando el oligonucleótido propuesto como sonda de ADN 3 4 Una muestra de la pared de la cueva de Altamira se recogió en un tubo de 1. ml estéril. La muestra se suspendió en paraformaldehido (PFA) al 4% y se mantuvo a 4ºC durante 4 horas. Se centrifugó a.000 x g durante minutos, se retiró el sobrenadante y se suspendió en solución de PBS (Phosphate Buffered Solution). El PBS se eliminó tras centrifugación, la muestra se resuspendió nuevamente en PBS y se almacenó a -ºC hasta que fue hibridada a las sondas fluorescentes. La preparación de la muestra sobre un portaobjetos y su hibridación con una sonda de ADN marcada fluorescentemente se realizó tal y como lo describió Zimmermann et al. (01) siguiendo el protocolo estandard para FISH. La astringencia idónea para cada sonda de ADN se obtuvo tras comparar el mismo procedimiento llevado a cabo a distintas concentraciones de formamida tal y como ha sido previamente descrito (por ejemplo, Zimmermann et al. 01). La observación de las muestras hibridadas se realizó con un microscopio de epifluorescencia Zeiss Axiophot. La sonda diseñada fue sintetizada con el marcaje fluorescente Cy3 por Thermos Corporation (Alemania). La secuencia de nucleótidos correspondiente a la sonda utilizada (ACIPHY631) se muestra en la Tabla 1. Este ejemplo demuestra que con la sonda utilizada podemos detectar Acidobacterias in situ por microscopía. 0 6
6 REIVINDICACIONES Secuencia aislada de nucleótidos útil para la detección, cuantificación y/o identificación de Acidobacterias caracterizada porque comprende la secuencia complementaria inversa a una secuencia parcial del gen ARN ribosómico 23S de Acidobacterias de SEQ ACIPHY631 (SEQ.ID.NO1) o su complementaria. 2. Sonda de ácido nucleico útil para la detección, cuantificación y/o identificación de Acidobacterias caracterizada porque comprende al menos una secuencia de nucleótidos según la reivindicación Kit útil para la detección, cuantificación y/o identificación de Acidobacterias caracterizado porque comprende al menos una secuencia según la reivindicación Kit de detección, cuantificación y/o identificación de Acidobacterias caracterizado porque comprende al menos una sonda según la reivindicación 2.. Método de detección, cuantificación, e identificación de Acidobacterias caracterizado porque utiliza al menos una secuencia según la reivindicación 1, o una sonda según la reivindicación 2, o un kit según las reivindicaciones 3 y Utilización de una o más secuencias según la reivindicación 1 como cebador o primer, para la amplificación, secuenciación y/o hibridación de secuencias de Acidobacterias. 7. Utilización de una o más secuencias según la reivindicación 1 como cebador o primer, en reacciones de PCR u otras reacciones de amplificación, FISH, micro y macroarrays. 8. Utilización de una o más secuencias según la reivindicación 1 para la detección, identificación y/o cuantificación de Acidobacterias en cualquier tipo de muestras. 9. Utilización de una o más sondas o cebadores (primers) según la reivindicación 2 para la detección y/o cuantificación de Acidobacterias.. Utilización de un kit según las reivindicaciones 3 y 4 para la detección, cuantificación y/o la identificación precisa de Acidobacterias. 11. Utilización de un kit según las reivindicaciones 3 y 4 caracterizada porque la detección, cuantificación y/o identificación de Acidobacterias se lleva a cabo en muestras ambientales, biológicas y/o médicas
7 7
8 8
9 <1> Consejo Superior de Investigacines Científicas LISTA DE SECUENCIAS <1> OLIGONUCLEÓTIDOS DIRIGIDOS AL ARN RIBOSÓMICO 23S DE ACIDOBACTERIAS. SU UTILI- ZACIÓN COMO PRIMER O SONDA EN PROCEDIMIENTOS DE DETECCIÓN <1> oligonucleótidos de Acidobacterias ARN ribosómico 23S <1> 22 1 <170> PatentIn version 3.1 <2> 1 <211> 18 <212> DNA <213> División Acidobacteria <0> 1 2 aactagccrg ctcattat
10 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 ES Nº de solicitud: Fecha de presentación de la solicitud: Fecha de prioridad: INFORME SOBRE EL ESTADO DE LA TÉCNICA 1 Int. Cl.: C12Q 1/68 (06.01) DOCUMENTOS RELEVANTES Categoría Documentos citados Reivindicaciones afectadas X ZIMMERMANN, J., GONZALEZ, J. M., SAIZ-JIMENEZ, C. Detection and 1-11 phylogenetic relationships of highly diverse uncultured Acidobacerial communities in Altamira Cave using 23S rrna sequence analyses. Geomicrobiology Journal. Octubre-Noviembre 0, Vol. 22, Nº 7-8, páginas ISSN X LUDWIG, W., DORN, S., SPRINGER, N. et al. PCR-based preparation 1-11 of 23S rrna-targeted group-specific polynucleotide probes. Applied and Environmental Microbiology. Septiembre 1994, Vol., Nº 9, páginas ISSN A PANKRATOV, T. A., BELOVA, S. E., DEDYSH, S. N. Evaluation of the 1-11 phylogenetic diversity of prokaryotic microorganisms in Sphagnum peat bogs by means of fluorescence in situ hybridization (FISH). Microbiology. Noviembre 0, Vol. 74, Nº 6, páginas ISSN Categoría de los documentos citados X: de particular relevancia Y: de particular relevancia combinado con otro/s de la misma categoría A: refleja el estado de la técnica El presente informe ha sido realizado para todas las reivindicaciones O: referido a divulgación no escrita P: publicado entre la fecha de prioridad y la de presentación de la solicitud E: documento anterior, pero publicado después de la fecha de presentación de la solicitud para las reivindicaciones nº: Fecha de realización del informe Examinador Página E. Relaño Reyes 1/1
Nuevos paneles de PCR Real Time: El diagnóstico molecular más rápido, fiable y eficaz
 IDEXX VetLab Suite IDEXX SNAP Tests Laboratorio de Referencia IDEXX Nuevos paneles de PCR Real Time: El diagnóstico molecular más rápido, fiable y eficaz Obtenga respuestas definitivas con la IDEXX RealPCR
IDEXX VetLab Suite IDEXX SNAP Tests Laboratorio de Referencia IDEXX Nuevos paneles de PCR Real Time: El diagnóstico molecular más rápido, fiable y eficaz Obtenga respuestas definitivas con la IDEXX RealPCR
CUESTIONES. 1. Por qué la PCR convencional no es cuantitativa?
 2º BIOQUÍMICA CUESTIONES 1. Por qué la PCR convencional no es cuantitativa? En la PCR convencional, la cuantificación del ADN de la muestra es complicada debido a que la eficacia de amplificación va disminuyendo
2º BIOQUÍMICA CUESTIONES 1. Por qué la PCR convencional no es cuantitativa? En la PCR convencional, la cuantificación del ADN de la muestra es complicada debido a que la eficacia de amplificación va disminuyendo
PCR gen 18S ARNr humano
 PCR gen 18S ARNr humano Ref.PCR18S 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa (PCR)
PCR gen 18S ARNr humano Ref.PCR18S 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa (PCR)
TÉCNICAS GENÓMICAS. 2) Cuantificación del número de virus presentes en muestras de sangre o suero: carga vírica
 TÉCNICAS GENÓMICAS Utilidad/Objetivos: 1) Detección de microorganismos directamente en muestras clínicas identificando un fragmento específico del genoma del microorganismo concreto 2) Cuantificación del
TÉCNICAS GENÓMICAS Utilidad/Objetivos: 1) Detección de microorganismos directamente en muestras clínicas identificando un fragmento específico del genoma del microorganismo concreto 2) Cuantificación del
PCR. Componentes del PCR. PCR Polymerase Chain Reaction (Reacción en Cadena de la Polimerasa)
 PCR PCR Polymerase Chain Reaction (Reacción en Cadena de la Polimerasa) Es una técnica de biología molecular descrita en 1986 por Kary Mullis. (Nobel de química en 1993) Necesidad de pruebas de diagnóstico
PCR PCR Polymerase Chain Reaction (Reacción en Cadena de la Polimerasa) Es una técnica de biología molecular descrita en 1986 por Kary Mullis. (Nobel de química en 1993) Necesidad de pruebas de diagnóstico
Practica la genética Ficha didáctica del profesorado Bachillerato
 Ficha didáctica del profesorado Bachillerato www.eurekamuseoa.es Extracción de ADN Cuál es la función de cada uno de los ingredientes utilizados para realizar la disolución tampón para la visualización
Ficha didáctica del profesorado Bachillerato www.eurekamuseoa.es Extracción de ADN Cuál es la función de cada uno de los ingredientes utilizados para realizar la disolución tampón para la visualización
Identificación varietal en vid por técnicas de Biología Molecular. Lic. Luciana Garcia Lic. Carolina Chiconofri
 Identificación varietal en vid por técnicas de Biología Molecular. Lic. Luciana Garcia Lic. Carolina Chiconofri OBJETIVO Desarrollar un banco de datos a partir de plantas de origen indudable y del uso
Identificación varietal en vid por técnicas de Biología Molecular. Lic. Luciana Garcia Lic. Carolina Chiconofri OBJETIVO Desarrollar un banco de datos a partir de plantas de origen indudable y del uso
Int. Cl. 7 : A63F 9/18
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 1 41 21 k Número de solicitud: 00001 1 k Int. Cl. 7 : A63F 9/18 H04Q 7/22 k 12 SOLICITUD DE PATENTE A1 22 kfecha de presentación:.02.00
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 1 41 21 k Número de solicitud: 00001 1 k Int. Cl. 7 : A63F 9/18 H04Q 7/22 k 12 SOLICITUD DE PATENTE A1 22 kfecha de presentación:.02.00
7.012 Serie de ejercicios 5
 Nombre Grupo 7.012 Serie de ejercicios 5 Pregunta 1 Al estudiar los problemas de esterilidad, usted intenta aislar un hipotético gen de conejo que explique la prolífica reproducción de estos animales.
Nombre Grupo 7.012 Serie de ejercicios 5 Pregunta 1 Al estudiar los problemas de esterilidad, usted intenta aislar un hipotético gen de conejo que explique la prolífica reproducción de estos animales.
El Banco Nacional de ADN oferta un control de calidad de muestras de ADN y ARN.
 PROGRAMA CONTROL DE CALIDAD DE MUESTRAS El Banco Nacional de ADN oferta un control de calidad de muestras de ADN y ARN. El programa completo de control de calidad de muestras de ADN y ARN engloba diferentes
PROGRAMA CONTROL DE CALIDAD DE MUESTRAS El Banco Nacional de ADN oferta un control de calidad de muestras de ADN y ARN. El programa completo de control de calidad de muestras de ADN y ARN engloba diferentes
Int. Cl. 6 : B42D 15/10. k 71 Solicitante/s: Juan Antonio García Geira. k 72 Inventor/es: García Geira, Juan Antonio
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 117 949 21 k Número de solicitud: 9601769 1 k Int. Cl. 6 : B42D 1/10 k 12 SOLICITUD DE PATENTE A1 k 22 Fecha de presentación:
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 117 949 21 k Número de solicitud: 9601769 1 k Int. Cl. 6 : B42D 1/10 k 12 SOLICITUD DE PATENTE A1 k 22 Fecha de presentación:
ES 2 302 587 A1 H04Q 7/22 (2006.01) G06F 9/445 (2006.01) OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA. 11 Número de publicación: 2 302 587
 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 302 587 21 Número de solicitud: 200503019 51 Int. Cl.: H04Q 7/22 (2006.01) G06F 9/445 (2006.01) 12 SOLICITUD DE PATENTE A1 22
19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 302 587 21 Número de solicitud: 200503019 51 Int. Cl.: H04Q 7/22 (2006.01) G06F 9/445 (2006.01) 12 SOLICITUD DE PATENTE A1 22
DETERMINACIÓN DEL FACTOR Rh por PCR
 Ref.PCRRh DETERMINACIÓN DEL FACTOR Rh por PCR 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa
Ref.PCRRh DETERMINACIÓN DEL FACTOR Rh por PCR 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa
APLICACIÓN DE LA PCR: DIAGNÓSTICO DE PARÁSITOS
 Prácticas docentes en la COD: 10-71 APLICACIÓN DE LA PCR: DIAGNÓSTICO DE PARÁSITOS FUNDAMENTO TEÓRICO La PCR es una técnica que permite llevar a cabo la síntesis in vitro de fragmentos de ADN. Está basada
Prácticas docentes en la COD: 10-71 APLICACIÓN DE LA PCR: DIAGNÓSTICO DE PARÁSITOS FUNDAMENTO TEÓRICO La PCR es una técnica que permite llevar a cabo la síntesis in vitro de fragmentos de ADN. Está basada
APLICADAS A LA ECOLOGÍA MICROBIANA
 TÉCNICAS MOLECULARES APLICADAS A LA ECOLOGÍA MICROBIANA Áreas de estudio tradicionales en la Ecología Microbiana: - Estudio de la diversidad microbiana, incluye aislamiento, identificación y cuantificación
TÉCNICAS MOLECULARES APLICADAS A LA ECOLOGÍA MICROBIANA Áreas de estudio tradicionales en la Ecología Microbiana: - Estudio de la diversidad microbiana, incluye aislamiento, identificación y cuantificación
Easy PDF Creator is professional software to create PDF. If you wish to remove this line, buy it now.
 Unidad Curricular: Virología y Micología Veterinaria 1 TRABAJO PRÁCTICO No. 3 AMPLIFICACIÓN DE GENES VIRALES Reacción en Cadena de la Polimerasa, conocida como PCR (por sus siglas en inglés: Polimerase
Unidad Curricular: Virología y Micología Veterinaria 1 TRABAJO PRÁCTICO No. 3 AMPLIFICACIÓN DE GENES VIRALES Reacción en Cadena de la Polimerasa, conocida como PCR (por sus siglas en inglés: Polimerase
Técnicas de Biología Molecular
 Técnicas de Biología Molecular DNA I. Enzimas de restricción Análisis Las enzimas de restricción fueron aisladas de bacterias; su función natural es proteger contra DNA extraño II. Separación electroforética
Técnicas de Biología Molecular DNA I. Enzimas de restricción Análisis Las enzimas de restricción fueron aisladas de bacterias; su función natural es proteger contra DNA extraño II. Separación electroforética
11 Número de publicación: 2 288 447. 21 Número de solicitud: 200702102. 51 Int. Cl.: 72 Inventor/es: Cabre Roige, Luis
 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 288 447 21 Número de solicitud: 200702102 51 Int. Cl.: A01G 9/02 (2006.01) A01G 27/04 (2006.01) 12 SOLICITUD DE PATENTE A2 22
19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 288 447 21 Número de solicitud: 200702102 51 Int. Cl.: A01G 9/02 (2006.01) A01G 27/04 (2006.01) 12 SOLICITUD DE PATENTE A2 22
METODOLOGÍAS UTILIZADAS EN INVESTIGACIÓN BÁSICA Y APLICADA REACCION EN CADENA DE LA POLIMERASA (PCR)
 METODOLOGÍAS UTILIZADAS EN INVESTIGACIÓN BÁSICA Y APLICADA REACCION EN CADENA DE LA POLIMERASA (PCR) Centro de de Microscopía Electrónica Facultad de de Ciencias Médicas Universidad Nacional de de Córdoba
METODOLOGÍAS UTILIZADAS EN INVESTIGACIÓN BÁSICA Y APLICADA REACCION EN CADENA DE LA POLIMERASA (PCR) Centro de de Microscopía Electrónica Facultad de de Ciencias Médicas Universidad Nacional de de Córdoba
Detección de patógenos en alimentos, utilizando la técnica de PCR, reacción en cadena de la polimerasa.
 Detección de patógenos en alimentos, utilizando la técnica de PCR, reacción en cadena de la polimerasa. Lic. Esp. Mariano Diego Massari 1er Congreso Bioquímico Córdoba 2011 8ª Jornada de Actualización
Detección de patógenos en alimentos, utilizando la técnica de PCR, reacción en cadena de la polimerasa. Lic. Esp. Mariano Diego Massari 1er Congreso Bioquímico Córdoba 2011 8ª Jornada de Actualización
MICRO 06. OTRAS TÉCNICAS DE DIAGNÓSTICO MICROBIOLÓGICO. ESPECTROMETRÍA DE MASAS CON TECNOLOGÍA MALDI-TOF PARA LA IDENTIFICACIÓN MICROBIANA
 MICRO 06. OTRAS TÉCNICAS DE DIAGNÓSTICO MICROBIOLÓGICO. ESPECTROMETRÍA DE MASAS CON TECNOLOGÍA MALDI-TOF PARA LA IDENTIFICACIÓN MICROBIANA I. DEFINICIÓN II. III. FUNDAMENTO METODOLOGÍA 1 I. DEFINICIÓN
MICRO 06. OTRAS TÉCNICAS DE DIAGNÓSTICO MICROBIOLÓGICO. ESPECTROMETRÍA DE MASAS CON TECNOLOGÍA MALDI-TOF PARA LA IDENTIFICACIÓN MICROBIANA I. DEFINICIÓN II. III. FUNDAMENTO METODOLOGÍA 1 I. DEFINICIÓN
Int. Cl. 7 : B28B 7/22
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 161 621 21 k Número de solicitud: 00990196 1 k Int. Cl. 7 : B28B 7/22 B28B 7/36 k 12 SOLICITUD DE PATENTE A1 22 kfecha de
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 161 621 21 k Número de solicitud: 00990196 1 k Int. Cl. 7 : B28B 7/22 B28B 7/36 k 12 SOLICITUD DE PATENTE A1 22 kfecha de
PCR en Tiempo Real. Introducción
 Introducción Página 1 de 6 Introducción general La reacción en cadena de la polimerasa, cuyas iniciales en inglés son PCR ("polymerase chain reaction"), es una técnica que fue desarrollada por Kary Mullis
Introducción Página 1 de 6 Introducción general La reacción en cadena de la polimerasa, cuyas iniciales en inglés son PCR ("polymerase chain reaction"), es una técnica que fue desarrollada por Kary Mullis
3. COMPONENTES. Tampón de electroforesis concentrado 2 x 50 ml 10 X (2 envases 500ml)
 PCR SIMULADA Ref.PCR Simulada (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa
PCR SIMULADA Ref.PCR Simulada (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa
Int. Cl. 7 : A63H 29/22
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 177 43 21 k Número de solicitud: 20000293 1 k Int. Cl. 7 : A63H 29/22 A63H 17/26 A63H 18/12 k 12 SOLICITUD DE PATENTE A1
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 177 43 21 k Número de solicitud: 20000293 1 k Int. Cl. 7 : A63H 29/22 A63H 17/26 A63H 18/12 k 12 SOLICITUD DE PATENTE A1
TaqMan GMO Maize Quantification Kit. Part No: 4481972
 TaqMan GMO Maize Quantification Kit Part No: 4481972 1. Introducción Los organismos modificados genéticamente (OMG) se encuentran ampliamente distribuidos, siendo la soja y el maíz los vegetales que ocupan
TaqMan GMO Maize Quantification Kit Part No: 4481972 1. Introducción Los organismos modificados genéticamente (OMG) se encuentran ampliamente distribuidos, siendo la soja y el maíz los vegetales que ocupan
AQUAGESTION. ISAv: Un acercamiento actualizado en la detección de sus variantes en la región. Departamento de Desarrollo y Laboratorio Diagnóstico.
 AQUAGESTION ISAv: Un acercamiento actualizado en la detección de sus variantes en la región. Departamento de Desarrollo y Laboratorio Diagnóstico. Noviembre 2011 ACTUALIDAD Este año Sernapesca confirma
AQUAGESTION ISAv: Un acercamiento actualizado en la detección de sus variantes en la región. Departamento de Desarrollo y Laboratorio Diagnóstico. Noviembre 2011 ACTUALIDAD Este año Sernapesca confirma
ES 2 146 184 A1. Número de publicación: 2 146 184 PATENTES Y MARCAS. Número de solicitud: 009802270. Int. Cl. 7 : A62C 27/00
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 146 184 21 k Número de solicitud: 009802270 51 k Int. Cl. 7 : A62C 27/00 k 12 SOLICITUD DE PATENTE A1 k 22 Fecha de presentación:
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 146 184 21 k Número de solicitud: 009802270 51 k Int. Cl. 7 : A62C 27/00 k 12 SOLICITUD DE PATENTE A1 k 22 Fecha de presentación:
PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN DE LAS COMPETENCIAS PROFESIONALES CUESTIONARIO DE AUTOEVALUACIÓN PARA LAS TRABAJADORAS Y TRABAJADORES
 MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
Técnicas moleculares.
 Técnicas moleculares. DMTV Carolina Acevedo Curso de Microbiología 2015 SÍNTESIS IN VITRO DE UNA GRAN CANTIDAD DE COPIAS DE UN SEGMENTO DE ADN EXISTENTE EN UNA MUESTRA. O sea. Amplificamos en forma exponencial
Técnicas moleculares. DMTV Carolina Acevedo Curso de Microbiología 2015 SÍNTESIS IN VITRO DE UNA GRAN CANTIDAD DE COPIAS DE UN SEGMENTO DE ADN EXISTENTE EN UNA MUESTRA. O sea. Amplificamos en forma exponencial
Int. Cl. 7 : A01G 25/02
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 184 605 21 k Número de solicitud: 200100858 51 k Int. Cl. 7 : A01G 25/02 A01G 25/06 k 12 SOLICITUD DE PATENTE A1 22 kfecha
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 184 605 21 k Número de solicitud: 200100858 51 k Int. Cl. 7 : A01G 25/02 A01G 25/06 k 12 SOLICITUD DE PATENTE A1 22 kfecha
ES 2 264 860 A1 G07C 9/00 (2006.01) H04M 1/725 (2006.01) H04M 11/00 (2006.01) OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA
 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 264 860 21 Número de solicitud: 200402000 51 Int. Cl.: G07C 9/00 (2006.01) H04M 1/725 (2006.01) H04M 11/00 (2006.01) 12 SOLICITUD
19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 264 860 21 Número de solicitud: 200402000 51 Int. Cl.: G07C 9/00 (2006.01) H04M 1/725 (2006.01) H04M 11/00 (2006.01) 12 SOLICITUD
ES 2 192 897 A1 B42F 5/00. Número de publicación: 2 192 897 PATENTES Y MARCAS. Número de solicitud: 200000528. Int. Cl. 7 : B42D 1/08 16.10.
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 192 897 21 k Número de solicitud: 200000528 51 k Int. Cl. 7 : B42D 1/08 B42F 5/00 k 12 SOLICITUD DE PATENTE A1 22 kfecha
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 192 897 21 k Número de solicitud: 200000528 51 k Int. Cl. 7 : B42D 1/08 B42F 5/00 k 12 SOLICITUD DE PATENTE A1 22 kfecha
EN LA LA EMPRESA EMPRESA
 PANEL DE OPINIÓN Nº 6 NIVELDE FORMACIÓN EN LA LA EMPRESA EMPRESA ESPAÑOLA RESULTADOSGenerales Más del 6 de las s que necesitan personal formado en idiomas detectan carencias sobre este aspecto en los candidatos
PANEL DE OPINIÓN Nº 6 NIVELDE FORMACIÓN EN LA LA EMPRESA EMPRESA ESPAÑOLA RESULTADOSGenerales Más del 6 de las s que necesitan personal formado en idiomas detectan carencias sobre este aspecto en los candidatos
ES 2 187 295 A1 G06F 17/60. Número de publicación: 2 187 295 PATENTES Y MARCAS. Número de solicitud: 200102423. Int. Cl. 7 : G06F 19/00 16.05.
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 187 29 21 k Número de solicitud: 200102423 1 k Int. Cl. 7 : G06F 19/00 G06F 17/60 k 12 SOLICITUD DE PATENTE A1 22 kfecha
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 187 29 21 k Número de solicitud: 200102423 1 k Int. Cl. 7 : G06F 19/00 G06F 17/60 k 12 SOLICITUD DE PATENTE A1 22 kfecha
11 Número de publicación: 2 284 312. 21 Número de solicitud: 200500732. 51 Int. Cl.: 72 Inventor/es: Gubertini Ciriza, Raúl
 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 284 312 21 Número de solicitud: 200500732 51 Int. Cl.: B65F 1/00 (2006.01) 12 PATENTE DE INVENCIÓN B1 22 Fecha de presentación:
19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 284 312 21 Número de solicitud: 200500732 51 Int. Cl.: B65F 1/00 (2006.01) 12 PATENTE DE INVENCIÓN B1 22 Fecha de presentación:
11 Número de publicación: 2 229 868. 21 Número de solicitud: 200202865. 51 Int. Cl. 7 : A01K 23/00. 72 Inventor/es: Balliu Falgueras, Carme
 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 229 868 21 Número de solicitud: 200202865 51 Int. Cl. 7 : A01K 23/00 12 SOLICITUD DE PATENTE A1 22 Fecha de presentación: 13.12.2002
19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 229 868 21 Número de solicitud: 200202865 51 Int. Cl. 7 : A01K 23/00 12 SOLICITUD DE PATENTE A1 22 Fecha de presentación: 13.12.2002
Biotecnología. Historia y aplicaciones Su utilización en el INTA Alto Valle. investigación
 Alejandro Giayetto Técnico INTA agiayetto@correo.inta.gov.ar Mirta Rossini Técnico INTA mrossini@correo.inta.gov.ar Diana Vera Biotecnóloga labfitopatologia@correo.inta.gov.ar investigación 10 Biotecnología
Alejandro Giayetto Técnico INTA agiayetto@correo.inta.gov.ar Mirta Rossini Técnico INTA mrossini@correo.inta.gov.ar Diana Vera Biotecnóloga labfitopatologia@correo.inta.gov.ar investigación 10 Biotecnología
PRUEBA RAPIDA EN EMBARAZADAS (n=62,214 2009-Junio 2010) NO REACTIVO n=218 REACTIVO INDETERMINADO. Tabla 9: Resultados Prueba rápida
 11-RESULTADOS 11.1-Interpretación y análisis de resultados Un total de de 62,214 mujeres embarazadas se realizaron la prueba rápida de VIH durante años 2009 hasta junio 2010 (Tabla 9). De ellas, 61,808
11-RESULTADOS 11.1-Interpretación y análisis de resultados Un total de de 62,214 mujeres embarazadas se realizaron la prueba rápida de VIH durante años 2009 hasta junio 2010 (Tabla 9). De ellas, 61,808
PRINCIPIOS DE LAS INVESTIGACIONES EPIDEMIOLOGICAS Y MEDICIÓN DE EFECTO-CAUSALIDAD PROGRAMA
 PRINCIPIOS DE LAS INVESTIGACIONES EPIDEMIOLOGICAS Y MEDICIÓN DE EFECTO-CAUSALIDAD Curso: 25 Hrs. Asistentes: 25 Costo: $15,000 (Quince Mil Pesos 00/100 M.N) OBJETIVO: Conocer algunos conceptos básicos
PRINCIPIOS DE LAS INVESTIGACIONES EPIDEMIOLOGICAS Y MEDICIÓN DE EFECTO-CAUSALIDAD Curso: 25 Hrs. Asistentes: 25 Costo: $15,000 (Quince Mil Pesos 00/100 M.N) OBJETIVO: Conocer algunos conceptos básicos
La PCR. La Reacción en Cadena de la Polimerasa es la herramienta más utilizada
 La PCR La Reacción en Cadena de la Polimerasa es la herramienta más utilizada PCR- Ventajas y Usos Amplificación ilimitada de secuencias de interés. Rápida, Sencilla y Eficaz. Técnica altamente sensible
La PCR La Reacción en Cadena de la Polimerasa es la herramienta más utilizada PCR- Ventajas y Usos Amplificación ilimitada de secuencias de interés. Rápida, Sencilla y Eficaz. Técnica altamente sensible
PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN DE LAS COMPETENCIAS PROFESIONALES CUESTIONARIO DE AUTOEVALUACIÓN PARA LAS TRABAJADORAS Y TRABAJADORES
 MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
MINISTERIO DE EDUCACIÓN SECRETARÍA DE ESTADO DE EDUCACIÓN Y FORMACIÓN PROFESIONAL DIRECCIÓN GENERAL DE FORMACIÓN PROFESIONAL INSTITUTO NACIONAL DE LAS CUALIFICACIONES PROCEDIMIENTO DE EVALUACIÓN Y ACREDITACIÓN
Int. Cl. 7 : A62C 13/00
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 149 67 21 k Número de solicitud: 009800216 1 k Int. Cl. 7 : A62C 13/00 A62C 13/62 A62C 13/76 k 12 SOLICITUD DE PATENTE A1
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 149 67 21 k Número de solicitud: 009800216 1 k Int. Cl. 7 : A62C 13/00 A62C 13/62 A62C 13/76 k 12 SOLICITUD DE PATENTE A1
Reacción en cadena de la polimerasa (PCR)
 Dr. Alejandro Leal Reacción en cadena de la polimerasa (PCR) La reacción en cadena de la polimerasa (PCR, por sus siglas en inglés de "polymerase chain reaction") es un método de amplificación in vitro
Dr. Alejandro Leal Reacción en cadena de la polimerasa (PCR) La reacción en cadena de la polimerasa (PCR, por sus siglas en inglés de "polymerase chain reaction") es un método de amplificación in vitro
11.2-DISCUSIÓN Prueba rápida
 11.2-DISCUSIÓN Prueba rápida Como se observa en la tabla 9 del total de las embarazadas (62,214) a las que se les realizo la prueba rápida un 99.3%(61,808) de ellas dio como resultado no reactivo, tan
11.2-DISCUSIÓN Prueba rápida Como se observa en la tabla 9 del total de las embarazadas (62,214) a las que se les realizo la prueba rápida un 99.3%(61,808) de ellas dio como resultado no reactivo, tan
Código: IDX-016 Ver: 1 TOXO. Sistema para la detección de la presencia de ADN de Toxoplasma gondii. Reg. MSP 21205
 Sistema para la detección de la presencia de ADN de Toxoplasma gondii Reg. MSP 21205 Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336 71 60. info@atgen.com.uy www.atgen.com.uy
Sistema para la detección de la presencia de ADN de Toxoplasma gondii Reg. MSP 21205 Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336 71 60. info@atgen.com.uy www.atgen.com.uy
ES 2 257 890 A1 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA. 11 Número de publicación: 2 257 890. 21 Número de solicitud: 200202551
 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 257 890 21 Número de solicitud: 200202551 51 Int. Cl. 7 : F16H 29/14 12 SOLICITUD DE PATENTE A1 22 Fecha de presentación: 20.01.2005
19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 257 890 21 Número de solicitud: 200202551 51 Int. Cl. 7 : F16H 29/14 12 SOLICITUD DE PATENTE A1 22 Fecha de presentación: 20.01.2005
Int. Cl. 7 : A61C 3/00. k 71 Solicitante/s: CORPORACIÓN O.I.B., S.L. k 72 Inventor/es: Rodríguez del Val, José María
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 195 742 21 k Número de solicitud: 200102098 51 k Int. Cl. 7 : A61C 3/00 k 12 SOLICITUD DE PATENTE A1 k 22 Fecha de presentación:
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 195 742 21 k Número de solicitud: 200102098 51 k Int. Cl. 7 : A61C 3/00 k 12 SOLICITUD DE PATENTE A1 k 22 Fecha de presentación:
- Clonar un gen (molde ADN o ARN)
 APLICACIONES PCR Aplicaciones de la PCR - Clonar un gen (molde ADN o ARN) - Secuencia conocida - Genes homólogos en especies próximas (primers degenerados) - Información de secuencia proteica (primers
APLICACIONES PCR Aplicaciones de la PCR - Clonar un gen (molde ADN o ARN) - Secuencia conocida - Genes homólogos en especies próximas (primers degenerados) - Información de secuencia proteica (primers
ES 2 197 008 A1. Número de publicación: 2 197 008 PATENTES Y MARCAS. Número de solicitud: 200201269. Int. Cl. 7 : A61D 19/02
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 197 008 21 k Número de solicitud: 200201269 1 k Int. Cl. 7 : A61D 19/02 k 12 SOLICITUD DE PATENTE A1 k 22 Fecha de presentación:
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 197 008 21 k Número de solicitud: 200201269 1 k Int. Cl. 7 : A61D 19/02 k 12 SOLICITUD DE PATENTE A1 k 22 Fecha de presentación:
INACTIVACIÓN DE LOS GENES SUPRESORES PTEN, DMBT1 Y P16 EN GLIOBLASTOMA MULTIFORME, ASTROCITOMAS ANAPLÁSICOS Y ASTROCITOMAS DE BAJO GRADO.
 IV CONGRESO VIRTUAL HISPANO AMERICANO DE ANATOMÍA PATOLÓGICA Abstract PDF CONTENIDO Comentarios Título Resumen Introducción Material Resultados Conclusiones Imágenes INACTIVACIÓN DE LOS GENES SUPRESORES
IV CONGRESO VIRTUAL HISPANO AMERICANO DE ANATOMÍA PATOLÓGICA Abstract PDF CONTENIDO Comentarios Título Resumen Introducción Material Resultados Conclusiones Imágenes INACTIVACIÓN DE LOS GENES SUPRESORES
Int. Cl. 7 : A01N 57/06. 22 kfecha de presentación: 10.03.1999 71 k Solicitante/s: Rafael Rodríguez Ramos Apartado de Correos, 8.
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 164 18 21 k Número de solicitud: 009900490 1 k Int. Cl. 7 : A01N 7/06 A01N 37/34 k 12 SOLICITUD DE PATENTE A1 22 kfecha de
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 164 18 21 k Número de solicitud: 009900490 1 k Int. Cl. 7 : A01N 7/06 A01N 37/34 k 12 SOLICITUD DE PATENTE A1 22 kfecha de
TEST de PATERNIDAD. Ref.PCR paternidad (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO
 Ref.PCR paternidad (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO TEST de PATERNIDAD Este experimento introduce a los alumnos en el uso del ADN y la PCR para simular una determinación de paternidad. Los estudiantes
Ref.PCR paternidad (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO TEST de PATERNIDAD Este experimento introduce a los alumnos en el uso del ADN y la PCR para simular una determinación de paternidad. Los estudiantes
PROCEDIMIENTO PARA LA UTILIZACIÓN DEL POLIMORFISMO DEL GEN COMT (CATECOL-OXI-METILTRANSFERASA) EN EL DIAGNÓSTICO DEL SÍNDROME DE FIBROMIALGIA
 2 PROCEDIMIENTO PARA LA UTILIZACIÓN DEL POLIMORFISMO DEL GEN COMT (CATECOL-OXI-METILTRANSFERASA) EN EL DIAGNÓSTICO DEL SÍNDROME DE FIBROMIALGIA D E S C R I P C I Ó N OBJETO DE LA INVENCIÓN La presente
2 PROCEDIMIENTO PARA LA UTILIZACIÓN DEL POLIMORFISMO DEL GEN COMT (CATECOL-OXI-METILTRANSFERASA) EN EL DIAGNÓSTICO DEL SÍNDROME DE FIBROMIALGIA D E S C R I P C I Ó N OBJETO DE LA INVENCIÓN La presente
C02F 1/02 F28G 9/00 //A61L 11/00
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k N. de publicación: ES 2 060 38 21 k Número de solicitud: 9202661 1 k Int. Cl. : C02F 9/00 C02F 1/02 F28G 9/00 //A61L 11/00 k 12 SOLICITUD DE PATENTE
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k N. de publicación: ES 2 060 38 21 k Número de solicitud: 9202661 1 k Int. Cl. : C02F 9/00 C02F 1/02 F28G 9/00 //A61L 11/00 k 12 SOLICITUD DE PATENTE
ES 2 527 885 R1 ESPAÑA 11. Número de publicación: 2 527 885. Número de solicitud: 201490113
 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 21 Número de publicación: 2 527 885 Número de solicitud: 201490113 51 Int. CI.: C12N 1/12 (2006.01) C10L 1/02 (2006.01) C12P 7/64 (2006.01) C12R 1/89
19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 21 Número de publicación: 2 527 885 Número de solicitud: 201490113 51 Int. CI.: C12N 1/12 (2006.01) C10L 1/02 (2006.01) C12P 7/64 (2006.01) C12R 1/89
Int. Cl. 6 : C09D 195/00
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 137 870 21 k Número de solicitud: 009702302 51 k Int. Cl. 6 : C09D 195/00 C08L 95/00 B05D 1/34 E04B 1/64 //(C09D 107:02 C09D
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 137 870 21 k Número de solicitud: 009702302 51 k Int. Cl. 6 : C09D 195/00 C08L 95/00 B05D 1/34 E04B 1/64 //(C09D 107:02 C09D
PROBLEMAS MAS FRECUENTES DURANTE LA SECUENCIACIÓN NO SE PRODUCE REACCION O ESTA DECAE POCO DESPUÉS DE COMENZAR
 PROBLEMAS MAS FRECUENTES DURANTE LA SECUENCIACIÓN NO SE PRODUCE REACCION O ESTA DECAE POCO DESPUÉS DE COMENZAR Las causas pueden ser las siguientes: No hay ADN o se encuentra en muy baja concentración.
PROBLEMAS MAS FRECUENTES DURANTE LA SECUENCIACIÓN NO SE PRODUCE REACCION O ESTA DECAE POCO DESPUÉS DE COMENZAR Las causas pueden ser las siguientes: No hay ADN o se encuentra en muy baja concentración.
RESULTADOS Y DISCUSIÓN. Estimación de la Concentración Proteica del Filtrado de Cultivo de Mycobacterium tuberculosis H37Rv
 RESULTADOS Y DISCUSIÓN Estimación de la Concentración Proteica del Filtrado de Cultivo de Mycobacterium tuberculosis H37Rv La curva estándar con la que se estimó la concentración proteica del filtrado
RESULTADOS Y DISCUSIÓN Estimación de la Concentración Proteica del Filtrado de Cultivo de Mycobacterium tuberculosis H37Rv La curva estándar con la que se estimó la concentración proteica del filtrado
Plantilla de Buenas Prácticas
 Marzo 2014 Plantilla de Buenas Prácticas Definición de buenas prácticas Una buena práctica se puede definir del siguiente modo: Una buena práctica no es tan sólo una práctica que se define buena en sí
Marzo 2014 Plantilla de Buenas Prácticas Definición de buenas prácticas Una buena práctica se puede definir del siguiente modo: Una buena práctica no es tan sólo una práctica que se define buena en sí
Instituto de Biomedicina y Biotecnología de Cantabria (IBBTEC) SERVICIO DE SECUENCIACIÓN MASIVA
 1. DESCRIPCIÓN DEL SERVICIO El servicio de Secuenciación Masiva tiene como finalidad el proporcionar asesoramiento y soporte técnico a los grupos de investigación interesados en realizar proyectos de ultrasecuenciación.
1. DESCRIPCIÓN DEL SERVICIO El servicio de Secuenciación Masiva tiene como finalidad el proporcionar asesoramiento y soporte técnico a los grupos de investigación interesados en realizar proyectos de ultrasecuenciación.
Plantilla de buenas prácticas
 Plantilla de Buenas Prácticas Julio 2015 Plantilla de buenas prácticas Esta plantilla proporciona información básica cerca las buenas prácticas, incluso también un formulario (p.3) para rellenar y documentar
Plantilla de Buenas Prácticas Julio 2015 Plantilla de buenas prácticas Esta plantilla proporciona información básica cerca las buenas prácticas, incluso también un formulario (p.3) para rellenar y documentar
CAPÍTULO 6 6.1 CONCLUSIONES Y RECOMENDACIONES
 CAPÍTULO 6 6.1 CONCLUSIONES Y RECOMENDACIONES El trabajo de investigación presentado anteriormente tuvo como objetivo principal realizar un Plan de Negocios para la introducción exitosa al mercado de una
CAPÍTULO 6 6.1 CONCLUSIONES Y RECOMENDACIONES El trabajo de investigación presentado anteriormente tuvo como objetivo principal realizar un Plan de Negocios para la introducción exitosa al mercado de una
Programa donde se inscribe la beca y/o la tesis: Interacciones biológicas: de las
 Titulo: Potencial uso simultáneo de micopatógenos biocontroladores de hormigas cortadoras de hojas. Autores: Natalia G. Armando, Jorge A. Marfetán, Patricia J. Folgarait Correo: ng.armando14@gmail.com
Titulo: Potencial uso simultáneo de micopatógenos biocontroladores de hormigas cortadoras de hojas. Autores: Natalia G. Armando, Jorge A. Marfetán, Patricia J. Folgarait Correo: ng.armando14@gmail.com
Ensayos Clínicos en Oncología
 Ensayos Clínicos en Oncología Qué son y para qué sirven? www.seom.org ESP 05/04 ON4 Con la colaboración de: Una parte muy importante de la Investigación en Oncología Médica se realiza a través de Ensayos
Ensayos Clínicos en Oncología Qué son y para qué sirven? www.seom.org ESP 05/04 ON4 Con la colaboración de: Una parte muy importante de la Investigación en Oncología Médica se realiza a través de Ensayos
Int. Cl. 7 : B41L 1/22. 22 kfecha de presentación: 03.09.2003 71 k Solicitante/s: SIGNE, S.A. C/ Ceuta, 12-A 14 28804 Alcalá de Henares, Madrid, ES
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 199 089 21 k Número de solicitud: 200302066 1 k Int. Cl. 7 : B41L 1/22 B41L 1/36 B41M /03 B42F 1/12 B42D 11/00 k 12 SOLICITUD
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 199 089 21 k Número de solicitud: 200302066 1 k Int. Cl. 7 : B41L 1/22 B41L 1/36 B41M /03 B42F 1/12 B42D 11/00 k 12 SOLICITUD
PROYECTO MEDICINA PERSONALIZADA PARA EL CÁNCER INFANTIL CÁNCER INFANTIL. Javier Alonso
 Página: 1 de 8 PROYECTO MEDICINA PERSONALIZADA PARA EL Javier Alonso Jefe de Área de Genética Humana. Jefe de la Unidad de Tumores Sólidos Infantiles del Instituto de Investigación de Enfermedades Raras,
Página: 1 de 8 PROYECTO MEDICINA PERSONALIZADA PARA EL Javier Alonso Jefe de Área de Genética Humana. Jefe de la Unidad de Tumores Sólidos Infantiles del Instituto de Investigación de Enfermedades Raras,
Int. Cl. 6 : E03B 3/28
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k N. de publicación: ES 2 082 720 21 k Número de solicitud: 9401386 51 k Int. Cl. 6 : E03B 3/28 B01D 5/00 k 12 SOLICITUD DE PATENTE A1 22 kfecha de
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k N. de publicación: ES 2 082 720 21 k Número de solicitud: 9401386 51 k Int. Cl. 6 : E03B 3/28 B01D 5/00 k 12 SOLICITUD DE PATENTE A1 22 kfecha de
ES 2 170 023 A1. Número de publicación: 2 170 023 PATENTES Y MARCAS. Número de solicitud: 200002844. Int. Cl. 7 : A41C 5/00
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 170 023 21 k Número de solicitud: 200002844 51 k Int. Cl. 7 : A41C 5/00 k 12 SOLICITUD DE PATENTE A1 k 22 Fecha de presentación:
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 170 023 21 k Número de solicitud: 200002844 51 k Int. Cl. 7 : A41C 5/00 k 12 SOLICITUD DE PATENTE A1 k 22 Fecha de presentación:
! INVESTIGADORES! DEL! CNIO! ENCUENTRAN! DOS! POSIBLES! NUEVAS!ESTRATEGIAS!PARA!CURAR!LA!PSORIASIS!!!
 INVESTIGADORES DEL CNIO ENCUENTRAN DOS POSIBLES NUEVASESTRATEGIASPARACURARLAPSORIASIS Experimentos en ratones y muestras derivadas de pacientes sugieren que se podría actuar contra las dianas ahora identificadas
INVESTIGADORES DEL CNIO ENCUENTRAN DOS POSIBLES NUEVASESTRATEGIASPARACURARLAPSORIASIS Experimentos en ratones y muestras derivadas de pacientes sugieren que se podría actuar contra las dianas ahora identificadas
CONSENTIMIENTO INFORMADO PARA ANÁLISIS PRENATAL NO INVASIVO DE TRISOMÍAS FETALES
 Ejemplar para el Solicitante CONSENTIMIENTO INFORMADO PARA ANÁLISIS PRENATAL NO INVASIVO DE TRISOMÍAS FETALES Propósito El análisis prenatal no invasivo analiza ADN fetal libre, circulante en la sangre
Ejemplar para el Solicitante CONSENTIMIENTO INFORMADO PARA ANÁLISIS PRENATAL NO INVASIVO DE TRISOMÍAS FETALES Propósito El análisis prenatal no invasivo analiza ADN fetal libre, circulante en la sangre
ES 2 388 275 B1. Aviso: ESPAÑA 11. Número de publicación: 2 388 275. Número de solicitud: 201130353 H04B 7/00 (2006.01)
 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 21 Número de publicación: 2 388 27 Número de solicitud: 20113033 1 Int. CI.: H04B 7/00 (2006.01) 12 PATENTE DE INVENCIÓN B1 22 Fecha de presentación:
19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 21 Número de publicación: 2 388 27 Número de solicitud: 20113033 1 Int. CI.: H04B 7/00 (2006.01) 12 PATENTE DE INVENCIÓN B1 22 Fecha de presentación:
k 11 N. de publicación: ES 2 035 769 k 21 Número de solicitud: 9101028 k 51 Int. Cl. 5 : A23B 9/10
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA k 11 N. de publicación: ES 2 0 769 k 21 Número de solicitud: 928 k 1 Int. Cl. : A23B 9/ A23L 1/182 k 12 SOLICITUD DE PATENTE A1 22 kfecha de presentación:
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA k 11 N. de publicación: ES 2 0 769 k 21 Número de solicitud: 928 k 1 Int. Cl. : A23B 9/ A23L 1/182 k 12 SOLICITUD DE PATENTE A1 22 kfecha de presentación:
Contenidos. INFORME ENCUESTA TELEFÓNICA. Curso 2009 10
 ENCUESTA DE OPINIÓN DEL ALUMNADO SOBRE LA ACTUACIÓN DOCENTE DEL PROFESORADO UNIVERSIDAD DE SEVILLA Curso 2009-2010 ENCUESTA TELEFÓNICA Contenidos Introducción.... 4 El Cuestionario... 5 El muestreo...
ENCUESTA DE OPINIÓN DEL ALUMNADO SOBRE LA ACTUACIÓN DOCENTE DEL PROFESORADO UNIVERSIDAD DE SEVILLA Curso 2009-2010 ENCUESTA TELEFÓNICA Contenidos Introducción.... 4 El Cuestionario... 5 El muestreo...
PROBLEMAS MÁS FRECUENTES Y POSIBLES SOLUCIONES
 PROBLEMAS MÁS FRECUENTES Y POSIBLES SOLUCIONES NO SE PRODUCE REACCIÓN O ÉSTA DECAE POCO DESPUÉS DE COMENZAR No hay ADN o hay menos del necesario No hay cebador o la concentración es inferior a la necesaria.
PROBLEMAS MÁS FRECUENTES Y POSIBLES SOLUCIONES NO SE PRODUCE REACCIÓN O ÉSTA DECAE POCO DESPUÉS DE COMENZAR No hay ADN o hay menos del necesario No hay cebador o la concentración es inferior a la necesaria.
imegen Alfa-1-AT Manual de Usuario Referencia: IMG-211
 Manual de Usuario imegen Alfa-1-AT Genotipado de las mutaciones Glu342Lys (PI-Z) y Glu264Val (PI-S) del gen SERPINA1 mediante PCR a tiempo real Referencia: Fabricado en España Garantías y responsabilidades
Manual de Usuario imegen Alfa-1-AT Genotipado de las mutaciones Glu342Lys (PI-Z) y Glu264Val (PI-S) del gen SERPINA1 mediante PCR a tiempo real Referencia: Fabricado en España Garantías y responsabilidades
Revisión del Universo de empresas para la Estimación de los Datos Del Mercado Español de Investigación de Mercados y Opinión.
 Revisión del Universo de empresas para la Estimación de los Datos Del Mercado Español de Investigación de Mercados y Opinión. (Enrique Matesanz y Vicente Castellanos, Año 2011) Según la experiencia acumulada
Revisión del Universo de empresas para la Estimación de los Datos Del Mercado Español de Investigación de Mercados y Opinión. (Enrique Matesanz y Vicente Castellanos, Año 2011) Según la experiencia acumulada
TEMA 3: EN QUÉ CONSISTE?
 Módulo 7 Sesión 3 5/16 TEMA 3: EN QUÉ CONSISTE? La metodología seguida para aplicar correctamente la técnica de RGT se basa en cuatro fases (Figura 1). En la primera de ellas, se seleccionan los elementos
Módulo 7 Sesión 3 5/16 TEMA 3: EN QUÉ CONSISTE? La metodología seguida para aplicar correctamente la técnica de RGT se basa en cuatro fases (Figura 1). En la primera de ellas, se seleccionan los elementos
B23K 23/00 //E01B 29/42 B60M 5/00
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k N. de publicación: ES 2 036 42 21 k Número de solicitud: 91412 1 k Int. Cl. : H01R 4/02 B23K 23/00 //E01B 29/42 BM /00 k 12 SOLICITUD DE PATENTE A2
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k N. de publicación: ES 2 036 42 21 k Número de solicitud: 91412 1 k Int. Cl. : H01R 4/02 B23K 23/00 //E01B 29/42 BM /00 k 12 SOLICITUD DE PATENTE A2
Int. Cl. 7 : G04B 45/00. 22 kfecha de presentación: 12.03.1998 71 k Solicitante/s: GHESA INGENIERIA Y TECNOLOGIA, S.A. Magallanes, 3 28015 Madrid, ES
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 143 941 21 k Número de solicitud: 00980030 1 k Int. Cl. 7 : G04B 4/00 B0B 17/08 k 12 SOLICITUD DE PATENTE A1 22 kfecha de
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 143 941 21 k Número de solicitud: 00980030 1 k Int. Cl. 7 : G04B 4/00 B0B 17/08 k 12 SOLICITUD DE PATENTE A1 22 kfecha de
Int. Cl. 6 : E01C 5/22
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 132 010 21 k Número de solicitud: 960100 1 k Int. Cl. 6 : E01C /22 B28B 1/00 k 12 SOLICITUD DE PATENTE A1 22 kfecha de presentación:
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 132 010 21 k Número de solicitud: 960100 1 k Int. Cl. 6 : E01C /22 B28B 1/00 k 12 SOLICITUD DE PATENTE A1 22 kfecha de presentación:
Int. Cl. 6 : F16C 11/04
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 133 06 21 k Número de solicitud: 9601130 1 k Int. Cl. 6 : F16C 11/04 A61G 7/002 k 12 SOLICITUD DE PATENTE A1 22 kfecha de
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 133 06 21 k Número de solicitud: 9601130 1 k Int. Cl. 6 : F16C 11/04 A61G 7/002 k 12 SOLICITUD DE PATENTE A1 22 kfecha de
BIOTECNOLOGÍA. 1.- Ingeniería Genética, ADN recombinante
 BIOTECNOLOGÍA 1.- Ingeniería Genética, ADN recombinante Técnica del ADN recombinante: es la más usada en ingeniería genética, esta basada en el uso de las enzimas de restricción o endonucleasas de restricción
BIOTECNOLOGÍA 1.- Ingeniería Genética, ADN recombinante Técnica del ADN recombinante: es la más usada en ingeniería genética, esta basada en el uso de las enzimas de restricción o endonucleasas de restricción
ES 2 181 595 A1. Número de publicación: 2 181 595 PATENTES Y MARCAS. Número de solicitud: 200101432. Int. Cl. 7 : A61C 8/00
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 181 595 21 k Número de solicitud: 200101432 51 k Int. Cl. 7 : A61C 8/00 k 12 SOLICITUD DE PATENTE A1 k 22 Fecha de presentación:
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k Número de publicación: 2 181 595 21 k Número de solicitud: 200101432 51 k Int. Cl. 7 : A61C 8/00 k 12 SOLICITUD DE PATENTE A1 k 22 Fecha de presentación:
ANALIZANDO GRAFICADORES
 ANALIZANDO GRAFICADORES María del Carmen Pérez E.N.S.P.A, Avellaneda. Prov. de Buenos Aires Instituto Superior del Profesorado "Dr. Joaquín V. González" Buenos Aires (Argentina) INTRODUCCIÓN En muchos
ANALIZANDO GRAFICADORES María del Carmen Pérez E.N.S.P.A, Avellaneda. Prov. de Buenos Aires Instituto Superior del Profesorado "Dr. Joaquín V. González" Buenos Aires (Argentina) INTRODUCCIÓN En muchos
11 Número de publicación: 2 321 774. 21 Número de solicitud: 200600040. 51 Int. Cl.: 74 Agente: Urízar Anasagasti, Jesús María
 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 321 774 21 Número de solicitud: 200600040 51 Int. Cl.: H04W 88/00 (2009.01) G08B 23/00 (2006.01) 12 SOLICITUD DE PATENTE A1 22
19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 321 774 21 Número de solicitud: 200600040 51 Int. Cl.: H04W 88/00 (2009.01) G08B 23/00 (2006.01) 12 SOLICITUD DE PATENTE A1 22
Reseñas. Ángeles Maldonado y Elena Fernández, Cindoc. El profesional de la información, vol. 9, nº 3, marzo de 2000
 Reseñas Análisis comparativo de buscadores en internet Por Ángeles Maldonado Martínez y Elena Fernández Sánchez Resumen de la comunicación presentada por las autoras a la conferencia Online Information
Reseñas Análisis comparativo de buscadores en internet Por Ángeles Maldonado Martínez y Elena Fernández Sánchez Resumen de la comunicación presentada por las autoras a la conferencia Online Information
Preguntas de selectividad en Andalucía. Ácidos nucleicos. Análisis e interpretación de imágenes, esquemas, figuras...
 Año 2001 Describa las funciones más relevantes de los nucleótidos. Cite un ejemplo de nucleótido que participe en cada una de ellas [1,5]. Explique las funciones de los distintos tipos de RNA que participan
Año 2001 Describa las funciones más relevantes de los nucleótidos. Cite un ejemplo de nucleótido que participe en cada una de ellas [1,5]. Explique las funciones de los distintos tipos de RNA que participan
Capítulo 5: METODOLOGÍA APLICABLE A LAS NORMAS NE AI
 Capítulo 5: METODOLOGÍA APLICABLE A LAS NORMAS NE AI La segunda fase del NIPE corresponde con la adecuación de las intervenciones de enfermería del sistema de clasificación N.I.C. (Nursing Intervention
Capítulo 5: METODOLOGÍA APLICABLE A LAS NORMAS NE AI La segunda fase del NIPE corresponde con la adecuación de las intervenciones de enfermería del sistema de clasificación N.I.C. (Nursing Intervention
Este documento proporciona la secuencia de pasos necesarios para la construcción de un Diagrama de Flujo. www.fundibeq.org
 DIAGRAMA DE FLUJO 1.- INTRODUCCIÓN Este documento proporciona la secuencia de pasos necesarios para la construcción de un Diagrama de Flujo. Muestra la importancia de dos aspectos clave en este proceso:
DIAGRAMA DE FLUJO 1.- INTRODUCCIÓN Este documento proporciona la secuencia de pasos necesarios para la construcción de un Diagrama de Flujo. Muestra la importancia de dos aspectos clave en este proceso:
11 Número de publicación: 2 290 597. 51 Int. Cl.: 74 Agente: Carpintero López, Francisco
 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 290 97 1 Int. Cl.: H01Q 1/2 (06.01) H01Q /00 (06.01) H01Q 21/ (06.01) 12 TRADUCCIÓN DE PATENTE EUROPEA T3 86 Número de solicitud
19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 290 97 1 Int. Cl.: H01Q 1/2 (06.01) H01Q /00 (06.01) H01Q 21/ (06.01) 12 TRADUCCIÓN DE PATENTE EUROPEA T3 86 Número de solicitud
ELABORACIÓN N DE MEZCLA PARA PCR. Raquel Asunción Lima Cordón
 ELABORACIÓN N DE MEZCLA PARA PCR Raquel Asunción Lima Cordón PCR Polymerase Chain reaction (reacción en cadena de la polimerasa) Sintetizar muchas veces un fragmento de ADN PCR: simulación de lo que sucede
ELABORACIÓN N DE MEZCLA PARA PCR Raquel Asunción Lima Cordón PCR Polymerase Chain reaction (reacción en cadena de la polimerasa) Sintetizar muchas veces un fragmento de ADN PCR: simulación de lo que sucede
Identificación y caracterización de células madres cancerígenas (CMCs) en Sarcoma de Ewing
 Identificación y caracterización de células madres cancerígenas (CMCs) en Sarcoma de Ewing Introducción Una célula madre o célula troncal es una célula que tiene capacidad de autorrenovarse mediante divisiones
Identificación y caracterización de células madres cancerígenas (CMCs) en Sarcoma de Ewing Introducción Una célula madre o célula troncal es una célula que tiene capacidad de autorrenovarse mediante divisiones
11 knúmero de publicación: 2 144 127. 51 kint. Cl. 7 : B07C 5/342. k 72 Inventor/es: Wahlquist, Anders. k 74 Agente: Esteban Pérez-Serrano, M ā Isabel
 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 144 127 1 Int. Cl. 7 : B07C /342 12 TRADUCCION DE PATENTE EUROPEA T3 86 Número de solicitud europea: 99331.6 86 Fecha de presentación
19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 Número de publicación: 2 144 127 1 Int. Cl. 7 : B07C /342 12 TRADUCCION DE PATENTE EUROPEA T3 86 Número de solicitud europea: 99331.6 86 Fecha de presentación
PCR a tiempo real. Sección de Biología Molecular, Servicio de Apoyo a la Investigación, Universidad de Murcia
 PCR a tiempo real Sección de Biología Molecular, Servicio de Apoyo a la Investigación, Universidad de Murcia PCR a tiempo real (PCRrt) Aplicaciones: - Cuantificación de ácidos nucleicos (AQ). - Estudio
PCR a tiempo real Sección de Biología Molecular, Servicio de Apoyo a la Investigación, Universidad de Murcia PCR a tiempo real (PCRrt) Aplicaciones: - Cuantificación de ácidos nucleicos (AQ). - Estudio
IES Pando Departamento de Biología y Geología 1
 IES Pando Departamento de Biología y Geología 1 2 Células en diversos estadios del ciclo celular en la raíz de ajo. 3 Diversos aspectos del núcleo durante el ciclo celular Ciclo celular 4 Repartición del
IES Pando Departamento de Biología y Geología 1 2 Células en diversos estadios del ciclo celular en la raíz de ajo. 3 Diversos aspectos del núcleo durante el ciclo celular Ciclo celular 4 Repartición del
ES 2 084 559 A1 B32B 19/04 F16S 1/00. N. de publicación: ES 2 084 559 PATENTES Y MARCAS. Número de solicitud: 9400233. Int. Cl.
 k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k N. de publicación: ES 2 084 9 21 k Número de solicitud: 90233 1 k Int. Cl. 6 : B32B 31/ B32B 19/04 F16S 1/00 k 12 SOLICITUD DE PATENTE A1 22 kfecha
k 19 OFICINA ESPAÑOLA DE PATENTES Y MARCAS ESPAÑA 11 k N. de publicación: ES 2 084 9 21 k Número de solicitud: 90233 1 k Int. Cl. 6 : B32B 31/ B32B 19/04 F16S 1/00 k 12 SOLICITUD DE PATENTE A1 22 kfecha
METODOLOGIA DEL PCR. Lic. Jorge Mato Luis. Laboratorio de Genética Molecular Hospital Clínico Quirúrgico Hermanos Ameijeiras
 METODOLOGIA DEL PCR Lic. Jorge Mato Luis Laboratorio de Genética Molecular Hospital Clínico Quirúrgico Hermanos Ameijeiras Desnaturalización del DNA 5 A G G T T A G T G G A C C C T T G A T 3 3 T C C A
METODOLOGIA DEL PCR Lic. Jorge Mato Luis Laboratorio de Genética Molecular Hospital Clínico Quirúrgico Hermanos Ameijeiras Desnaturalización del DNA 5 A G G T T A G T G G A C C C T T G A T 3 3 T C C A
Universidad de Tarapacá. Investigación de Mercados Internacionales
 Universidad de Tarapacá Investigación de Mercados Internacionales Unidad III Tema 1: Análisis del Potencial Exportador de la Organización Profesor: Gustavo Gómez Velásquez Qué entendemos por el Análisis
Universidad de Tarapacá Investigación de Mercados Internacionales Unidad III Tema 1: Análisis del Potencial Exportador de la Organización Profesor: Gustavo Gómez Velásquez Qué entendemos por el Análisis
Entender el funcionamiento de los relojes permitiría lidiar con ciertas patologías en humanos. 28 ACTUALIDAD EN I+D RIA / Vol. 41 / N.
 28 ACTUALIDAD EN I+D RIA / Vol. 41 / N.º 1 Entender el funcionamiento de los relojes permitiría lidiar con ciertas patologías en humanos Abril 2015, Argentina 29 Relojes biológicos en plantas Ajustar el
28 ACTUALIDAD EN I+D RIA / Vol. 41 / N.º 1 Entender el funcionamiento de los relojes permitiría lidiar con ciertas patologías en humanos Abril 2015, Argentina 29 Relojes biológicos en plantas Ajustar el
