11.1 Expresión de los transcritos del subcomplejo SG-SSPN en el tejido adiposo parametrial.
|
|
|
- Virginia Padilla Quintero
- hace 8 años
- Vistas:
Transcripción
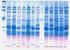
1 11. RESULTADOS Mediante este trabajo se identificó la expresión de los transcritos de α, β, γ, δ, ε y ζ SG y sspn en tejido adiposo parametrial de la rata y se localizó la proteína sspn en la membrana de los adipocitos. A continuación se detallan en apartados distintos los resultados obtenidos en este estudio Expresión de los transcritos del subcomplejo SG-SSPN en el tejido adiposo parametrial. Para la identificación de la expresión de los transcritos de los componentes del subcomplejo SG-SSPN se extrajo el ARN total del músculo esquelético y tejido adiposo parametrial de la rata. Se obtuvo en promedio una concentración de ARN total de µg/µl, por tejido. En la figura 6 se pueden observar los ARN s totales obtenidos a partir de tejido adiposo, así como músculo esquelético de la rata (mismo que se utilizó como control positivo) sometidos a electroforesis. Una vez cuantificado y habiendo verificado la pureza de los ARN s totales (tabla 6), se escogió la muestra 4 (concentración de 0.51 µg ARN / ml) para músculo esquelético y la muestra 7 (concentración de 0.30 µg ARN / ml) para tejido adiposo a partir de los cuales se procedió a continuar con los ensayos de RT-PCR. Para llevar a cabo los ensayos de RT-PCR se diseñaron oligonucleótidos específicos para cada uno de los transcritos de los miembros del subcomplejo SG-SSPN. Para el caso de la gapdh cuyo transcrito fue considerado un control constitutivo se utilizaron oligonucleótidos diseñados en ratón. Como resultado de la RT-PCR se obtuvieron los productos amplificados de los tamaños esperados: 363 pb para el caso de α SG; 476 pb para β SG; 488 pb para γ SG; 193 pb para δ SG; 696 pb para ε SG; 397 pb para ζ SG; 449 pb para sarcospan y el tamaño esperado del producto amplificado para gapdh de 274 pb (figura 7-a). En el caso de ζ SG la expresión fue casi imperceptible en comparación con lo observado para el resto de los sarcoglicanos en ambos tejidos. Para comprobar la
2 expresión de este transcrito se obtuvieron los productos amplificados de tamaño esperado mediante un PCR anidado (125 pb) y semianidados (172 pb y 350 pb) a partir de las combinaciones posibles entre dos pares de oligonucleótidos específicos (figura 7-b).
3 Figura 6. Análisis de la integridad del ARN total extraído a partir del músculo esquelético (1, 2, 3 y 4) y tejido adiposo parametrial (5, 6, 7 y 8) de la rata. Electroforesis en gel de agarosa al 1.0% teñido con bromuro de etidio (0.5 µg/ml). ME = músculo esquelético; TAP = tejido adiposo parametrial; 28 S = RNA ribosomal subunidad grande (28); 18 S = RNA ribosomal subunidad chica (18); trna = RNA de transferencia. Tabla 6. Cuantificación y pureza del ARN total. Tejido A 260 A 280 Relación µg ARN / µl 1 ME 0,527 0,239 2,210 1,05 2 ME 0,590 0,274 2,153 1,18 3 ME 0,337 0,154 2,197 0,67 4 ME 0,254 0,113 2,244 0,51 5 TAP 0,072 0,025 2,883 0,14 6 TAP 0,077 0,029 2,641 0,15 7 TAP 0,151 0,070 2,170 0,30 8 TAP 0,087 0,034 2,545 0,17 Cada medición se hizo por duplicado. Los valores que se presentan son el promedio de ambas mediciones. ME = músculo esquelético, TAP = tejido adiposo parametrial.
4 1000 pb 500 pb 100 pb α β γ δ ε ζ sspn gapdh M ME TAP ME TAP ME TAP ME TAP ME TAP ME TAP ME TAP ME TAP C(1) C(2) 696 pb 488 pb 476 pb 449 pb 397 pb 363 pb 274 pb 193 pb Figura 7-a. Identificación de los productos amplificados por PCR del subcomplejo SG-SPN. α-sarcoglicano (α) (1, 2), β-sarcoglicano (β) (3, 4), γ-sarcoglicano (γ) (5, 6), δ-sarcoglicano (δ) (7, 8), ε-sarcoglicano (ε) (9, 10), ζ-sarcoglicano (ζ) (11, 12), sarcospan (sspn) (13, 14) y gliceraldehido 3 fosfato deshidrogenasa (gapdh) (15, 16). Electroforesis en gel de agarosa al 2.0% teñido con bromuro de etidio (0.5 µg/ml). M = marcador de peso molecular escalera de 100 pares de bases (pb), C(1) = control negativo de RT-PCR (sin RNA), C(2) = control negativo de PCR (sin cdna), ME = músculo esquelético; TAP = tejido adiposo parametrial. ζ a b c gapdh M ME TAP ME TAP ME TAP ME TAP 500 pb 100 pb pb 274 pb 172 pb 125 pb Figura 7-b. Identificación de los productos amplificados por PCR anidado y semianidado de ζ sarcoglicano. ζ-sarcoglicano F1-R1 (ζ a) (1, 2), ζ-sarcoglicano F1-R (ζ b) (3, 4), ζ-sarcoglicano F-R1 (ζ c) (5, 6), y gliceraldehido 3 fosfato deshidrogenasa (gapdh) (7, 8). Electroforesis en gel de agarosa al 2.0% teñido con bromuro de etidio (0.5 µg/ml). M = marcador de peso molecular escalera de 100 pares de bases (pb), ME = músculo esquelético; TAP = tejido adiposo parametrial.
5 Para corroborar que los transcritos amplificados de sspn y sgcz corresponden a la secuencia reportada respectiva del mismo transcrito, el producto obtenido del RT-PCR se secuenció. Las secuencias obtenidas para el transcrito amplificado de sarcospan (figura 8ac) y ζ sarcoglicano (figura 9a-c) provenientes de tejido adiposo parametrial corresponden a 449 pb y 350 pb respectivamente. Mediante la composición de las secuencias obtenidas contra las secuencias reportadas del ARNm de ratón (NM_010656) y humano (NM_005086) se determinó una homología de >85% entre estas secuencias, lo cual a su vez confirma la identidad de los productos de PCR. En vista de que a la fecha no se ha reportado la secuencia del gen de sarcospan en rata, la secuencia homóloga del transcrito se ubicó en el genoma de la rata mediante un análisis con el programa BLAST de la página web NCBI (datos no mostrados) estableciendo tentativamente que el gen sspn de la rata se localiza en el locus 4q44. La homología de la secuencia obtenida para el transcrito amplificado de sspn así como la secuencia de aminoácidos correspondiente determinada in silico se analizó mediante un programa de alineamiento múltiple. La secuencia obtenida del transcrito de sarcospan de rata es 94.6% (24 mal apareamientos de 449 pb; 425/449 pb) y 85.9% (63 mal apareamientos de 449 pb; 386/449 pb) homóloga a los fragmentos alineados de la secuencia de nucleótidos reportados para ratón (NM_010656) y humano (NM_005086) respectivamente (figura 10-a). La secuencia traducida del transcrito de sarcospan es 96.0% (6 mal apareamientos de 150 aa; 144/150 aa) y 88.0% (18 mal apareamientos de 150 aa; 132/150 aa) homóloga a los fragmentos alineados de las secuencias peptídicas reportadas para ratón (NP_034786) y humano (NP_005077) respectivamente (figura 10-b).
6 8-a. Secuencia sentido (sspn)
7 8-b. Secuencia antisentido (sspn)
8 8-c. Secuencia homóloga (sspn) 1 GAGGAGGAGG CAAGGACCTG TTGCGGCTGC CGCTTTCCGC TGCTGCTGGC GCTGCTGCAG 61 CTGGCCCTGG GCATCGCGGT GACTGTGCTG GGCTTCCTCA TGGCGAGCAT CAGCCCCTCC 121 CTGCTAGTCA GAGACACTCC GTTCTGGGCT GGGATCATTG TCTGCGTGGT GGCCTACCTT 181 GGACTGTTCA TGCTTTGTGT CTCATACCAA GTTGACGAGA GGACGTGTGT CCAGTTTTCT 241 ATGAAGGTGT TTTATTTCCT GCTGAGTGCC CTCGGCCTGA TGGTCTGCAC GCTGGCCGTG 301 GCCTTCGCCG CCCACCACTA TTCCCTGCTT GCACAGTTTA CCTGTGAAAC CTCCCTGGAT 361 TCTTGCCAGT GCCGGCTGCC TTCCGCGGAG CCTCTCAGCA GGGCCTTTGT TTACAGGGAT 421 GTGACTGACT GTAGCAGCAT CACTGGTACT TTCAAATTGT TCTTAGTCAT CCAGATGGTT 481 CTAAACCTGG TCTGTGGCCT GGTGTGCTTG CTGGCTTGCT TTGTGATGTG GAAACACAGG 541 TACCAGGTCT TTTATGTGGG TGTTGGGCTG CGCTCCCTGA TGGCTTCTGA TGGCC Figura 8. Secuencias obtenidas para el transcrito amplificado de sarcospan. (a) Secuencia sentido (foward) del transcrito amplificado de sarcospan. Las flechas indican el principio y fin de la secuencia alineada (410 pb). (b) Secuencia antisentido (reverse) del transcrito amplificado de sarcospan. Las flechas indican el principio y fin de la secuencia alineada (399 pb). (c) Secuencia homóloga (595 pb, >90%) del gen de sarcospan de Rattus norvegicus (ref NW_ Rn4_2219 en NCBI database). Las letras remarcadas en negritas corresponden a los sitios blanco de los oligonucleótidos forward y reverse correspondientes. La secuencia resaltada en gris (409 pb) corresponde a la secuencia obtenida a partir del transcrito amplificado. La secuenciación se verificó por duplicado.
9 9-a. Secuencia sentido (sgcz)
10 9-b. Secuencia antisentido (sgcz)
11 9-c. Secuencia homóloga (scgz) 1 GGAGCTGAGG CTGTTGAGGC CCAGTGTAAA AGATTTGAAG TGAGAGCCAG TGAAGACGGC 61 AGGGTGCTGT TTTCTGCAGA TGAAGATGAG ATCACTATTG GGGCTGAGAA GCTAAAGGTT 121 ACAGGGACTG AAGGAGCAGT ATTTGGGCAC TCTGTGGAAA CACCTCACGT CAGAGCAGAG 181 CCATCTCAAG ACCTCAGGCT TGAATCACCT ACCAGATCCT TGATAATGGA GGCTCCACGT 241 GGGGTCCAGG TGAGTGCTGC TGCAGGTGAC TTCAAGGCTA CCTGCAGGAA GGAGCTGCAT 301 TTACAGTCCA CAGAAGGAGA GATTTTTCTA AATGCAGATT CAATCCGGCT GGGAAATCTA 361 CCAATCGGTT CCTTCTCTTC TTCACCCAGC TCTTCAAATT CTCGACAGAC AGTGTATGAA 421 CTGTGCGTCT GCCCCAATGG CAAACTCTAC CTTTCTCCGG CTGGGGTAGA CTCCACCTGT 481 CAGTCCAGTA GTAGCATTTG CTTGTGGAGC TGA Figura 9. Secuencias obtenidas para el transcrito amplificado de ζ sarcoglicano. (a) Secuencia sentido (foward) del transcrito amplificado de ζ sarcoglicano. Las flechas indican el principio y fin de la secuencia alineada (310 pb). (b) Secuencia antisentido (reverse) del transcrito amplificado de ζ sarcoglicano. Las flechas indican el principio y fin de la secuencia alineada (313 pb). (c) Secuencia homóloga (513 pb, >90%) del gen ζ sarcoglicano de Rattus norvegicus (XM_ en NCBI database). Las letras remarcadas en negritas corresponden a los sitios blanco de los oligonucleótidos forward y reverse correspondientes. La secuencia resaltada en gris (310 pb) corresponde a la secuencia obtenida a partir del transcrito amplificado. La secuenciación se verificó por duplicado.
12 1 50 HS GCTAGTCAGG GACACTCCAT TTTGGGCTGG GATCATTGTC TGCTTAGTGG MM GCTAGTCAGA GATACTCCGT TCTGGGCTGG GATCATTGTC TGCGTGGTGG RN GCTAGTCAGA GACACTCCGT TCTGGGCTGG GATCATTGTC TGCGTGGTGG Consenso GCTAGTCAGa GAcACTCCgT TcTGGGCTGG GATCATTGTC TGCgTgGTGG HS CCTATCTTGG CTTGTTTATG CTTTGTGTCT CATATCAGGT TGACGAACGG MM CTTACCTTGG ACTGTTCATG CTTTGTGTCT CATACCAAGT TGACGAGAGG RN CCTACCTTGG ACTGTTCATG CTTTGTGTCT CATACCAAGT TGACGAGAGG Consenso CcTAcCTTGG actgttcatg CTTTGTGTCT CATAcCAaGT TGACGAgaGG HS ACATGTATTC AATTTTCTAT GAAACTGTTA TACTTTCTGC TGAGTGCCCT MM ACATGTGTCC AGTTTTCTAT GAAGGTATTC TACTTCCTGT TGAGTGCCCT RN ACGTGTGTCC AGTTTTCTAT GAAGGTGTTT TATTTCCTGC TGAGTGCCCT Consenso ACaTGTgTcC AgTTTTCTAT GAAggTgTT. TAcTTcCTGc TGAGTGCCCT HS GGGCCTGACG GTCTGTGTGC TGGCCGTGGC CTTTGCCGCC CACCACTATT MM CGGCCTGATG GTCTGCATGC TGGCTGTGGC CTTTGCCGCC CACCACTACT RN CGGCCTGATG GTCTGCACGC TGGCCGTGGC CTTCGCCGCC CACCACTATT Consenso cggcctgatg GTCTGcatGC TGGCcGTGGC CTTtGCCGCC CACCACTAtT HS CGCAGCTCAC ACAGTTTAC CTGTGAGACCA CACTCGACTC TTGCCAGTGC MM CCCTGCTTGC GCAGTTTAC CTGCGAGACCT CCCTGGATTC TTGCCAGTGC RN CCCTGCTTGC ACAGTTTAC CTGTGAAACCT CCCTGGATTC TTGCCAGTGC Consenso CcCtGCTtgC acagtttac CTGtGAgACCt CcCTgGAtTC TTGCCAGTGC HS AAACTGCCCT CCTCGGAGCC GCTCAGCAGG ACCTTTGTTT ACCGGGATGT MM AAGCTGCCTT CCTCGGAGCC GCTCAGCAGG GCCTTTGTTT ACAGGGATGT RN CGGCTGCCTT CCGCGGAGCC TCTCAGCAGG GCCTTTGTTT ACAGGGATGT Consenso aagctgcctt CCtCGGAGCC gctcagcagg gcctttgttt ACaGGGATGT HS GACGGACTGT ACCAGCGTCA CTGGCACTTT CAAACTGTTC TTACTCATCC MM GACTGACTGT ACCAGCGTCA CTGGCACTTT CAAATTGTTC TTAATCATCC RN GACTGACTGT AGCAGCATCA CTGGTACTTT CAAATTGTTC TTAGTCATCC Consenso GACtGACTGT AcCAGCgTCA CTGGcACTTT CAAAtTGTTC TTA.TCATCC HS AGATGATTCT TAATTTGGTC TGCGGCCTTG TGTGCTTGTT GGCCTGCTTT MM AGATGGTCCT AAACCTGGTC TGTGGCCTCG TGTGCTTGCT GGCTTGCTTT RN AGATGGTTCT AAACCTGGTC TGTGGCCTGG TGTGCTTGCT GGCTTGCTTT Consenso AGATGgTtCT aaacctggtc TGtGGCCT.G TGTGCTTGcT GGCtTGCTTT HS GTGATGTGGA AACATAGGTA CCAGGTCTTC TATGTGGGTG TCAGGATAT MM GTGATGTGGA AACACAGGTA CCAGGTCTTT TATGTGGGTG TTGGGCTGC RN GTGATGTGGA AACACAGGTA CCAGGTCTTT TATGTGGGTG TTGGGCTGC Consenso GTGATGTGGA AACAcAGGTA CCAGGTCTTt TATGTGGGTG TtgGGcTgc Figura 10-a. Alineamiento múltiple de la secuencia obtenida para el transcrito de sspn (449 pb). Las letras remarcadas en negritas corresponden a los sitios de cambio en la secuencia de nucleótidos. Las letras resaltadas en gris corresponden a los sitios donde ninguna de las bases se conserva entre las tres especies. Consenso, secuencia consenso; HS, Homo sapiens (humano); MM, Mus musculus (ratón); RN, Rattus norvegicus (rata).
13 NH HS MGKNKQPRGQ QRQGGPPAAD AAGPDDMEPK KGTGAPKECG EEEPRTCCGC MM MGR KPSPRAQELP EEEARTCCGC RN Consenso k...e.. eee.rtccgc TM1 TM HS RFPLLLALLQ LALGIAVTVV GFLMASISSS LLVRDTPFWA GIIVCLVAYL MM RFPLLLALLQ LALGIAVTVL GFLMASISPS LLVRDTPFWA GIIVCVVAYL RN LVRDTPFWA GIIVCVVAYL Consenso rfplllallq lalgiavtv. gflmasis.s llvrdtpfwa GIIVCvVAYL TM HS GLFMLCVSYQ VDERTCIQFS MKLLYFLLSA LGLTVCVLAV AFAAHHYSQL MM GLFMLCVSYQ VDERTCVQFS MKVFYFLLSA LGLMVCMLAV AFAAHHYSLL RN GLFMLCVSYQ VDERTCVQFS MKVFYFLLSA LGLMVCTLAV AFAAHHYSLL Consenso GLFMLCVSYQ VDERTC!QFS MKvfYFLLSA LGLmVC.LAV AFAAHHYSlL LOOP TM HS TQFTCETTLD SCQCKLPSSE PLSRTFVYRD VTDCTSVTGT FKLFLLIQMI MM AQFTCETSLD SCQCKLPSSE PLSRAFVYRD VTDCTSVTGT FKLFLIIQMV RN AQFTCETSLD SCQCRLPSAE PLSRAFVYRD VTDCSSITGT FKLFLVIQMV Consenso aqftcetsld SCQCkLPSsE PLSRaFVYRD VTDCtS!TGT FKLFL.IQM! COO HS LNLVCGLVCL LACFVMWKHR YQVFYVGVRI CSLTASEGPQ QKI MM LNLVCGLVCL LACFVMWKHR YQVFYVGVGL RSLMASDGQL PKA RN LNLVCGLVCL LACFVMWKHR YQVFYVGVGL Consenso LNLVCGLVCL LACFVMWKHR YQVFYVGVgl.sl.as.g...k. Figura 10-b. Alineamiento múltiple de la secuencia traducida del transcrito de sspn (150 aa). Las letras remarcadas en negritas corresponden a los sitios de cambio en la secuencia peptídica. Las letras resaltadas en gris corresponden a los sitios donde ninguno de los aminoácidos se conserva entre las tres especies. COO -, región carboxilo terminal; Consenso, secuencia consenso; HS, Homo sapiens (humano); LOOP, asa extracelular; MM, Mus musculus (ratón); NH 2 +, región amino terminal; RN, Rattus norvegicus (rata); TM1, dominio transmembranal 1; TM2, dominio transmembranal 2; TM3, dominio transmembranal 3; TM4, dominio transmembranal 4;!, símbolo que denota la presencia de cualquiera de los aminoácidos I ó V.
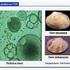
14 Después de observar que todos los transcritos del complejo SG-SSPN se expresan en tejido adiposo parametrial se procedió a realizar los ensayos de inmunofluorescencia Expresión de la proteína sarcospan en el tejido adiposo parametrial. La presencia de la proteína sarcospan se hizo evidente por medio de los ensayos de inmunofluorescencia indirecta en los frotis de tejido adiposo fresco. Para este tipo de ensayos se utilizaron anticuerpos específicos que reconocen los últimos 13 aa de la región C-terminal de la proteína sarcospan. Como se muestra en la figura 11, la proteína sarcospan se localiza en la membrana de los adipocitos procedentes del tejido adiposo parametrial. Es importante señalar que se observó una mayor tinción cerca de las uniones intercelulares de los adipocitos (fig. 11-b), lo que sugiere una mayor cantidad de proteína en estas zonas. La especificidad del anticuerpo fue comprobada con el control negativo al cual únicamente se le añadió el anticuerpo secundario comprobando un reconocimiento específico del anticuerpo (datos no mostrados).
15 (a) (b) (1) 20X 40X (2) 20X 40X (3) 20X 40X Figura 11. Ensayo de inmunofluorescencia indirecta con anticuerpos específicos para la región COO - de sarcospan (sspn) en adipocitos de rata. (a) Frotis de tejido adiposo (Magnificación 20x). La tinción fluorescente denota la membrana de los adipocitos constituyentes. (b) Acercamiento de una zona central correspondiente al inciso a (Magnificación 40x). Las flechas indican las zonas (uniones intracelulares) de aparente mayor tinción en los adipocitos. (1-3) Diferentes vistas de los frotis de tejido adiposo. Tinción verde = Conjugado Isotiocianato de Fluoresceína (FITC)
12. DISCUSIONES Y PERSPECTIVAS
 12. DISCUSIONES Y PERSPECTIVAS Originalmente los sarcoglicanos y sarcospan fueron caracterizados en músculo esquelético como un subcomplejo integral del complejo DGC, el cual es crítico para la estabilidad
12. DISCUSIONES Y PERSPECTIVAS Originalmente los sarcoglicanos y sarcospan fueron caracterizados en músculo esquelético como un subcomplejo integral del complejo DGC, el cual es crítico para la estabilidad
Comprobando la calidad del DNA genómico mediante electroforesis en gel
 Comprobando la calidad del DNA genómico mediante electroforesis en gel GELES 1 Y 2 Agarosa 0.8 %, electroforesis a 1 V/cm Muestras: Se ha cargado muestras de DNA genómico no digerido, antes (líneas impares)
Comprobando la calidad del DNA genómico mediante electroforesis en gel GELES 1 Y 2 Agarosa 0.8 %, electroforesis a 1 V/cm Muestras: Se ha cargado muestras de DNA genómico no digerido, antes (líneas impares)
CAPÍTULO VI. Expresión de genes relacionados con apoptosis
 CAPÍTULO VI Expresión de genes relacionados con apoptosis 1.- Introducción 2.- Protocolos para análisis genéticos 3.- Resultados en MCF-7 4.- Discusión 1.- Introducción Como se ha descrito anteriormente,
CAPÍTULO VI Expresión de genes relacionados con apoptosis 1.- Introducción 2.- Protocolos para análisis genéticos 3.- Resultados en MCF-7 4.- Discusión 1.- Introducción Como se ha descrito anteriormente,
10. MATERIALES Y MÉTODOS
 10. MATERIALES Y MÉTODOS A continuación se presenta un esquema general de la estrategia experimental del presente trabajo. Esquema de trabajo Modelo animal (Ratas hembras) Disección de los tejidos (TAP
10. MATERIALES Y MÉTODOS A continuación se presenta un esquema general de la estrategia experimental del presente trabajo. Esquema de trabajo Modelo animal (Ratas hembras) Disección de los tejidos (TAP
Easy PDF Creator is professional software to create PDF. If you wish to remove this line, buy it now.
 Unidad Curricular: Virología y Micología Veterinaria 1 TRABAJO PRÁCTICO No. 3 AMPLIFICACIÓN DE GENES VIRALES Reacción en Cadena de la Polimerasa, conocida como PCR (por sus siglas en inglés: Polimerase
Unidad Curricular: Virología y Micología Veterinaria 1 TRABAJO PRÁCTICO No. 3 AMPLIFICACIÓN DE GENES VIRALES Reacción en Cadena de la Polimerasa, conocida como PCR (por sus siglas en inglés: Polimerase
AQUAGESTION. ISAv: Un acercamiento actualizado en la detección de sus variantes en la región. Departamento de Desarrollo y Laboratorio Diagnóstico.
 AQUAGESTION ISAv: Un acercamiento actualizado en la detección de sus variantes en la región. Departamento de Desarrollo y Laboratorio Diagnóstico. Noviembre 2011 ACTUALIDAD Este año Sernapesca confirma
AQUAGESTION ISAv: Un acercamiento actualizado en la detección de sus variantes en la región. Departamento de Desarrollo y Laboratorio Diagnóstico. Noviembre 2011 ACTUALIDAD Este año Sernapesca confirma
APLICACIÓN DE LA PCR: DIAGNÓSTICO DE PARÁSITOS
 Prácticas docentes en la COD: 10-71 APLICACIÓN DE LA PCR: DIAGNÓSTICO DE PARÁSITOS FUNDAMENTO TEÓRICO La PCR es una técnica que permite llevar a cabo la síntesis in vitro de fragmentos de ADN. Está basada
Prácticas docentes en la COD: 10-71 APLICACIÓN DE LA PCR: DIAGNÓSTICO DE PARÁSITOS FUNDAMENTO TEÓRICO La PCR es una técnica que permite llevar a cabo la síntesis in vitro de fragmentos de ADN. Está basada
El Banco Nacional de ADN oferta un control de calidad de muestras de ADN y ARN.
 PROGRAMA CONTROL DE CALIDAD DE MUESTRAS El Banco Nacional de ADN oferta un control de calidad de muestras de ADN y ARN. El programa completo de control de calidad de muestras de ADN y ARN engloba diferentes
PROGRAMA CONTROL DE CALIDAD DE MUESTRAS El Banco Nacional de ADN oferta un control de calidad de muestras de ADN y ARN. El programa completo de control de calidad de muestras de ADN y ARN engloba diferentes
METODOLOGÍAS UTILIZADAS EN INVESTIGACIÓN BÁSICA Y APLICADA REACCION EN CADENA DE LA POLIMERASA (PCR)
 METODOLOGÍAS UTILIZADAS EN INVESTIGACIÓN BÁSICA Y APLICADA REACCION EN CADENA DE LA POLIMERASA (PCR) Centro de de Microscopía Electrónica Facultad de de Ciencias Médicas Universidad Nacional de de Córdoba
METODOLOGÍAS UTILIZADAS EN INVESTIGACIÓN BÁSICA Y APLICADA REACCION EN CADENA DE LA POLIMERASA (PCR) Centro de de Microscopía Electrónica Facultad de de Ciencias Médicas Universidad Nacional de de Córdoba
III. METODOLOGÍA EXPERIMENTAL
 III. METODOLOGÍA EXPERIMENTAL 3.1 Análisis Previos Se utilizaron los filtros con muestra de partículas suspendidas en el aire PM 10 que el Instituto Municipal de Ecología (IME) proporcionó para llevar
III. METODOLOGÍA EXPERIMENTAL 3.1 Análisis Previos Se utilizaron los filtros con muestra de partículas suspendidas en el aire PM 10 que el Instituto Municipal de Ecología (IME) proporcionó para llevar
DETERMINACIÓN DEL FACTOR Rh por PCR
 Ref.PCRRh DETERMINACIÓN DEL FACTOR Rh por PCR 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa
Ref.PCRRh DETERMINACIÓN DEL FACTOR Rh por PCR 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa
3. COMPONENTES. Tampón de electroforesis concentrado 2 x 50 ml 10 X (2 envases 500ml)
 PCR SIMULADA Ref.PCR Simulada (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa
PCR SIMULADA Ref.PCR Simulada (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa
Detección de patógenos en alimentos, utilizando la técnica de PCR, reacción en cadena de la polimerasa.
 Detección de patógenos en alimentos, utilizando la técnica de PCR, reacción en cadena de la polimerasa. Lic. Esp. Mariano Diego Massari 1er Congreso Bioquímico Córdoba 2011 8ª Jornada de Actualización
Detección de patógenos en alimentos, utilizando la técnica de PCR, reacción en cadena de la polimerasa. Lic. Esp. Mariano Diego Massari 1er Congreso Bioquímico Córdoba 2011 8ª Jornada de Actualización
5. MATERIALES Y MÉTODOS
 5. MATERIALES Y MÉTODOS 5.1 Equipos Los siguientes termocicladores se emplearon para la amplificación por PCR: - Perkin Elmer, GeneAmp PCR System 2400. - Perkin Elmer, GeneAmp PCR System 9600. - Applied
5. MATERIALES Y MÉTODOS 5.1 Equipos Los siguientes termocicladores se emplearon para la amplificación por PCR: - Perkin Elmer, GeneAmp PCR System 2400. - Perkin Elmer, GeneAmp PCR System 9600. - Applied
INACTIVACIÓN DE LOS GENES SUPRESORES PTEN, DMBT1 Y P16 EN GLIOBLASTOMA MULTIFORME, ASTROCITOMAS ANAPLÁSICOS Y ASTROCITOMAS DE BAJO GRADO.
 IV CONGRESO VIRTUAL HISPANO AMERICANO DE ANATOMÍA PATOLÓGICA Abstract PDF CONTENIDO Comentarios Título Resumen Introducción Material Resultados Conclusiones Imágenes INACTIVACIÓN DE LOS GENES SUPRESORES
IV CONGRESO VIRTUAL HISPANO AMERICANO DE ANATOMÍA PATOLÓGICA Abstract PDF CONTENIDO Comentarios Título Resumen Introducción Material Resultados Conclusiones Imágenes INACTIVACIÓN DE LOS GENES SUPRESORES
Técnicas moleculares.
 Técnicas moleculares. DMTV Carolina Acevedo Curso de Microbiología 2015 SÍNTESIS IN VITRO DE UNA GRAN CANTIDAD DE COPIAS DE UN SEGMENTO DE ADN EXISTENTE EN UNA MUESTRA. O sea. Amplificamos en forma exponencial
Técnicas moleculares. DMTV Carolina Acevedo Curso de Microbiología 2015 SÍNTESIS IN VITRO DE UNA GRAN CANTIDAD DE COPIAS DE UN SEGMENTO DE ADN EXISTENTE EN UNA MUESTRA. O sea. Amplificamos en forma exponencial
Código: IDK-010 Ver: 1. Proteína G C825T. Sistema para la detección de la mutación C825T en el gene de la proteína G.
 C825T Sistema para la detección de la mutación C825T en el gene de la proteína G. Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336 71 60. Info@atgen.com.uy www.atgen.com.uy
C825T Sistema para la detección de la mutación C825T en el gene de la proteína G. Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336 71 60. Info@atgen.com.uy www.atgen.com.uy
P.C.R. "Técnica de amplificación enzimática de secuencias específicas de DNA"
 P.C.R. "Técnica de amplificación enzimática de secuencias específicas de DNA" Paso 1: Desnaturalización del DNA Paso 2: Hibridación de los "Primers" Paso 3: Extensión Paso 1: Desnaturalización del DNA
P.C.R. "Técnica de amplificación enzimática de secuencias específicas de DNA" Paso 1: Desnaturalización del DNA Paso 2: Hibridación de los "Primers" Paso 3: Extensión Paso 1: Desnaturalización del DNA
FICHA PÚBLICA DEL PROYECTO
 FICHA PÚBLICA DEL PROYECTO PROGRAMA DE ESTÍMULOS A LA INNOVACIÓN NUMERO DE PROYECTO: 214028 EMPRESA BENEFICIADA: PHARMACOS EXAKTA S.A. DE C.V. TÍTULO DEL PROYECTO: DESARROLLO DE UN MINI-ARREGLO DE ANTIGENOS
FICHA PÚBLICA DEL PROYECTO PROGRAMA DE ESTÍMULOS A LA INNOVACIÓN NUMERO DE PROYECTO: 214028 EMPRESA BENEFICIADA: PHARMACOS EXAKTA S.A. DE C.V. TÍTULO DEL PROYECTO: DESARROLLO DE UN MINI-ARREGLO DE ANTIGENOS
Código: IDX-016 Ver: 1 TOXO. Sistema para la detección de la presencia de ADN de Toxoplasma gondii. Reg. MSP 21205
 Sistema para la detección de la presencia de ADN de Toxoplasma gondii Reg. MSP 21205 Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336 71 60. info@atgen.com.uy www.atgen.com.uy
Sistema para la detección de la presencia de ADN de Toxoplasma gondii Reg. MSP 21205 Valdense 3616. 11700. Montevideo. Uruguay. Teléfono (598) 2 336 83 01. Fax (598) 2 336 71 60. info@atgen.com.uy www.atgen.com.uy
Técnicas de Biología Molecular
 Técnicas de Biología Molecular DNA I. Enzimas de restricción Análisis Las enzimas de restricción fueron aisladas de bacterias; su función natural es proteger contra DNA extraño II. Separación electroforética
Técnicas de Biología Molecular DNA I. Enzimas de restricción Análisis Las enzimas de restricción fueron aisladas de bacterias; su función natural es proteger contra DNA extraño II. Separación electroforética
- Clonar un gen (molde ADN o ARN)
 APLICACIONES PCR Aplicaciones de la PCR - Clonar un gen (molde ADN o ARN) - Secuencia conocida - Genes homólogos en especies próximas (primers degenerados) - Información de secuencia proteica (primers
APLICACIONES PCR Aplicaciones de la PCR - Clonar un gen (molde ADN o ARN) - Secuencia conocida - Genes homólogos en especies próximas (primers degenerados) - Información de secuencia proteica (primers
PCR gen 18S ARNr humano
 PCR gen 18S ARNr humano Ref.PCR18S 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa (PCR)
PCR gen 18S ARNr humano Ref.PCR18S 1.OBJETIVO DEL EXPERIMENTO El objetivo de este experimento es introducir a los estudiantes en los principios y práctica de la Reacción en Cadena de la Polimerasa (PCR)
ELABORACIÓN N DE MEZCLA PARA PCR. Raquel Asunción Lima Cordón
 ELABORACIÓN N DE MEZCLA PARA PCR Raquel Asunción Lima Cordón PCR Polymerase Chain reaction (reacción en cadena de la polimerasa) Sintetizar muchas veces un fragmento de ADN PCR: simulación de lo que sucede
ELABORACIÓN N DE MEZCLA PARA PCR Raquel Asunción Lima Cordón PCR Polymerase Chain reaction (reacción en cadena de la polimerasa) Sintetizar muchas veces un fragmento de ADN PCR: simulación de lo que sucede
Reacción en cadena de la polimerasa (PCR)
 Dr. Alejandro Leal Reacción en cadena de la polimerasa (PCR) La reacción en cadena de la polimerasa (PCR, por sus siglas en inglés de "polymerase chain reaction") es un método de amplificación in vitro
Dr. Alejandro Leal Reacción en cadena de la polimerasa (PCR) La reacción en cadena de la polimerasa (PCR, por sus siglas en inglés de "polymerase chain reaction") es un método de amplificación in vitro
CLASE DE RESOLUCIÓN DE PROBLEMAS DE PCR LIC. BIOTECNOLOGÍA 2015
 CLASE DE RESOLUCIÓN DE PROBLEMAS DE PCR LIC. BIOTECNOLOGÍA 2015 DEFINICIÓN PCR: Constituye la técnica más importante para amplificar ácidos nucleicos in vitro. Ambas hebras del DNA de interés son replicadas
CLASE DE RESOLUCIÓN DE PROBLEMAS DE PCR LIC. BIOTECNOLOGÍA 2015 DEFINICIÓN PCR: Constituye la técnica más importante para amplificar ácidos nucleicos in vitro. Ambas hebras del DNA de interés son replicadas
VECTORES. Módulo, dirección y sentido de un vector fijo En un vector fijo se llama módulo del mismo a la longitud del segmento que lo define.
 VECTORES El estudio de los vectores es uno de tantos conocimientos de las matemáticas que provienen de la física. En esta ciencia se distingue entre magnitudes escalares y magnitudes vectoriales. Se llaman
VECTORES El estudio de los vectores es uno de tantos conocimientos de las matemáticas que provienen de la física. En esta ciencia se distingue entre magnitudes escalares y magnitudes vectoriales. Se llaman
ELECTROFORESIS. Agarosa. Poliacrilamida
 ELECTROFORESIS DE ADN ELECTROFORESIS Agarosa Poliacrilamida Finalidad de la electroforesis Separar Identificar Purificar 1 2 3 4 5 Tinción del ADN Bromuro de etidio Absorbancia a 302 y 366 y emisión a
ELECTROFORESIS DE ADN ELECTROFORESIS Agarosa Poliacrilamida Finalidad de la electroforesis Separar Identificar Purificar 1 2 3 4 5 Tinción del ADN Bromuro de etidio Absorbancia a 302 y 366 y emisión a
Test ( o Prueba ) de Hipótesis
 Test de Hipótesis 1 Test ( o Prueba ) de Hipótesis Ejemplo: Una muestra de 36 datos tiene una media igual a 4.64 Qué puede deducirse acerca de la población de donde fue tomada? Se necesita contestar a
Test de Hipótesis 1 Test ( o Prueba ) de Hipótesis Ejemplo: Una muestra de 36 datos tiene una media igual a 4.64 Qué puede deducirse acerca de la población de donde fue tomada? Se necesita contestar a
Identificación varietal en vid por técnicas de Biología Molecular. Lic. Luciana Garcia Lic. Carolina Chiconofri
 Identificación varietal en vid por técnicas de Biología Molecular. Lic. Luciana Garcia Lic. Carolina Chiconofri OBJETIVO Desarrollar un banco de datos a partir de plantas de origen indudable y del uso
Identificación varietal en vid por técnicas de Biología Molecular. Lic. Luciana Garcia Lic. Carolina Chiconofri OBJETIVO Desarrollar un banco de datos a partir de plantas de origen indudable y del uso
velocidades de movimiento mediante la aplicación de un campo eléctrico a través de una matriz porosa
 INTRODUCCIÓN En general, la electroforesis es una técnica que separa las moléculas en base a sus diferentes velocidades de movimiento mediante la aplicación de un campo eléctrico a través de una matriz
INTRODUCCIÓN En general, la electroforesis es una técnica que separa las moléculas en base a sus diferentes velocidades de movimiento mediante la aplicación de un campo eléctrico a través de una matriz
Informe de Servicio Social. actividades tienen en la población meta y acerca del aprendizaje obtenido por el prestador de
 Informe de Servicio Social Definición En este documento se reportan las actividades realizadas como parte del servicio social, así como los resultados obtenidos. Generalmente incluye una reflexión acerca
Informe de Servicio Social Definición En este documento se reportan las actividades realizadas como parte del servicio social, así como los resultados obtenidos. Generalmente incluye una reflexión acerca
CURSO DE EXTENSIÓN TEÓRICO PRÁCTICO HERRAMIENTAS EFICIENTES PARA LA IDENTIFICACIÓN DE LEVADURAS DE INTERÉS AGROINDUSTRIAL
 LIBRO DE MEMORIAS 2 CURSO DE EXTENSIÓN TEÓRICO PRÁCTICO HERRAMIENTAS EFICIENTES PARA LA IDENTIFICACIÓN DE LEVADURAS DE INTERÉS AGROINDUSTRIAL Santiago de Cali, 23 al 28 de agosto de 2010 3 Libro de memorias
LIBRO DE MEMORIAS 2 CURSO DE EXTENSIÓN TEÓRICO PRÁCTICO HERRAMIENTAS EFICIENTES PARA LA IDENTIFICACIÓN DE LEVADURAS DE INTERÉS AGROINDUSTRIAL Santiago de Cali, 23 al 28 de agosto de 2010 3 Libro de memorias
Identificación y caracterización de células madres cancerígenas (CMCs) en Sarcoma de Ewing
 Identificación y caracterización de células madres cancerígenas (CMCs) en Sarcoma de Ewing Introducción Una célula madre o célula troncal es una célula que tiene capacidad de autorrenovarse mediante divisiones
Identificación y caracterización de células madres cancerígenas (CMCs) en Sarcoma de Ewing Introducción Una célula madre o célula troncal es una célula que tiene capacidad de autorrenovarse mediante divisiones
ESTRUCTURA GENERAL DE LOS AMINOACIDOS A ph FISIOLOGICO
 ESTRUCTURA GENERAL DE LOS AMINOACIDOS A ph FISIOLOGICO Todos los aminoácidos tienen, como mínimo, dos grupos titulables o ionizables, cada uno con un pka característico y, por tanto, con dos zonas tampón
ESTRUCTURA GENERAL DE LOS AMINOACIDOS A ph FISIOLOGICO Todos los aminoácidos tienen, como mínimo, dos grupos titulables o ionizables, cada uno con un pka característico y, por tanto, con dos zonas tampón
AUTOR: JORGE CONTRERAS PINEDA 1. Titulo:
 Página 1 de 1 1. Titulo: Electroforesis de DNA 2. Objetivo Conocer los principios básicos de la electroforesis horizontal en geles de agarosa y aplicarlo para la separación de DNA humano, plasmídico, recombinante
Página 1 de 1 1. Titulo: Electroforesis de DNA 2. Objetivo Conocer los principios básicos de la electroforesis horizontal en geles de agarosa y aplicarlo para la separación de DNA humano, plasmídico, recombinante
Materiales para la secuenciación de ADN
 Introduccion La Secuenciación Sanger es un método de secuenciación de ADN en el que el ADN diana se desnaturaliza y se hibrida con un cebador de oligonucleótidos, que se extiende entonces gracias a la
Introduccion La Secuenciación Sanger es un método de secuenciación de ADN en el que el ADN diana se desnaturaliza y se hibrida con un cebador de oligonucleótidos, que se extiende entonces gracias a la
Técnicas de Biología Molecular. Dr. Luis Salazar N Depto. de Ciencias Básicas / UFRO
 Técnicas de Biología Molecular Dr. Luis Salazar N Depto. de Ciencias Básicas / UFRO 2004 Extracción de ácidos nucleicos o o DNA RNA Tipos de Muestras Sangre total (EDTA) Saliva Líquido Amniótico Bulbo
Técnicas de Biología Molecular Dr. Luis Salazar N Depto. de Ciencias Básicas / UFRO 2004 Extracción de ácidos nucleicos o o DNA RNA Tipos de Muestras Sangre total (EDTA) Saliva Líquido Amniótico Bulbo
DETECCIÓN DE C. jejuni EN HAMBURGUESA DE POLLO POR PCR TRADICIONAL PRT-712.04-082
 Página 1 de 5 1. OBJETIVO Detectar la presencia de Campylobacter jejuni en hamburguesa de pollo mediante técnica de PCR. 2. CAMPO DE APLICACIÓN Y ALCANCE Aplicar este procedimiento a muestras de hamburguesa
Página 1 de 5 1. OBJETIVO Detectar la presencia de Campylobacter jejuni en hamburguesa de pollo mediante técnica de PCR. 2. CAMPO DE APLICACIÓN Y ALCANCE Aplicar este procedimiento a muestras de hamburguesa
CUESTIONES. 1. Por qué la PCR convencional no es cuantitativa?
 2º BIOQUÍMICA CUESTIONES 1. Por qué la PCR convencional no es cuantitativa? En la PCR convencional, la cuantificación del ADN de la muestra es complicada debido a que la eficacia de amplificación va disminuyendo
2º BIOQUÍMICA CUESTIONES 1. Por qué la PCR convencional no es cuantitativa? En la PCR convencional, la cuantificación del ADN de la muestra es complicada debido a que la eficacia de amplificación va disminuyendo
BANCOS. Manejo de Bancos. Como crear una ficha de Banco? Como modificar los datos de una ficha de Banco? Como borrar una ficha de Banco?
 BANCOS El Sistema de Gestión Administrativa permite el manejo de los movimientos bancarios. Seleccionada la opción de Bancos, el sistema presentara las siguientes opciones. Manejo de Bancos Manejo de movimientos
BANCOS El Sistema de Gestión Administrativa permite el manejo de los movimientos bancarios. Seleccionada la opción de Bancos, el sistema presentara las siguientes opciones. Manejo de Bancos Manejo de movimientos
versus PCR en Tiempo Real PCR convencional no es cuantitativo
 PCR convencional o PCR de punto final versus PCR en Tiempo Real PCR convencional no es cuantitativo S Lobos C - U de Chile 1 PCR clásico La cantidad de producto no está relacionada con la cantidad de DNA
PCR convencional o PCR de punto final versus PCR en Tiempo Real PCR convencional no es cuantitativo S Lobos C - U de Chile 1 PCR clásico La cantidad de producto no está relacionada con la cantidad de DNA
UNIVERSIDAD DE COSTA RICA FACULTAD DE INGENIERÍA ESCUELA DE INGENIERÍA ELÉCTRICA LABORATORIO DE MÁQUINAS ELÉCTRICAS I
 UNIVERSIDAD DE COSTA RICA FACULTAD DE INGENIERÍA ESCUELA DE INGENIERÍA ELÉCTRICA LABORATORIO DE MÁQUINAS ELÉCTRICAS I Reporte 1 INTEGRANTES FÉLIX SUÁREZ BONILLA A45276 FECHA DE ENTREGA JUEVES, 15 DE FEBRERO
UNIVERSIDAD DE COSTA RICA FACULTAD DE INGENIERÍA ESCUELA DE INGENIERÍA ELÉCTRICA LABORATORIO DE MÁQUINAS ELÉCTRICAS I Reporte 1 INTEGRANTES FÉLIX SUÁREZ BONILLA A45276 FECHA DE ENTREGA JUEVES, 15 DE FEBRERO
7.012 Serie de ejercicios 5
 Nombre Grupo 7.012 Serie de ejercicios 5 Pregunta 1 Al estudiar los problemas de esterilidad, usted intenta aislar un hipotético gen de conejo que explique la prolífica reproducción de estos animales.
Nombre Grupo 7.012 Serie de ejercicios 5 Pregunta 1 Al estudiar los problemas de esterilidad, usted intenta aislar un hipotético gen de conejo que explique la prolífica reproducción de estos animales.
RESULTADOS Y DISCUSION. Los datos para la variable número de hojas por planta. Se recolectaron en 4 puntos al azar
 IX. RESULTADOS Y DISCUSION 9.1. Número de hojas por planta Los datos para la variable número de hojas por planta. Se recolectaron en 4 puntos al azar por parcela en la parcela útil, muestreando 3 plantas
IX. RESULTADOS Y DISCUSION 9.1. Número de hojas por planta Los datos para la variable número de hojas por planta. Se recolectaron en 4 puntos al azar por parcela en la parcela útil, muestreando 3 plantas
Técnicas descritas en el curso 7.28
 Técnicas descritas en el curso 7.28 Técnica: Clase 1 Experimento de incorporación de dntps Ensayo de extensión del cebador Ensayo de unión en filtro Electroforesis en gel Análisis de ADN Helicasa Polaridad
Técnicas descritas en el curso 7.28 Técnica: Clase 1 Experimento de incorporación de dntps Ensayo de extensión del cebador Ensayo de unión en filtro Electroforesis en gel Análisis de ADN Helicasa Polaridad
PROBLEMAS MÁS FRECUENTES Y POSIBLES SOLUCIONES
 PROBLEMAS MÁS FRECUENTES Y POSIBLES SOLUCIONES NO SE PRODUCE REACCIÓN O ÉSTA DECAE POCO DESPUÉS DE COMENZAR No hay ADN o hay menos del necesario No hay cebador o la concentración es inferior a la necesaria.
PROBLEMAS MÁS FRECUENTES Y POSIBLES SOLUCIONES NO SE PRODUCE REACCIÓN O ÉSTA DECAE POCO DESPUÉS DE COMENZAR No hay ADN o hay menos del necesario No hay cebador o la concentración es inferior a la necesaria.
PCR. Componentes del PCR. PCR Polymerase Chain Reaction (Reacción en Cadena de la Polimerasa)
 PCR PCR Polymerase Chain Reaction (Reacción en Cadena de la Polimerasa) Es una técnica de biología molecular descrita en 1986 por Kary Mullis. (Nobel de química en 1993) Necesidad de pruebas de diagnóstico
PCR PCR Polymerase Chain Reaction (Reacción en Cadena de la Polimerasa) Es una técnica de biología molecular descrita en 1986 por Kary Mullis. (Nobel de química en 1993) Necesidad de pruebas de diagnóstico
DIAGNÓSTICO DE LABORATORIO DE DENGUE EN PANAMÁ
 DIAGNÓSTICO DE LABORATORIO DE DENGUE EN PANAMÁ TM Brechla Moreno A. Instituto Conmemorativo Gorgas de Estudios de la Salud, Panamá Departamento de Virología y Biotecnología 2013 TÉCNICAS PARA LA DETECCIÓN
DIAGNÓSTICO DE LABORATORIO DE DENGUE EN PANAMÁ TM Brechla Moreno A. Instituto Conmemorativo Gorgas de Estudios de la Salud, Panamá Departamento de Virología y Biotecnología 2013 TÉCNICAS PARA LA DETECCIÓN
PROYECTO MEDICINA PERSONALIZADA PARA EL CÁNCER INFANTIL CÁNCER INFANTIL. Javier Alonso
 Página: 1 de 8 PROYECTO MEDICINA PERSONALIZADA PARA EL Javier Alonso Jefe de Área de Genética Humana. Jefe de la Unidad de Tumores Sólidos Infantiles del Instituto de Investigación de Enfermedades Raras,
Página: 1 de 8 PROYECTO MEDICINA PERSONALIZADA PARA EL Javier Alonso Jefe de Área de Genética Humana. Jefe de la Unidad de Tumores Sólidos Infantiles del Instituto de Investigación de Enfermedades Raras,
Detección Mediante PCR de Fusarium oxysporum f. sp. lycopersici raza 3 en el Cultivo de Tomate en República Dominicana.
 Detección Mediante PCR de Fusarium oxysporum f. sp. lycopersici raza 3 en el Cultivo de Tomate en República Dominicana. Rosa María Méndez Bautista, M.Sc * Juan.T. Camejo MSc. y Deisy Pérez PhD. * Fitopatóloga
Detección Mediante PCR de Fusarium oxysporum f. sp. lycopersici raza 3 en el Cultivo de Tomate en República Dominicana. Rosa María Méndez Bautista, M.Sc * Juan.T. Camejo MSc. y Deisy Pérez PhD. * Fitopatóloga
Caracterización morfo-agronómica y molecular de frijoles criollos de color rojo claro en Nicaragua y de frijoles negros en Ipala, Guatemala
 Caracterización morfo-agronómica y molecular de frijoles criollos de color rojo claro en Nicaragua y de frijoles negros en Ipala, Guatemala IICA/Red SICTA-CIAT INFORME DE AVANCE Gerardo Gallego - Harold
Caracterización morfo-agronómica y molecular de frijoles criollos de color rojo claro en Nicaragua y de frijoles negros en Ipala, Guatemala IICA/Red SICTA-CIAT INFORME DE AVANCE Gerardo Gallego - Harold
Operación de Microsoft Excel. Guía del Usuario Página 79. Centro de Capacitación en Informática
 Manejo básico de base de datos Unas de las capacidades de Excel es la de trabajar con listas o tablas de información: nombres, direcciones, teléfonos, etc. Excel puede trabajar con tablas de información
Manejo básico de base de datos Unas de las capacidades de Excel es la de trabajar con listas o tablas de información: nombres, direcciones, teléfonos, etc. Excel puede trabajar con tablas de información
ELECTROFORESIS BASICA
 Ref.ELECBASICA (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO ELECTROFORESIS BASICA El objetivo de este experimento es introducir a los alumnos en el conocimiento de la teoría electroforética y familiarizarse
Ref.ELECBASICA (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO ELECTROFORESIS BASICA El objetivo de este experimento es introducir a los alumnos en el conocimiento de la teoría electroforética y familiarizarse
6 FIBRAS DE TEJIDO CONJUNTIVO
 6 FIBRAS DE TEJIDO CONJUNTIVO ESTRUCTURA DEL TEMA: 6.1 Generalidades. 6.2 Fibras de colágeno. 6.3 Fibras de reticulina. 6.4 Fibras elásticas. 6.1. GENERALIDADES El tejido conjuntivo se forma por dos elementos
6 FIBRAS DE TEJIDO CONJUNTIVO ESTRUCTURA DEL TEMA: 6.1 Generalidades. 6.2 Fibras de colágeno. 6.3 Fibras de reticulina. 6.4 Fibras elásticas. 6.1. GENERALIDADES El tejido conjuntivo se forma por dos elementos
CUARTA GUÍA DE EJERCICIOS: PRUEBAS DE HIPÓTESIS
 CUARTA GUÍA DE EJERCICIOS: PRUEBAS DE HIPÓTESIS UN ESTUDIO SOBRE CARBOXIHEMOGLOBINA EN SANGRE En el estudio experimental que aquí presentamos se seleccionó al azar una muestra de 37 estudiantes de una
CUARTA GUÍA DE EJERCICIOS: PRUEBAS DE HIPÓTESIS UN ESTUDIO SOBRE CARBOXIHEMOGLOBINA EN SANGRE En el estudio experimental que aquí presentamos se seleccionó al azar una muestra de 37 estudiantes de una
SEGUNDA PRUEBA PARCIAL 20 MAYO 2015 PROF. CALVENTUS EVALUACIÓN DE TRES MÉTODOS DE ENSEÑANZA-APRENDIZAJE (ME-A)
 PSICOLOGÍA U.S.T. Estadística Inferencial SEGUNDA PRUEBA PARCIAL 20 MAYO 2015 PROF. CALVENTUS Nombre: Ptje: Nota: Esta prueba consta de 7 Preguntas y un total de 18 Puntos. La aprobación se consigue al
PSICOLOGÍA U.S.T. Estadística Inferencial SEGUNDA PRUEBA PARCIAL 20 MAYO 2015 PROF. CALVENTUS Nombre: Ptje: Nota: Esta prueba consta de 7 Preguntas y un total de 18 Puntos. La aprobación se consigue al
INSTITUTO VALLADOLID PREPARATORIA página 9
 INSTITUTO VALLADOLID PREPARATORIA página 9 página 10 FACTORIZACIÓN CONCEPTO Para entender el concepto teórico de este tema, es necesario recordar lo que se mencionó en la página referente al nombre que
INSTITUTO VALLADOLID PREPARATORIA página 9 página 10 FACTORIZACIÓN CONCEPTO Para entender el concepto teórico de este tema, es necesario recordar lo que se mencionó en la página referente al nombre que
III. Material genético. b. Composición y estructura del RNA.
 III. Material genético b. Composición y estructura del RNA. RNA (ácido ribonucléico) Polímero de nucleótidos La pentosa de los nucleótidos es la Ribosa: en la posición 2' del anillo del azúcar hay un grupo
III. Material genético b. Composición y estructura del RNA. RNA (ácido ribonucléico) Polímero de nucleótidos La pentosa de los nucleótidos es la Ribosa: en la posición 2' del anillo del azúcar hay un grupo
Enzimas de restricción
 BIOTECNOLOGIA Enzimas de restricción Endonucleasas que reconocen dianas específicas en el ADN Protegen a cada cepa de bacterias de otro ADN que no pertenece al sistema El ADN propio está protegido porque
BIOTECNOLOGIA Enzimas de restricción Endonucleasas que reconocen dianas específicas en el ADN Protegen a cada cepa de bacterias de otro ADN que no pertenece al sistema El ADN propio está protegido porque
Profr. Efraín Soto Apolinar. Factorización
 Factorización La factorización es la otra parte de la historia de los productos notables. Esto es, ambas cosas se refieren a las mismas fórmulas, pero en los productos notables se nos daba una operación
Factorización La factorización es la otra parte de la historia de los productos notables. Esto es, ambas cosas se refieren a las mismas fórmulas, pero en los productos notables se nos daba una operación
RESULTADOS Y DISCUSIÓN. Estimación de la Concentración Proteica del Filtrado de Cultivo de Mycobacterium tuberculosis H37Rv
 RESULTADOS Y DISCUSIÓN Estimación de la Concentración Proteica del Filtrado de Cultivo de Mycobacterium tuberculosis H37Rv La curva estándar con la que se estimó la concentración proteica del filtrado
RESULTADOS Y DISCUSIÓN Estimación de la Concentración Proteica del Filtrado de Cultivo de Mycobacterium tuberculosis H37Rv La curva estándar con la que se estimó la concentración proteica del filtrado
TRABAJO Y ENERGÍA. W = F d [Joule] W = F d cos α. Donde F y d son los módulos de la fuerza y el desplazamiento, y α es el ángulo que forman F y d.
![TRABAJO Y ENERGÍA. W = F d [Joule] W = F d cos α. Donde F y d son los módulos de la fuerza y el desplazamiento, y α es el ángulo que forman F y d. TRABAJO Y ENERGÍA. W = F d [Joule] W = F d cos α. Donde F y d son los módulos de la fuerza y el desplazamiento, y α es el ángulo que forman F y d.](/thumbs/31/15114944.jpg) C U R S O: FÍSICA COMÚN MATERIAL: FC-09 TRABAJO Y ENERGÍA La energía desempeña un papel muy importante en el mundo actual, por lo cual se justifica que la conozcamos mejor. Iniciamos nuestro estudio presentando
C U R S O: FÍSICA COMÚN MATERIAL: FC-09 TRABAJO Y ENERGÍA La energía desempeña un papel muy importante en el mundo actual, por lo cual se justifica que la conozcamos mejor. Iniciamos nuestro estudio presentando
Sesión 3 - Movimiento Diferencial
 Sesión 3 - Movimiento Diferencial Qué aprenderemos en esta sesión? Para entender como nuestro robot se va a desplazar por cualquier superficie, debemos aprender la manera en que lo hace, por eso, en esta
Sesión 3 - Movimiento Diferencial Qué aprenderemos en esta sesión? Para entender como nuestro robot se va a desplazar por cualquier superficie, debemos aprender la manera en que lo hace, por eso, en esta
Práctico: Genética bacteriana 2007.
 Práctico: Genética bacteriana 2007. Actividad integrada Departamento de Genética Departamento de Bacteriología y Virología. OBJETIVOS Objetivos generales El estudiante al terminar la actividad práctica
Práctico: Genética bacteriana 2007. Actividad integrada Departamento de Genética Departamento de Bacteriología y Virología. OBJETIVOS Objetivos generales El estudiante al terminar la actividad práctica
Reacción en cadena de la polymerasa (PCR)
 Reacción en cadena de la polymerasa (PCR) 1 PCR Que es? Es una técnica in vitro diseñada para amplificar una región específica de DNA. Es extremadamente sensible, con la capacidad de amplificar millones
Reacción en cadena de la polymerasa (PCR) 1 PCR Que es? Es una técnica in vitro diseñada para amplificar una región específica de DNA. Es extremadamente sensible, con la capacidad de amplificar millones
CONCEPTOS Y CRITERIOS DE LOS INDICADORES DE CALIDAD
 CONCEPTOS Y CRITERIOS DE LOS INDICADORES DE CALIDAD Las tablas con los indicadores de calidad recogen los siguientes campos: 1. Denominación de la actividad. Nombre que aparece en el Programa Estadístico
CONCEPTOS Y CRITERIOS DE LOS INDICADORES DE CALIDAD Las tablas con los indicadores de calidad recogen los siguientes campos: 1. Denominación de la actividad. Nombre que aparece en el Programa Estadístico
PROCEDIMIENTO PARA LA UTILIZACIÓN DEL POLIMORFISMO DEL GEN COMT (CATECOL-OXI-METILTRANSFERASA) EN EL DIAGNÓSTICO DEL SÍNDROME DE FIBROMIALGIA
 2 PROCEDIMIENTO PARA LA UTILIZACIÓN DEL POLIMORFISMO DEL GEN COMT (CATECOL-OXI-METILTRANSFERASA) EN EL DIAGNÓSTICO DEL SÍNDROME DE FIBROMIALGIA D E S C R I P C I Ó N OBJETO DE LA INVENCIÓN La presente
2 PROCEDIMIENTO PARA LA UTILIZACIÓN DEL POLIMORFISMO DEL GEN COMT (CATECOL-OXI-METILTRANSFERASA) EN EL DIAGNÓSTICO DEL SÍNDROME DE FIBROMIALGIA D E S C R I P C I Ó N OBJETO DE LA INVENCIÓN La presente
2. Los organizadores nucleares aportan información para la síntesis de: a- ARNm b- ARNr c- ARNt d- Histonas
 CBC UBA 2º Parcial Biología (54) Paseo Colon Apellido y Nombre:... DNI...Comisión Nº... Lea atentamente cada pregunta con sus opciones de respuesta. Marque en su grilla la opción correspondiente a la respuesta
CBC UBA 2º Parcial Biología (54) Paseo Colon Apellido y Nombre:... DNI...Comisión Nº... Lea atentamente cada pregunta con sus opciones de respuesta. Marque en su grilla la opción correspondiente a la respuesta
Qué son los monomios?
 Qué son los monomios? Recordemos qué es una expresión algebraica. Definición Una expresión algebraica es aquella en la que se utilizan letras, números y signos de operaciones. Si se observan las siguientes
Qué son los monomios? Recordemos qué es una expresión algebraica. Definición Una expresión algebraica es aquella en la que se utilizan letras, números y signos de operaciones. Si se observan las siguientes
SISTEMA DIÉDRICO PARA INGENIEROS. David Peribáñez Martínez DEMO
 SISTEMA DIÉDRICO PARA INGENIEROS David Peribáñez Martínez SISTEMA DIÉDRICO PARA INGENIEROS David Peribáñez Martínez Valderrebollo 20, 1 A 28031 MADRID 1ª Edición Ninguna parte de esta publicación, incluido
SISTEMA DIÉDRICO PARA INGENIEROS David Peribáñez Martínez SISTEMA DIÉDRICO PARA INGENIEROS David Peribáñez Martínez Valderrebollo 20, 1 A 28031 MADRID 1ª Edición Ninguna parte de esta publicación, incluido
2. NIVEL MEDIO 1. NIVEL BASICO BIOLOGIA MOLECULAR 2.1 DNA SALIVA
 BIOLOGIA MOLECULAR Hemos elaborado un programa en 3 niveles, en función del tipo de estudiante y las posibilidades del centro educativo: 1. NIVEL BASICO 2. NIVEL MEDIO DANAEXTRACTOR KIT Práctica que constituye
BIOLOGIA MOLECULAR Hemos elaborado un programa en 3 niveles, en función del tipo de estudiante y las posibilidades del centro educativo: 1. NIVEL BASICO 2. NIVEL MEDIO DANAEXTRACTOR KIT Práctica que constituye
PCR? PCR en el diagnóstico? Objetivo: Obtener un gran número de copias de un fragmento particular de ADN a partir de una cantidad mínima original.
 PCR? Objetivo: Obtener un gran número de copias de un fragmento particular de ADN a partir de una cantidad mínima original. PCR en el diagnóstico? A partir de una mezcla compleja de ADN, se puede realizar
PCR? Objetivo: Obtener un gran número de copias de un fragmento particular de ADN a partir de una cantidad mínima original. PCR en el diagnóstico? A partir de una mezcla compleja de ADN, se puede realizar
Clase de apoyo de matemáticas Ángulos Escuela 765 Lago Puelo Provincia de Chubut
 Clase de apoyo de matemáticas Ángulos Escuela 765 Lago Puelo Provincia de Chubut Este texto intenta ser un complemento de las clases de apoyo de matemáticas que se están realizando en la escuela 765 de
Clase de apoyo de matemáticas Ángulos Escuela 765 Lago Puelo Provincia de Chubut Este texto intenta ser un complemento de las clases de apoyo de matemáticas que se están realizando en la escuela 765 de
23. Hidrólisis ácida y enzimática del glucógeno
 23. Hidrólisis ácida y enzimática del glucógeno Emilia Martínez Galisteo, Carmen Alicia Padilla Peña, Concepción García Alfonso, José Antonio Bárcena Ruiz, Jesús Diez Dapena. Departamento de Bioquímica
23. Hidrólisis ácida y enzimática del glucógeno Emilia Martínez Galisteo, Carmen Alicia Padilla Peña, Concepción García Alfonso, José Antonio Bárcena Ruiz, Jesús Diez Dapena. Departamento de Bioquímica
ELECTROFORESIS AVANZADA
 Ref.ELECAVANZADA (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO ELECTROFORESIS AVANZADA El objetivo de este experimento es introducir a los alumnos en el conocimiento de la teoría electroforética y familiarizarse
Ref.ELECAVANZADA (4 prácticas) 1.OBJETIVO DEL EXPERIMENTO ELECTROFORESIS AVANZADA El objetivo de este experimento es introducir a los alumnos en el conocimiento de la teoría electroforética y familiarizarse
PROBLEMAS MAS FRECUENTES DURANTE LA SECUENCIACIÓN NO SE PRODUCE REACCION O ESTA DECAE POCO DESPUÉS DE COMENZAR
 PROBLEMAS MAS FRECUENTES DURANTE LA SECUENCIACIÓN NO SE PRODUCE REACCION O ESTA DECAE POCO DESPUÉS DE COMENZAR Las causas pueden ser las siguientes: No hay ADN o se encuentra en muy baja concentración.
PROBLEMAS MAS FRECUENTES DURANTE LA SECUENCIACIÓN NO SE PRODUCE REACCION O ESTA DECAE POCO DESPUÉS DE COMENZAR Las causas pueden ser las siguientes: No hay ADN o se encuentra en muy baja concentración.
Organización Cultura Liberal, A.C.
 2 Organización Cultura Liberal, A.C. 4.2 Organización Cultura Liberal, A.C. El 28 de julio de 2009, la Organización Cultura Liberal, A.C. entregó en tiempo y forma el Informe sobre el origen, monto y aplicación
2 Organización Cultura Liberal, A.C. 4.2 Organización Cultura Liberal, A.C. El 28 de julio de 2009, la Organización Cultura Liberal, A.C. entregó en tiempo y forma el Informe sobre el origen, monto y aplicación
Análisis de la Varianza (ANOVA) de un factor y test a posteriori.
 Análisis de la Varianza (ANOVA) de un factor y test a posteriori. Ejercicios Temas 8 y 9 (Resuelto) 1. Problema 5 Se quiere estudiar el efecto de distintas dosis de un medicamento para combatir a los parásitos
Análisis de la Varianza (ANOVA) de un factor y test a posteriori. Ejercicios Temas 8 y 9 (Resuelto) 1. Problema 5 Se quiere estudiar el efecto de distintas dosis de un medicamento para combatir a los parásitos
Tema 1: Fundamentos de lógica, teoría de conjuntos y estructuras algebraicas: Apéndice
 Tema 1: Fundamentos de lógica, teoría de conjuntos y estructuras algebraicas: Apéndice 1 Polinomios Dedicaremos este apartado al repaso de los polinomios. Se define R[x] ={a 0 + a 1 x + a 2 x 2 +... +
Tema 1: Fundamentos de lógica, teoría de conjuntos y estructuras algebraicas: Apéndice 1 Polinomios Dedicaremos este apartado al repaso de los polinomios. Se define R[x] ={a 0 + a 1 x + a 2 x 2 +... +
Nuevos paneles de PCR Real Time: El diagnóstico molecular más rápido, fiable y eficaz
 IDEXX VetLab Suite IDEXX SNAP Tests Laboratorio de Referencia IDEXX Nuevos paneles de PCR Real Time: El diagnóstico molecular más rápido, fiable y eficaz Obtenga respuestas definitivas con la IDEXX RealPCR
IDEXX VetLab Suite IDEXX SNAP Tests Laboratorio de Referencia IDEXX Nuevos paneles de PCR Real Time: El diagnóstico molecular más rápido, fiable y eficaz Obtenga respuestas definitivas con la IDEXX RealPCR
Instituto de Biomedicina y Biotecnología de Cantabria (IBBTEC) SERVICIO DE SECUENCIACIÓN MASIVA
 1. DESCRIPCIÓN DEL SERVICIO El servicio de Secuenciación Masiva tiene como finalidad el proporcionar asesoramiento y soporte técnico a los grupos de investigación interesados en realizar proyectos de ultrasecuenciación.
1. DESCRIPCIÓN DEL SERVICIO El servicio de Secuenciación Masiva tiene como finalidad el proporcionar asesoramiento y soporte técnico a los grupos de investigación interesados en realizar proyectos de ultrasecuenciación.
DIAGNOSTICO VIROLOGICO MOLECULAR. Dr. Gerardo Andino
 DIAGNOSTICO VIROLOGICO MOLECULAR Dr. Gerardo Andino DIAGNÓSTICO MOLECULAR La tecnología empleada para la detección de genomas virales mediante la amplificación de secuencias específicas (PCR y reacciones
DIAGNOSTICO VIROLOGICO MOLECULAR Dr. Gerardo Andino DIAGNÓSTICO MOLECULAR La tecnología empleada para la detección de genomas virales mediante la amplificación de secuencias específicas (PCR y reacciones
VECTORES. Se representa gráficamente por medio de una flecha, por ejemplo: Todos los vectores poseen las siguientes características:
 Un vector v es un segmento orientado. VECTORES Se representa gráficamente por medio de una flecha, por ejemplo: Todos los vectores poseen las siguientes características: Punto de aplicación: es el lugar
Un vector v es un segmento orientado. VECTORES Se representa gráficamente por medio de una flecha, por ejemplo: Todos los vectores poseen las siguientes características: Punto de aplicación: es el lugar
BCN CHECKPOINT: DETECCIÓN DE INFECCIONES AGUDAS Y SUPRESIÓN RÁPIDA DE LA CARGA VIRAL
 BCN CHECKPOINT: DETECCIÓN DE INFECCIONES AGUDAS Y SUPRESIÓN RÁPIDA DE LA CARGA VIRAL Michael Meulbroek, Ferran Pujol, Jorge Saz, Félix Pérez, Albert Dalmau-Bueno, Héctor Taboada, Giovanni Marazzi, Antonio
BCN CHECKPOINT: DETECCIÓN DE INFECCIONES AGUDAS Y SUPRESIÓN RÁPIDA DE LA CARGA VIRAL Michael Meulbroek, Ferran Pujol, Jorge Saz, Félix Pérez, Albert Dalmau-Bueno, Héctor Taboada, Giovanni Marazzi, Antonio
Tema 1. Presentación. Consideraciones históricas. Concepto de Citología e Histología. Objetivos de la asignatura. Relaciones interdisciplinarias.
 1 Tema 1. Presentación. Consideraciones históricas. Concepto de Citología e Histología. Objetivos de la asignatura. Relaciones interdisciplinarias. PRESENTACIÓN La asignatura de Citología e histología
1 Tema 1. Presentación. Consideraciones históricas. Concepto de Citología e Histología. Objetivos de la asignatura. Relaciones interdisciplinarias. PRESENTACIÓN La asignatura de Citología e histología
GENÉTICA: Herencia, Expresión génica, Replicación, biotecnología Selectividad: herencia
 GENÉTICA: Herencia, Expresión génica, Replicación, biotecnología Selectividad: herencia 5 JUN9.- Existen caracteres que no se comportan típicamente como los Mendelianos y sus patrones de herencia muestran
GENÉTICA: Herencia, Expresión génica, Replicación, biotecnología Selectividad: herencia 5 JUN9.- Existen caracteres que no se comportan típicamente como los Mendelianos y sus patrones de herencia muestran
CÁTEDRA: QUIMICA GUIA DE PROBLEMAS Nº 10
 CÁTEDRA: QUIMICA GUIA DE PROBLEMAS Nº 10 TEMA: ph, NEUTRALIZACIÓN Y EQUILIBRIO ÁCIDO BASE OBJETIVOS: Clasificar ácidos y bases de acuerdo al potencial de hidrógeno. PRERREQUISITOS: Tener conocimiento de
CÁTEDRA: QUIMICA GUIA DE PROBLEMAS Nº 10 TEMA: ph, NEUTRALIZACIÓN Y EQUILIBRIO ÁCIDO BASE OBJETIVOS: Clasificar ácidos y bases de acuerdo al potencial de hidrógeno. PRERREQUISITOS: Tener conocimiento de
Normativa para Vigilancia epidemiológica de las infecciones respiratorias agudas Provincia de Buenos Aires 27 de Abril de 2010
 Normativa para Vigilancia epidemiológica de las infecciones respiratorias agudas Provincia de Buenos Aires 27 de Abril de 2010 La vigilancia de las infecciones respiratorias agudas (IRA) incluye los eventos
Normativa para Vigilancia epidemiológica de las infecciones respiratorias agudas Provincia de Buenos Aires 27 de Abril de 2010 La vigilancia de las infecciones respiratorias agudas (IRA) incluye los eventos
Módulo 1 Biología Molecular Genética Molecular II 2009. Módulo 1. Amplificación de un fragmento de ADN genómico por PCR
 Módulo 1 Amplificación de un fragmento de ADN genómico por PCR En este primer módulo se amplificará por PCR, mediante el uso de oligonucleótidos específicos, un fragmento de ADN genómico de Aspergillus
Módulo 1 Amplificación de un fragmento de ADN genómico por PCR En este primer módulo se amplificará por PCR, mediante el uso de oligonucleótidos específicos, un fragmento de ADN genómico de Aspergillus
EJERCICIOS PROPUESTOS. 3 rad x x 2. 4 rad d) 2 rad
 TRIGONOMETRÍA EJERCICIOS PROPUESTOS.. Indica la medida de estos ángulos en radianes. a) º c) º b) º d) º a) º rad c) rad º rad b) rad º rad d) rad rad º º Epresa en grados los siguientes ángulos. a) rad
TRIGONOMETRÍA EJERCICIOS PROPUESTOS.. Indica la medida de estos ángulos en radianes. a) º c) º b) º d) º a) º rad c) rad º rad b) rad º rad d) rad rad º º Epresa en grados los siguientes ángulos. a) rad
TaqMan GMO Maize Quantification Kit. Part No: 4481972
 TaqMan GMO Maize Quantification Kit Part No: 4481972 1. Introducción Los organismos modificados genéticamente (OMG) se encuentran ampliamente distribuidos, siendo la soja y el maíz los vegetales que ocupan
TaqMan GMO Maize Quantification Kit Part No: 4481972 1. Introducción Los organismos modificados genéticamente (OMG) se encuentran ampliamente distribuidos, siendo la soja y el maíz los vegetales que ocupan
MICROBIOLOGÍA DE LOS ALIMENTOS 2015 INGENIERÍA EN ALIMENTOS LICENCIATURA EN BIOQUÍMICA TRABAJO PRÁCTICO N 1 REACCIÓN EN CADENA DE LA POLIMERASA (PCR)
 MICROBIOLOGÍA DE LOS ALIMENTOS 2015 INGENIERÍA EN ALIMENTOS LICENCIATURA EN BIOQUÍMICA TRABAJO PRÁCTICO N 1 REACCIÓN EN CADENA DE LA POLIMERASA (PCR) OBJETIVOS - Definir PCR, conocer los reactivos que
MICROBIOLOGÍA DE LOS ALIMENTOS 2015 INGENIERÍA EN ALIMENTOS LICENCIATURA EN BIOQUÍMICA TRABAJO PRÁCTICO N 1 REACCIÓN EN CADENA DE LA POLIMERASA (PCR) OBJETIVOS - Definir PCR, conocer los reactivos que
x : N Q 1 x(1) = x 1 2 x(2) = x 2 3 x(3) = x 3
 3 Sucesiones - Fernando Sánchez - - Cálculo I de números racionales 03 10 2015 Los números reales son aproximaciones que se van haciendo con números racionales. Estas aproximaciones se llaman sucesiones
3 Sucesiones - Fernando Sánchez - - Cálculo I de números racionales 03 10 2015 Los números reales son aproximaciones que se van haciendo con números racionales. Estas aproximaciones se llaman sucesiones
Índice. 4. Protocolo de envío de muestras 9 5. Problemas más frecuentes durante la secuenciación 10 6. Algunos datos y formulas de utilidad 17
 Índice Introducción 1 1. Modalidades de secuenciación 2 a. Secuenciación de una sola cadena 2 b. Secuenciación analítica 3 c. Secuenciación diagnóstica 3 2. Oligonucleótidos disponibles 5 3. Protocolo
Índice Introducción 1 1. Modalidades de secuenciación 2 a. Secuenciación de una sola cadena 2 b. Secuenciación analítica 3 c. Secuenciación diagnóstica 3 2. Oligonucleótidos disponibles 5 3. Protocolo
SIIT SISTEMA INFORMÁTICO DE INSPECCIONES DE TRABAJO. Modulo de Planificación Manual de Usuario
 SISTEMA INFORMÁTICO DE INSPECCIONES DE TRABAJO Modulo de Planificación Manual de Usuario Oficina General de Estadística e Informática Oficina de Informática Unidad de Análisis y Desarrollo MÓDULO DE PLANIFICACIÓN
SISTEMA INFORMÁTICO DE INSPECCIONES DE TRABAJO Modulo de Planificación Manual de Usuario Oficina General de Estadística e Informática Oficina de Informática Unidad de Análisis y Desarrollo MÓDULO DE PLANIFICACIÓN
Representación de un Vector
 VECTORES Vectores Los vectores se caracterizan por tener una magnitud, expresable por un número real, una dirección y un sentido. Un ejemplo de vectores son los desplazamientos. Otro ejemplo de vectores
VECTORES Vectores Los vectores se caracterizan por tener una magnitud, expresable por un número real, una dirección y un sentido. Un ejemplo de vectores son los desplazamientos. Otro ejemplo de vectores
CONCLUSIONES. Conclusiones CONCLUSIONES METODOLÓGICAS. Diseño experimental
 Conclusiones Conclusiones CONCLUSIONES CONCLUSIONES METODOLÓGICAS Diseño experimental 1. Los protocolos experimentales de extracción, amplificación y secuenciación de DNA antiguo deben adecuarse a la
Conclusiones Conclusiones CONCLUSIONES CONCLUSIONES METODOLÓGICAS Diseño experimental 1. Los protocolos experimentales de extracción, amplificación y secuenciación de DNA antiguo deben adecuarse a la
TÉCNICAS GENÓMICAS. 2) Cuantificación del número de virus presentes en muestras de sangre o suero: carga vírica
 TÉCNICAS GENÓMICAS Utilidad/Objetivos: 1) Detección de microorganismos directamente en muestras clínicas identificando un fragmento específico del genoma del microorganismo concreto 2) Cuantificación del
TÉCNICAS GENÓMICAS Utilidad/Objetivos: 1) Detección de microorganismos directamente en muestras clínicas identificando un fragmento específico del genoma del microorganismo concreto 2) Cuantificación del

