Análisis de datos de Microarreglos (usos y espectatívas ) Gerardo Coello Coutiño Unidad de Cómputo, Instituto de Fisiología Celular, UNAM
|
|
|
- José María Montes Maldonado
- hace 5 años
- Vistas:
Transcripción
1 Análisis de datos de Microarreglos (usos y espectatívas ) Gerardo Coello Coutiño Unidad de Cómputo, Instituto de Fisiología Celular, UNAM
2 MICROARREGLOS DE DNA Es una colección de oligos de DNA arreglados en una matriz o superficie sólida. Cada spot se considera un gen individual. Existen 2 tipos de microarreglos (canal único y doble canal) Puede albergar hasta genes. Generalmente son usados para medir el nivel de expresión de mrna en miles de genes simultáneamente.
3 ANTECEDENTES A más una década de su surgimiento, los microarreglos de DNA no han resultado ser la panacea que se creyó originalmente. Los microarreglos de DNA pueden ser, todavía, una herramienta útil. El análisis simultáneo de miles de genes en condiciones experimentales puede ayudar en la prevención, diagnóstico y terapia de enfermedades. Han permitido entender mejor enfermedades complejas, sobre todo aquellas que provocan cambios metabólicos generalizados.
4 COMPLEJIDAD FUNCIONAL Un sistema de análisis de datos de microarreglos, debe incorporar información adicional, de tal forma que nos permita visualizar la complejidad de la condición experimental, enfatizando las interacciones y regulación que ocurren en los sistemas biológicos. Considerar la expresión génica (mrna) exclusivamente, generalmente nos lleva a conclusiones producto de hallazgos estadísticos.
5 ANALISIS DE DATOS DE MICROARREGLOS No existe un estándar, generalmente se siguen un conjunto de pasos: 1) Preproceso filtrado de genes. a) Normalización de los datos. b) Eliminación de genes contradictorios, ruido, etc. 2) Obtención de un conjunto de genes sub/sobreexpresados. a) Gran cantidad de métodos, desde estadística simple hasta simulaciones Monte Carlo, pasando por redes neuronales. b) genarise ( 3) Agrupamiento o clustering de acuerdo al nivel de expresión. a) Basados en distancias (k means, c means, vecinos cercanos, ) redes neuronales, mapas autoorganizados, FFT, etc. 4) Exploración funcional, no utilizan nivel de expresión. a) Utilizan clasificaciones funcionales como Gene Ontology.
6 FUENTES IMPORTANTES Vías metabólicas y algo mas: Reactome (Cold Spring Harbor) y Pathways (Kegg), son, acaso, las bases de datos mas importantes en rutas metabólicas, ligandos, enzimas, función biológica y otros chismes. Vocabularios controlados y otras clasificaciones funcionales: Gene Ontology (GO). Los principales genomas han adoptado GO para anotar todos sus genes. Por otro lado, Uniprot hace anotaciones con GO a todos las proteínas curadas de su base de datos (GOA).
7 GENE ONTOLOGY (GO) Base de conocimiento, fundamentadas en la evidencia, ya sea experimental, bibliográfica o inferida electrónicamente. GO es una clasificación funcional basada en evidencias. GO es jerárquico. GO es una estructura artificial y su estructura misma puede ser modelada GO es una gráfica dirigida acíclica (DAG) GO es dinámica, se actualiza cada 30 minutos GO es la clasificación funcional mas usada y mejor anotada.
8 GO describe 3 atributos (ontologías) de los productos génicos: Molecular function (MF): Qué funciones tiene a nivel molecular? Biological process (BP): A qué procesos biológicos contribuyen esas funciones? Celullar component (CC): Dónde esta localizado en la célula? Los productos génicos participan también en otras instancias biológicas, complejas en si mismas: a) Rutas metabólicas (pathways) b) Regulación génica. c) Interacciones proteína proteína, proteina DNA, etc
9 1) Consiste de una red (DAG) cuyos nodos (términos) incluyen definiciones y descripciones funcionales de los genes. 2) Relaciones entre los nodos, principalmente: a) is a b) part of 3) Genes asociados a cada nodo, vía archivos de asociación, disponibles en los principales genomas eucariontes secuenciados
10 PROPUESTA PARA UN ANALISIS FUNCIONAL CON GENE ONTOLOGY (MAGO) 1) La población corresponde al genoma/microarreglo bajo estudio 2) La muestra de genes de entrada son todos aquellos genes del microarreglo que están up/down regulados. 3) Para cada nodo de GO y para cada ontología (BP, MF, CC) evalúa: a) Cuál es la representatividad de la muestra de entrada en el nodo? Calcula indice de representatividad omega. b) Cuál es la representatividad del nodo en la muestra de entrada? Calcula indice de representatividad rho. 4) Para todos aquellos nodos sub/sobre representados simultáneamente bajo las condiciones a y b, evalúa una métrica (función de evaluación), que depende de las variables omega y rho.
11 while (root) { hojas < get_hojas foreach hoja (hojas) { calcula omega(hoja) calcula rho(hoja) if (pvalue_rho && pvalue_omeg < p value) calcula f(omega, rho) } } remueve hoja } Root
12 METODOLOGIA GENERAL 1) A partir de los datos de un microarreglo, obtener el conjunto de genes sobre/sub (UP/DOWN) expresados usando genarise (Z score >= 1.5). Genes sobre expresados Genes sub expresados 2) Con los conjuntos UP/DOWN se hace una clasificación funcional usando Gene Ontology (MAGO p<=0.05) obtenemos los nodos significativos para BP y MF. Genes sobre expresados + Genes sub expresados BP MF
13 3) Para cada conjunto UP/DOWN, la unión de genes de los nodos significativos BP + MF es el conjunto de entrada para obtener los pathways mejor representados (significativos) en KEGG, utilizando una variación del algoritmo usado en Gene Ontology. Genes GO BP + Genes GO MF Genes KEGG Pathways UP Genes KEGG Pathways DOWN Pathways significativos
14 4) Para cada gráfica (UP/DOWN) de pathways significativos, obtenemos el pathway mas visitado aplicando el siguiente algoritmo: APSP Floyd-Warshall foreach shortest_path (u,v) = path_vertices(shortest_path); foreach vertex (@vertices) { $mas_visitado{vertex}++ } } mas_visitado = max( keys %mas_visitado) 5) Cada pathway mas visitado genera un MetaPathway, que incluye a todos los pathways que inciden en él. Pathway mas visitado Gráfica MetaPathways
15 6) Genera una gráfica (metagenes) de todos genes presentes en el Pathway. Gráfica MetaPathways Red de genes 7) Se obtienen los genes más visitados de la red de genes 8) Se obtiene la gráfica final exclusiva de los genes mas visitados y todas las relaciones que existen entre ellos.
16 Pathways involucrados (Ruta mas visitada) Análisis funcional con Gene Ontology Microarreglo t es n va s) e l r e ad o s ne visit e G as (m Red de genes MetaPathways
17 VALIDACIÓN DEL MODELO 1)Obtenemos todos los genes de las vías metabólicas de diabetes (tipo I, tipo II, juvenil) y los genes de todas las rutas metabólicas que se relacionan de manera directa con estos pathways. Obtenemos APSP con estos genes y obtenemos una muestra con los más visitados y los menos visitados. 2)Estos genes los consideramos como entrada en MAGO y los clasificamos funcionalmente. a) Reportados por MAGO MF (no BP) b) Pahways encontrados con la muestra adhoc 300 c) Pathways a partir de una muestra más visitados 30 30
18 RESULTADOS 1) Partiendo de microarreglos de células hepáticas; 5 de individuos delgados y sanos y 4 individuos obesos y diabéticos. Se normalizaron y analizaron exclusivamente los 300 genes relacionados con diabetes. a) No se encontró ningún gen específico a ninguna condición experimental 2) Se hizo el mismo análisis con todos los genes por cada microarreglo. a) Se encontraron 5 no genes expresados en los individuos sanos y 32 genes no expresados en los individuos diabéticos (10 genes no siquiera anotados). b) Se utilizaron estos genes como entrada de MAGO y se observó esto 3) Con los 27 genes encendidos/apagados se construyó una gráfica metagenes 27
19 GRACIAS POR SU ATENCION Especialmente: Dr. José Galaviz Antonio Coello Pérez MC. Ana María Escalante Dr. Jorge Ramírez Sergio Rojas Fac. Ciencias, UNAM Fac. Ciencias, UNAM IFC, UNAM IFC, UNAM IFC,UNAM
20 PROPUESTA PARA UN ANALISIS FUNCIONAL CON GENE ONTOLOGY (MAGO) 1) La población corresponde al genoma bajo estudio 2) La muestra de genes de entrada son todos aquellos genes del microarreglo que están up/down regulados. 3) Para cada nodo de GO y para cada ontología (BP, MF, CC) evalúa: a) Cuál es la representatividad de la muestra de entrada en el nodo? Calcula indice de representatividad omega. b) Cuál es la representatividad del nodo en la muestra de entrada? Calcula indice de representatividad rho. 4) Para todos aquellos nodos sobrerepresentados simultáneamente bajo las condiciones a y b, evalúa una métrica (función de evaluación), que depende de las variables omega y rho.
21 CALCULO DE OMEGA ω= Io Ie ( n ) M Ie ( n ) ; ( Io Ie ( n )) 0, pvalue 0.01 N Io = Número de genes de la muestra en el nodo n Io Ie ( n ) = nio N Número de genes que esperamos en un muestreo al azar de tamaño n M pvalue = P(i Io) ( )( ) = ( ) M M i i =Io N M n i N n N = Número de genes en el genoma o microarreglo n = Tamaño de la muestra M = Número de genes asociados al nodo de GO pvalue expectativa de encontrar cuando menos (Io) genes al azar
22 CALCULO DE RHO ρ= N M Io Ie ( M ) M Ie ( M ) Io = Número de genes de la muestra en el nodo Ie ( M ) = Io M ; ( Io Ie ( M )) 0, p value 0.01 pvalue MIo N Número de genes que esperamos en un muestreo al azar de tamaño M = P(i Io) ( )( ) = ( ) M M i i =Io N M M i N M N = Número de genes en el genoma o microarreglo M = Tamaño de la muestra M = Número de genes asociados al nodo de GO pvalue expectativa de encontrar cuando menos (Io) genes al azar
23 Definimos omega y rho como componentes de un vector en el círculo unitario. Para cada nodo (ni) de GO: v ni = ( ω ni, ρ ni ) y en coordenadas polares: v i = ( v i,θ ) 2 donde : 2 v i = ωn i + ρ n i norma Euclidiana de v i θ = arctan ρni ωn i Tanto mejores valores de un nodo cualquiera, cuanto la magnitud del vector Vi es máxima. Esto es, cuando los componentes de Vi se maximizan simul táneamente. π ρ ni ω ni = ρ ni = 1 ; vi = 2 ; θ = = 4 ω ni
24 Sea γ = tan ( 2θ π 2 ) [ π 2, π 2] con la propiedad un cero en el valor óptimo La cual mapea a θ =π 4 θ en todo ℜ cuando [θ = 0, θ = π 2] Función de Evaluación Necesitamos una función que nos entregue calificaciones exponencialmente mayores en aquellos nodos con mayor magnitud y equilibrio. vi 2 y θ π 4 Se propone la siguiente función de evaluación: f i ( v i, θ) = v i e tan 2 ( γi )
25 Efectuando manipulaciones trigonométricas y algebraicas tenemos que tan 2 (γi ) ωn i 4 +ρn i 4 = 4ω 2 ρ 2 ni ni 12 y sustituyendo en nuestra función de evaluación obtenemos finalmente fi ( ρ ni,ω ni ) = ρ ni + ω ni e ω n 4 + ρ ni 4 i 4 ω ni 2 ρ ni 2
26 while (root) { hojas < get_hojas foreach hoja (hojas) { calcula omega(hoja) calcula rho(hoja) if (pvalue_rho && pvalue_omeg < p value) calcula f(omega, rho) } } remueve hoja } Root
Técnicas de Minería de Datos
 Técnicas de Minería de Datos Act. Humberto Ramos S. 1 Qué es Minería de datos? El desarrollo de dispositivos tecnológicos para acumular datos a bajo costo. Acumulación o registro de gran cantidad de datos.
Técnicas de Minería de Datos Act. Humberto Ramos S. 1 Qué es Minería de datos? El desarrollo de dispositivos tecnológicos para acumular datos a bajo costo. Acumulación o registro de gran cantidad de datos.
GENOMICA Y PROTEOMICA
 GENOMICA Y PROTEOMICA Dr. José A Gutiérrez Bustamante Area de Genética y Biología Molecular y Celular Depto. de Morfología Humana Fac. de Medicina - UNT Célula ADN gen A gen B gen C ARN Tecnología Bioinformática
GENOMICA Y PROTEOMICA Dr. José A Gutiérrez Bustamante Area de Genética y Biología Molecular y Celular Depto. de Morfología Humana Fac. de Medicina - UNT Célula ADN gen A gen B gen C ARN Tecnología Bioinformática
Gene Ontology: GO Prof. Dr. José L. Oliver
 Gene Ontology: GO los bioquímicos caracterizan las proteínas por su actividad y concentración los genéticos caracterizan los genes por sus fenotipos y sus mutaciones todos los biólogos reconocen ahora
Gene Ontology: GO los bioquímicos caracterizan las proteínas por su actividad y concentración los genéticos caracterizan los genes por sus fenotipos y sus mutaciones todos los biólogos reconocen ahora
Predicción de potencia en el parque eólico de Villonaco, Loja, Ecuador. Alberto Reyes y Tania Guerrero INER Ecuador
 Predicción de potencia en el parque eólico de Villonaco, Loja, Ecuador Alberto Reyes y Tania Guerrero INER Ecuador INTRODUCCIÓN El comportamiento del viento presenta alto grado de aleatoriedad, incertidumbre
Predicción de potencia en el parque eólico de Villonaco, Loja, Ecuador Alberto Reyes y Tania Guerrero INER Ecuador INTRODUCCIÓN El comportamiento del viento presenta alto grado de aleatoriedad, incertidumbre
UNIVERSIDAD NACIONAL AUTÓNOMA DE MÉXICO FACULTAD DE ESTUDIOS SUPERIORES IZTACALA CARRERA BIOLOGÍA PLAN DE ESTUDIOS UNIFICADO MÓDULO DE GENÉTICA
 UNIVERSIDAD NACIONAL AUTÓNOMA DE MÉXICO FACULTAD DE ESTUDIOS SUPERIORES IZTACALA CARRERA BIOLOGÍA PLAN DE ESTUDIOS UNIFICADO MÓDULO DE GENÉTICA Objetivo general del módulo: Analizar cómo está organizado,
UNIVERSIDAD NACIONAL AUTÓNOMA DE MÉXICO FACULTAD DE ESTUDIOS SUPERIORES IZTACALA CARRERA BIOLOGÍA PLAN DE ESTUDIOS UNIFICADO MÓDULO DE GENÉTICA Objetivo general del módulo: Analizar cómo está organizado,
Una introducción a la Biología de Sistemas y a la dinámica de los sistemas biológicos.
 Una introducción a la Biología de Sistemas y a la dinámica de los sistemas biológicos. Raúl Guantes Grupo de Biodinámica y Biología Computacional Instituto de Ciencia i de Materiales Nicolás Cabrera Cb
Una introducción a la Biología de Sistemas y a la dinámica de los sistemas biológicos. Raúl Guantes Grupo de Biodinámica y Biología Computacional Instituto de Ciencia i de Materiales Nicolás Cabrera Cb
TEMA 1: INTRODUCCIÓN N AL PROCESADO Y ANÁLISIS DE DATOS
 Procesado y Análisis de Datos Ambientales. Curso 2009-2010. José D. Martín, Emilio Soria, Antonio J. Serrano TEMA 1: INTRODUCCIÓN N AL PROCESADO Y ANÁLISIS DE DATOS ÍNDICE Introducción. Selección de variables.
Procesado y Análisis de Datos Ambientales. Curso 2009-2010. José D. Martín, Emilio Soria, Antonio J. Serrano TEMA 1: INTRODUCCIÓN N AL PROCESADO Y ANÁLISIS DE DATOS ÍNDICE Introducción. Selección de variables.
Acoplamientos no-lineales entre metabolismo y regulación transcripcional: Un enfoque de termodinámica irreversible
 Acoplamientos no-lineales entre metabolismo y regulación transcripcional: Un enfoque de termodinámica irreversible Dr. Enrique Hernández Lemus Congreso Mexicano de Ciencias de la Complejidad www.inmegen.gob.mx
Acoplamientos no-lineales entre metabolismo y regulación transcripcional: Un enfoque de termodinámica irreversible Dr. Enrique Hernández Lemus Congreso Mexicano de Ciencias de la Complejidad www.inmegen.gob.mx
Comunidades. Buscando grupos naturales de nodos
 Comunidades Buscando grupos naturales de nodos cliques, -componentes (Newman 7.8.1, 7.8.2) similaridad (N7.12) Geometria: means topologia: equivalencia estructural vs equivalencia regular Clustering jerarquico
Comunidades Buscando grupos naturales de nodos cliques, -componentes (Newman 7.8.1, 7.8.2) similaridad (N7.12) Geometria: means topologia: equivalencia estructural vs equivalencia regular Clustering jerarquico
MODULARIDAD Y ESTRUCTURA DE COMUNIDADES EN REDES MATI
 MODULARIDAD Y ESTRUCTURA DE COMUNIDADES EN REDES MATI María Isabel Cardeñosa Sánchez Abraham Peña Hoyos 1 Modularidad y estructura de comunidades en redes Introducción Muchos sistemas de interés científico
MODULARIDAD Y ESTRUCTURA DE COMUNIDADES EN REDES MATI María Isabel Cardeñosa Sánchez Abraham Peña Hoyos 1 Modularidad y estructura de comunidades en redes Introducción Muchos sistemas de interés científico
Análisis de Datos. Combinación de clasificadores. Profesor: Dr. Wilfrido Gómez Flores
 Análisis de Datos Combinación de clasificadores Profesor: Dr. Wilfrido Gómez Flores 1 Introducción Diversos algoritmos de clasificación están limitados a resolver problemas binarios, es decir, con dos
Análisis de Datos Combinación de clasificadores Profesor: Dr. Wilfrido Gómez Flores 1 Introducción Diversos algoritmos de clasificación están limitados a resolver problemas binarios, es decir, con dos
Adyacencias generalizadas en genes, Ancho de Banda y Agrupamientos en la evolución de la levadura
 en genes, Ancho de Banda y Agrupamientos en la evolución de la levadura Edgar HERNÁNDEZ VENTURA CINVESTAV-Zacatenco 24 de Junio de 2010 Edgar HERNÁNDEZ VENTURA (CINVESTAV) Adjacencias Generalizadas 24
en genes, Ancho de Banda y Agrupamientos en la evolución de la levadura Edgar HERNÁNDEZ VENTURA CINVESTAV-Zacatenco 24 de Junio de 2010 Edgar HERNÁNDEZ VENTURA (CINVESTAV) Adjacencias Generalizadas 24
CONTENIDO MODELOS PARA LA LOCALIZACION DE PLANTA
 MODELOS PARA LA LOCALIZACION DE PLANTA PROFESOR: DR. JORGE ACUÑA A. 1 CONTENIDO Modelos de localización Modelos de optimización Modelo del centro de gravedad Modelo de distancias (Ardalan) Trayectorias
MODELOS PARA LA LOCALIZACION DE PLANTA PROFESOR: DR. JORGE ACUÑA A. 1 CONTENIDO Modelos de localización Modelos de optimización Modelo del centro de gravedad Modelo de distancias (Ardalan) Trayectorias
Obligatoria asignatura Programa elaborado por:
 PROGRAMA DE ESTUDIO Programa Educativo: Área de Formación : Licenciatura en Gestión Ambiental General BIOLOGÍA Horas teóricas: 2 Horas prácticas: 4 Total de Horas: 6 Total de créditos: 8 Clave: Tipo :
PROGRAMA DE ESTUDIO Programa Educativo: Área de Formación : Licenciatura en Gestión Ambiental General BIOLOGÍA Horas teóricas: 2 Horas prácticas: 4 Total de Horas: 6 Total de créditos: 8 Clave: Tipo :
ASIGNATURA: TECNOLOGÍA DE DNA RECOMBINANTE
 Página 1 de 6 CARACTERÍSTICAS GENERALES * Tipo: Formación básica, Obligatoria, Optativa Trabajo de fin de grado, Prácticas externas Duración: Cuatrimestral Semestre / s: 4 Número de créditos ECTS: 6 Idioma
Página 1 de 6 CARACTERÍSTICAS GENERALES * Tipo: Formación básica, Obligatoria, Optativa Trabajo de fin de grado, Prácticas externas Duración: Cuatrimestral Semestre / s: 4 Número de créditos ECTS: 6 Idioma
Análisis de Datos. Red de función de base radial. Profesor: Dr. Wilfrido Gómez Flores
 Análisis de Datos Red de función de base radial Profesor: Dr. Wilfrido Gómez Flores 1 Introducción Las funciones de base radial han sido utilizadas en diversas técnicas de reconocimiento de patrones como
Análisis de Datos Red de función de base radial Profesor: Dr. Wilfrido Gómez Flores 1 Introducción Las funciones de base radial han sido utilizadas en diversas técnicas de reconocimiento de patrones como
Método de los Mínimos Cuadrados Recursivos
 Método de los Mínimos Cuadrados Recursivos Teodoro Alamo a Ingeniería de Control Tercer Curso GITI Escuela Superior de Ingenieros Sevilla Formulación del problema Supongamos que los escalares y i, i =
Método de los Mínimos Cuadrados Recursivos Teodoro Alamo a Ingeniería de Control Tercer Curso GITI Escuela Superior de Ingenieros Sevilla Formulación del problema Supongamos que los escalares y i, i =
Curso de Inteligencia Artificial
 Curso de Inteligencia Artificial Modelos Ocultos de Markov Gibran Fuentes Pineda IIMAS, UNAM Redes Bayesianas Representación gráfica de relaciones probabilísticas Relaciones causales entre variables aleatorias
Curso de Inteligencia Artificial Modelos Ocultos de Markov Gibran Fuentes Pineda IIMAS, UNAM Redes Bayesianas Representación gráfica de relaciones probabilísticas Relaciones causales entre variables aleatorias
Carrera: Químico Farmacobiólogo. Asignatura: Biología Molecular. Área del Conocimiento: Fundamental. Molecular. Licenciatura Químico Farmacobiólogo
 Carrera: Químico Farmacobiólogo Asignatura: Biología Molecular Área del Conocimiento: Fundamental Generales de la Asignatura: Nombre de la Asignatura: Biología Clave Asignatura: Nivel: Carrera: Frecuencia
Carrera: Químico Farmacobiólogo Asignatura: Biología Molecular Área del Conocimiento: Fundamental Generales de la Asignatura: Nombre de la Asignatura: Biología Clave Asignatura: Nivel: Carrera: Frecuencia
Elda Falconi de la F. Reyna Fócil M., Salomón Páramo D. Fecha de elaboración: 12 de mayo de 2010 Fecha de última actualización: 17 mayo de 2010
 PROGRAMA DE ESTUDIO Programa Educativo: Área de Formación : Licenciatura en Biología, Ing. Ambiental y Gestión Ambiental General BIOLOGÍA Horas teóricas: 2 Horas : 4 Total de Horas: 6 Total de créditos:
PROGRAMA DE ESTUDIO Programa Educativo: Área de Formación : Licenciatura en Biología, Ing. Ambiental y Gestión Ambiental General BIOLOGÍA Horas teóricas: 2 Horas : 4 Total de Horas: 6 Total de créditos:
NUTRICIÓN MOLECULAR. Nutrigenética y Nutrigenómica. Academia de Medicina Genómica Semestre Ene-Jun 2017.
 NUTRICIÓN MOLECULAR Nutrigenética y Nutrigenómica Academia de Medicina Genómica Semestre Ene-Jun 2017. 1 La relación entre la alimentación, la salud y la genómica. La dieta es un factor ambiental que afecta
NUTRICIÓN MOLECULAR Nutrigenética y Nutrigenómica Academia de Medicina Genómica Semestre Ene-Jun 2017. 1 La relación entre la alimentación, la salud y la genómica. La dieta es un factor ambiental que afecta
Tutorial Uso y manejo básico de EupathDB. TritrypDB como modelo.
 Tutorial Uso y manejo básico de EupathDB. TritrypDB como modelo. Dr. Luis Miguel de Pablos Torró FEBS associated Postdoctoral Researcher. University of Cambridge. EuPathDB (hfp://eupathdb.org) es una base
Tutorial Uso y manejo básico de EupathDB. TritrypDB como modelo. Dr. Luis Miguel de Pablos Torró FEBS associated Postdoctoral Researcher. University of Cambridge. EuPathDB (hfp://eupathdb.org) es una base
UNIVERSIDAD CARLOS III DE MADRID Ingeniería Informática Examen de Investigación Operativa
 UNIVERSIDAD CARLOS III DE MADRID Ingeniería Informática Examen de Investigación Operativa 8 de Septiembre de 23 25 puntos Dado el problema lineal máx x + x 2 x 3 sa x + x 2 + x 3 2 2x x 2 x 3 2 x, se pide
UNIVERSIDAD CARLOS III DE MADRID Ingeniería Informática Examen de Investigación Operativa 8 de Septiembre de 23 25 puntos Dado el problema lineal máx x + x 2 x 3 sa x + x 2 + x 3 2 2x x 2 x 3 2 x, se pide
Forma polar de números complejos (repaso breve)
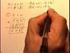 Forma polar de números complejos (repaso breve) Objetivos. pasar la forma polar de números complejos. quisitos. Números complejos, funciones trigonométricas, valor absoluto de números complejos, circunferencia
Forma polar de números complejos (repaso breve) Objetivos. pasar la forma polar de números complejos. quisitos. Números complejos, funciones trigonométricas, valor absoluto de números complejos, circunferencia
REDES NEURONALES. Una esquema simplificado de una neurona se muestra en la siguiente figura. Cuerpo celular. Dendrita. Axón.
 REDES NEURONALES Las redes neuronales constituyen una poderosa herramienta para modelar sistemas, especialmente no lineales, sean dinámicos o estáticos. En el cuerpo celular se realizan la mayoría de las
REDES NEURONALES Las redes neuronales constituyen una poderosa herramienta para modelar sistemas, especialmente no lineales, sean dinámicos o estáticos. En el cuerpo celular se realizan la mayoría de las
Definiciones: conjuntos, grafos, y árboles. Agustín J. González ELO 320: Estructura de Datos y Algoritmos. 2002
 Definiciones: conjuntos, grafos, y árboles Agustín J. González ELO 320: Estructura de Datos y Algoritmos. 2002 1 Conjuntos (sets) y Grafos (graphs) Un Conjunto es una colección de objetos distintos. No
Definiciones: conjuntos, grafos, y árboles Agustín J. González ELO 320: Estructura de Datos y Algoritmos. 2002 1 Conjuntos (sets) y Grafos (graphs) Un Conjunto es una colección de objetos distintos. No
Minería de Datos Web. Cursada 2018
 Minería de Datos Web Cursada 2018 Proceso de Minería de Texto Clustering de Documentos Clasificación de Documentos Es un método supervisado para dividir documentos en base a categorías predefinidas Los
Minería de Datos Web Cursada 2018 Proceso de Minería de Texto Clustering de Documentos Clasificación de Documentos Es un método supervisado para dividir documentos en base a categorías predefinidas Los
Ejercicios - Resolución de problemas lineales. Método Simplex
 Ejercicios - Resolución de problemas lineales. Método Simplex Programación Matemática LADE Curso 8/9. Dado el problema lineal máx x x x + x s.a. x + x + x = 4 x + x 4 x justifica que el punto x = ( T es
Ejercicios - Resolución de problemas lineales. Método Simplex Programación Matemática LADE Curso 8/9. Dado el problema lineal máx x x x + x s.a. x + x + x = 4 x + x 4 x justifica que el punto x = ( T es
TÉCNICO SUPERIOR UNIVERSITARIO EN QUÍMICA ÁREA BIOTECNOLOGÍA EN COMPETENCIAS PROFESIONALES ASIGNATURA DE PROCESOS DE LA SALUD
 TÉCNICO SUPERIOR UNIVERSITARIO EN QUÍMICA ÁREA BIOTECNOLOGÍA EN COMPETENCIAS PROFESIONALES ASIGNATURA DE PROCESOS DE LA SALUD UNIDADES DE APRENDIZAJE 1. Competencias Transformar materias primas a través
TÉCNICO SUPERIOR UNIVERSITARIO EN QUÍMICA ÁREA BIOTECNOLOGÍA EN COMPETENCIAS PROFESIONALES ASIGNATURA DE PROCESOS DE LA SALUD UNIDADES DE APRENDIZAJE 1. Competencias Transformar materias primas a través
Programa de Estudios por Competencias Biología Molecular. Área de docencia: MORFOFUNCIONAL
 I. IDENTIFICACIÓN DEL CURSO Programa de Estudios por Competencias Biología Molecular ORGANISMO ACADÉMICO: Facultad de Medicina Programa Educativo: Licenciatura en Médico Cirujano Aprobación por los H.H.
I. IDENTIFICACIÓN DEL CURSO Programa de Estudios por Competencias Biología Molecular ORGANISMO ACADÉMICO: Facultad de Medicina Programa Educativo: Licenciatura en Médico Cirujano Aprobación por los H.H.
Introducción al NCBI
 Introducción al NCBI National Center for Biotechnology Information Andrés M. Pinzón Centro de Bioinformática Instituto de Biotecnología Universidad Nacional de Colombia Qué es el NCBI? http://www.ncbi.nlm.nih.gov/
Introducción al NCBI National Center for Biotechnology Information Andrés M. Pinzón Centro de Bioinformática Instituto de Biotecnología Universidad Nacional de Colombia Qué es el NCBI? http://www.ncbi.nlm.nih.gov/
DNA MICROARRAYS: EXPERIMENTOS COMPARATIVOS. JUAN CARLOS OLIVEROS COLLAZOS BioinfoGP, CNB-CSIC
 DNA MICROARRAYS: EXPERIMENTOS COMPARATIVOS BioinfoGP, CNB-CSIC INTRODUCCIÓN GENERAL GENOMAS, GENES Y PROTEÍNAS GENOMA: CONJUNTO DE TODOS LOS GENES DE UN ORGANISMO GEN: UNIDAD DE ALMACENAMIENTO DE INFORMACIÓN
DNA MICROARRAYS: EXPERIMENTOS COMPARATIVOS BioinfoGP, CNB-CSIC INTRODUCCIÓN GENERAL GENOMAS, GENES Y PROTEÍNAS GENOMA: CONJUNTO DE TODOS LOS GENES DE UN ORGANISMO GEN: UNIDAD DE ALMACENAMIENTO DE INFORMACIÓN
1. Análisis de Conglomerados
 1. Análisis de Conglomerados El objetivo de este análisis es formar grupos de observaciones, de manera que todas las unidades en un grupo sean similares entre ellas pero que sean diferentes a aquellas
1. Análisis de Conglomerados El objetivo de este análisis es formar grupos de observaciones, de manera que todas las unidades en un grupo sean similares entre ellas pero que sean diferentes a aquellas
Competencias Generales
 3.2. COMPETENCIAS Competencias Generales Se muestra a continuación el listado final de competencias generales del título: CG01. Desarrollar las habilidades de aprendizaje necesarias para emprender actividades
3.2. COMPETENCIAS Competencias Generales Se muestra a continuación el listado final de competencias generales del título: CG01. Desarrollar las habilidades de aprendizaje necesarias para emprender actividades
Dinámica del Robot. UCR ECCI CI-2657 Robótica Prof. M.Sc. Kryscia Daviana Ramírez Benavides
 UCR ECCI CI-2657 Robótica Prof. M.Sc. Kryscia Daviana Ramírez Benavides Introducción La dinámica se ocupa de la relación entre las fuerzas que actúan sobre un cuerpo y el movimiento en el que se origina.
UCR ECCI CI-2657 Robótica Prof. M.Sc. Kryscia Daviana Ramírez Benavides Introducción La dinámica se ocupa de la relación entre las fuerzas que actúan sobre un cuerpo y el movimiento en el que se origina.
Perfil de egreso del programa educativo.
 Perfil de egreso del programa educativo. PERIODO: AGOSTO 2010 - FEBRERO 2011 PLANEACIÓN DEL CURSO El egresado de la Facultad de Ingeniería en Sistemas de producción agropecuaria, será un profesional capaz
Perfil de egreso del programa educativo. PERIODO: AGOSTO 2010 - FEBRERO 2011 PLANEACIÓN DEL CURSO El egresado de la Facultad de Ingeniería en Sistemas de producción agropecuaria, será un profesional capaz
COMPETENCIAS DEL MÁSTER EN INVESTIGACIÓN BIOMÉDICA POR LA UNIVERSIDAD DE NAVARRA
 COMPETENCIAS DEL MÁSTER EN INVESTIGACIÓN BIOMÉDICA POR LA UNIVERSIDAD DE NAVARRA Competencias generales del Máster en Investigación Biomédica por la Universidad de Navarra CG1: Abordar un reto biomédico
COMPETENCIAS DEL MÁSTER EN INVESTIGACIÓN BIOMÉDICA POR LA UNIVERSIDAD DE NAVARRA Competencias generales del Máster en Investigación Biomédica por la Universidad de Navarra CG1: Abordar un reto biomédico
Herramientas de Bioinformática en NGS
 Herramientas de Bioinformática en NGS Ing. Sergio Gonzalez CICVyA - Instituto de Biotecnología INTA gonzalez.sergio@inta.gob.ar Temario Introducción NGS Análisis de calidad Ensamblado Anotación Estructural
Herramientas de Bioinformática en NGS Ing. Sergio Gonzalez CICVyA - Instituto de Biotecnología INTA gonzalez.sergio@inta.gob.ar Temario Introducción NGS Análisis de calidad Ensamblado Anotación Estructural
Grado en Biotecnología
 Grado en Biotecnología Competencias Generales Se muestra a continuación el listado final de competencias generales del título: CG01. Aplicar de forma profesional a su trabajo los conocimientos adquiridos
Grado en Biotecnología Competencias Generales Se muestra a continuación el listado final de competencias generales del título: CG01. Aplicar de forma profesional a su trabajo los conocimientos adquiridos
Grafos y Redes. 3. Resolución: Dibujar el camino sin levantar el lápiz y pasando sólo una vez por cada arco o arista.
 Grafos y Redes. Nodos: vértices, 2, 3 2. Arcos: aristas, conexión entre nodos. 2, 54, etc. 3. Resolución: Dibujar el camino sin levantar el lápiz y pasando sólo una vez por cada arco o arista. 4. Grado
Grafos y Redes. Nodos: vértices, 2, 3 2. Arcos: aristas, conexión entre nodos. 2, 54, etc. 3. Resolución: Dibujar el camino sin levantar el lápiz y pasando sólo una vez por cada arco o arista. 4. Grado
Biología (54208) Profesora: Dra. Marlys Campos
 Biología (54208) Profesora: Dra. Marlys Campos 2-2016 Profesora Teoría: Dra. Marlys Campos C. http://www.udesantiagovirtual.cl/moodle2/ Teoría: Lunes (13:50-15:20) Jueves (9:40-11:10) Laboratorio: Lunes
Biología (54208) Profesora: Dra. Marlys Campos 2-2016 Profesora Teoría: Dra. Marlys Campos C. http://www.udesantiagovirtual.cl/moodle2/ Teoría: Lunes (13:50-15:20) Jueves (9:40-11:10) Laboratorio: Lunes
Unidad N 13: Regulación de la Expresión génica en Procariontes
 Unidad N 13: Regulación de la Expresión génica en Procariontes IMPORANCIA DE LA REGULACIÓN GÉNICA Las bacterias poseen numerosos mecanismos para controlar la expresión de sus miles de genes, con los cuales
Unidad N 13: Regulación de la Expresión génica en Procariontes IMPORANCIA DE LA REGULACIÓN GÉNICA Las bacterias poseen numerosos mecanismos para controlar la expresión de sus miles de genes, con los cuales
UNIVERSIDAD AUTÓNOMA DE SAN LUIS POTOSÍ FACULTAD DE CIENCIAS QUÍMICAS POSGRADO EN CIENCIAS FARMACOBIOLÓGICAS Programas de Cursos
 BIOLOGÍA MOLECULAR Y ADN RECOMBINANTE Profesores Dra. Perla del Carmen Niño Moreno Profesor-Investigador Tiempo Completo Nivel VI Dra. Ruth Elena Soria Guerra. Profesor-Investigador Tiempo Completo Nivel
BIOLOGÍA MOLECULAR Y ADN RECOMBINANTE Profesores Dra. Perla del Carmen Niño Moreno Profesor-Investigador Tiempo Completo Nivel VI Dra. Ruth Elena Soria Guerra. Profesor-Investigador Tiempo Completo Nivel
Dra. Tzvetanka Dimitrova Dinkova Lab 103, Depto. Bioquimica, Conjunto E, Fac. Quimica Tel: ; correo electronico:
 GENETICA y BIOLOGIA MOLECULAR Dra. Tzvetanka Dimitrova Dinkova Lab 103, Depto. Bioquimica, Conjunto E, Fac. Quimica Tel: 56225277; correo electronico: cesy@unam.mx Apoyo material audiovisual, referencias
GENETICA y BIOLOGIA MOLECULAR Dra. Tzvetanka Dimitrova Dinkova Lab 103, Depto. Bioquimica, Conjunto E, Fac. Quimica Tel: 56225277; correo electronico: cesy@unam.mx Apoyo material audiovisual, referencias
PLAN 401 E X Á M E N E S P A R C I A L E S HORARIO
 411 412 413 414 COMPETENCIA COMUNICATIVA 2 27 8 15 BIOÉTICA 27 24 5 12 AS104 09:00 CÁLCULO Y ALGEBRA LINEAL 2 27 8 15 AS104 08:00 QUÍMICA GENERAL 28 25 6 13 AS104 11:00 EVOLUCIÓN Y SISTEMÁTICA 26 23 4
411 412 413 414 COMPETENCIA COMUNICATIVA 2 27 8 15 BIOÉTICA 27 24 5 12 AS104 09:00 CÁLCULO Y ALGEBRA LINEAL 2 27 8 15 AS104 08:00 QUÍMICA GENERAL 28 25 6 13 AS104 11:00 EVOLUCIÓN Y SISTEMÁTICA 26 23 4
Sistemas de Reconocimiento de Patrones
 Sistemas de Reconocimiento de Patrones p. 1/33 Sistemas de Reconocimiento de Patrones Luis Vázquez GTI - IIE Facultad de Ingeniería Universidad de la República Sistemas de Reconocimiento de Patrones p.
Sistemas de Reconocimiento de Patrones p. 1/33 Sistemas de Reconocimiento de Patrones Luis Vázquez GTI - IIE Facultad de Ingeniería Universidad de la República Sistemas de Reconocimiento de Patrones p.
Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular
 Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular Aislamiento, análisis y manipulación de ácidos nucleicos Generación de moléculas de DNA recombinante Ingeniería Genética AISLAMIENTO
Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular Aislamiento, análisis y manipulación de ácidos nucleicos Generación de moléculas de DNA recombinante Ingeniería Genética AISLAMIENTO
Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular
 Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular Aislamiento, análisis y manipulación de ácidos nucleicos Generación de moléculas de DNA recombinante Ingeniería Genética AISLAMIENTO
Unidad9. Principios de Ingeniería Genética Aplicaciones de Biología Molecular Aislamiento, análisis y manipulación de ácidos nucleicos Generación de moléculas de DNA recombinante Ingeniería Genética AISLAMIENTO
UNIVERSIDAD JUÁREZ AUTÓNOMA DE TABASCO DIVISIÓN ACADÉMICA DE CIENCIAS BIOLÓGICAS LICENCIATURA EN ECOLOGIA
 UNIVERSIDAD JUÁREZ AUTÓNOMA TABASCO DIVISIÓN ACADÉMICA CIENCIAS BIOLÓGICAS LICENCIATURA EN ECOLOGIA ASIGNATURA: BIOLOGÍA AREA: SUSTANTIVA PROFESIONAL HORAS TEORICAS: 3 HORAS PRACTICAS:3 CREDITOS:9 ASIGNATURAS
UNIVERSIDAD JUÁREZ AUTÓNOMA TABASCO DIVISIÓN ACADÉMICA CIENCIAS BIOLÓGICAS LICENCIATURA EN ECOLOGIA ASIGNATURA: BIOLOGÍA AREA: SUSTANTIVA PROFESIONAL HORAS TEORICAS: 3 HORAS PRACTICAS:3 CREDITOS:9 ASIGNATURAS
Campo Magnético en un alambre recto.
 Campo Magnético en un alambre recto. A.M. Velasco (133384) J.P. Soler (133380) O.A. Botina (133268) Departamento de física, facultad de ciencias, Universidad Nacional de Colombia Resumen. Se hizo pasar
Campo Magnético en un alambre recto. A.M. Velasco (133384) J.P. Soler (133380) O.A. Botina (133268) Departamento de física, facultad de ciencias, Universidad Nacional de Colombia Resumen. Se hizo pasar
El primer asomo de la raíz cuadrada de un número negativo se presentó en la stereometría de Herón de Alejandría (año 50), y más tarde en la
 El primer asomo de la raíz cuadrada de un número negativo se presentó en la stereometría de Herón de Alejandría (año 50), y más tarde en la aritmética de Diofanto (año 275). 56 8i 14 + 10i 1. Trata la
El primer asomo de la raíz cuadrada de un número negativo se presentó en la stereometría de Herón de Alejandría (año 50), y más tarde en la aritmética de Diofanto (año 275). 56 8i 14 + 10i 1. Trata la
Formulación del problema de la ruta más corta en programación lineal
 Formulación del problema de la ruta más corta en programación lineal En esta sección se describen dos formulaciones de programación lineal para el problema de la ruta más corta. Las formulaciones son generales,
Formulación del problema de la ruta más corta en programación lineal En esta sección se describen dos formulaciones de programación lineal para el problema de la ruta más corta. Las formulaciones son generales,
Análisis de imágenes digitales
 Análisis de imágenes digitales SEGMENTACIÓN DE LA IMAGEN Segmentación basada en texturas INTRODUCCIÓN La textura provee información sobre la distribución espacio-local del color o niveles de intensidades
Análisis de imágenes digitales SEGMENTACIÓN DE LA IMAGEN Segmentación basada en texturas INTRODUCCIÓN La textura provee información sobre la distribución espacio-local del color o niveles de intensidades
Inteligencia de Negocio
 UNIVERSIDAD DE GRANADA E.T.S. de Ingenierías Informática y de Telecomunicación Departamento de Ciencias de la Computación e Inteligencia Artificial Inteligencia de Negocio Guión de Prácticas Práctica 3:
UNIVERSIDAD DE GRANADA E.T.S. de Ingenierías Informática y de Telecomunicación Departamento de Ciencias de la Computación e Inteligencia Artificial Inteligencia de Negocio Guión de Prácticas Práctica 3:
Representación y manipulación de grafos: caminos, expansión, cortes y flujos
 Un grafo G es un par de conjuntos G =(V,E) Representación y manipulación de grafos: caminos, expansión, cortes y flujos V = un conjunto de n vértices u, v, w V E = un conjunto de m aristas V = n, E = m
Un grafo G es un par de conjuntos G =(V,E) Representación y manipulación de grafos: caminos, expansión, cortes y flujos V = un conjunto de n vértices u, v, w V E = un conjunto de m aristas V = n, E = m
CURSO DE POSTGRADO BIOLOGIA CELULAR Y MOLECULAR AVANZADA
 UNIVERSIDAD DE CHILE FACULTAD DE MEDICINA ESCUELA DE POSTGRADO CURSO DE POSTGRADO BIOLOGIA CELULAR Y MOLECULAR AVANZADA Nombre Curso SEMESTRE 1º AÑO 2015 PROF. ENCARGADO ANDREW QUEST VICENTE TORRES MARIO
UNIVERSIDAD DE CHILE FACULTAD DE MEDICINA ESCUELA DE POSTGRADO CURSO DE POSTGRADO BIOLOGIA CELULAR Y MOLECULAR AVANZADA Nombre Curso SEMESTRE 1º AÑO 2015 PROF. ENCARGADO ANDREW QUEST VICENTE TORRES MARIO
TÉCNICAS INTELIGENTES EN BIOINFORMÁTICA. Alineamiento múltiple de secuencias
 TÉCNICAS INTELIGENTES EN BIOINFORMÁTICA Alineamiento múltiple de secuencias Mario de J. Pérez Jiménez Grupo de investigación en Computación Natural Dpto. Ciencias de la Computación e Inteligencia Artificial
TÉCNICAS INTELIGENTES EN BIOINFORMÁTICA Alineamiento múltiple de secuencias Mario de J. Pérez Jiménez Grupo de investigación en Computación Natural Dpto. Ciencias de la Computación e Inteligencia Artificial
UNIDAD 4: SEÑALIZACIÓN CELULAR
 UNIDAD 4: SEÑALIZACIÓN CELULAR SEÑALIZACIÓN CELULAR El mecanismo básico Requiere: 1. Un LIGANDO (molécula señalizadora) 2. Un RECEPTOR (molécula receptora) que une al ligando Conjunto de procesos o etapas
UNIDAD 4: SEÑALIZACIÓN CELULAR SEÑALIZACIÓN CELULAR El mecanismo básico Requiere: 1. Un LIGANDO (molécula señalizadora) 2. Un RECEPTOR (molécula receptora) que une al ligando Conjunto de procesos o etapas
Nombre/Código: Septiembre Parcial II
 1 Cálculo II Sección 1 Guillermo Mantilla Nombre/Código: Septiembre 11 1 Parcial II Instrucciones: Duración 7mins. Durante el examen no son permitidos libros, notas, calculadoras, celulares o en general
1 Cálculo II Sección 1 Guillermo Mantilla Nombre/Código: Septiembre 11 1 Parcial II Instrucciones: Duración 7mins. Durante el examen no son permitidos libros, notas, calculadoras, celulares o en general
Adriana Schnek, Alicia Massarini CURTIS. BIOLOGÍA
 Adriana Schnek, Alicia Massarini CURTIS. BIOLOGÍA AUTORES Adriana Schnek, Alicia Massarini EAN: 9789500603348 Edición: 7ª Especialidad: Biología Páginas: 1160 Encuadernación: Cartoné Formato:20 cm x 28
Adriana Schnek, Alicia Massarini CURTIS. BIOLOGÍA AUTORES Adriana Schnek, Alicia Massarini EAN: 9789500603348 Edición: 7ª Especialidad: Biología Páginas: 1160 Encuadernación: Cartoné Formato:20 cm x 28
Los pasos que se dan son:
 Hasta ahora hemos admitido que podemos trabajar con la red de cores de nuestro sólido usando una aproximación clásica lo que nos ha permitido determinar los «modos normales de vibración» en el sentido
Hasta ahora hemos admitido que podemos trabajar con la red de cores de nuestro sólido usando una aproximación clásica lo que nos ha permitido determinar los «modos normales de vibración» en el sentido
Minería de datos clínicos y biológicos en el proyecto EU-ADR
 Minería de datos clínicos y biológicos en el proyecto EU-ADR Laura I. Furlong Programa de Recerca en Informàtica Biomèdica (GRIB) IMIM (Institut de Recerca Hospital del Mar) Universitat Pompeu Fabra IV
Minería de datos clínicos y biológicos en el proyecto EU-ADR Laura I. Furlong Programa de Recerca en Informàtica Biomèdica (GRIB) IMIM (Institut de Recerca Hospital del Mar) Universitat Pompeu Fabra IV
TÉCNICAS INTELIGENTES EN BIOINFORMÁTICA CLUSTERING
 TÉCNICAS INTELIGENTES EN BIOINFORMÁTICA CLUSTERING Mario de J. Pérez Jiménez Grupo de investigación en Computación Natural Dpto. Ciencias de la Computación e Inteligencia Artificial Universidad de Sevilla
TÉCNICAS INTELIGENTES EN BIOINFORMÁTICA CLUSTERING Mario de J. Pérez Jiménez Grupo de investigación en Computación Natural Dpto. Ciencias de la Computación e Inteligencia Artificial Universidad de Sevilla
Evaluación de la incertidumbre en el cálculo de áreas sobre una determinada cartografía
 Evaluación de la incertidumbre en el cálculo de áreas sobre una determinada cartografía Planteamiento del problema Antecedentes Resultados Conclusiones 1 Planteamiento del problema Habitualmente se presentan
Evaluación de la incertidumbre en el cálculo de áreas sobre una determinada cartografía Planteamiento del problema Antecedentes Resultados Conclusiones 1 Planteamiento del problema Habitualmente se presentan
APORTE AL DISEÑO DE ENGRANAJES NO CIRCULARES CILÍNDRICOS RECTOS
 UNIVERSIDAD POLITÉCNICA DE CATALUÑA Escuela Técnica Superior de Ingeniería Industrial de Barcelona Departamento de Ingeniería Mecánica Tesis Doctoral APORTE AL DISEÑO DE ENGRANAJES NO CIRCULARES CILÍNDRICOS
UNIVERSIDAD POLITÉCNICA DE CATALUÑA Escuela Técnica Superior de Ingeniería Industrial de Barcelona Departamento de Ingeniería Mecánica Tesis Doctoral APORTE AL DISEÑO DE ENGRANAJES NO CIRCULARES CILÍNDRICOS
LA FORMA TRIGONOMETRICA DE LOS NUMEROS COMPLEJOS Y EL TEOREMA DE MOIVRE. Capítulo 7 Sec. 7.5 y 7.6
 LA FORMA TRIGONOMETRICA DE LOS NUMEROS COMPLEJOS Y EL TEOREMA DE MOIVRE Capítulo 7 Sec. 7.5 y 7.6 El Plano Complejo Se puede utilizar un plano de coordenadas para representar números complejos. Si cada
LA FORMA TRIGONOMETRICA DE LOS NUMEROS COMPLEJOS Y EL TEOREMA DE MOIVRE Capítulo 7 Sec. 7.5 y 7.6 El Plano Complejo Se puede utilizar un plano de coordenadas para representar números complejos. Si cada
Estadística con R. Clasificadores
 Estadística con R Clasificadores Análisis discriminante lineal (estadístico) Árbol de decisión (aprendizaje automático) Máquina soporte vector (aprendizaje automático) Análisis discriminante lineal (AD)
Estadística con R Clasificadores Análisis discriminante lineal (estadístico) Árbol de decisión (aprendizaje automático) Máquina soporte vector (aprendizaje automático) Análisis discriminante lineal (AD)
MOVIMIENTO DEL AGUA EN FORMACIONES GEOLÓGICAS. 4.1 Conservación de Fluido de Masa
 MOVIMIENTO DEL AGUA EN FORMACIONES GEOLÓGICAS 4.1 Conservación de Fluido de Masa Considerando un fluido elemental con volumen V y superficie S que está asociado a un cuerpo fluido (en este caso agua).
MOVIMIENTO DEL AGUA EN FORMACIONES GEOLÓGICAS 4.1 Conservación de Fluido de Masa Considerando un fluido elemental con volumen V y superficie S que está asociado a un cuerpo fluido (en este caso agua).
BIOLOGÍA III Unidad 1. Cómo los procesos metabólicos energéticos contribuyen a la conservación de los sistemas biológicos?
 BIOLOGÍA III Unidad 1. Cómo los procesos metabólicos energéticos contribuyen a la conservación de los sistemas biológicos? 15 Propósito: Describirá la importancia del metabolismo, a través del análisis
BIOLOGÍA III Unidad 1. Cómo los procesos metabólicos energéticos contribuyen a la conservación de los sistemas biológicos? 15 Propósito: Describirá la importancia del metabolismo, a través del análisis
Ruta más Corta con una sóla Fuente de Inicio (Single-Source Shortest Paths) DR. JESÚS A. GONZÁLEZ BERNAL CIENCIAS COMPUTACIONALES INAOE
 Ruta más Corta con una sóla Fuente de Inicio (Single-Source Shortest Paths) 1 DR. JESÚS A. GONZÁLEZ BERNAL CIENCIAS COMPUTACIONALES INAOE Problema de Encontrar la Ruta más Corta 2 Se requiere llegar de
Ruta más Corta con una sóla Fuente de Inicio (Single-Source Shortest Paths) 1 DR. JESÚS A. GONZÁLEZ BERNAL CIENCIAS COMPUTACIONALES INAOE Problema de Encontrar la Ruta más Corta 2 Se requiere llegar de
Resistencia de los Materiales
 Resistencia de los Materiales Clase 4: Torsión y Transmisión de Potencia Dr.Ing. Luis Pérez Pozo luis.perez@usm.cl Pontificia Universidad Católica de Valparaíso Escuela de Ingeniería Industrial Primer
Resistencia de los Materiales Clase 4: Torsión y Transmisión de Potencia Dr.Ing. Luis Pérez Pozo luis.perez@usm.cl Pontificia Universidad Católica de Valparaíso Escuela de Ingeniería Industrial Primer
TOTAL DE CRÉDITOS 6 DOCENTE RESPONSABLE. Jorge Iglesias / Pamela Ramírez DATOS DE CONTACTO CORREO ELECTRÓNICO
 FACULTAD DE CIENCIAS NATURALES Y EXACTAS Pedagogía en Biología y Ciencias Actividad Curricular "Fisiología Vegetal ESTRUCTURA DE LA ACTIVIDAD CURRCICULAR NOMBRE DEL MODULO Fisiología Vegetal TOTAL DE CRÉDITOS
FACULTAD DE CIENCIAS NATURALES Y EXACTAS Pedagogía en Biología y Ciencias Actividad Curricular "Fisiología Vegetal ESTRUCTURA DE LA ACTIVIDAD CURRCICULAR NOMBRE DEL MODULO Fisiología Vegetal TOTAL DE CRÉDITOS
Genética y Bioética (Gen-Ética)
 Genética y Bioética (Gen-Ética) Dr. Jorge Ramírez Zenteno Chihuahua. Chih. Marzo 16 de 2016 Donde la vida y la Ética se Articulan Es el espacio de intervención modificadora de nuestro material genético
Genética y Bioética (Gen-Ética) Dr. Jorge Ramírez Zenteno Chihuahua. Chih. Marzo 16 de 2016 Donde la vida y la Ética se Articulan Es el espacio de intervención modificadora de nuestro material genético
MATRIZ DE ARBOLES DE DECISION
 MATRIZ DE ARBOLES DE DECISION Los árboles son un subconjunto importante de los grafos, y son una herramienta útil para describir estructuras que presentan algún tipo de jerarquía. Las dificultades de las
MATRIZ DE ARBOLES DE DECISION Los árboles son un subconjunto importante de los grafos, y son una herramienta útil para describir estructuras que presentan algún tipo de jerarquía. Las dificultades de las
Tema 2 - Algoritmos en redes Hoja de problemas
 .T.S.I.I.T - Grado en Ingeniería de Tecnologías de Telecomunicación Redes de omunicaciones - urso 0/08 Tema - lgoritmos en redes Hoja de problemas Problema. ncontrar, aplicando los algoritmos de ijkstra
.T.S.I.I.T - Grado en Ingeniería de Tecnologías de Telecomunicación Redes de omunicaciones - urso 0/08 Tema - lgoritmos en redes Hoja de problemas Problema. ncontrar, aplicando los algoritmos de ijkstra
Repaso de conceptos de álgebra lineal
 MÉTODOS AVANZADOS EN APRENDIZAJE ARTIFICIAL: TEORÍA Y APLICACIONES A PROBLEMAS DE PREDICCIÓN Manuel Sánchez-Montañés Luis Lago Ana González Escuela Politécnica Superior Universidad Autónoma de Madrid Repaso
MÉTODOS AVANZADOS EN APRENDIZAJE ARTIFICIAL: TEORÍA Y APLICACIONES A PROBLEMAS DE PREDICCIÓN Manuel Sánchez-Montañés Luis Lago Ana González Escuela Politécnica Superior Universidad Autónoma de Madrid Repaso
Gráficos estadísticos
 Gráficos estadísticos Francisco García (fgarcia@cipf.es) CIPF s Research Development Programme 29 de octubre de 2014 Índex 1 Introducción 2 Gráficos con R Qué es R? Ejemplos y ejercicios 3 Herramientas
Gráficos estadísticos Francisco García (fgarcia@cipf.es) CIPF s Research Development Programme 29 de octubre de 2014 Índex 1 Introducción 2 Gráficos con R Qué es R? Ejemplos y ejercicios 3 Herramientas
Aprendizaje Automatizado
 Aprendizaje Automatizado Aprendizaje Automatizado Programas que mejoran su comportamiento con la experiencia. Dos formas de adquirir experiencia: A partir de ejemplos suministrados por un usuario (un conjunto
Aprendizaje Automatizado Aprendizaje Automatizado Programas que mejoran su comportamiento con la experiencia. Dos formas de adquirir experiencia: A partir de ejemplos suministrados por un usuario (un conjunto
Introducción a la Bioinformática
 Introducción a la Dr. Eduardo A. RODRÍGUEZ TELLO CINVESTAV-Tamaulipas 16 de mayo del 2013 Dr. Eduardo RODRÍGUEZ T. (CINVESTAV) Introducción a la 16 de mayo del 2013 1 / 37 1 Introducción Qué es bioinformática?
Introducción a la Dr. Eduardo A. RODRÍGUEZ TELLO CINVESTAV-Tamaulipas 16 de mayo del 2013 Dr. Eduardo RODRÍGUEZ T. (CINVESTAV) Introducción a la 16 de mayo del 2013 1 / 37 1 Introducción Qué es bioinformática?
UNIVERSIDAD AUTÓNOMA DE NUEVO LEÓN FACULTAD DE CIENCIAS BIOLÓGICAS PROGRAMA EDUCATIVO DE LICENCIADO EN BIOTECNOLOGÍA GENÓMICA
 UNIVERSIDAD AUTÓNOMA DE NUEVO LEÓN FACULTAD DE CIENCIAS BIOLÓGICAS PROGRAMA EDUCATIVO DE LICENCIADO EN BIOTECNOLOGÍA GENÓMICA PROGRAMA ANALÍTICO DE BIOLOGÍA DE SISTEMAS 1. Datos de identificación: Nombre
UNIVERSIDAD AUTÓNOMA DE NUEVO LEÓN FACULTAD DE CIENCIAS BIOLÓGICAS PROGRAMA EDUCATIVO DE LICENCIADO EN BIOTECNOLOGÍA GENÓMICA PROGRAMA ANALÍTICO DE BIOLOGÍA DE SISTEMAS 1. Datos de identificación: Nombre
CAPITULO 3: PASOS REALIZADOS PARA LA DETECCIÓN DE BORDES DE IMÁGENES A COLOR
 CAPITULO 3: PASOS REALIZADOS PARA LA DETECCIÓN DE BORDES DE IMÁGENES A COLOR El algoritmo realizado para la detección de bordes de imágenes a color se basa en el operador Canny. La filosofía del operador
CAPITULO 3: PASOS REALIZADOS PARA LA DETECCIÓN DE BORDES DE IMÁGENES A COLOR El algoritmo realizado para la detección de bordes de imágenes a color se basa en el operador Canny. La filosofía del operador
Redes de Comunicaciones
 Redes de omunicaciones jercicios Tema. lgoritmos de encaminamiento Ramón güero alvo epartamento de Ingeniería de omunicaciones ste tema se publica bajo Licencia: rea:ve ommons Y- N- S.0 .T.S.I.I.T - Grado
Redes de omunicaciones jercicios Tema. lgoritmos de encaminamiento Ramón güero alvo epartamento de Ingeniería de omunicaciones ste tema se publica bajo Licencia: rea:ve ommons Y- N- S.0 .T.S.I.I.T - Grado
Simulación perceptual
 Simulación En ingeniería, una simulación tiene como objetivo mostrar el comportamiento de un modelo digital bajo condiciones específicas, sean estas ideales, reales o extremas, dando como resultado datos
Simulación En ingeniería, una simulación tiene como objetivo mostrar el comportamiento de un modelo digital bajo condiciones específicas, sean estas ideales, reales o extremas, dando como resultado datos
Redes de Interacción de Proteínas. David A. Juan CNIO. Grupo de Biología Computacional y Estructural.
 Redes de Interacción de Proteínas David A. Juan CNIO. Grupo de Biología Computacional y Estructural. dadejuan@cnio.es 1. 2. 3. 4. 5. 6. Interacciones entre proteínas Fundamentales para comprender la función
Redes de Interacción de Proteínas David A. Juan CNIO. Grupo de Biología Computacional y Estructural. dadejuan@cnio.es 1. 2. 3. 4. 5. 6. Interacciones entre proteínas Fundamentales para comprender la función
Método de Box Muller. Método Polar Generación de eventos en Procesos de Poisson. Método de Box-Muller. Métodos de generación de v. a.
 Método de Box Muller Método Polar Generación de eventos en Procesos de Poisson Si X e Y son normales estándar indepientes, entonces R 2 = X 2 + Y 2, tan(θ) = Y X determinan variables R 2 y Θ indepientes.
Método de Box Muller Método Polar Generación de eventos en Procesos de Poisson Si X e Y son normales estándar indepientes, entonces R 2 = X 2 + Y 2, tan(θ) = Y X determinan variables R 2 y Θ indepientes.
MATEMÁTICAS ORIENTADAS A LAS ENSEÑANZAS ACADÉMICAS CONTENIDOS
 MATEMÁTICAS ORIENTADAS A LAS ENSEÑANZAS ACADÉMICAS CONTENIDOS BLOQUE 1. PROCESOS, MÉTODOS Y ACTITUDES EN MATEMÁTICAS Los contenidos de este bloque se desarrollan de forma simultánea al resto de bloques
MATEMÁTICAS ORIENTADAS A LAS ENSEÑANZAS ACADÉMICAS CONTENIDOS BLOQUE 1. PROCESOS, MÉTODOS Y ACTITUDES EN MATEMÁTICAS Los contenidos de este bloque se desarrollan de forma simultánea al resto de bloques
Grafos: algunas definiciones
 Grafos: algunas definiciones Un grafo dirigido G es un par (V, E), donde V es un conjunto finito de nodos (o vértices) y E es una relación binaria sobre V. Un grafo no dirigido G es un par (V, E), donde
Grafos: algunas definiciones Un grafo dirigido G es un par (V, E), donde V es un conjunto finito de nodos (o vértices) y E es una relación binaria sobre V. Un grafo no dirigido G es un par (V, E), donde
SUPERFICIES DE REVOLUCIÓN
 SUPERFICIES DE REVOLUCIÓN Si a una curva Γ (Generatriz), la giramos alrededor de un eje (eje de rotación), obtenemos una superficie, que se llamará superficie de revolución. Como se aprecia en las siguientes
SUPERFICIES DE REVOLUCIÓN Si a una curva Γ (Generatriz), la giramos alrededor de un eje (eje de rotación), obtenemos una superficie, que se llamará superficie de revolución. Como se aprecia en las siguientes
Examen Final de Cálculo Vectorial MATE PREGUNTAS ABIERTAS TEMA A Diciembre 6 de Nombre: Código:
 UNIVERSIDAD DE LOS ANDES DEPARTAMENTO DE MATEMÁTICAS Examen Final de Cálculo Vectorial MATE 1207 PREGUNTAS ABIERTAS TEMA A Diciembre 6 de 2017 Este es un examen individual, no se permite el uso de libros,
UNIVERSIDAD DE LOS ANDES DEPARTAMENTO DE MATEMÁTICAS Examen Final de Cálculo Vectorial MATE 1207 PREGUNTAS ABIERTAS TEMA A Diciembre 6 de 2017 Este es un examen individual, no se permite el uso de libros,
Todos los Pares de Rutas más Cortas (All-Pairs Shortest Paths) DR. JESÚS A. GONZÁLEZ BERNAL CIENCIAS COMPUTACIONALES INAOE
 Todos los Pares de Rutas más Cortas (All-Pairs Shortest Paths) DR. JESÚS A. GONZÁLEZ BERNAL CIENCIAS COMPUTACIONALES INAOE Problema de Encontrar todos los Pares de Rutas más Cortas 2 Encontrar las rutas
Todos los Pares de Rutas más Cortas (All-Pairs Shortest Paths) DR. JESÚS A. GONZÁLEZ BERNAL CIENCIAS COMPUTACIONALES INAOE Problema de Encontrar todos los Pares de Rutas más Cortas 2 Encontrar las rutas
HOJA DE TRABAJO 2. Construyendo las identidades Pitagóricas
 INSTITUCIÓN EDUCATIVA RURAL GIOVANNI MONTINI Vereda Colombia Km 41 GUIA DIDÁCTICA CÓDIGO VERSIÓN PÁGINA GAPP01 01 1 de 5 HOJA DE TRABAJO 2. Construyendo las identidades Pitagóricas Nombre del estudiante:
INSTITUCIÓN EDUCATIVA RURAL GIOVANNI MONTINI Vereda Colombia Km 41 GUIA DIDÁCTICA CÓDIGO VERSIÓN PÁGINA GAPP01 01 1 de 5 HOJA DE TRABAJO 2. Construyendo las identidades Pitagóricas Nombre del estudiante:
4º ESO APLICADA ESTÁNDARES DE APRENDIZAJE EVALUABLES CRITERIOS DE EVALUACIÓN Y COMPETENCIAS CLAVE
 CONTENIDOS 4º ESO APLICADA CRITERIOS DE EVALUACIÓN Y COMPETENCIAS CLAVE ESTÁNDARES DE APRENDIZAJE EVALUABLES TEMA 1: Números reales Número irracional. Conjunto de números reales. Radicales. Operaciones
CONTENIDOS 4º ESO APLICADA CRITERIOS DE EVALUACIÓN Y COMPETENCIAS CLAVE ESTÁNDARES DE APRENDIZAJE EVALUABLES TEMA 1: Números reales Número irracional. Conjunto de números reales. Radicales. Operaciones
ÁRBOLES CRISTIAN ALFREDO MUÑOZ ÁLVAREZ JUAN DAVID LONDOÑO CASTRO JUAN PABLO CHACÓN PEÑA EDUARDO GONZALES
 ÁRBOLES CRISTIAN ALFREDO MUÑOZ ÁLVAREZ JUAN DAVID LONDOÑO CASTRO JUAN PABLO CHACÓN PEÑA EDUARDO GONZALES ÁRBOL Un árbol es un grafo no dirigido, conexo, sin ciclos (acíclico), y que no contiene aristas
ÁRBOLES CRISTIAN ALFREDO MUÑOZ ÁLVAREZ JUAN DAVID LONDOÑO CASTRO JUAN PABLO CHACÓN PEÑA EDUARDO GONZALES ÁRBOL Un árbol es un grafo no dirigido, conexo, sin ciclos (acíclico), y que no contiene aristas
4.3. COMPETENCIA MATEMÁTICA
 4.3. COMPETENCIA MATEMÁTICA 4.3.1. Distribución del alumnado por niveles de competencia A continuación presentamos la distribución de las alumnas y los alumnos por niveles en la Competencia matemática
4.3. COMPETENCIA MATEMÁTICA 4.3.1. Distribución del alumnado por niveles de competencia A continuación presentamos la distribución de las alumnas y los alumnos por niveles en la Competencia matemática
PRUEBAS SOLEMNES II SEMESTRE DE 2011 APRENDIZAJES ESPERADOS Y CONTENIDOS A EVALUAR
 Y CONTENIDOS A EVALUAR 5 básico Estructura y funciones de los seres vivos Describir la organización y la función básica del sistema respiratorio e identificar sus principales órganos y estructuras: pulmones,
Y CONTENIDOS A EVALUAR 5 básico Estructura y funciones de los seres vivos Describir la organización y la función básica del sistema respiratorio e identificar sus principales órganos y estructuras: pulmones,
Estructuras Jerárquicas inducidas por estímulo externo en redes dinámicas adaptativas
 Universidad de Los Andes Facultad de Ciencias Centro de Física Fundamental Area de Caos y Sistemas Complejos Estructuras Jerárquicas inducidas por estímulo externo en redes dinámicas adaptativas Victor
Universidad de Los Andes Facultad de Ciencias Centro de Física Fundamental Area de Caos y Sistemas Complejos Estructuras Jerárquicas inducidas por estímulo externo en redes dinámicas adaptativas Victor
Colegio San Patricio. Biología. 3 0 Año
 Colegio San Patricio Biología 3 0 Año Año 2016 Fundamentos La enseñanza de la Biología implica procesos dinámicos y que pueda enriquecer los intereses de los alumnos, y que tengan la posibilidad de preguntarse
Colegio San Patricio Biología 3 0 Año Año 2016 Fundamentos La enseñanza de la Biología implica procesos dinámicos y que pueda enriquecer los intereses de los alumnos, y que tengan la posibilidad de preguntarse
